wbc <- function() {
ini({
## Note that the UI can take expressions
## Also note that these initial estimates should be provided on the log-scale
log_CIRC0 <- log(7.21)
log_MTT <- log(124)
log_SLOPU <- log(28.9)
log_GAMMA <- log(0.239)
## Initial estimates should be high for SAEM ETAs
eta.CIRC0 ~ .1
eta.MTT ~ .03
eta.SLOPU ~ .2
## Also true for additive error (also ignored in SAEM)
prop.err <- 10
})
model({
CIRC0 = exp(log_CIRC0 + eta.CIRC0)
MTT = exp(log_MTT + eta.MTT)
SLOPU = exp(log_SLOPU + eta.SLOPU)
GAMMA = exp(log_GAMMA)
# PK parameters from input dataset
CL = CLI
V1 = V1I
V2 = V2I
Q = 204
CONC = centr/V1
# PD parameters
NN = 3
KTR = (NN + 1)/MTT
EDRUG = 1 - SLOPU * CONC
FDBK = (CIRC0 / circ)^GAMMA
CIRC = circ
prol(0) = CIRC0
tr1(0) = CIRC0
tr2(0) = CIRC0
tr3(0) = CIRC0
circ(0) = CIRC0
d/dt(centr) = periph * Q/V2 - centr * (CL/V1 + Q/V1)
d/dt(periph) = centr * Q/V1 - periph * Q/V2
d/dt(prol) = KTR * prol * EDRUG * FDBK - KTR * prol
d/dt(tr1) = KTR * prol - KTR * tr1
d/dt(tr2) = KTR * tr1 - KTR * tr2
d/dt(tr3) = KTR * tr2 - KTR * tr3
d/dt(circ) = KTR * tr3 - KTR * circ
CIRC ~ prop(prop.err)
})
}Fit model using saem
d3 <- read.csv("Simulated_WBC_pacl_ddmore_samePK_nlmixr.csv", na.strings = ".")
fit.S <- nlmixr(wbc, d3, est="saem", list(print=0), table=list(cwres=TRUE, npde=TRUE))
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#>
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#>
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:02
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#>
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#>
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
#> [====|====|====|====|====|====|====|====|====|====] 0:00:00
library(xpose.nlmixr2)
xpdb <- xpose_data_nlmixr(fit.S)
plot(fit.S)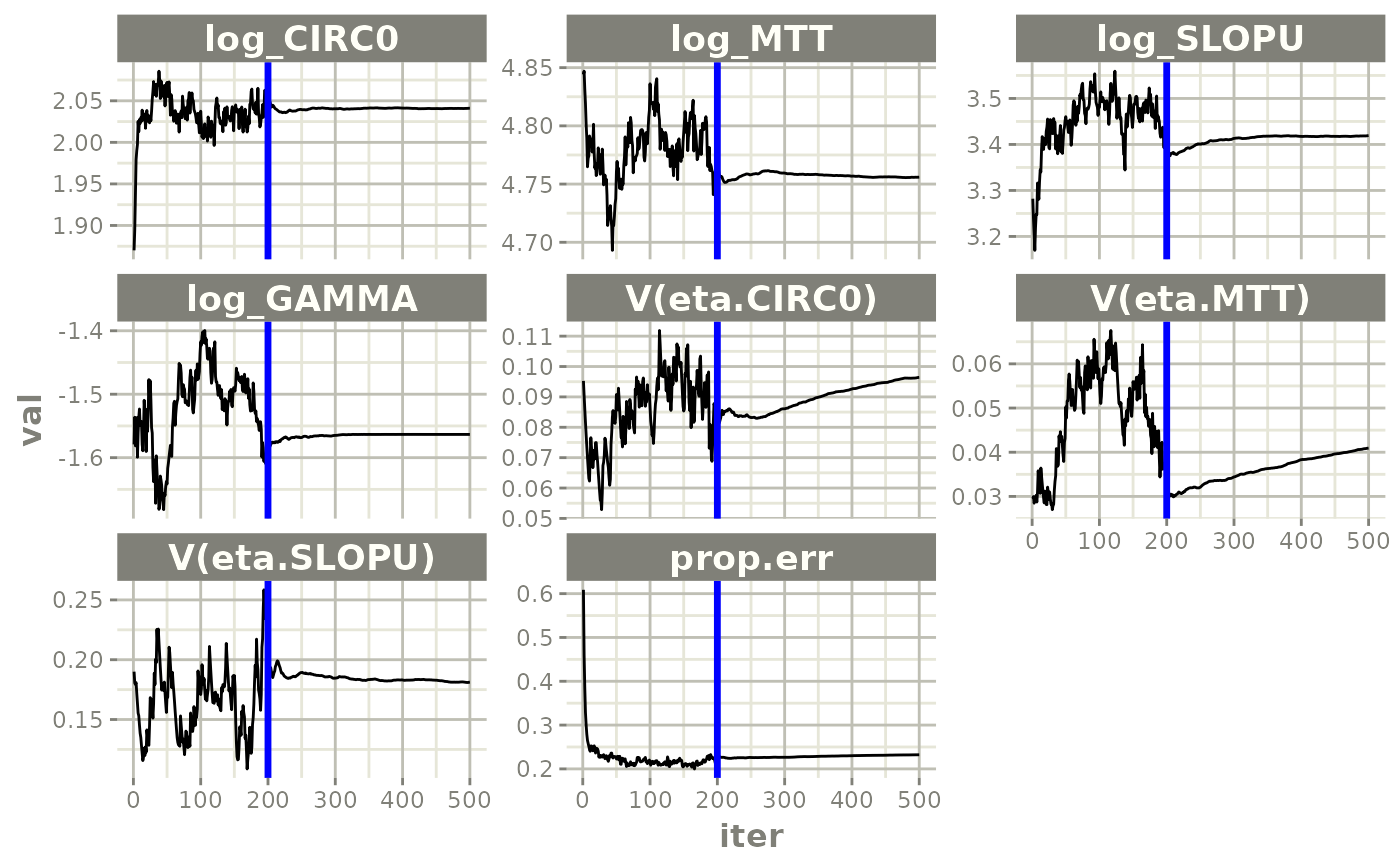
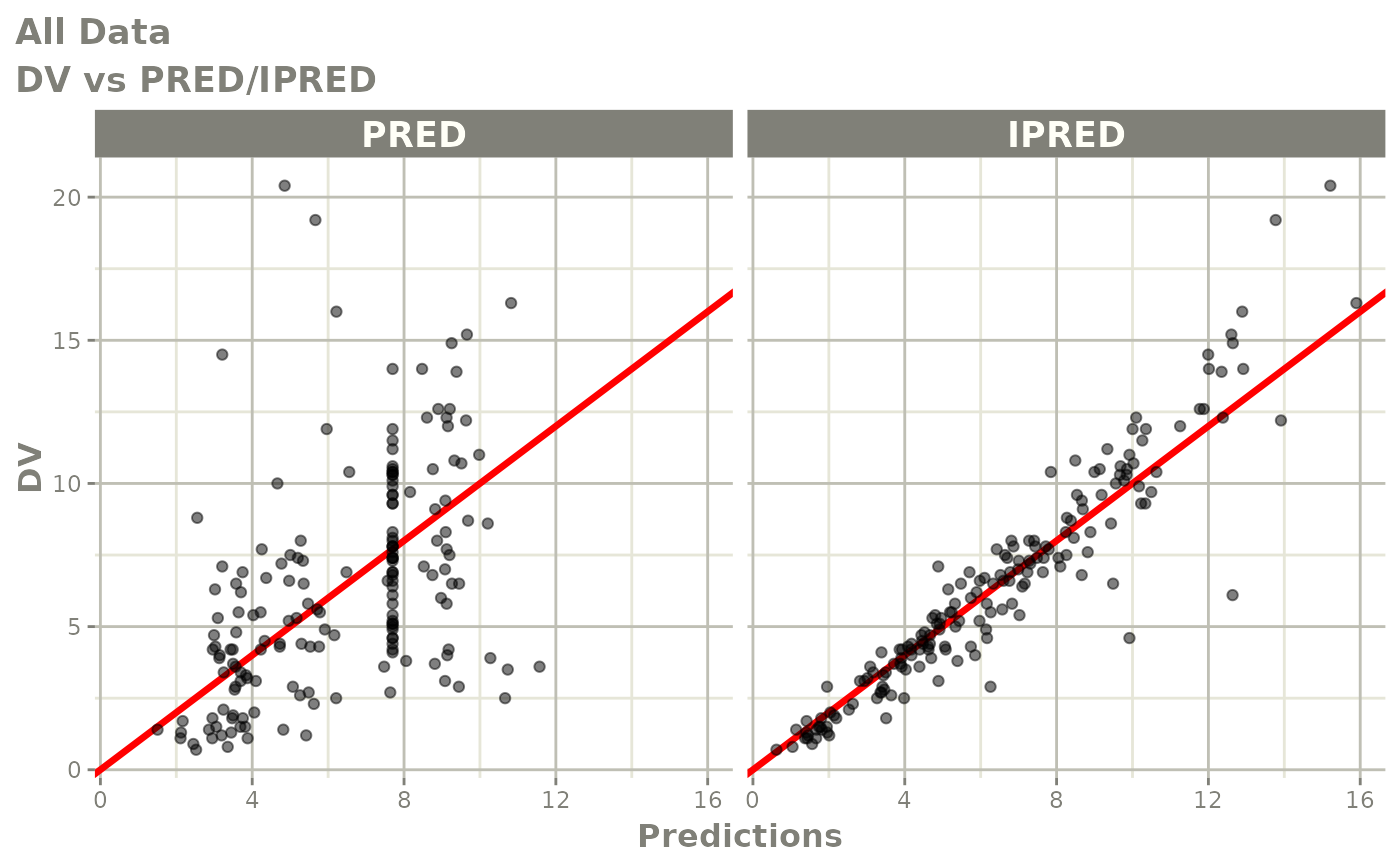
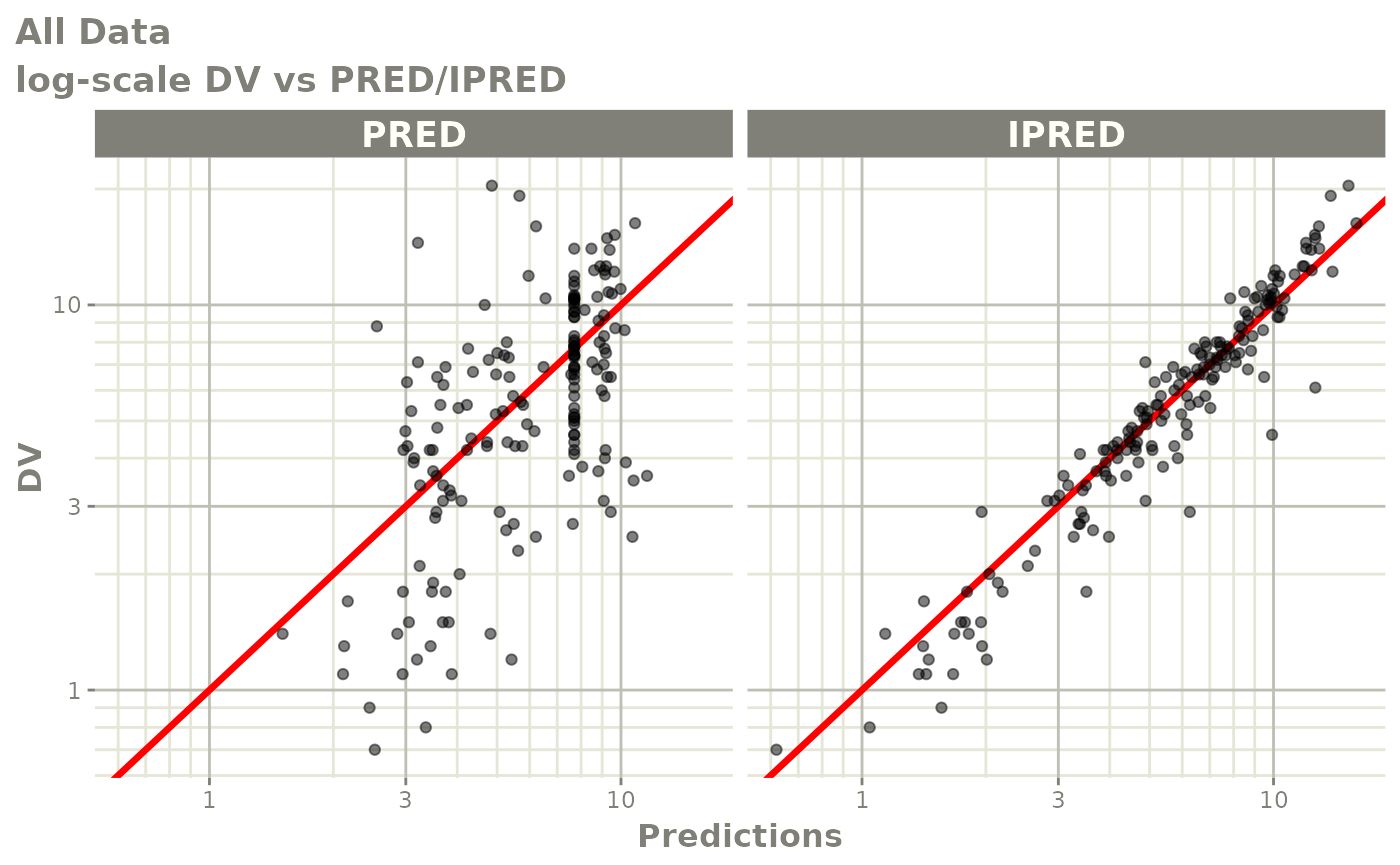
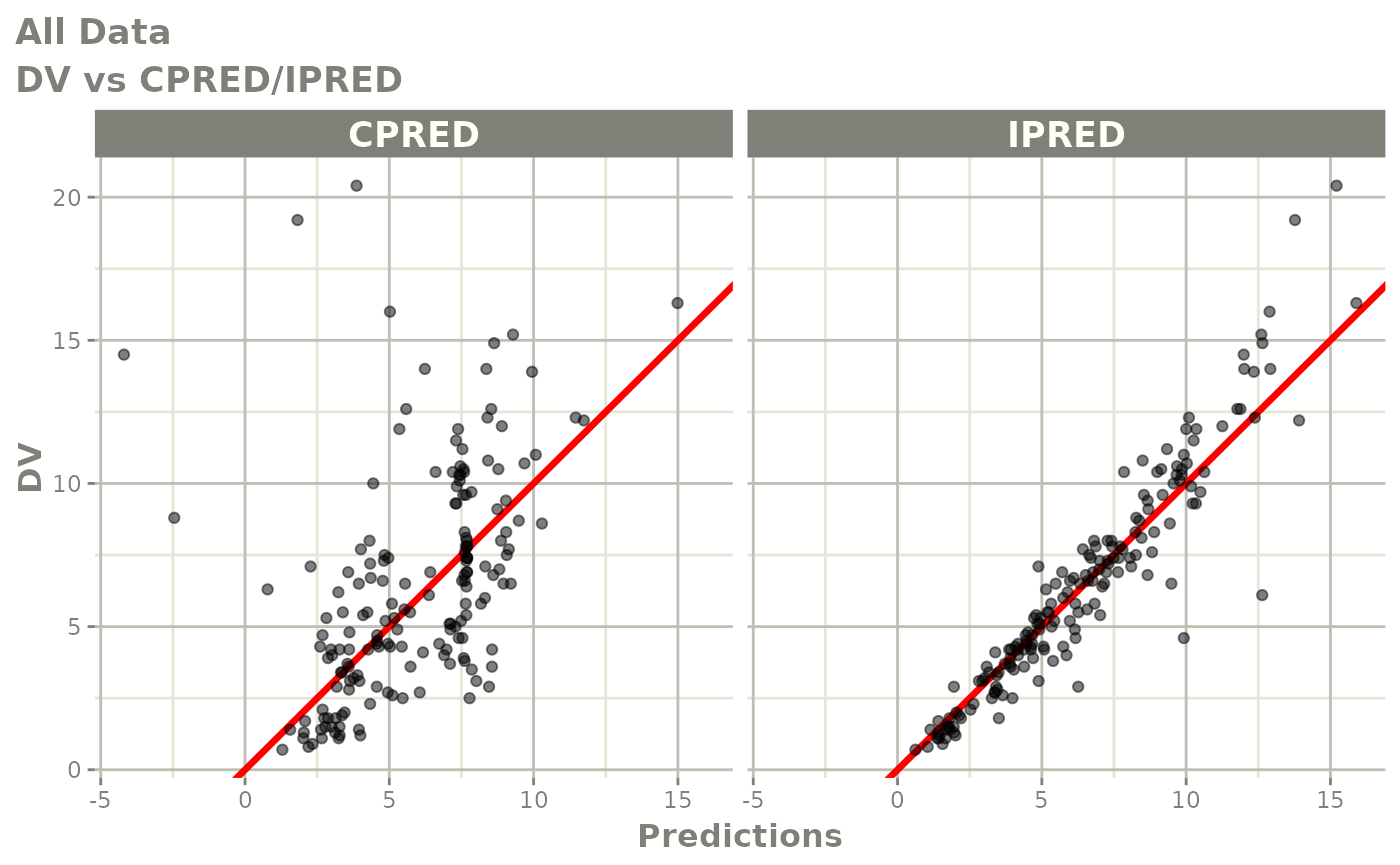
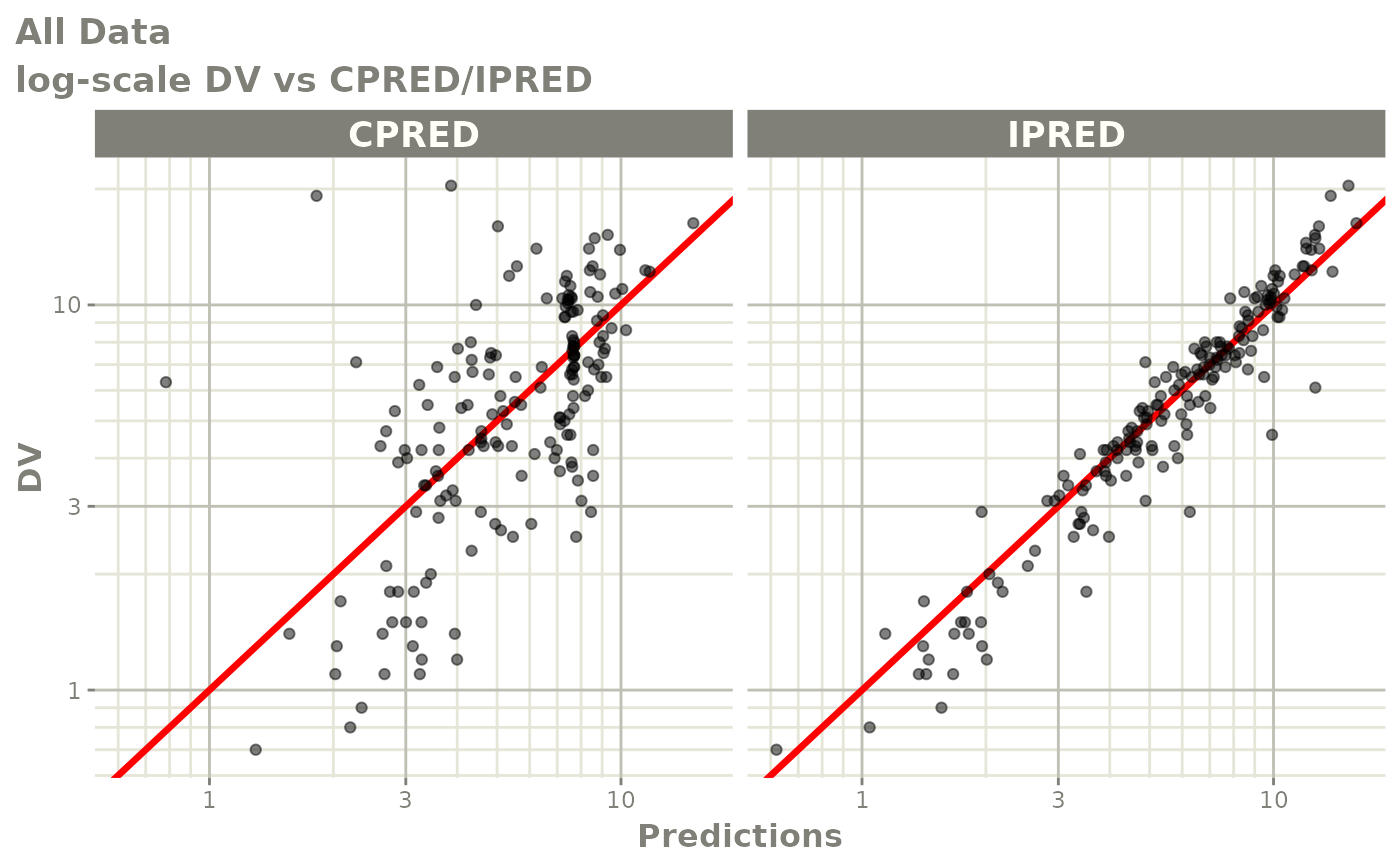
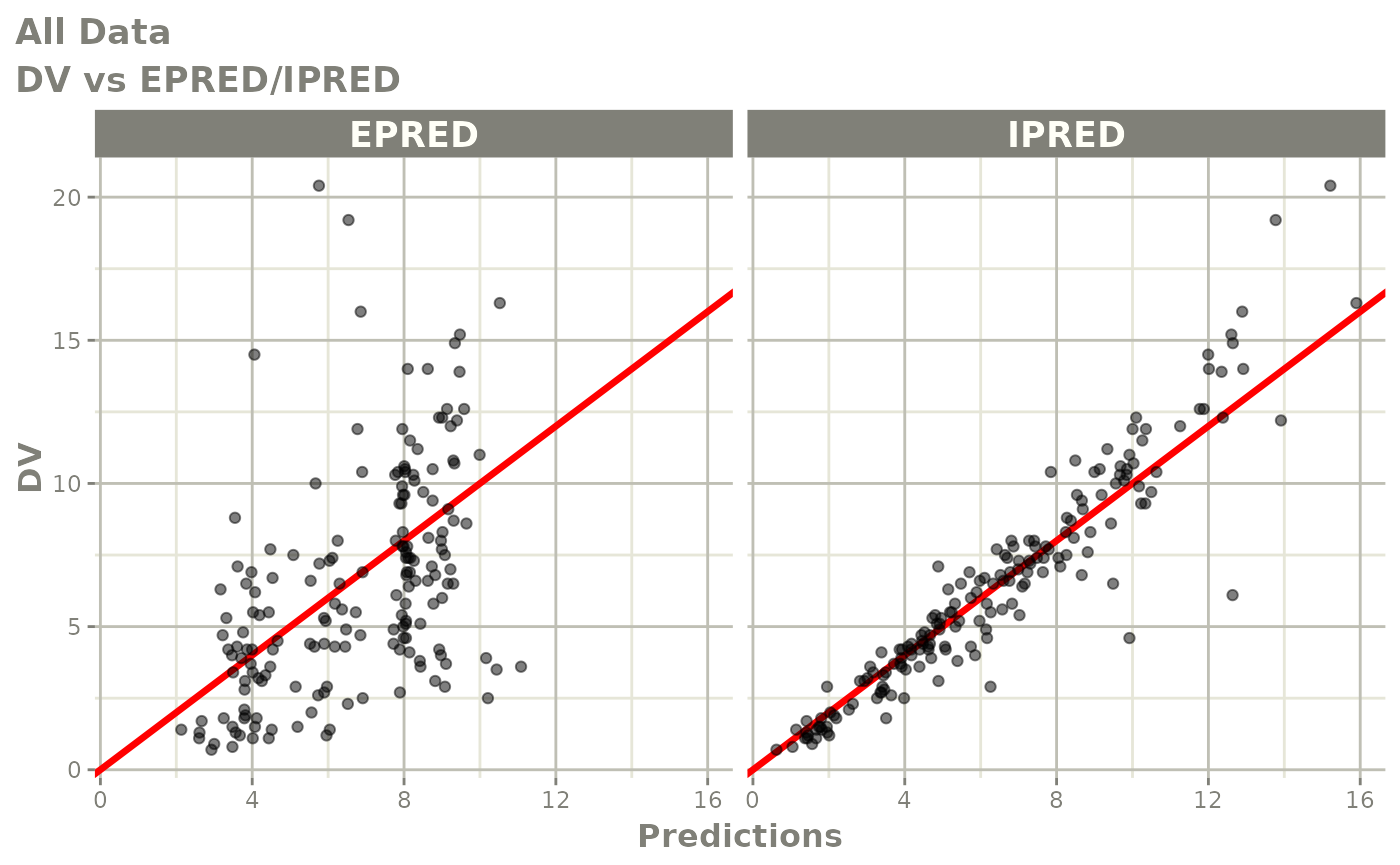
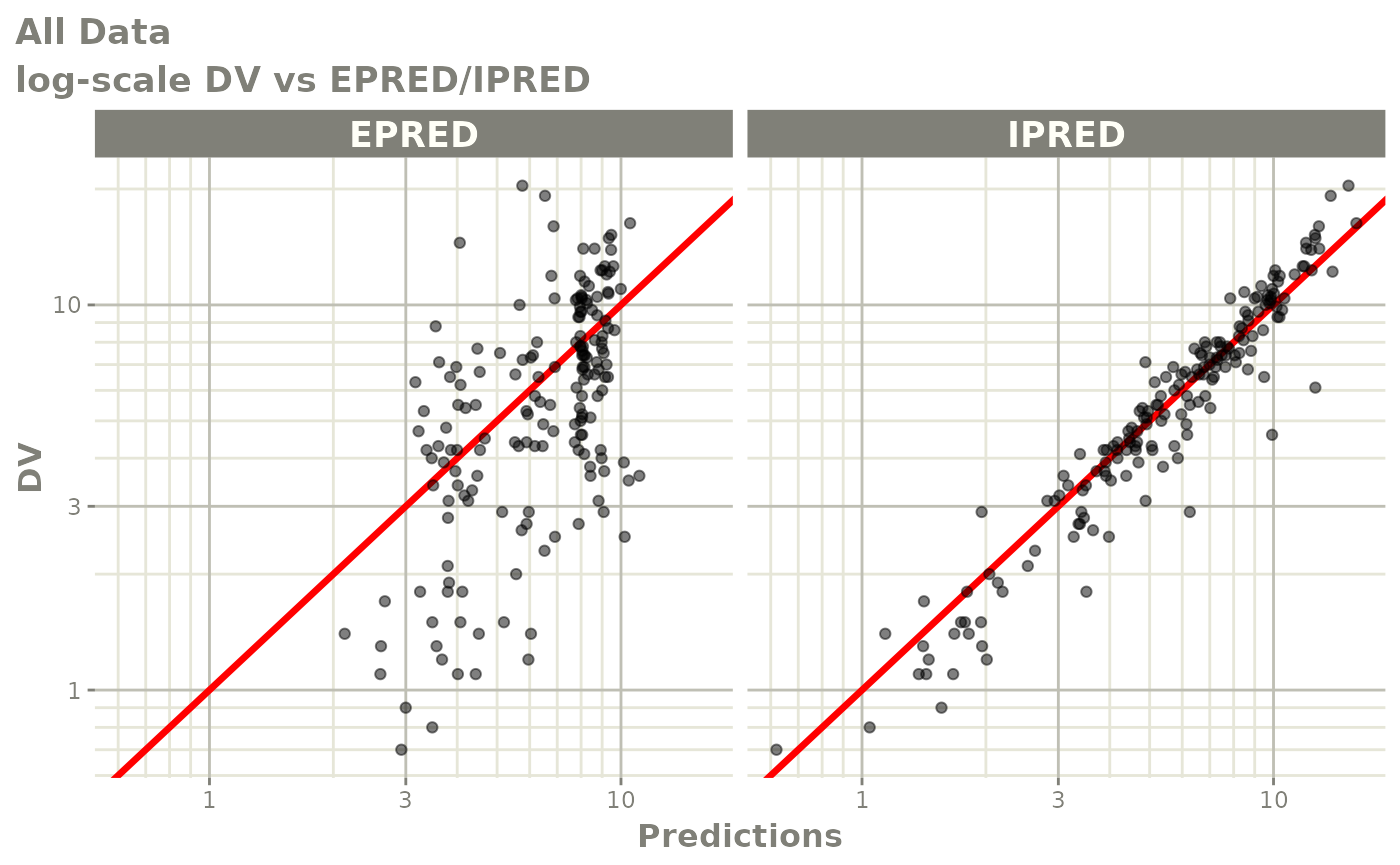
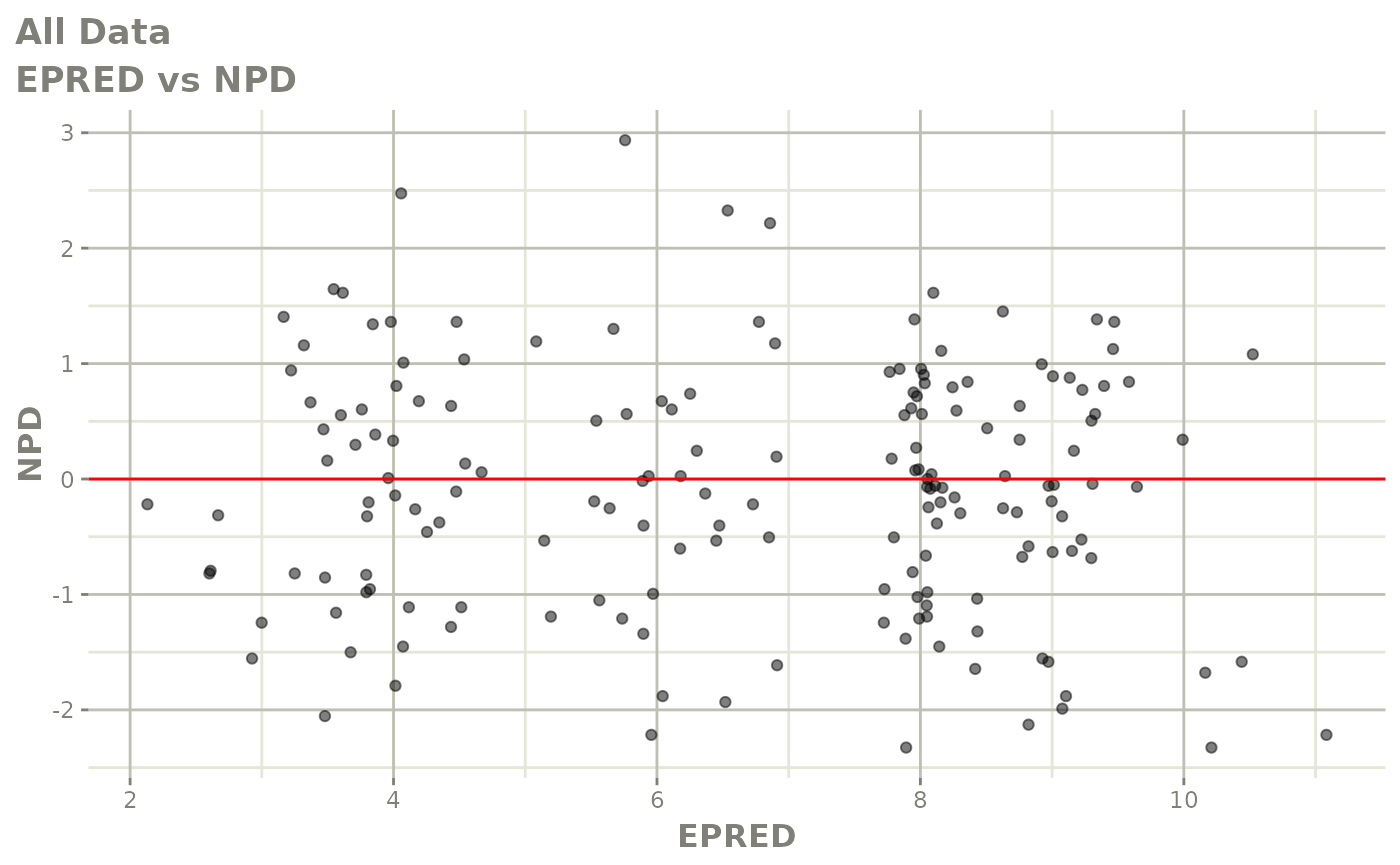
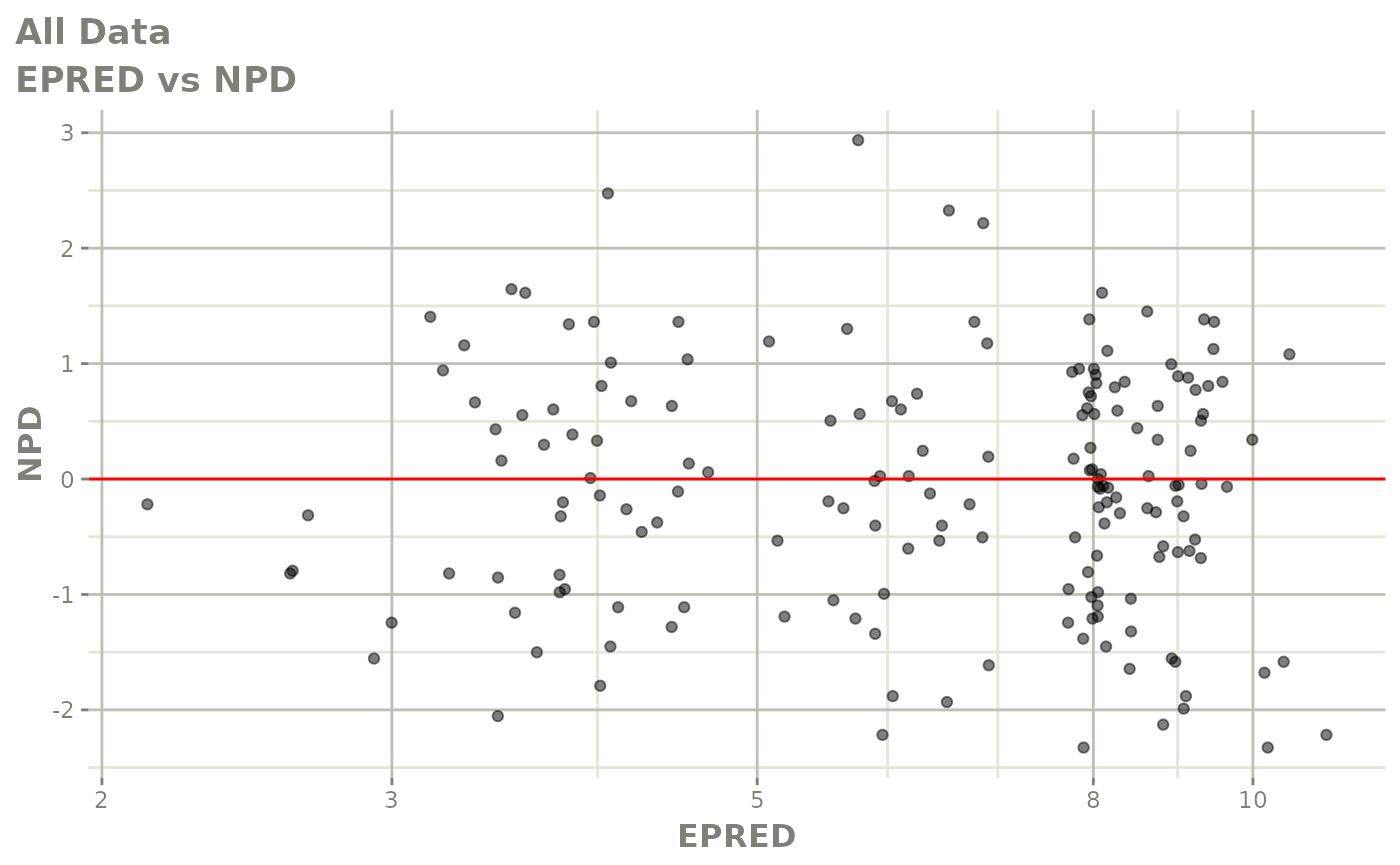
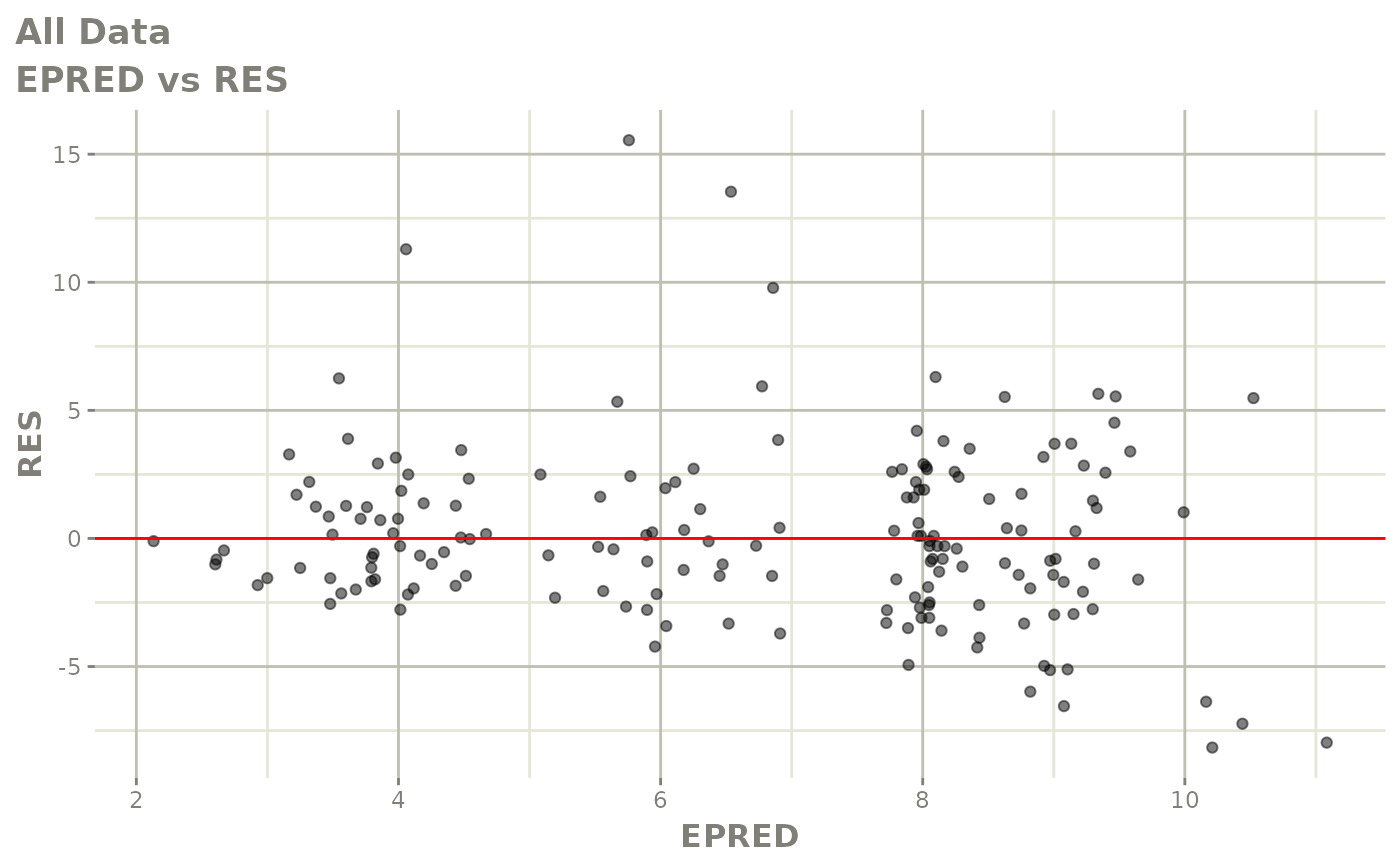
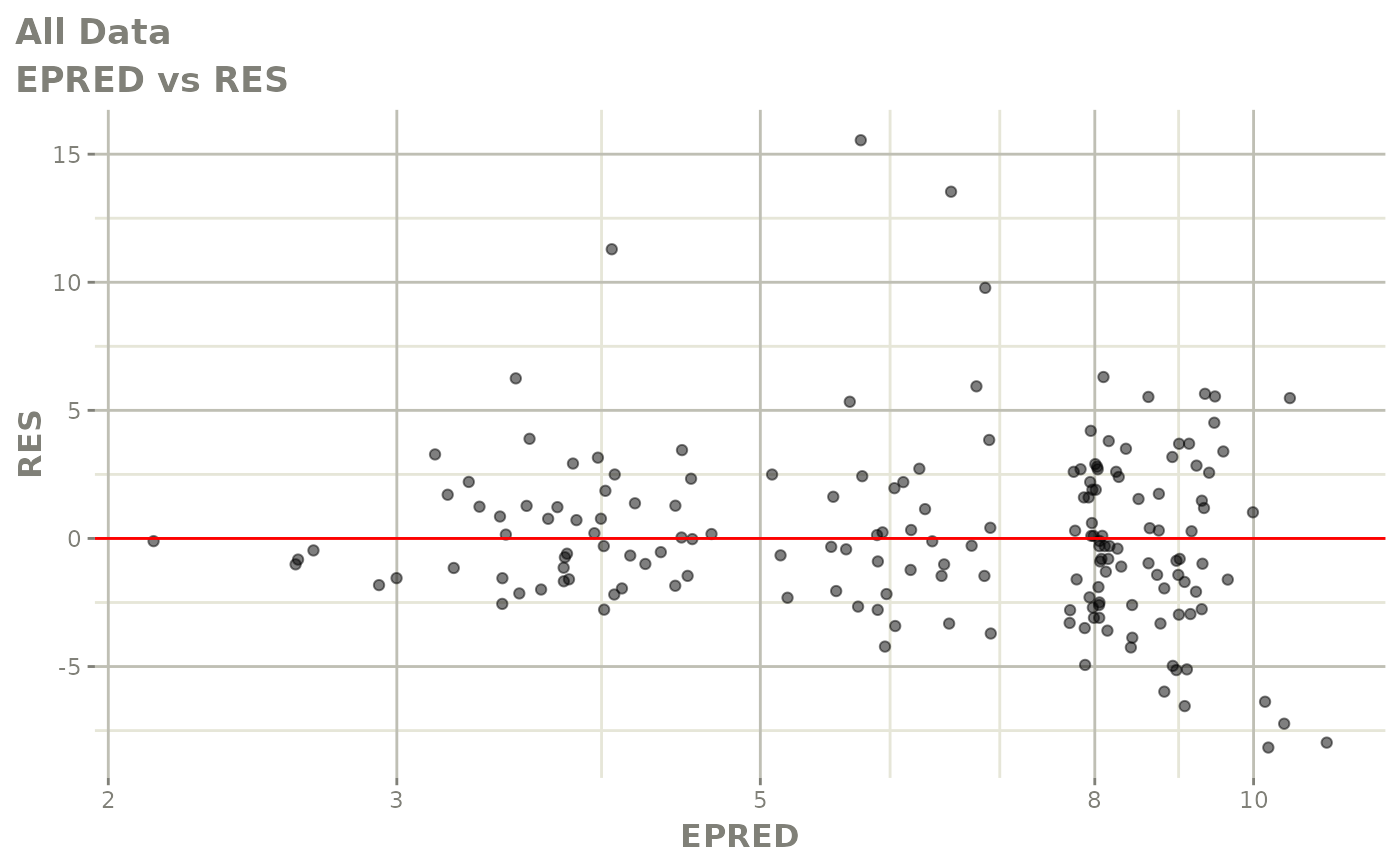
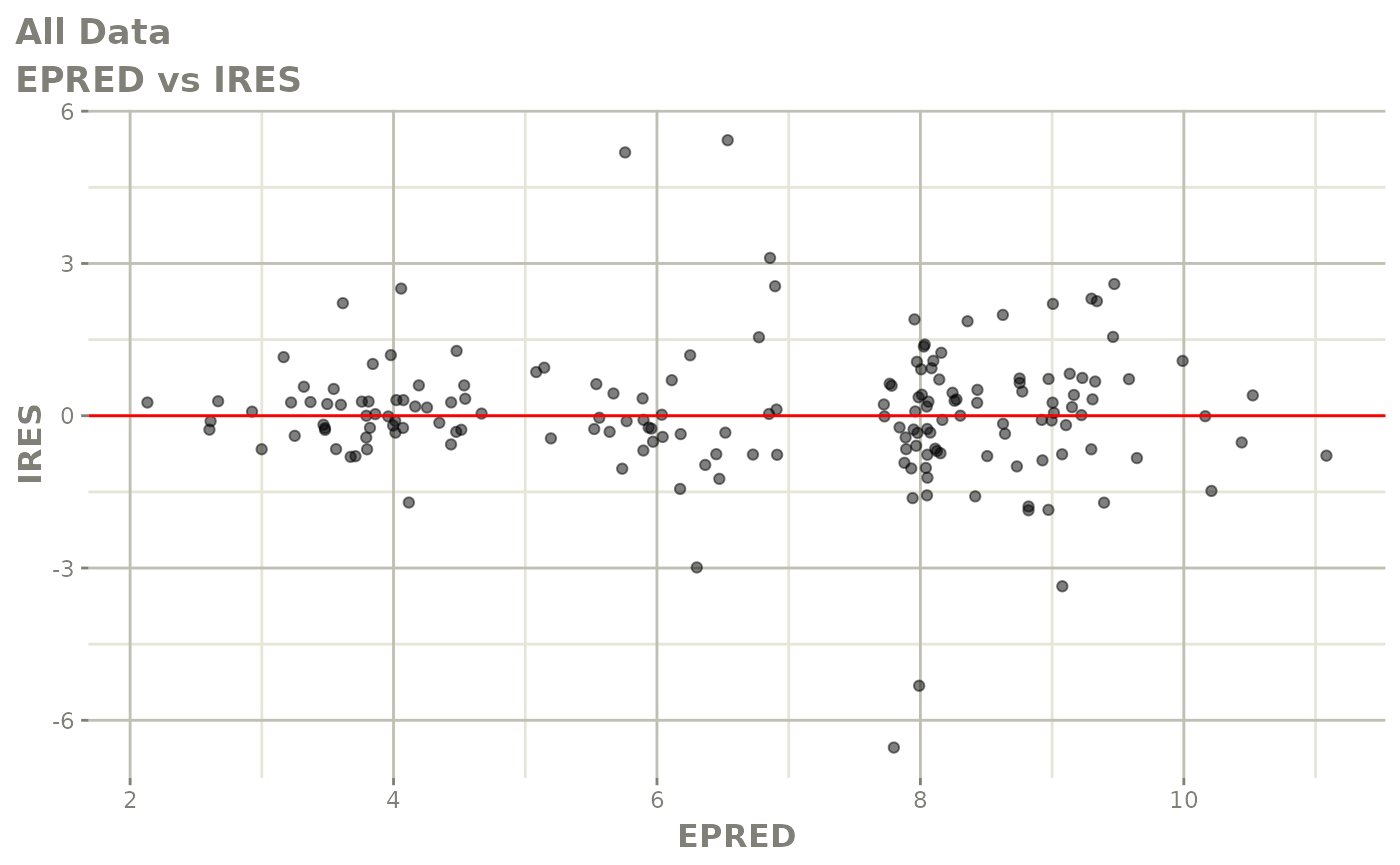
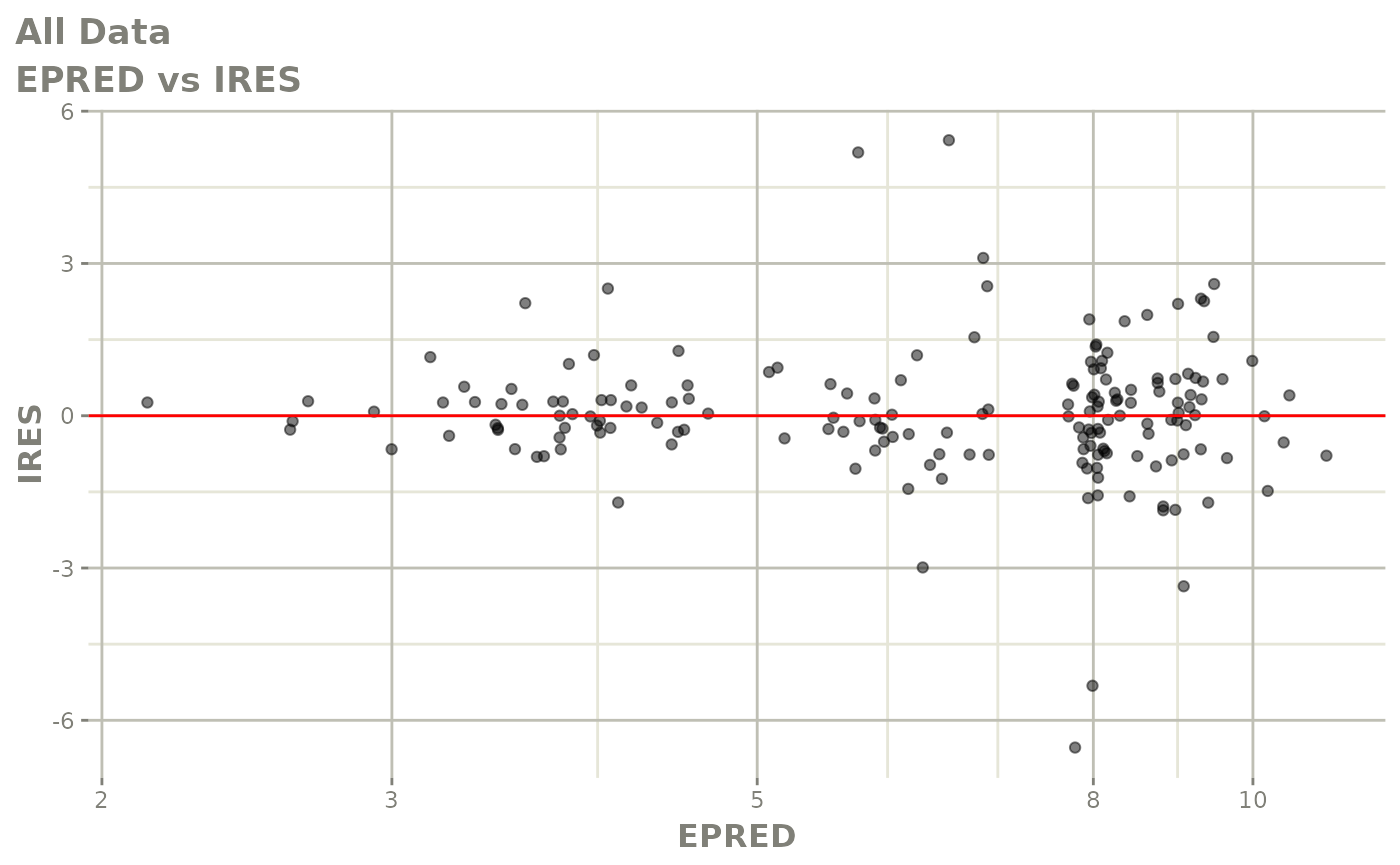
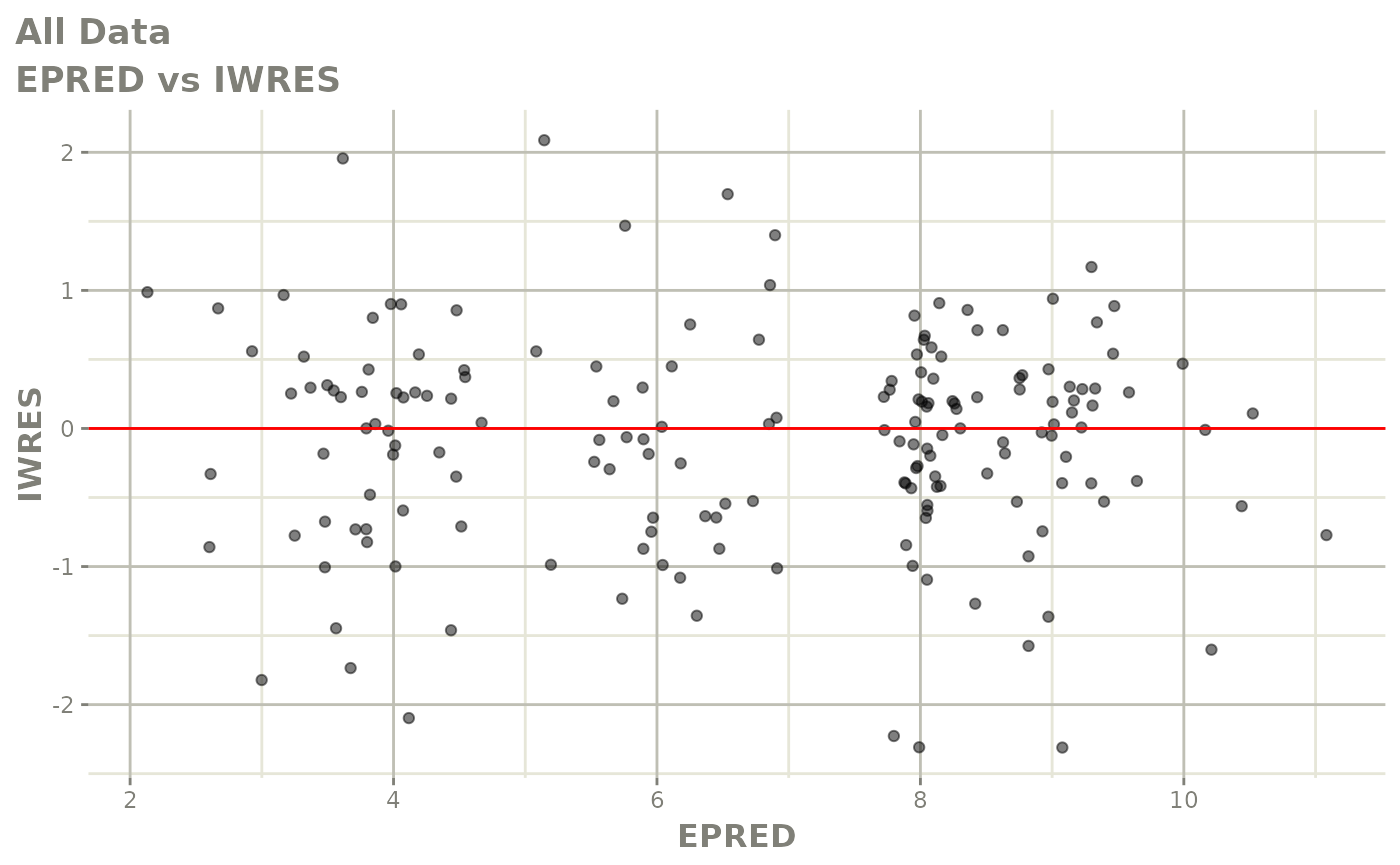
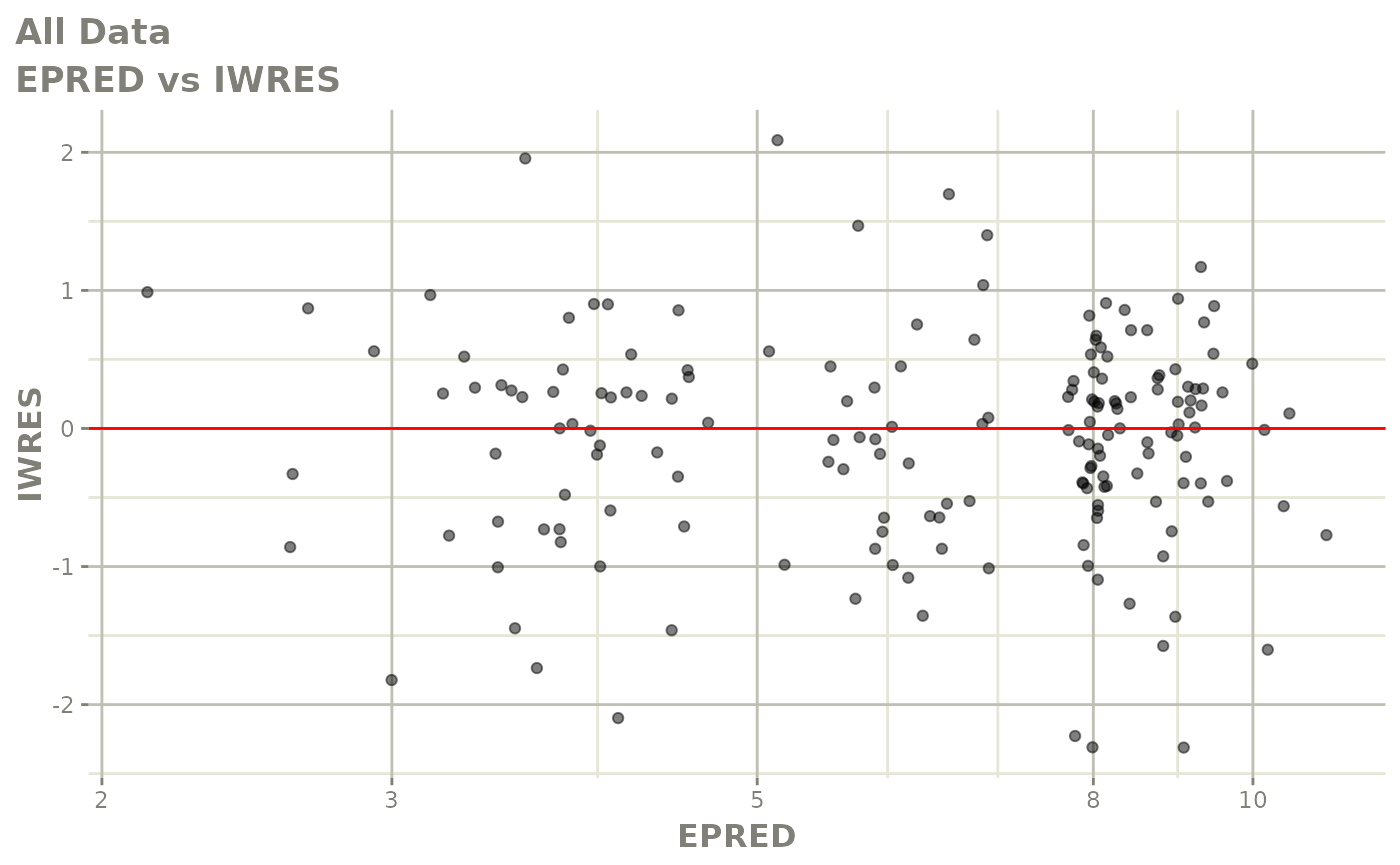
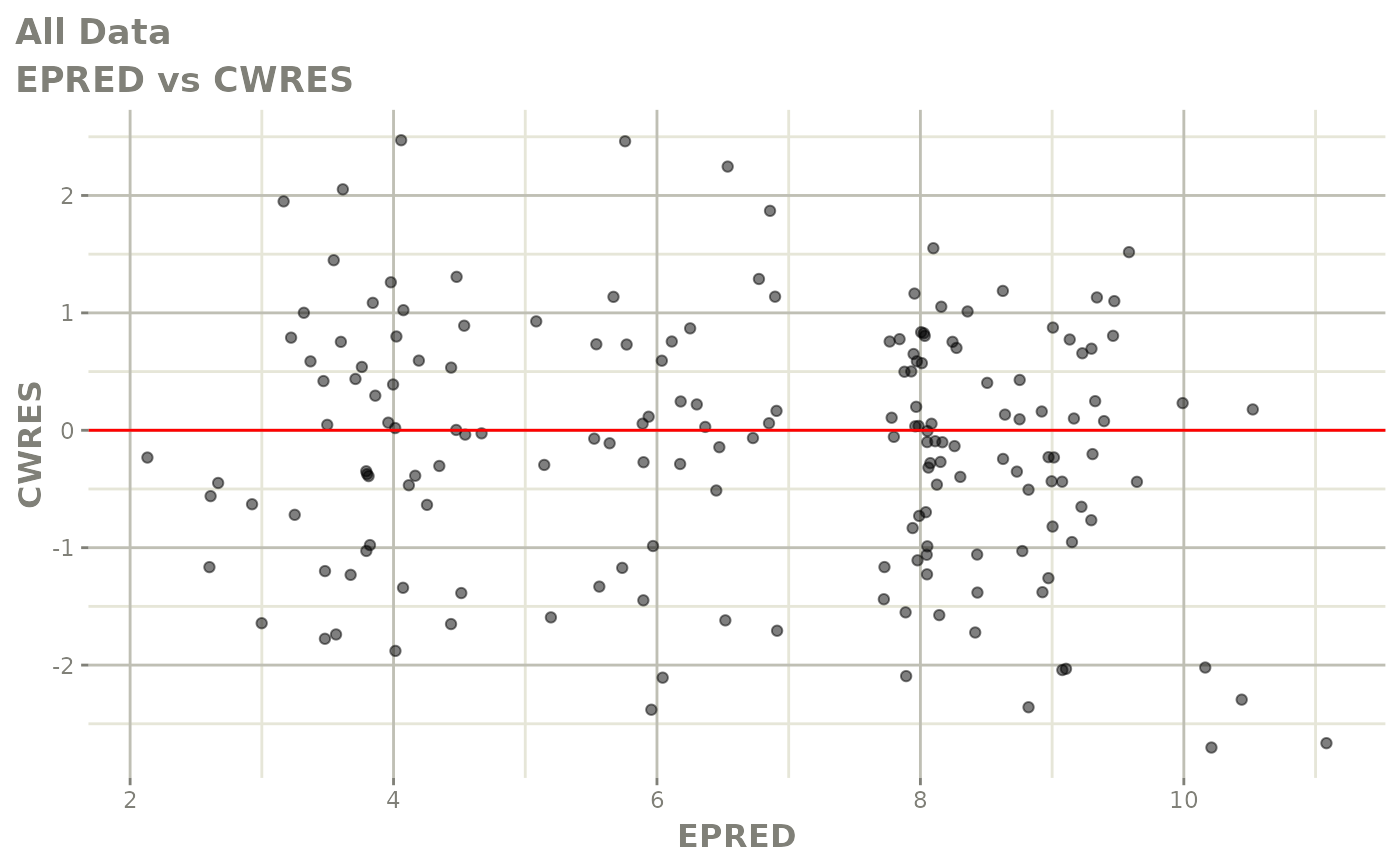
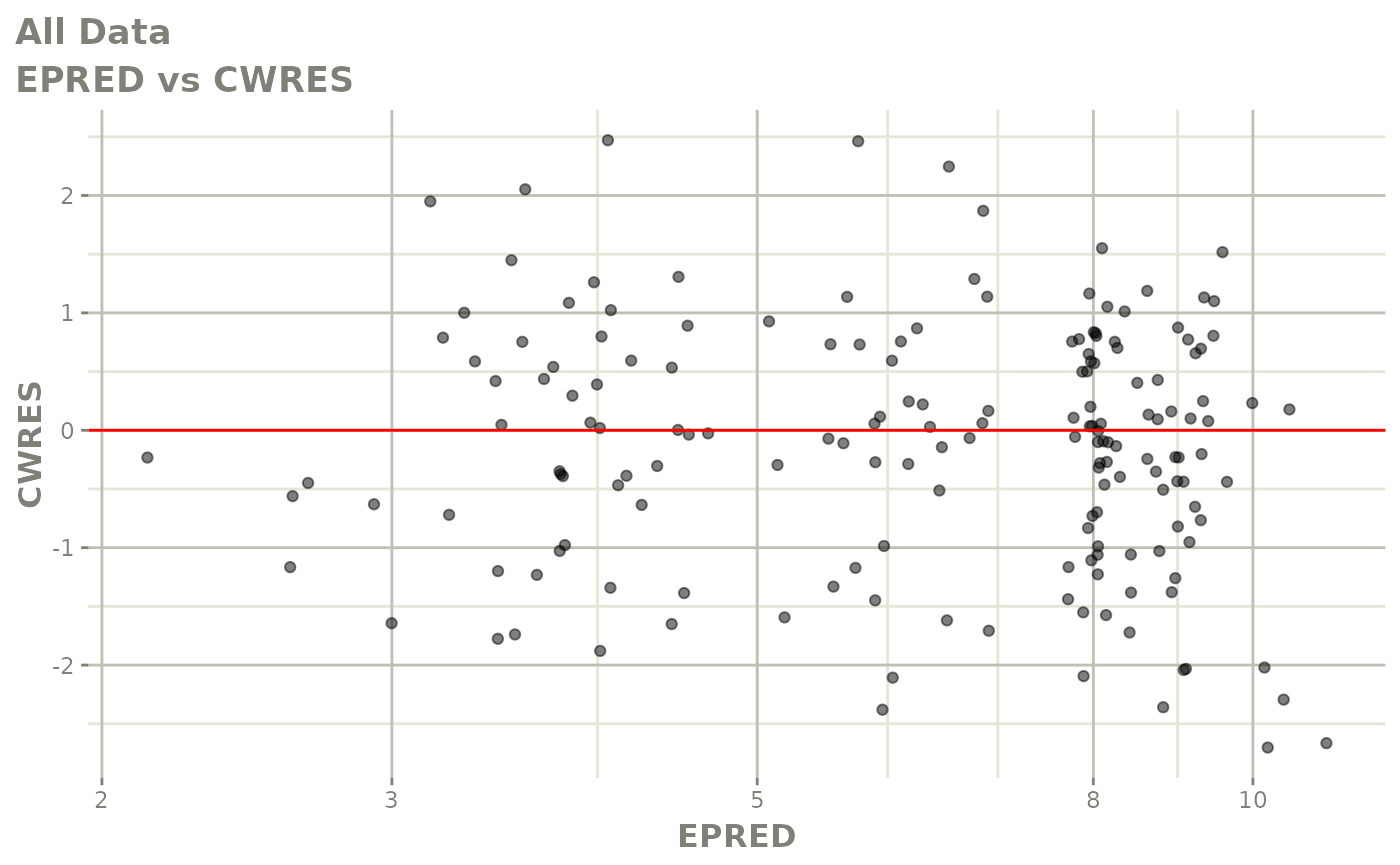
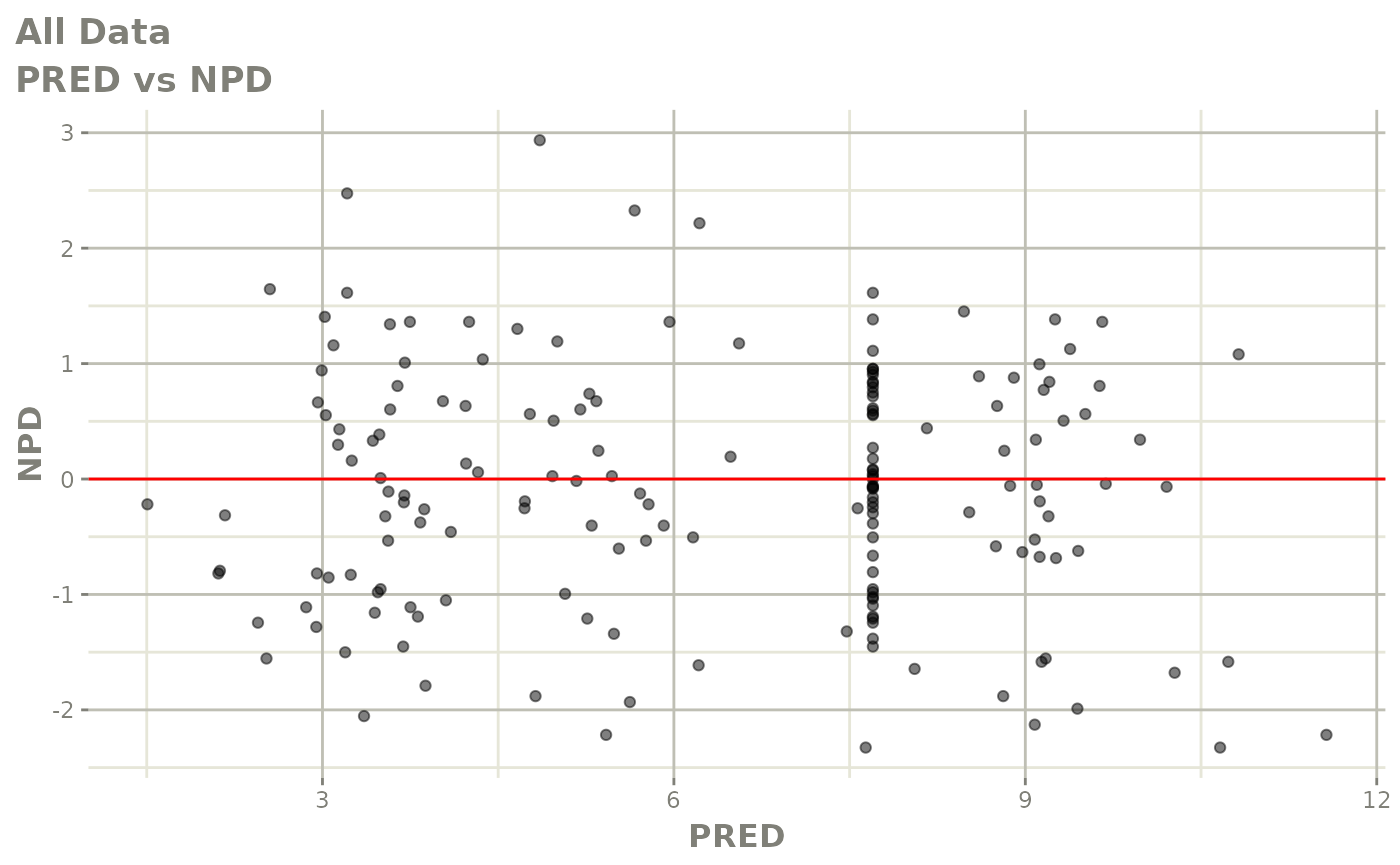
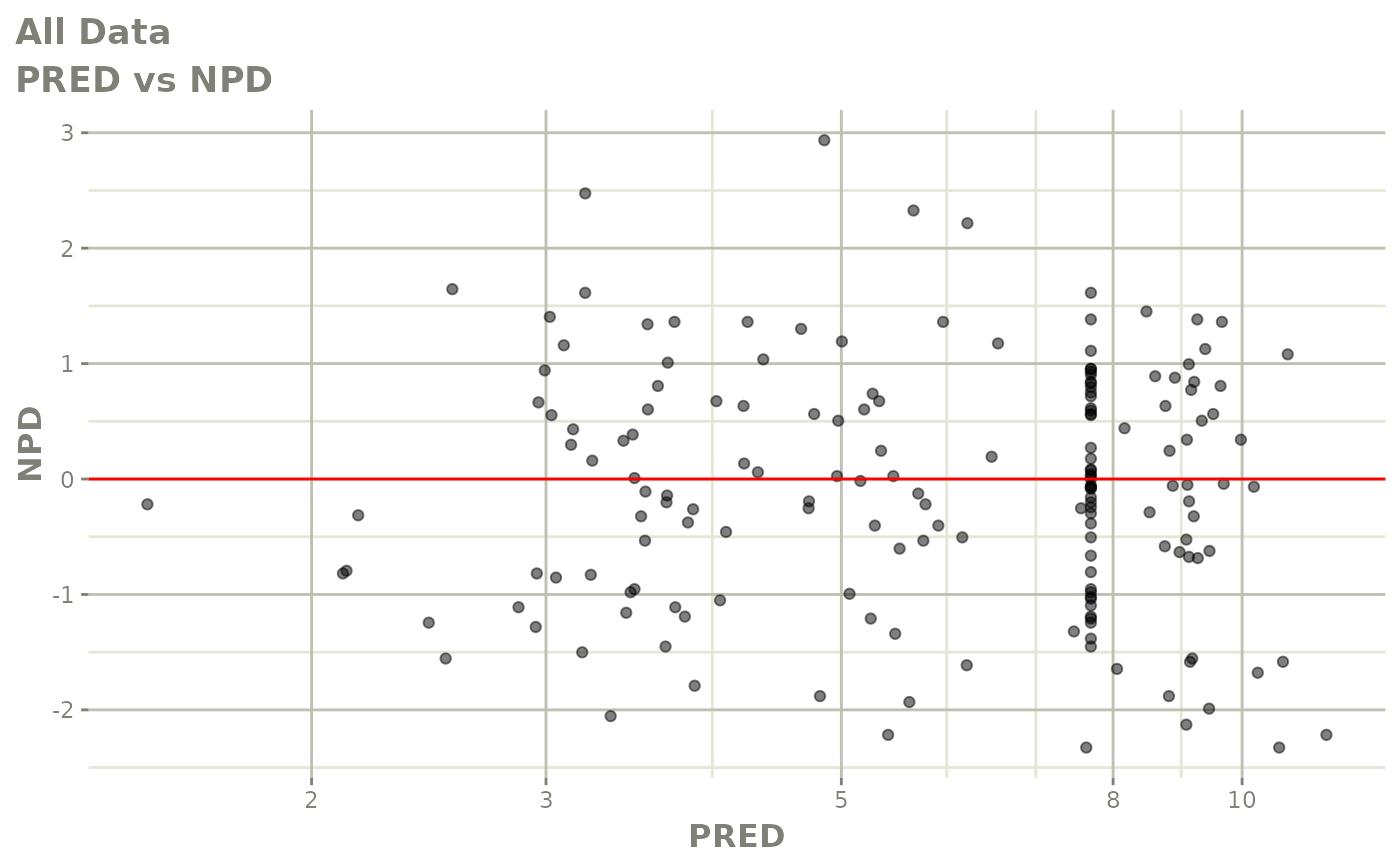
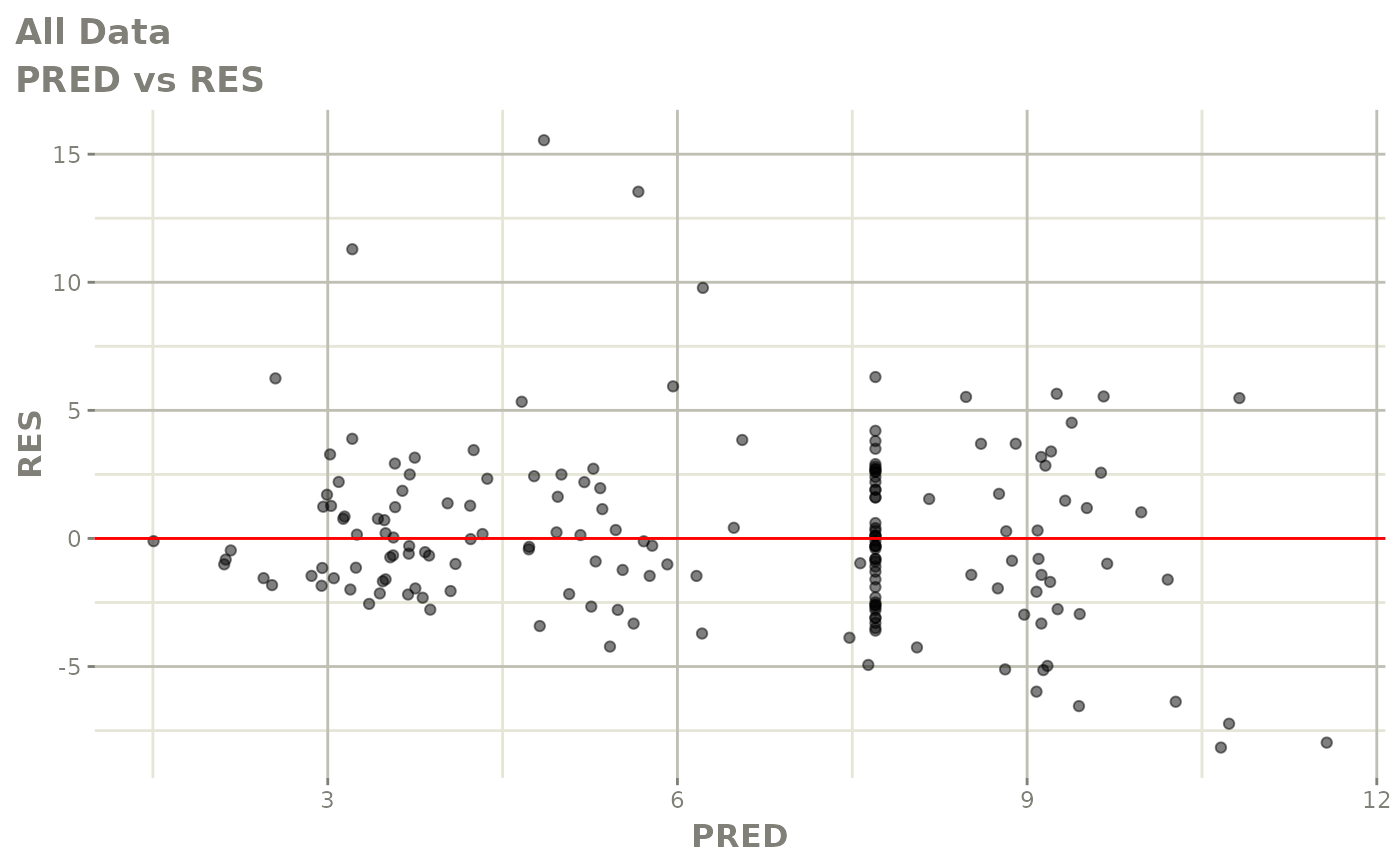
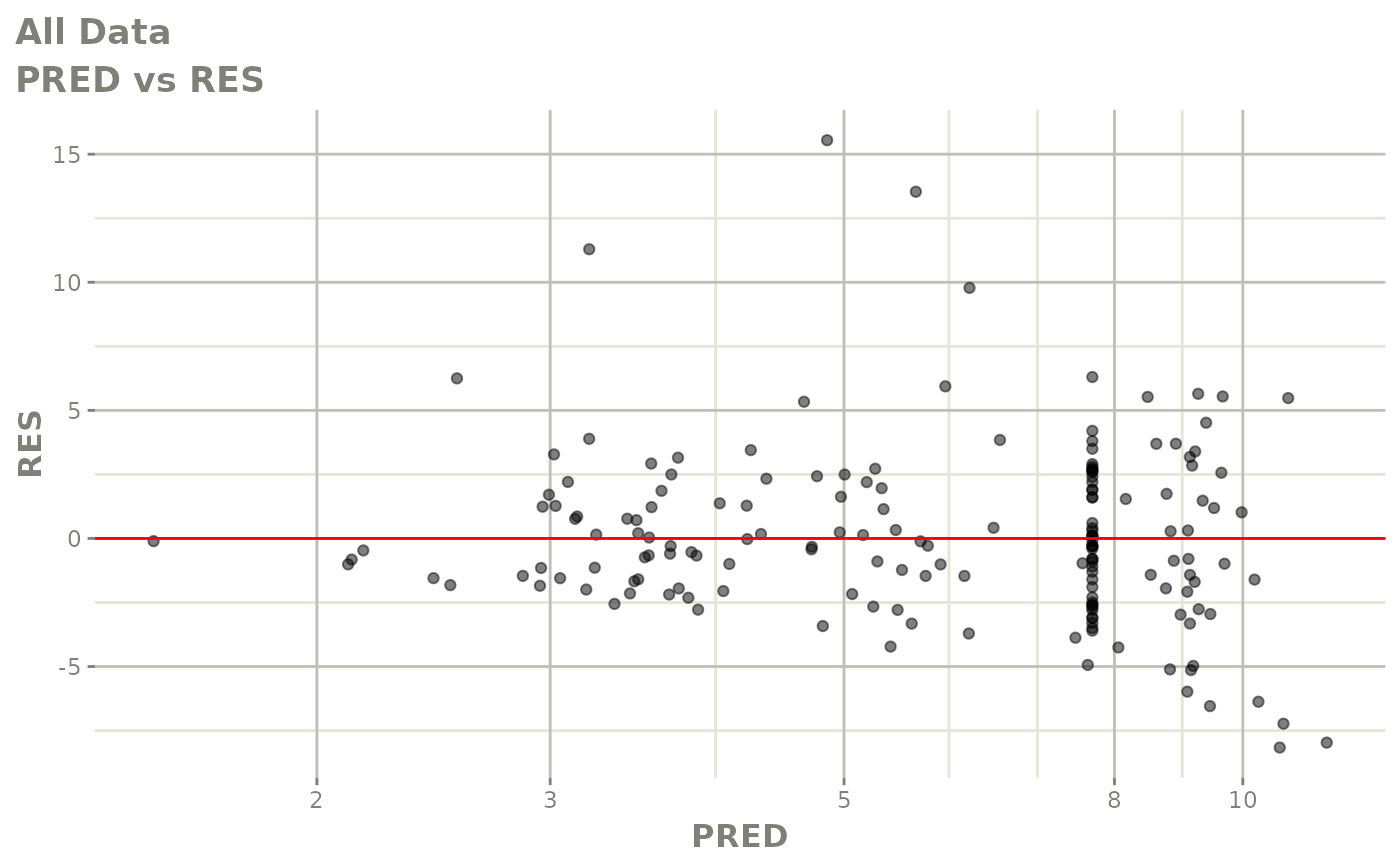
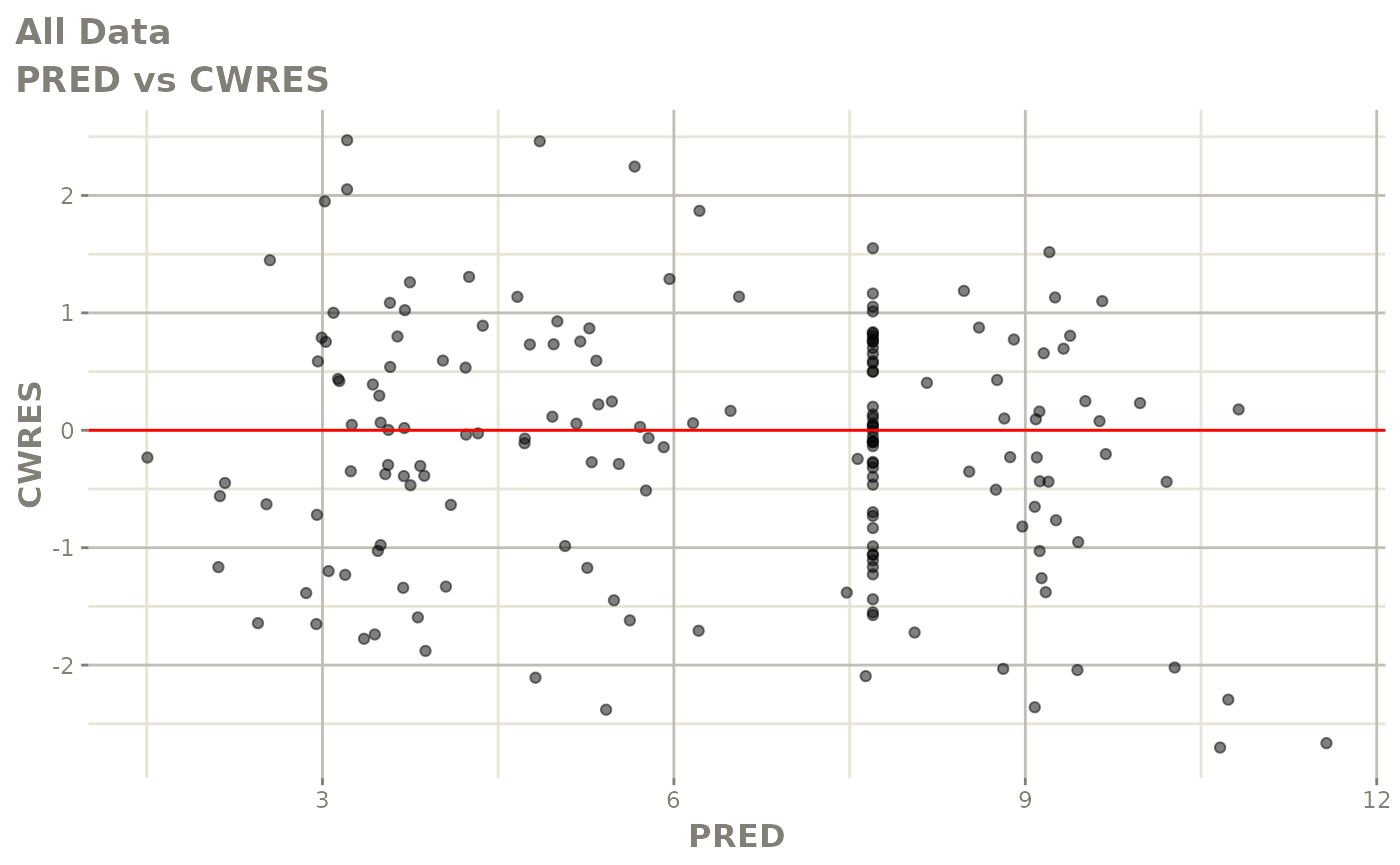
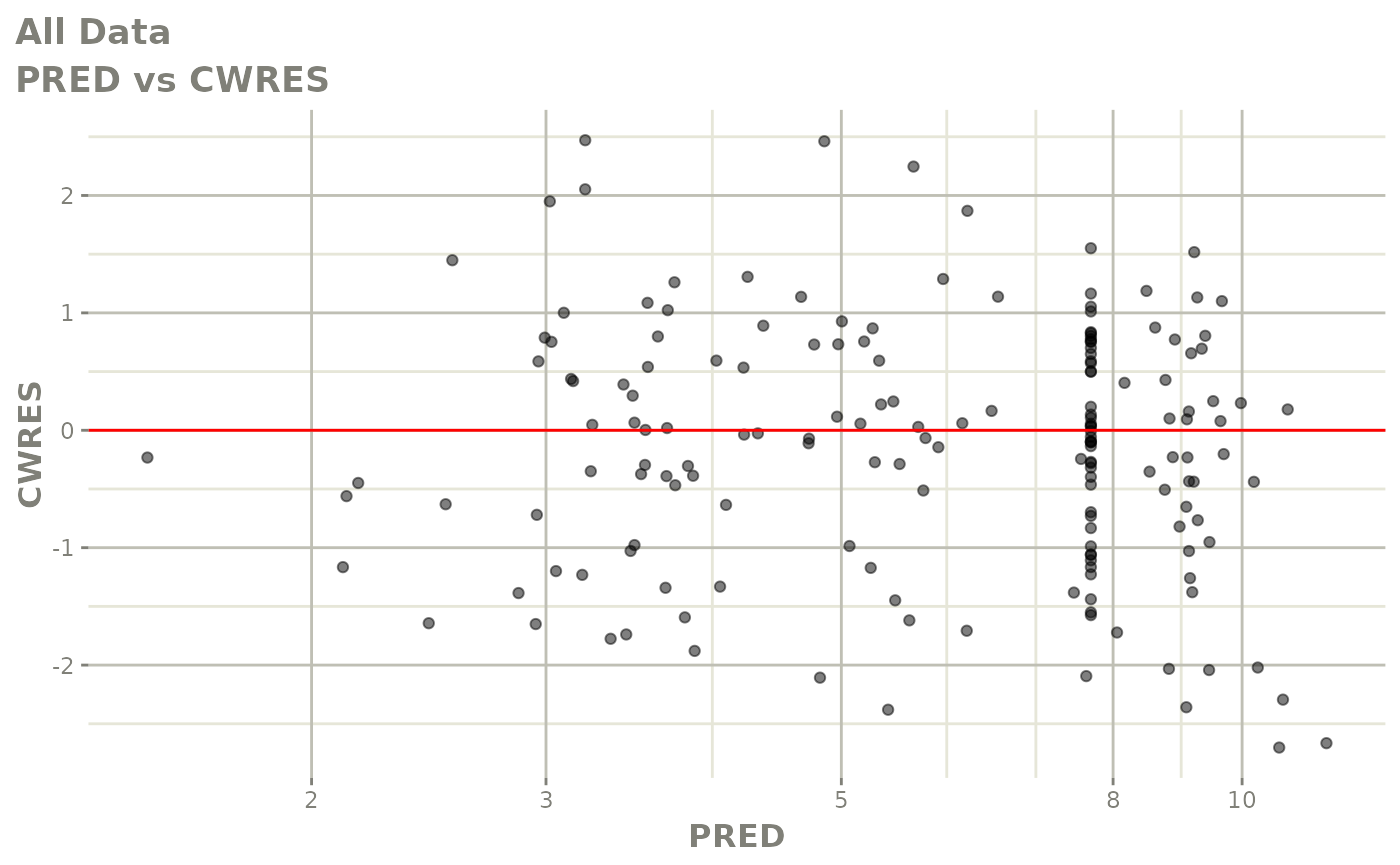
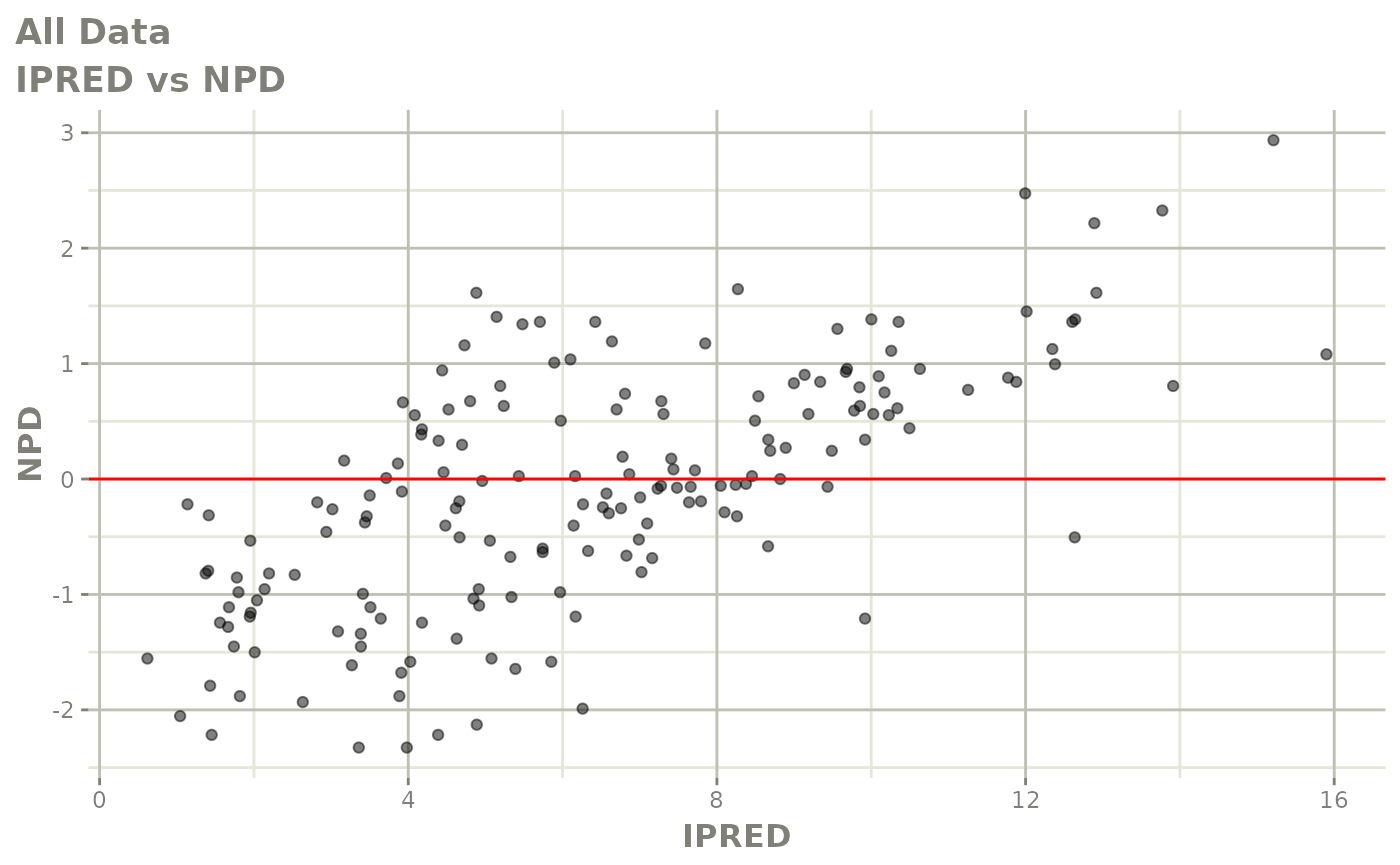
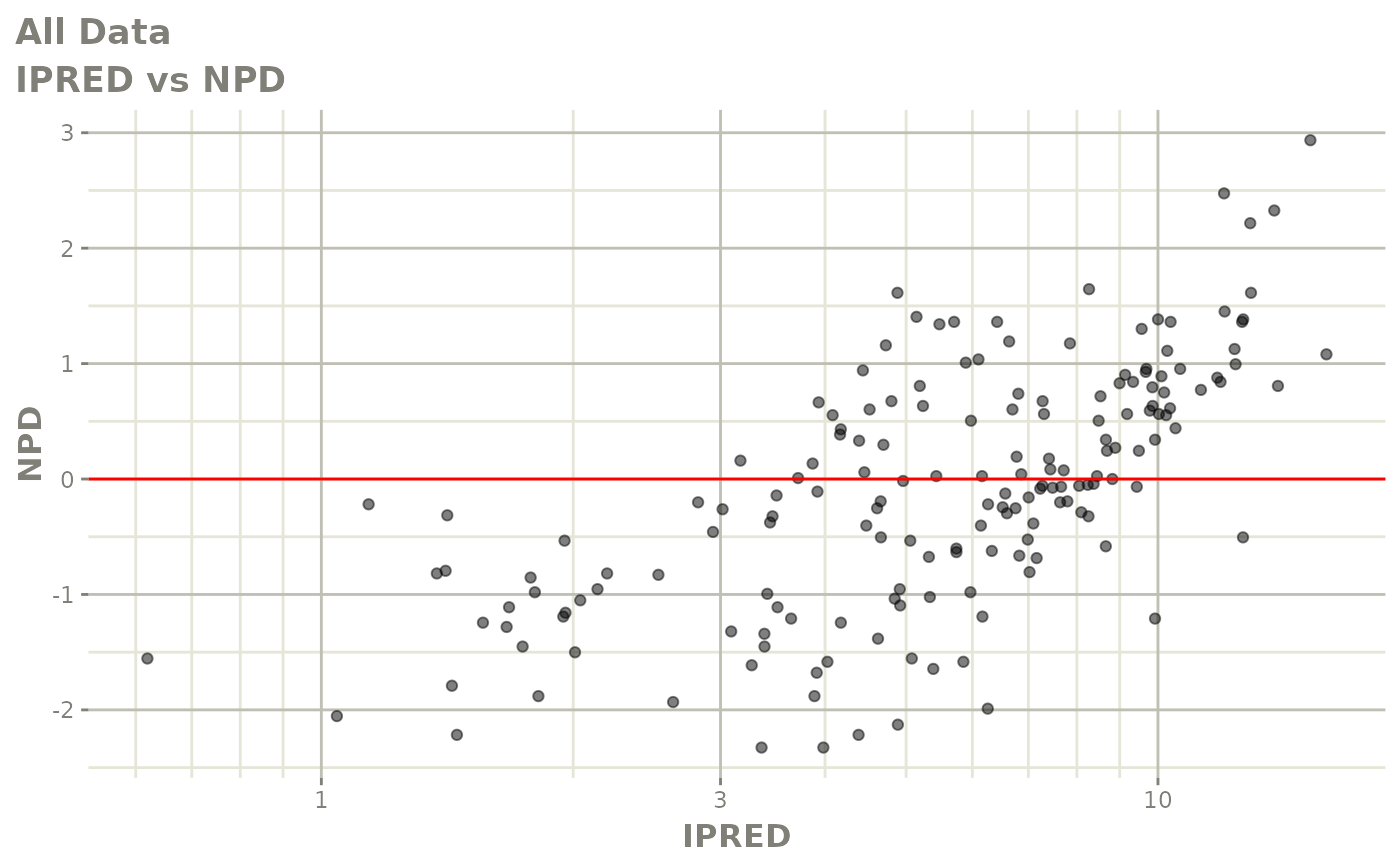
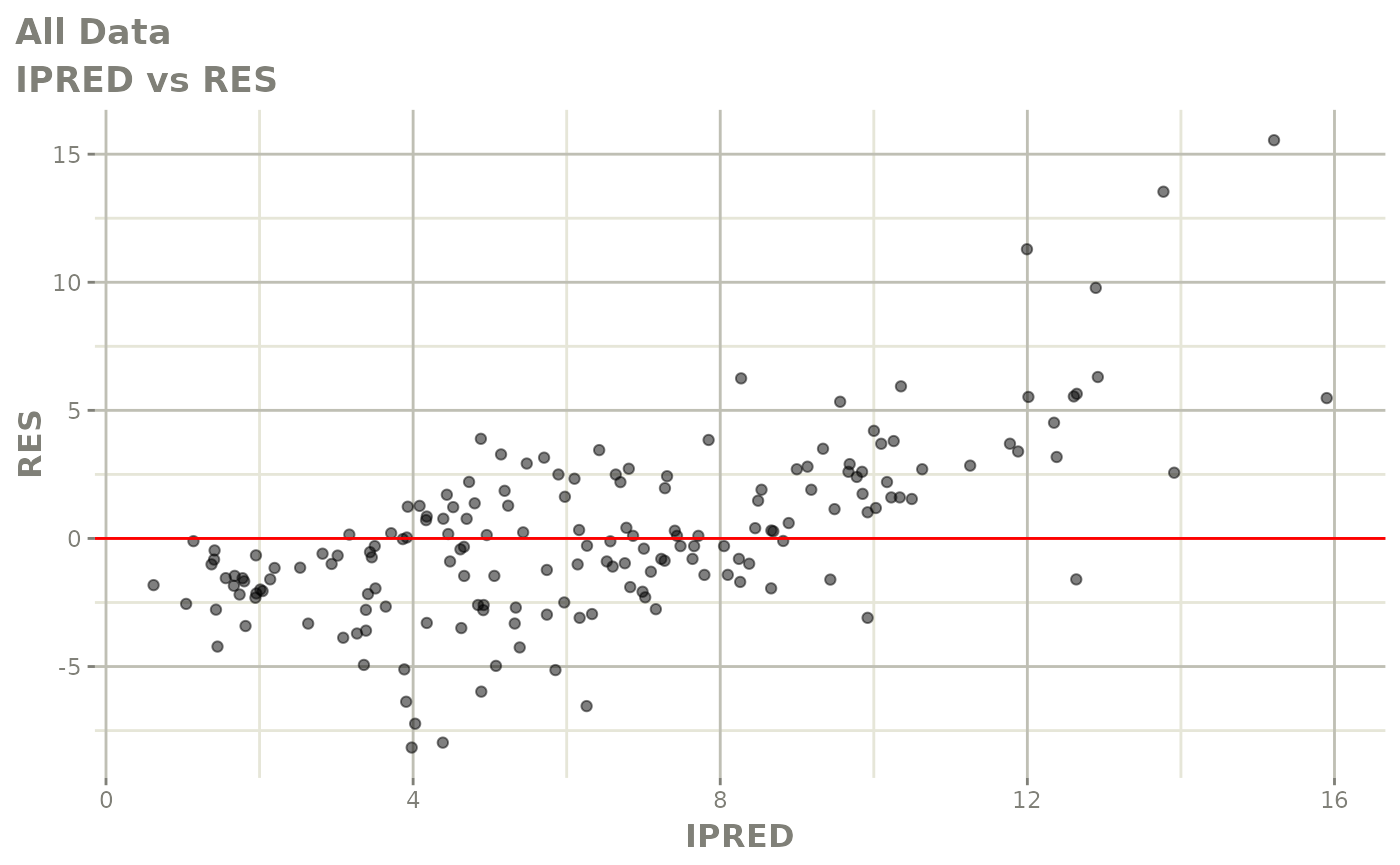
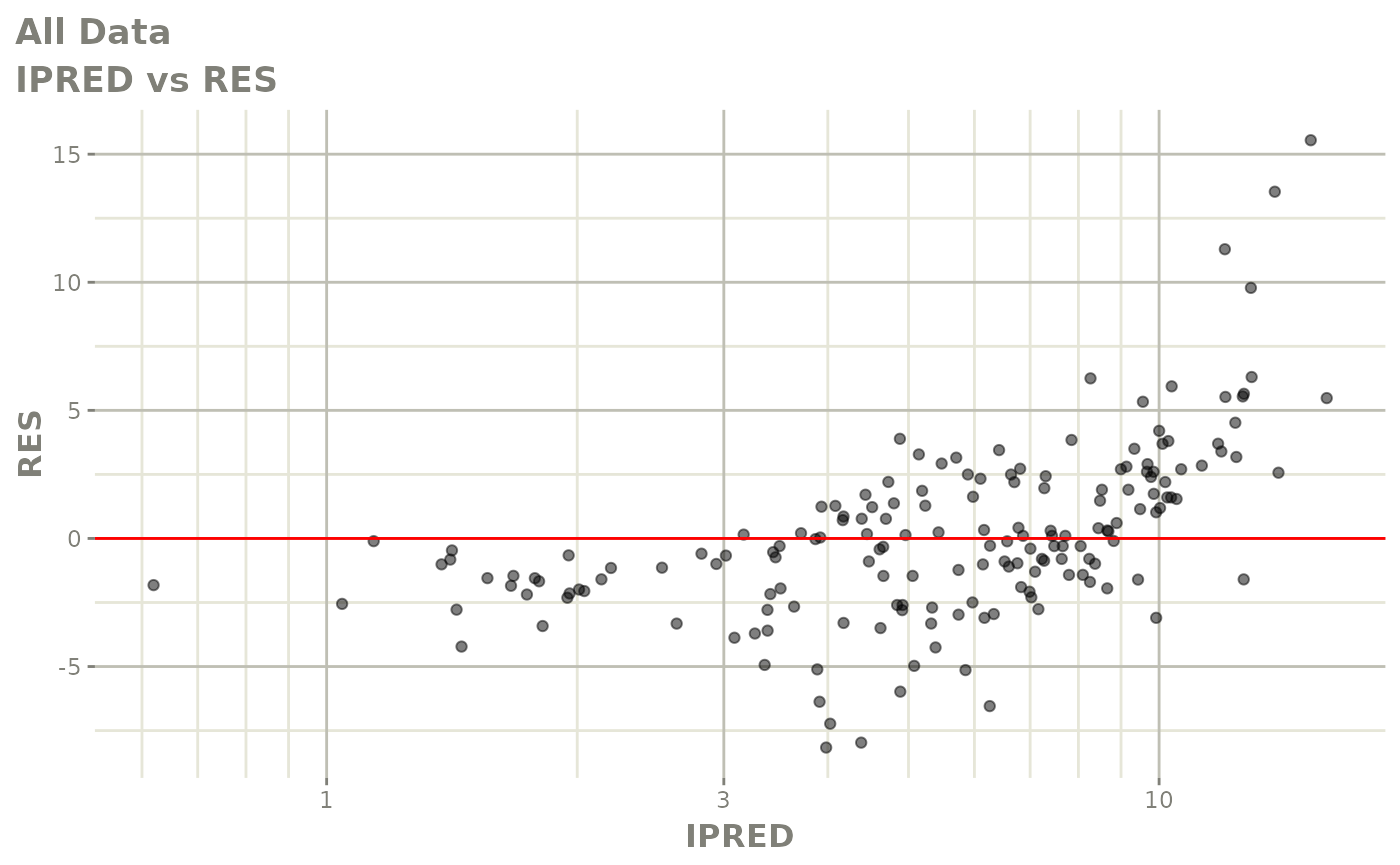
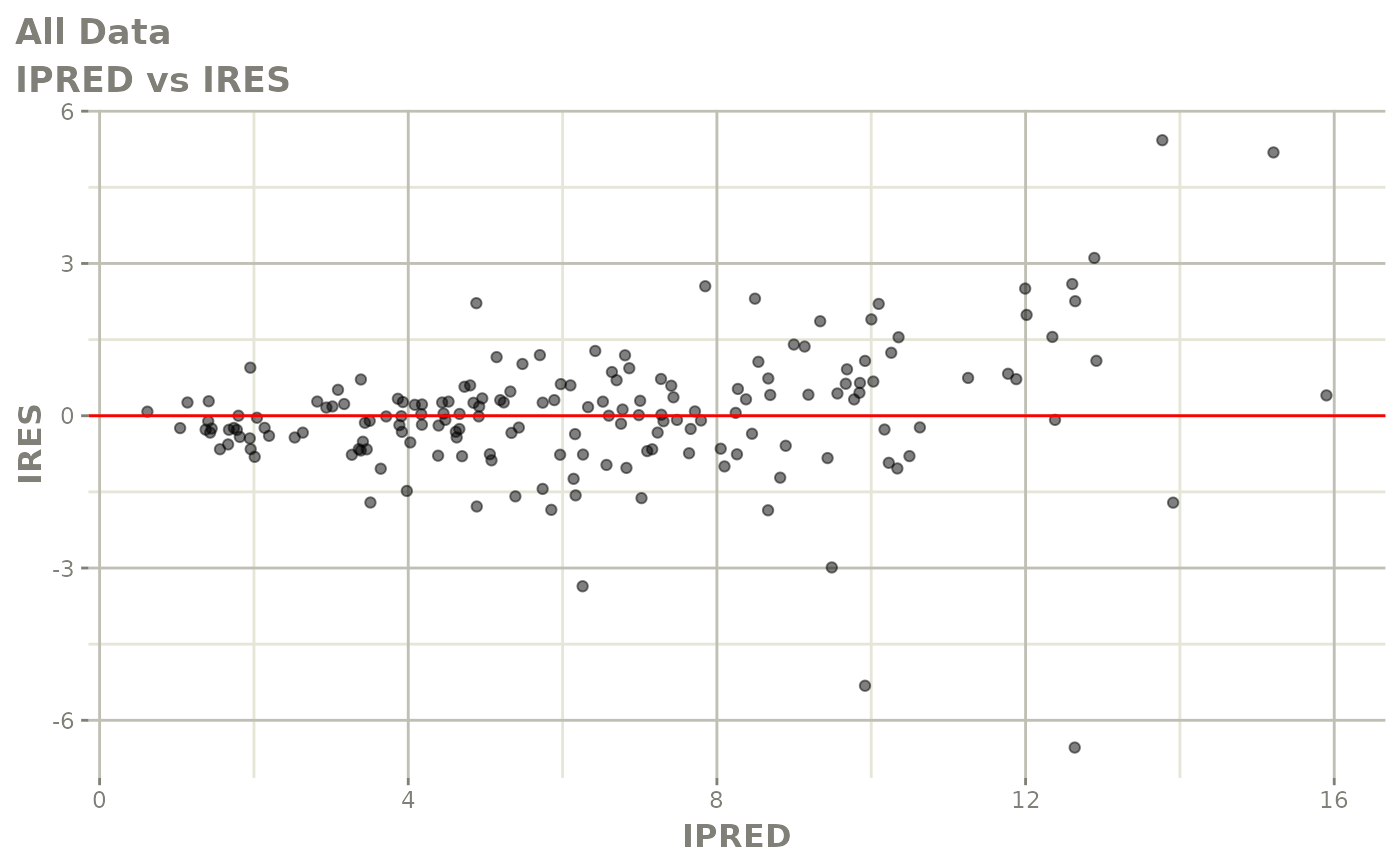
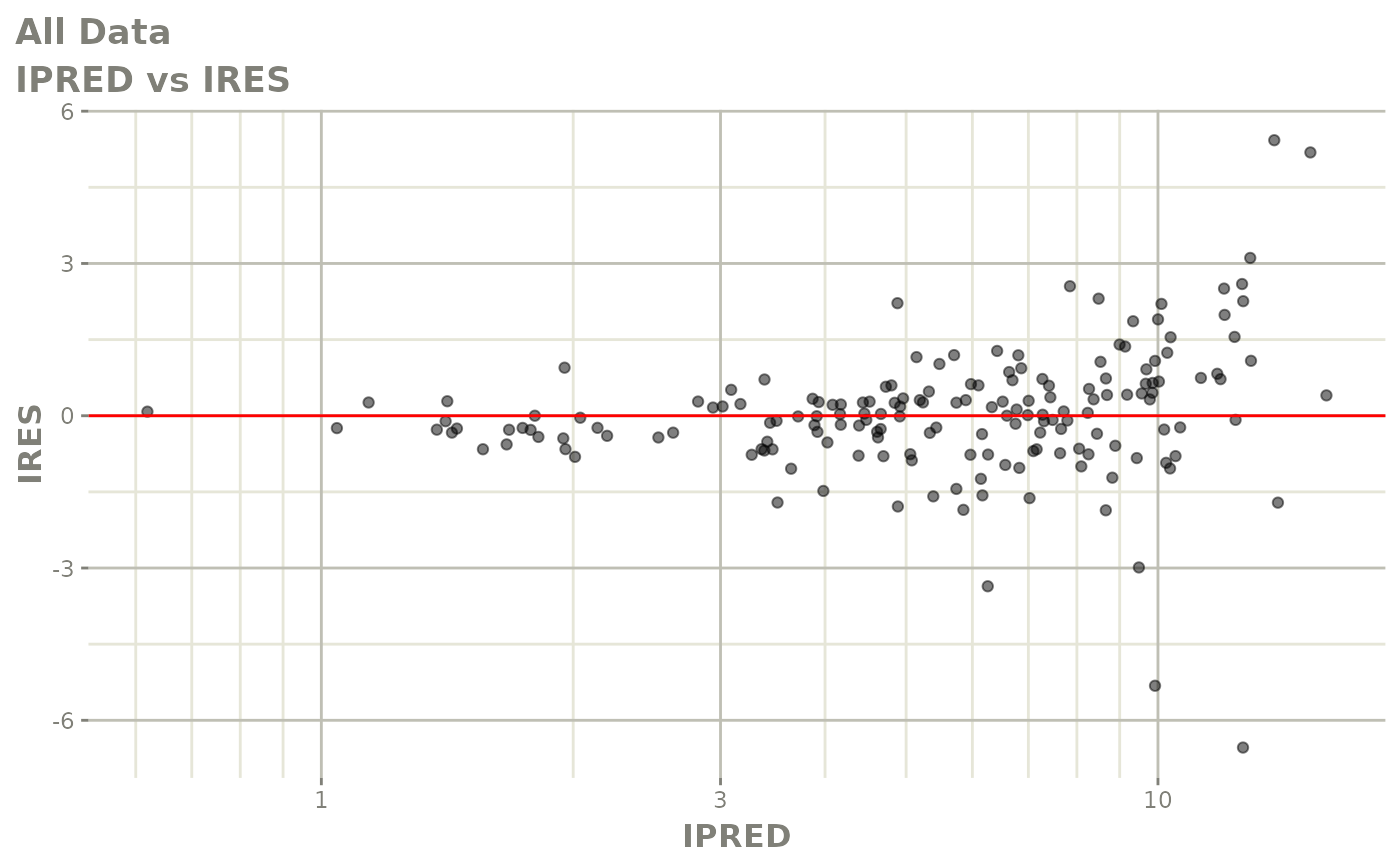
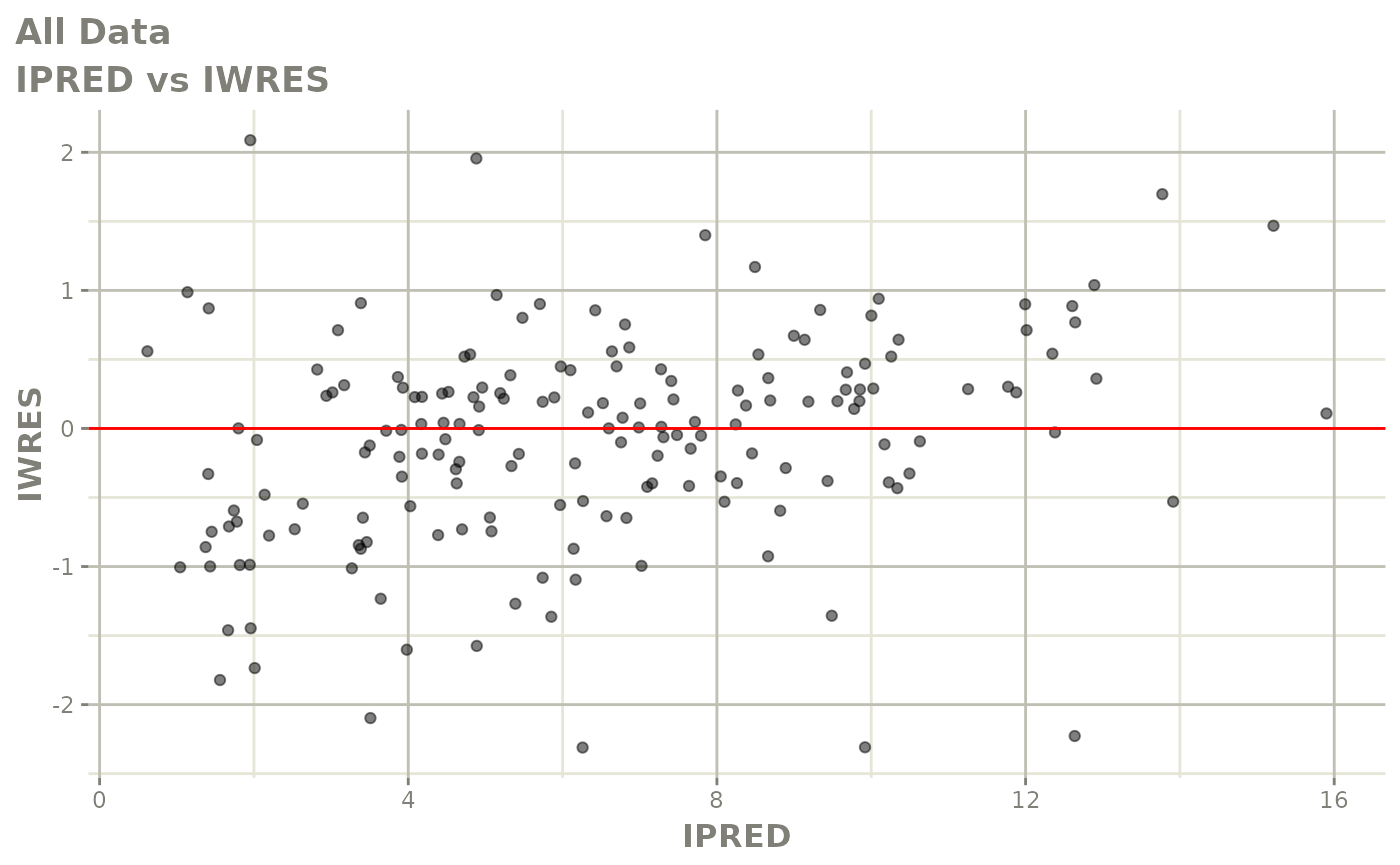
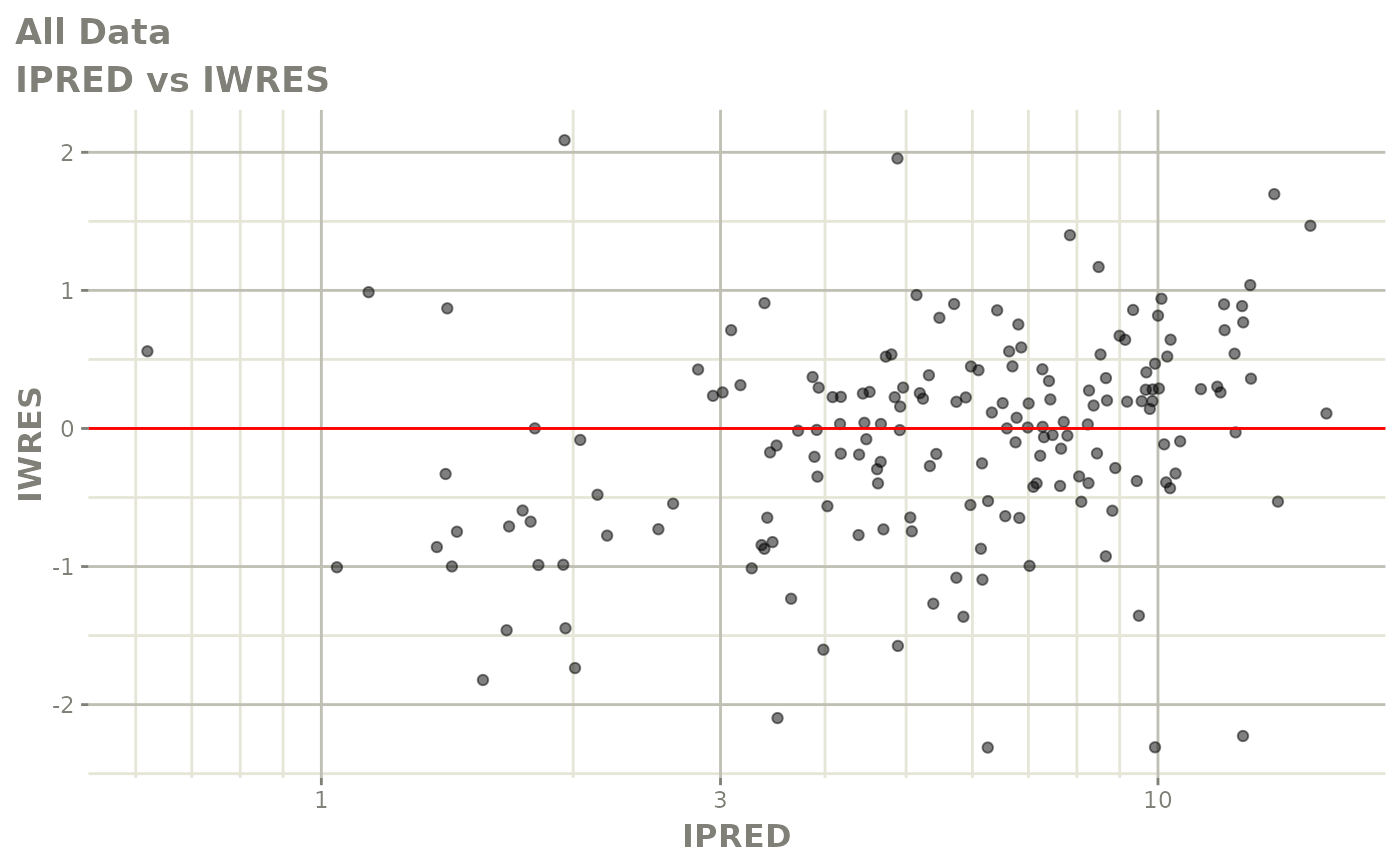
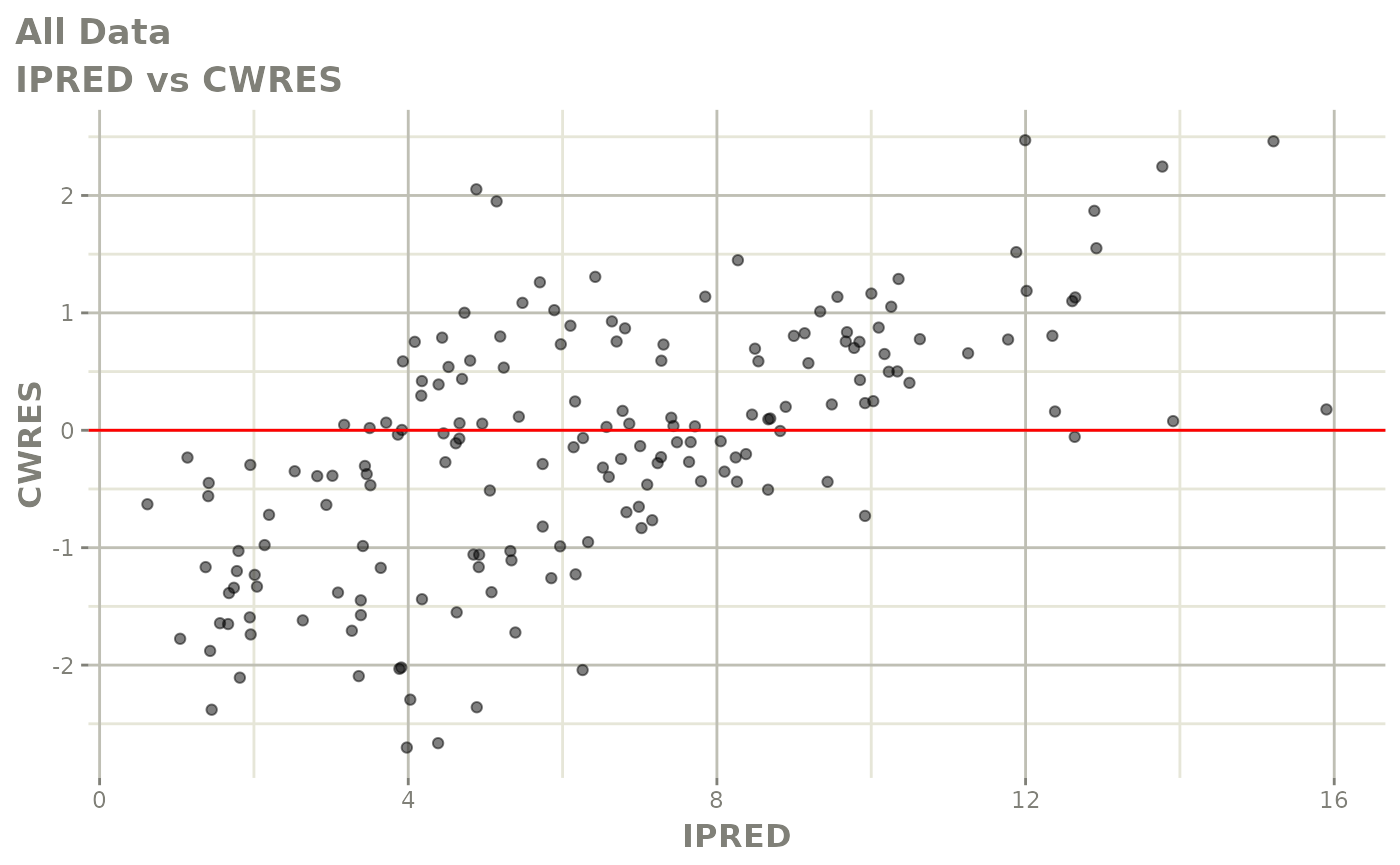
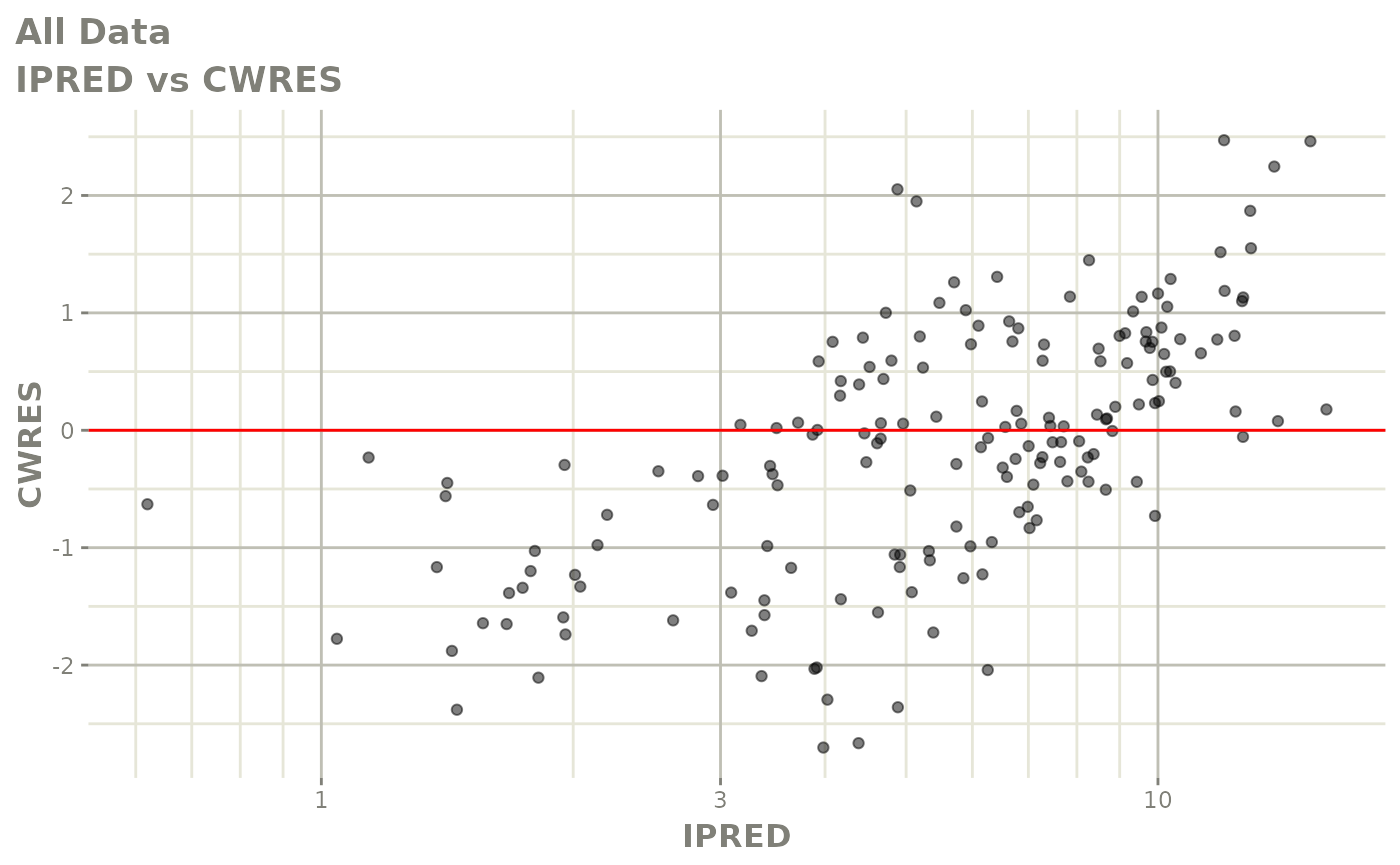
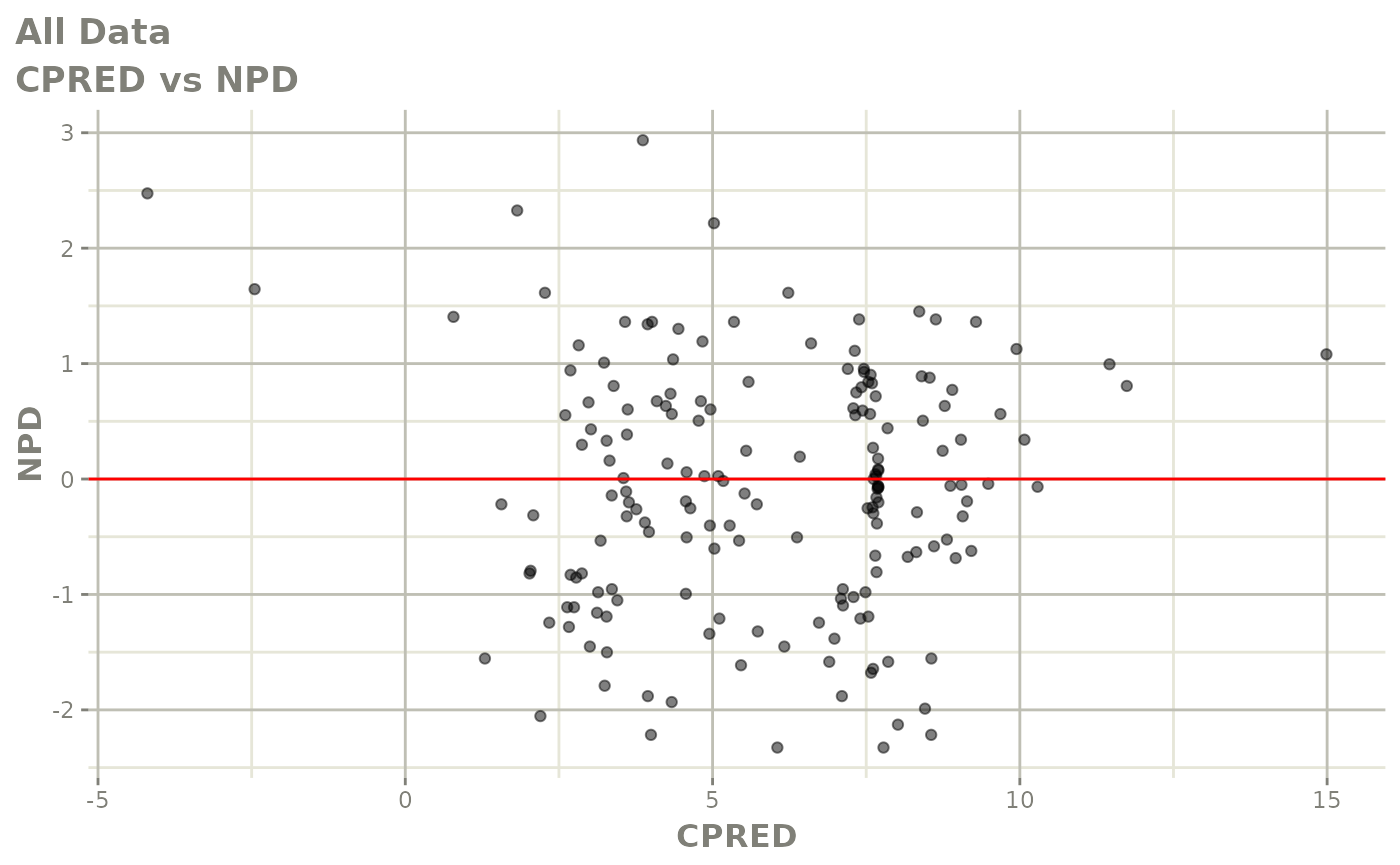
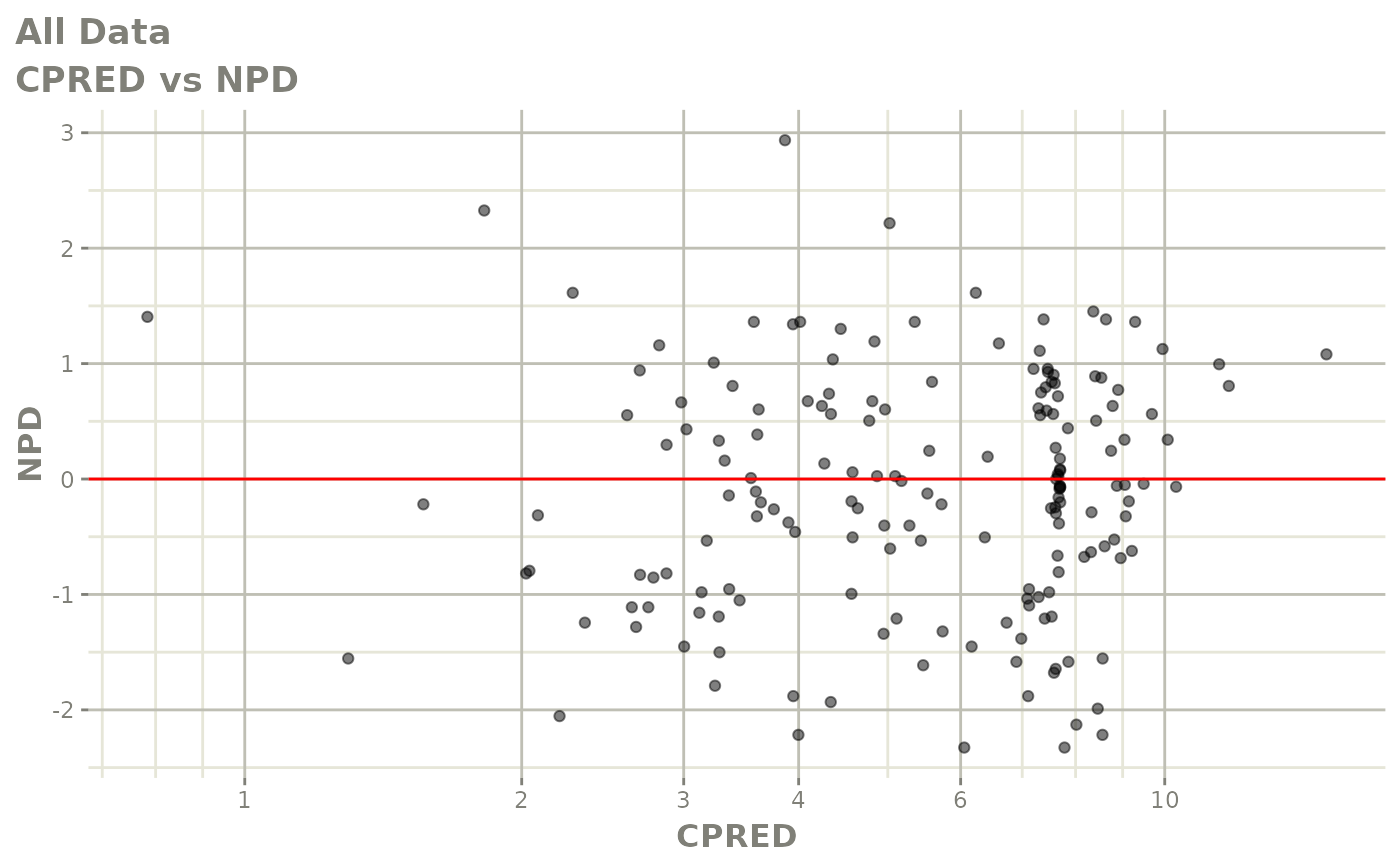
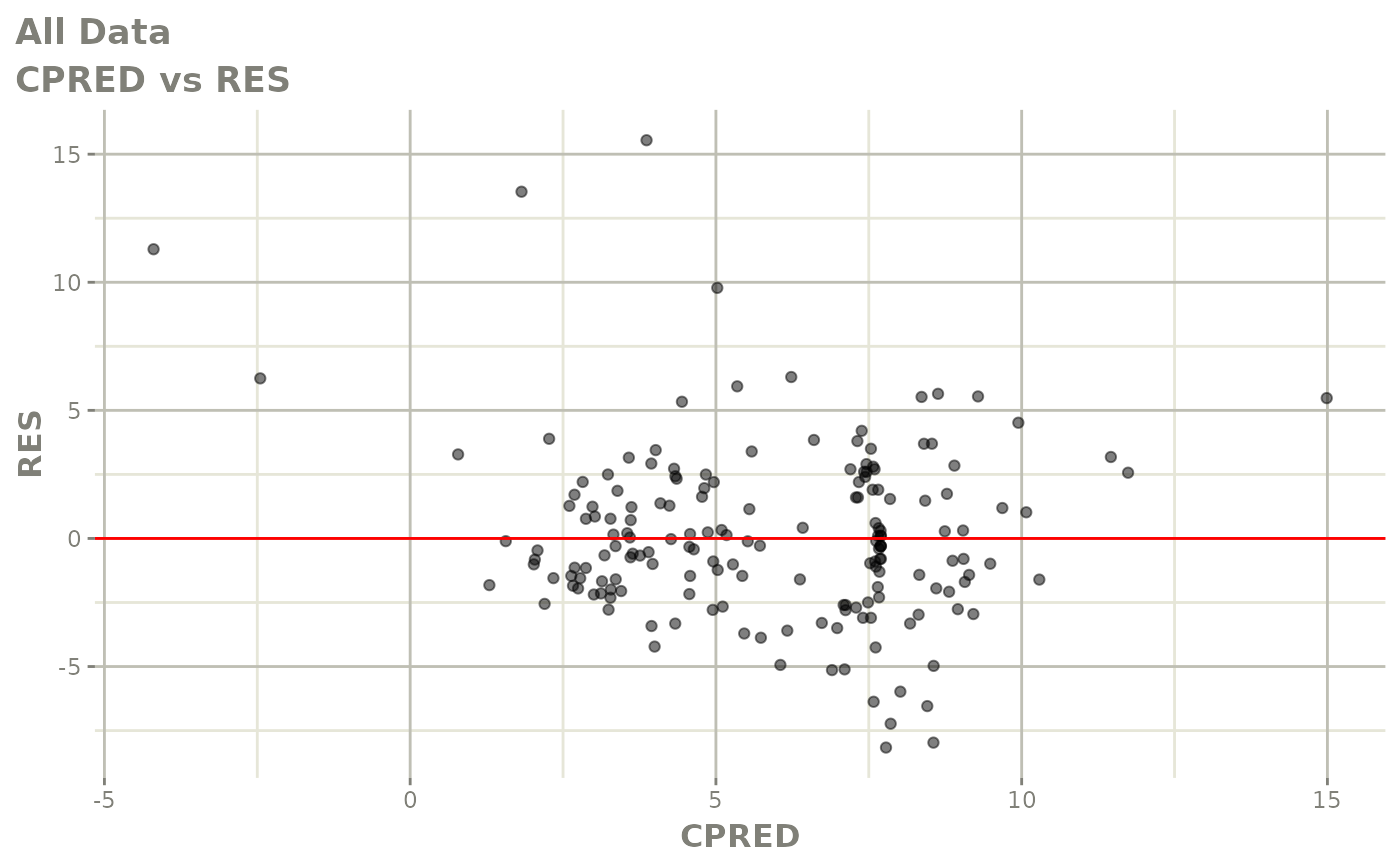
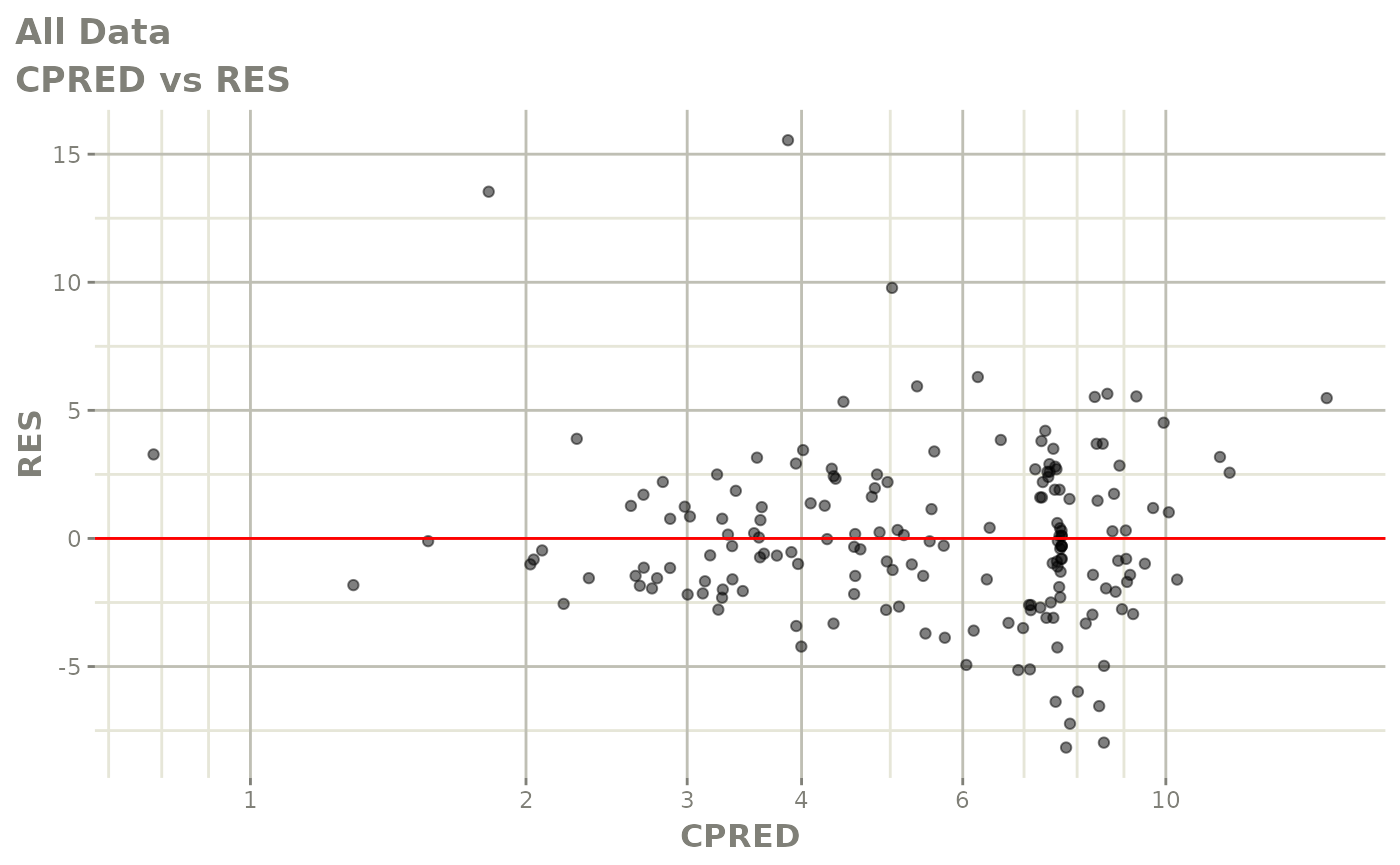
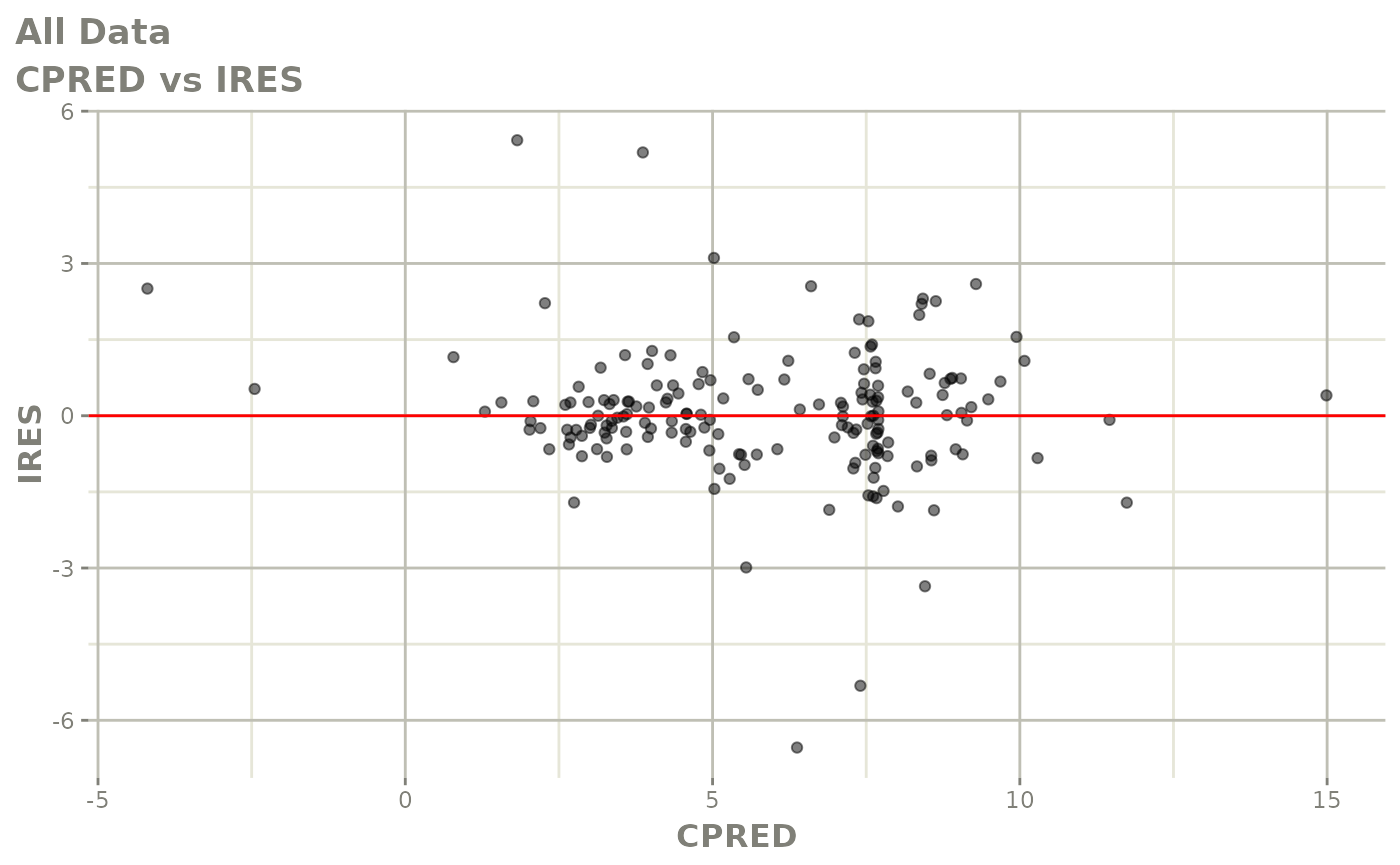
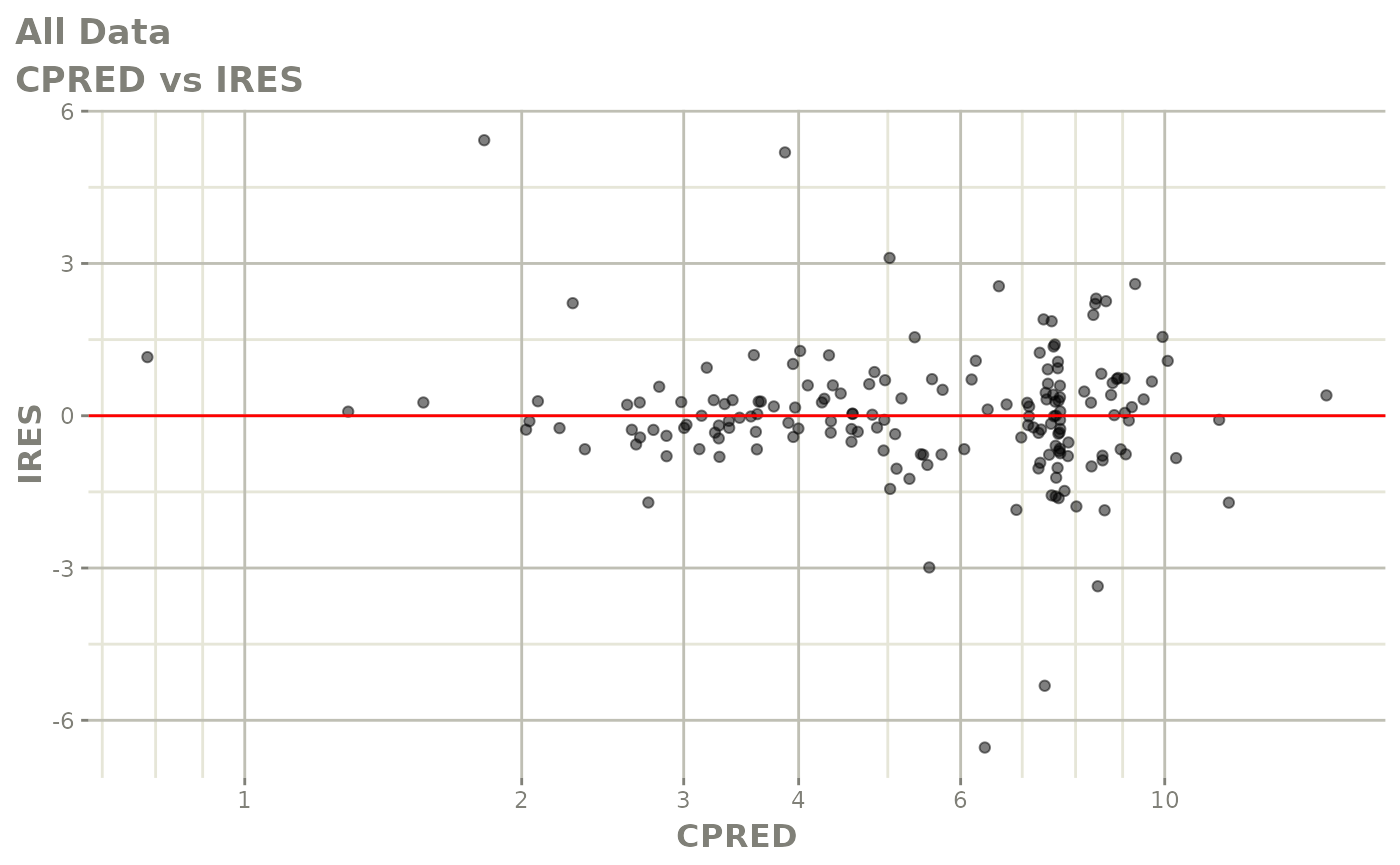
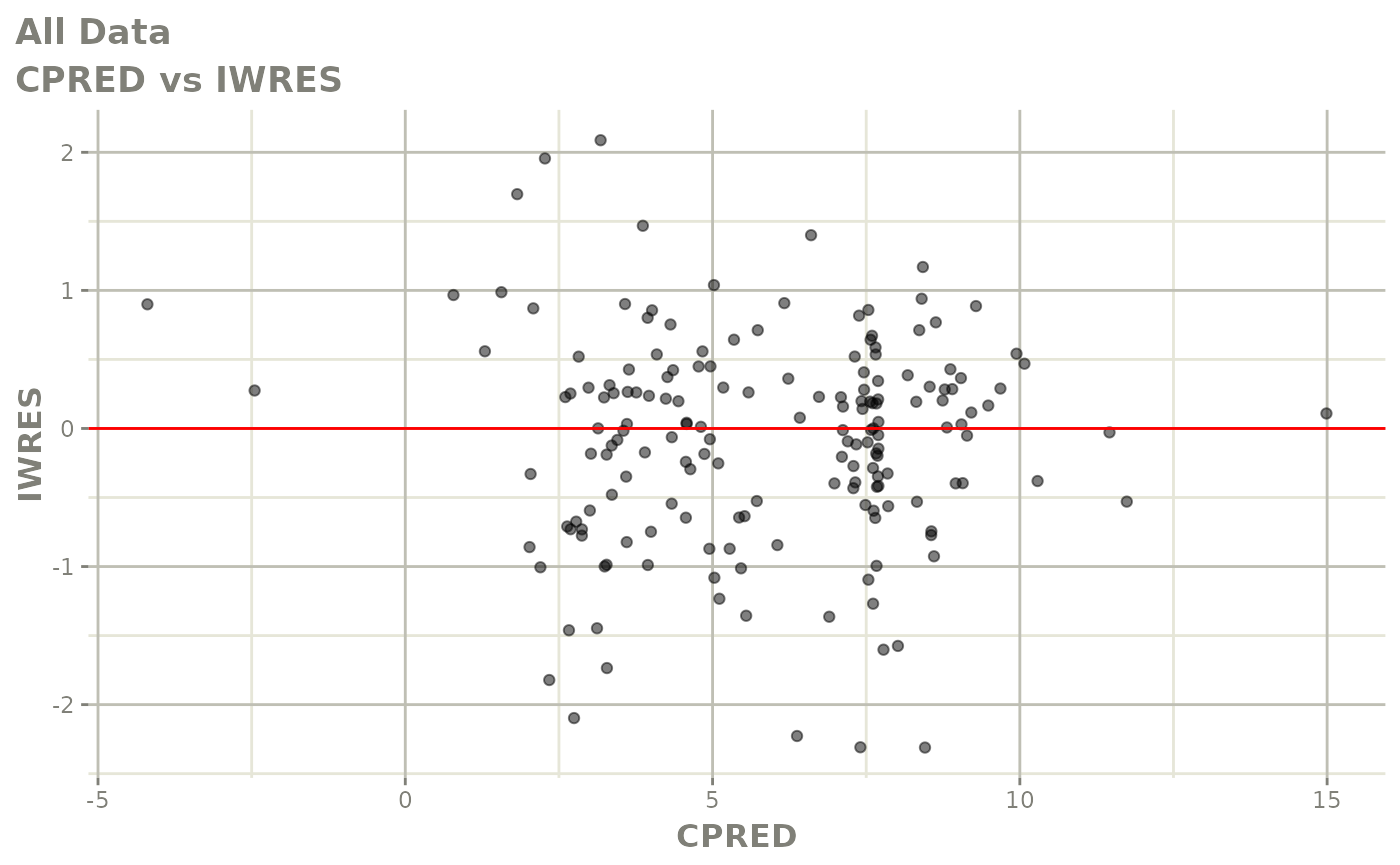
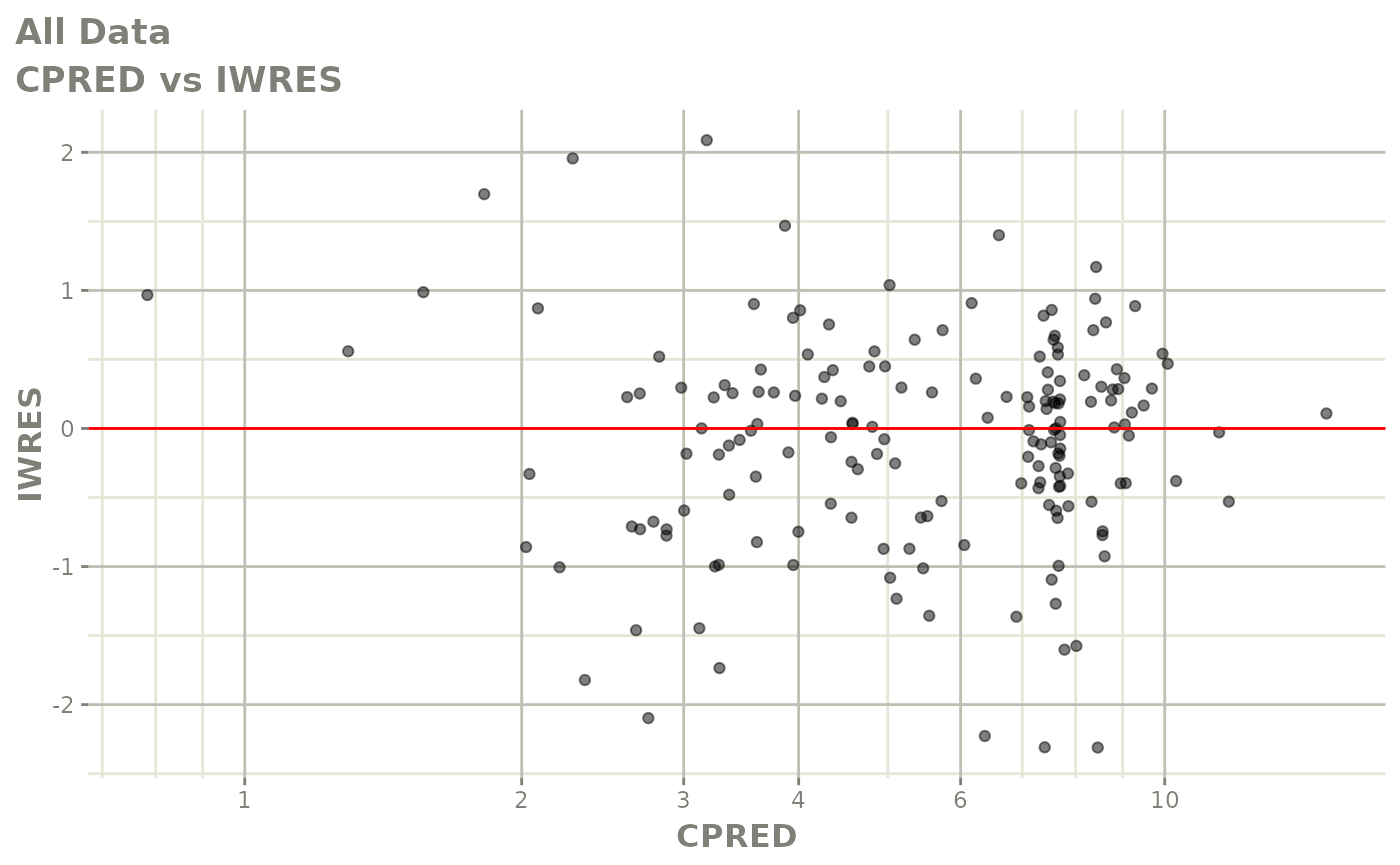
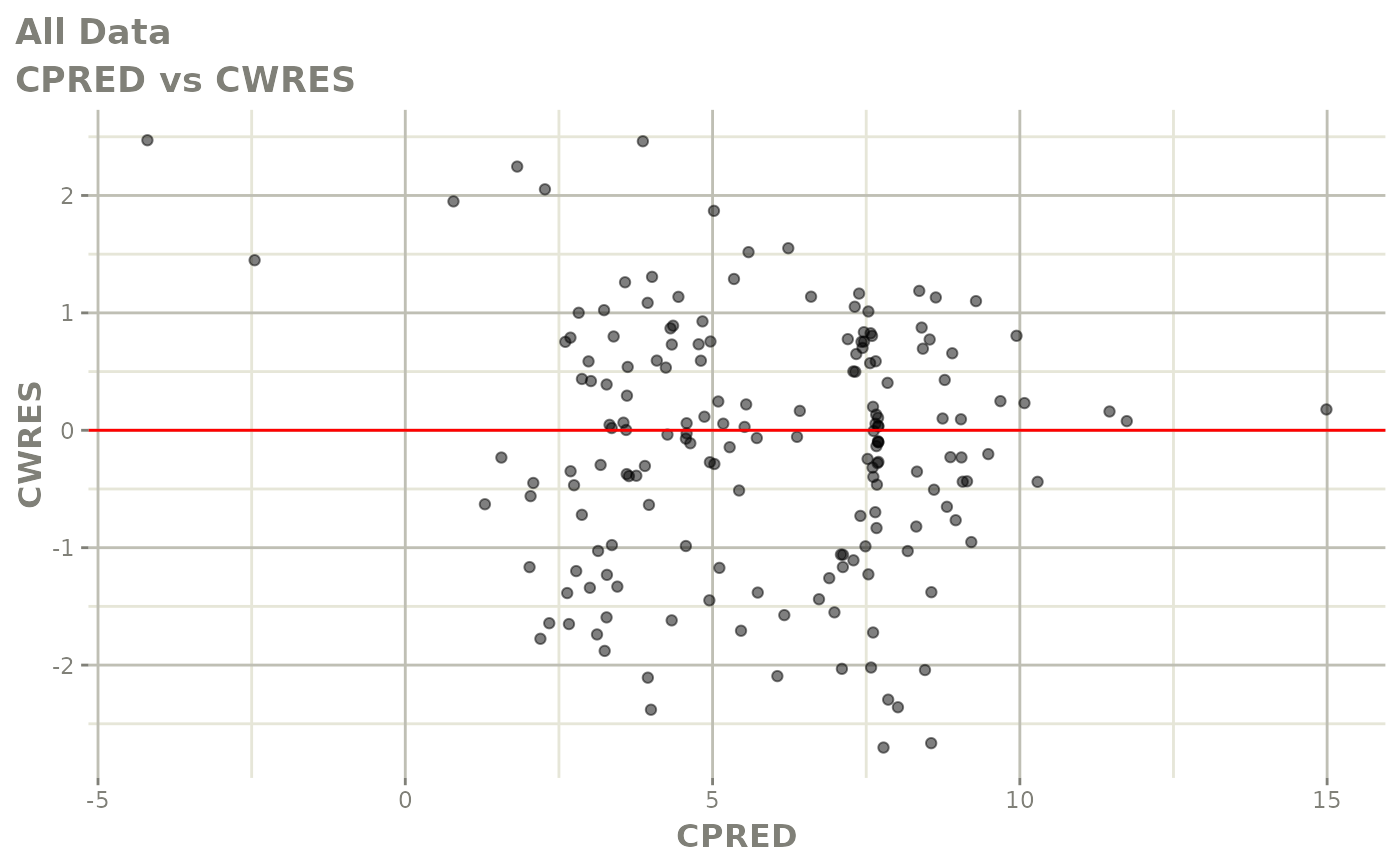
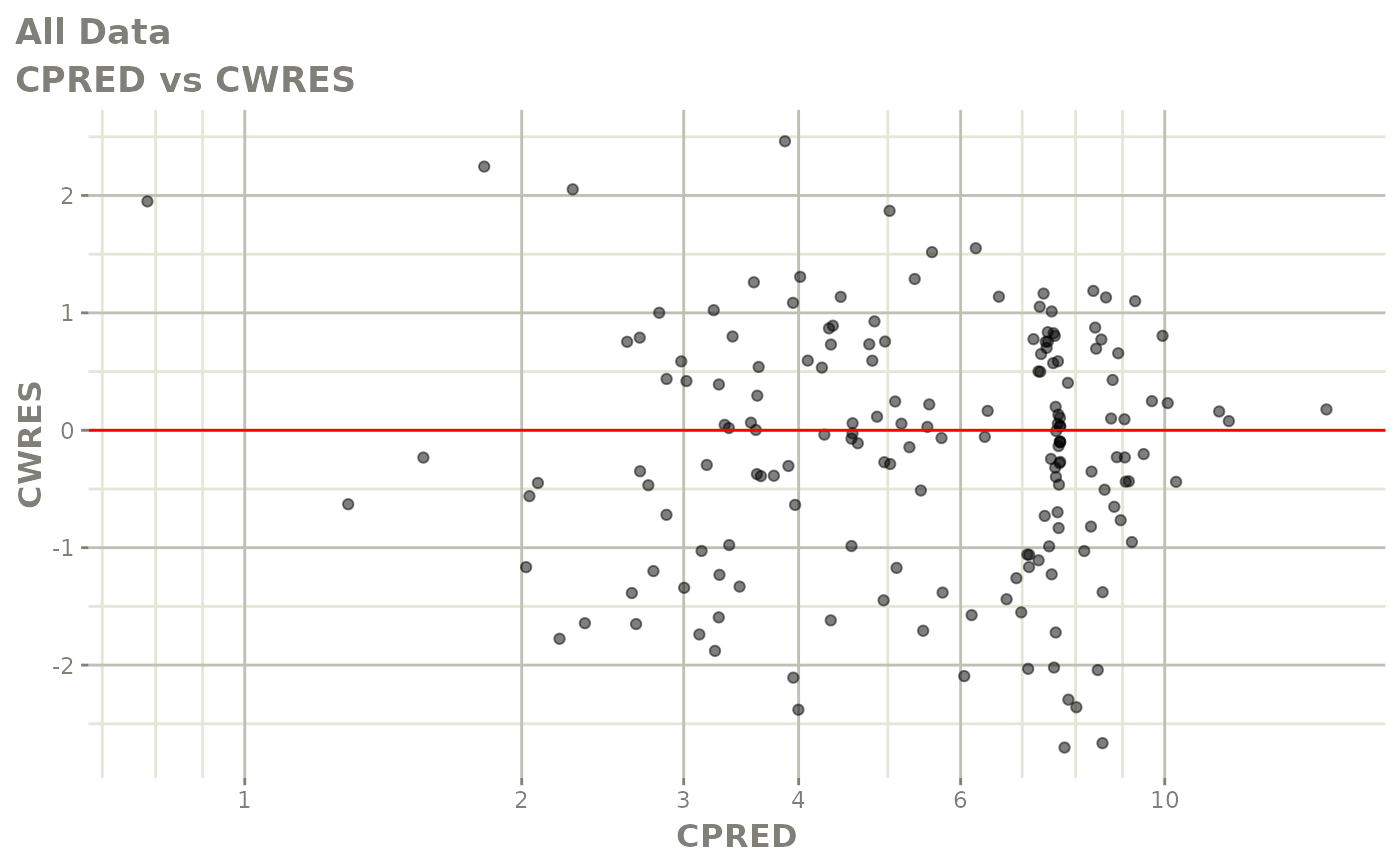
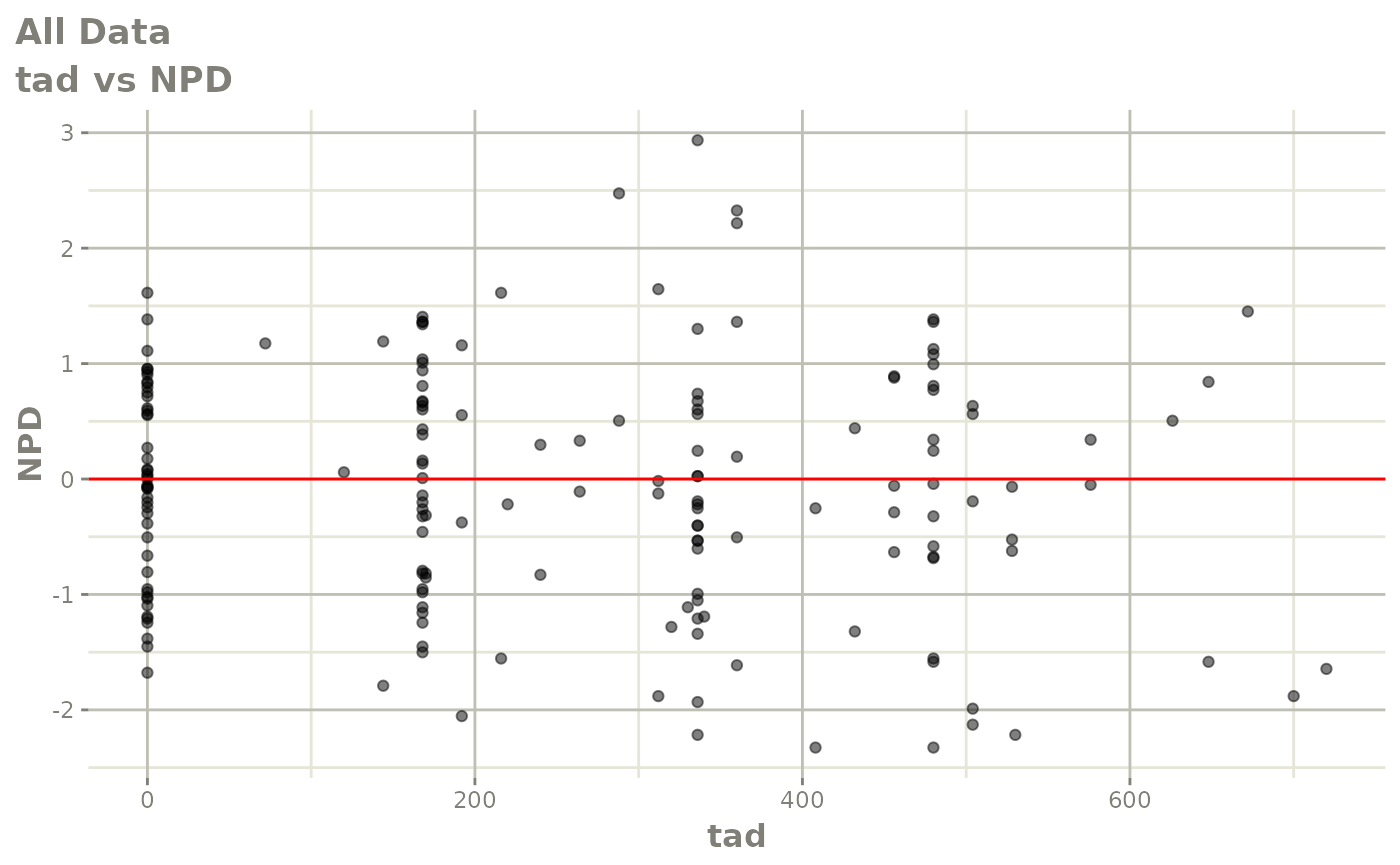
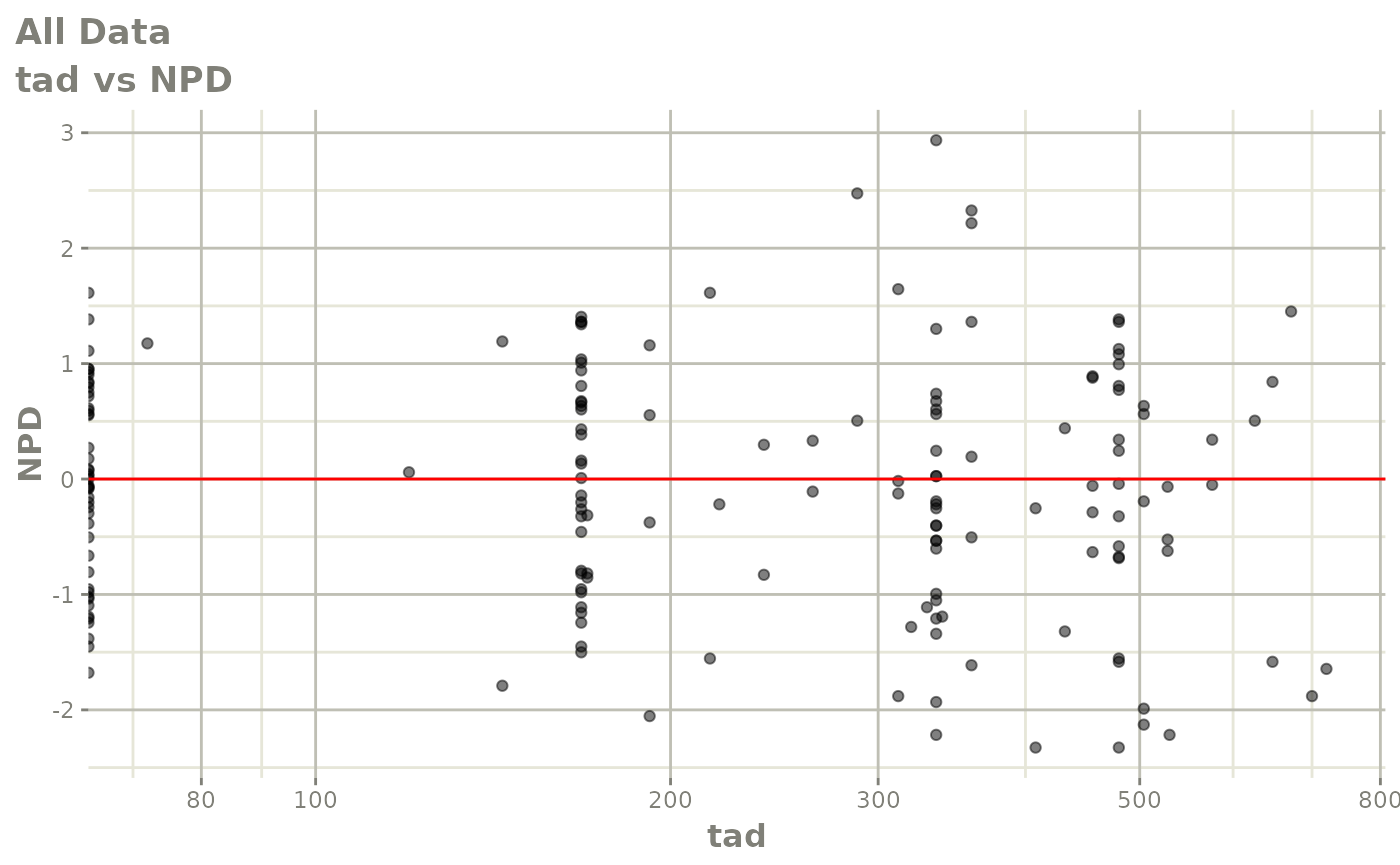
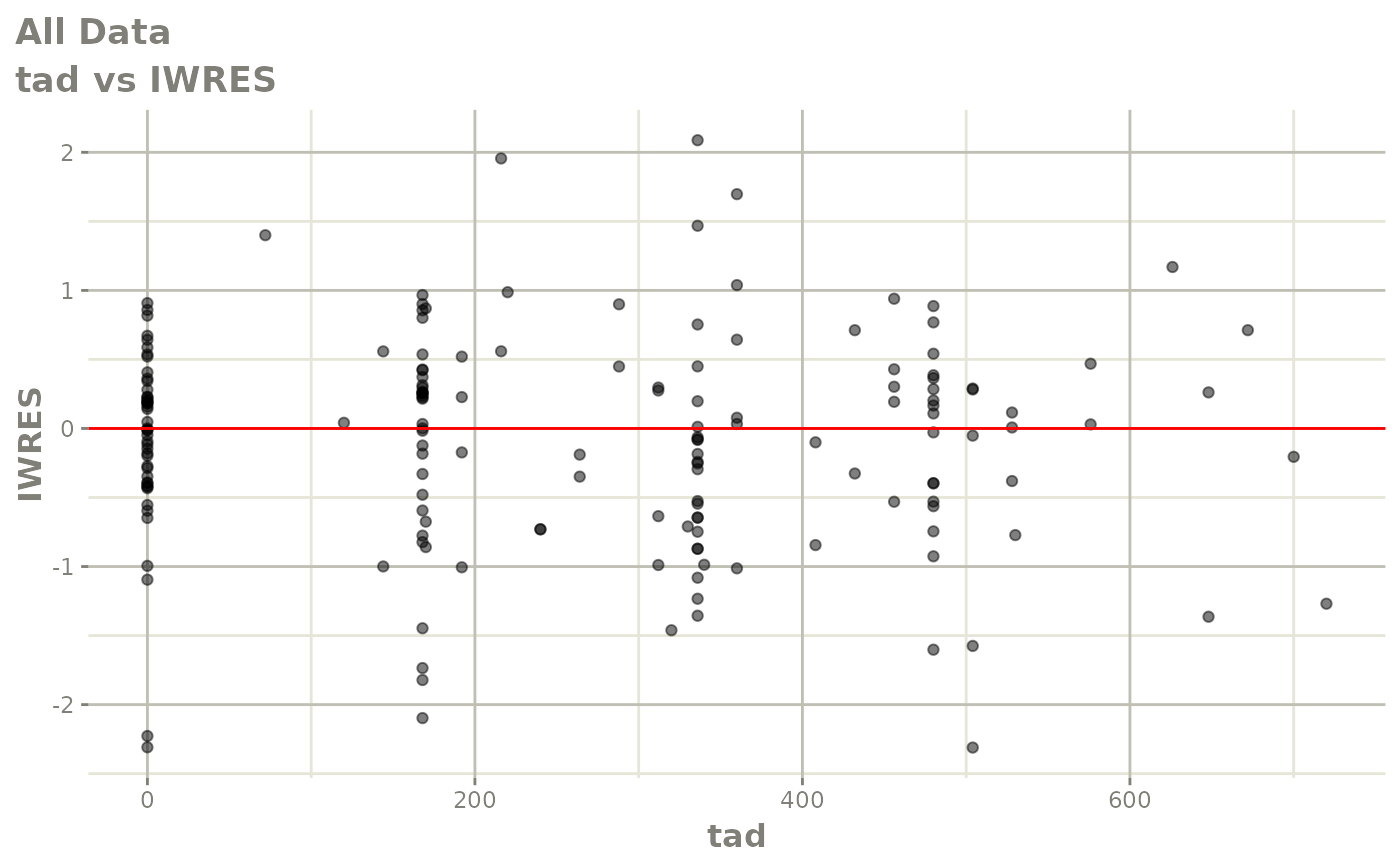
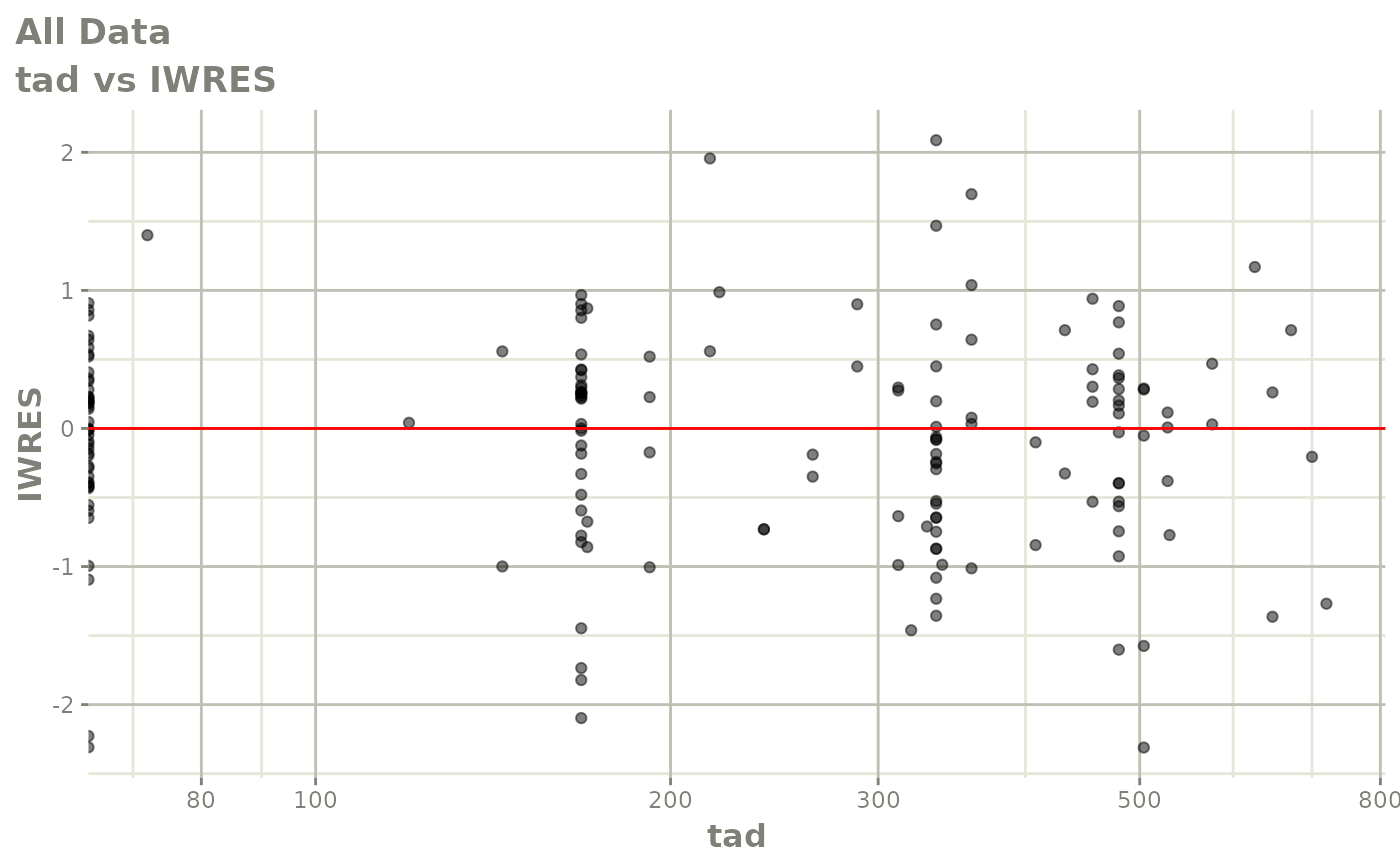
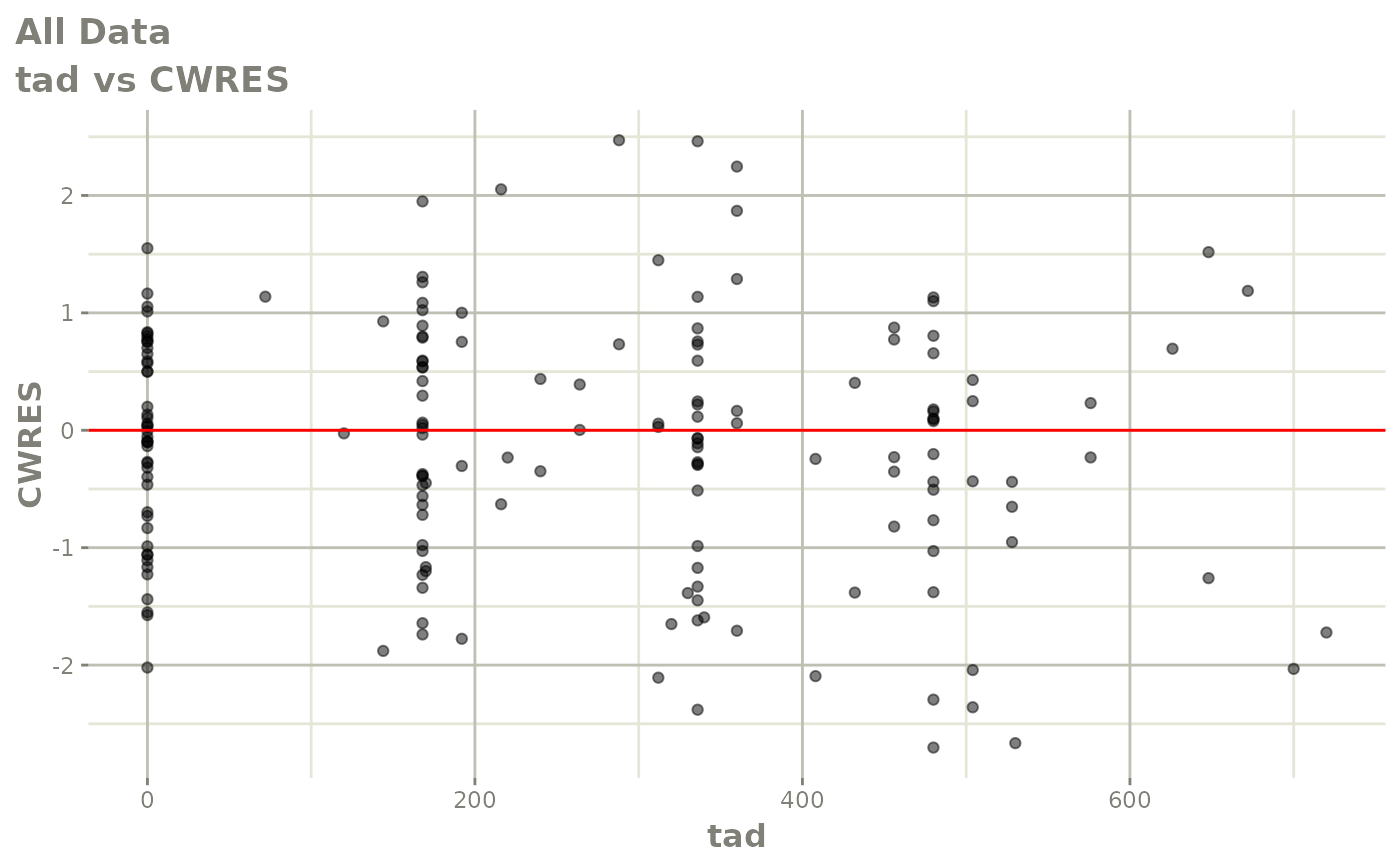
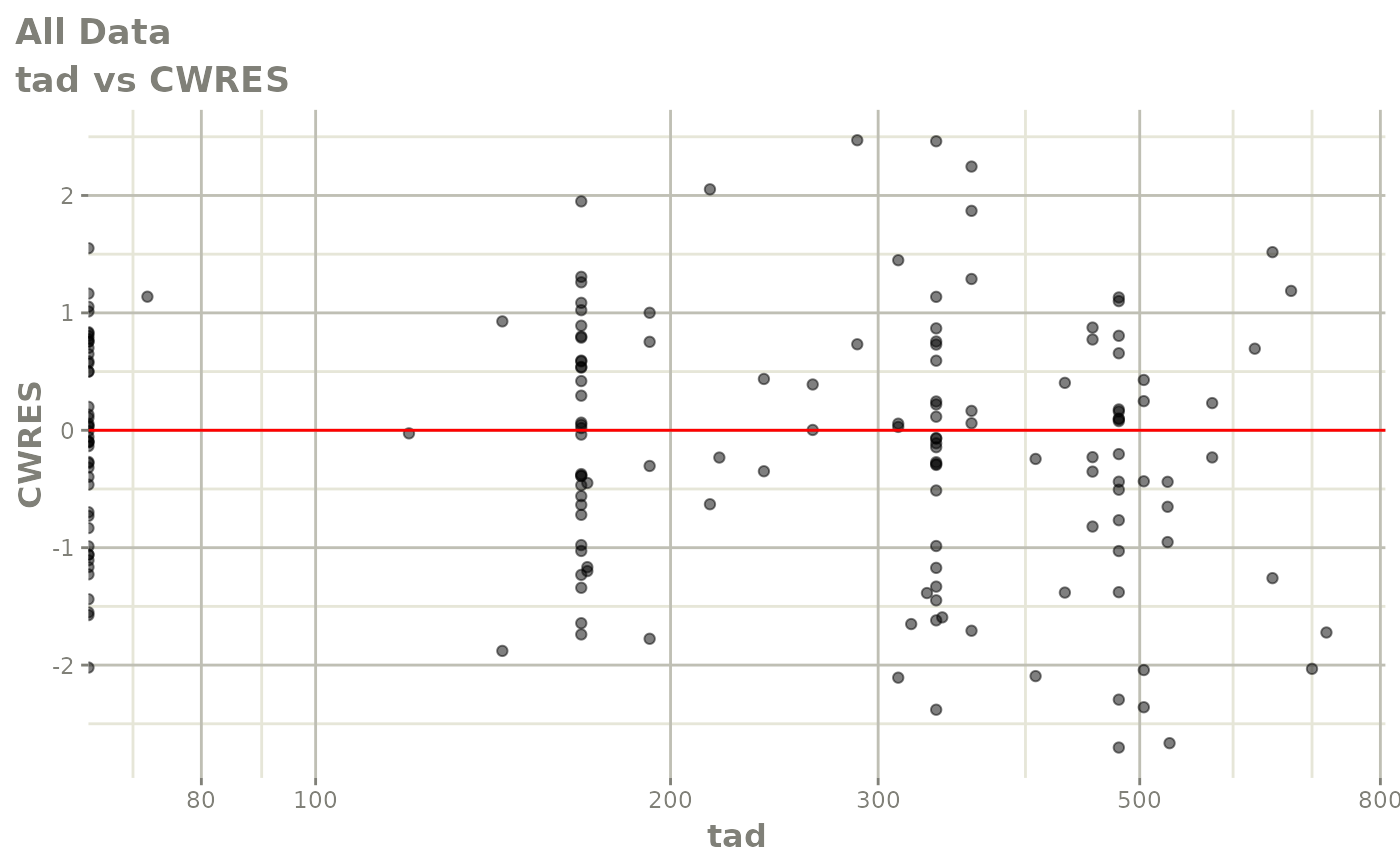
print(dv_vs_pred(xpdb) +
ylab("Observed Neutrophil Count (10^9/L)") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))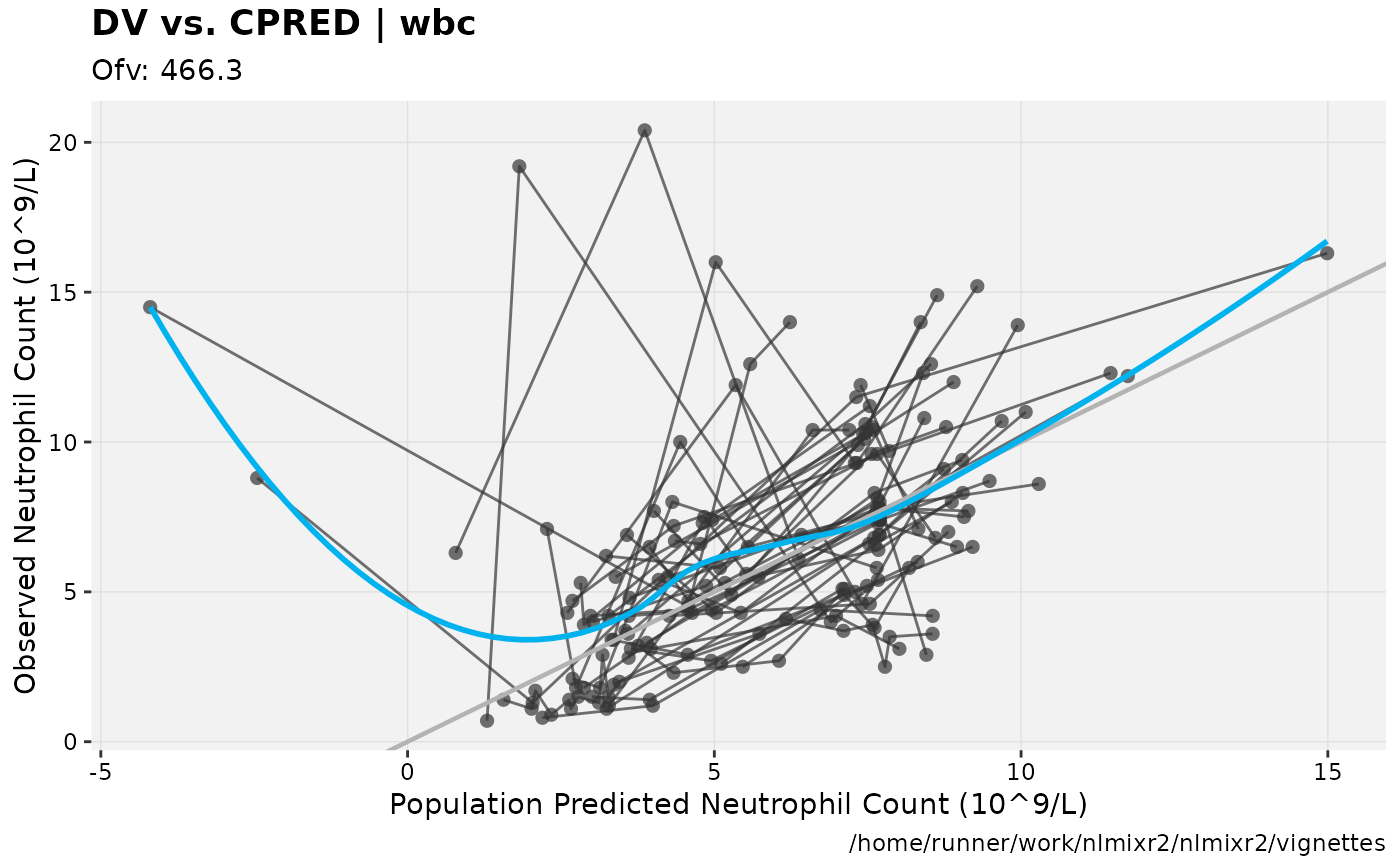
print(dv_vs_ipred(xpdb) +
ylab("Observed Neutrophil Count (10^9/L)") +
xlab("Individual Predicted Neutrophil Count (10^9/L)"))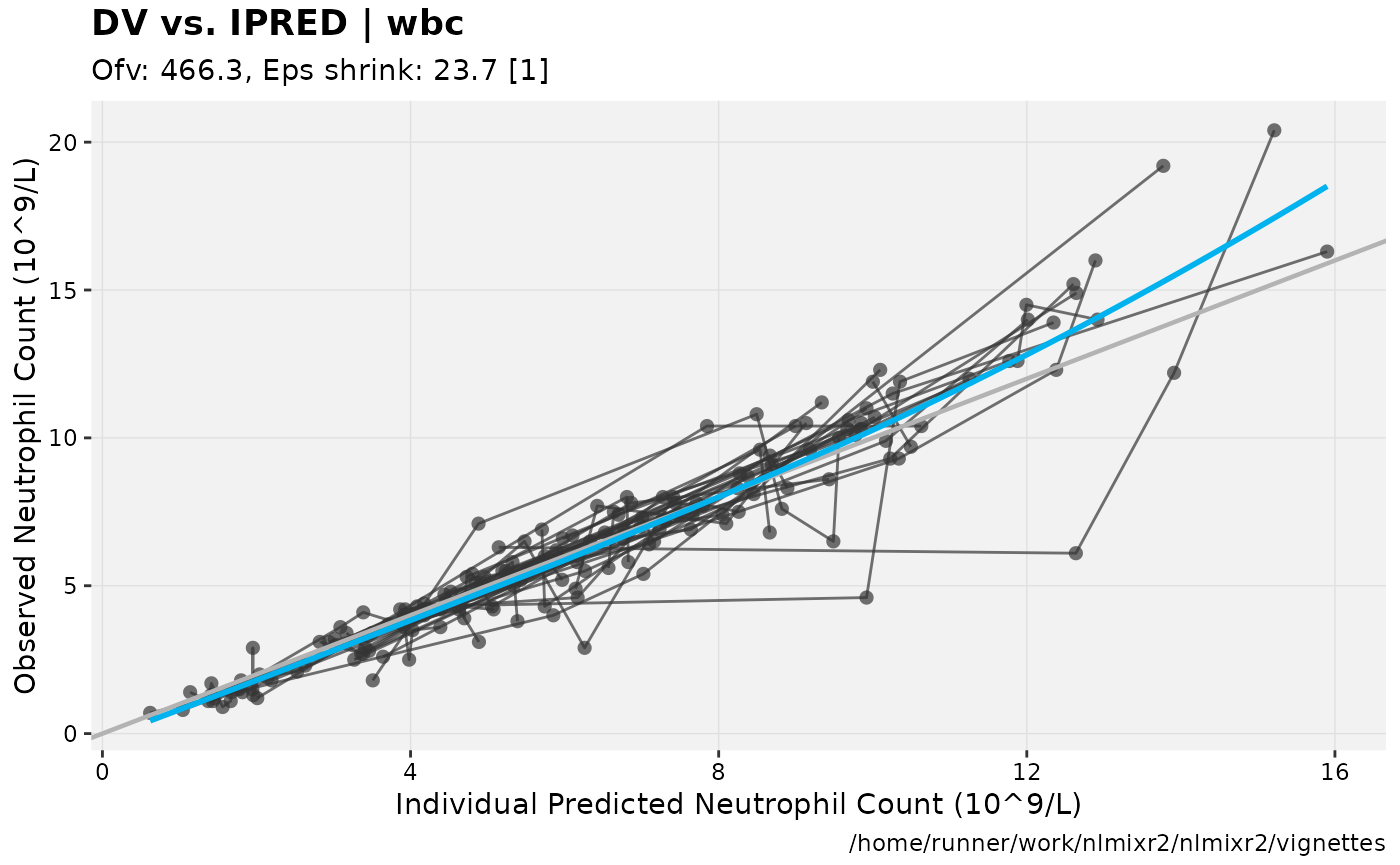
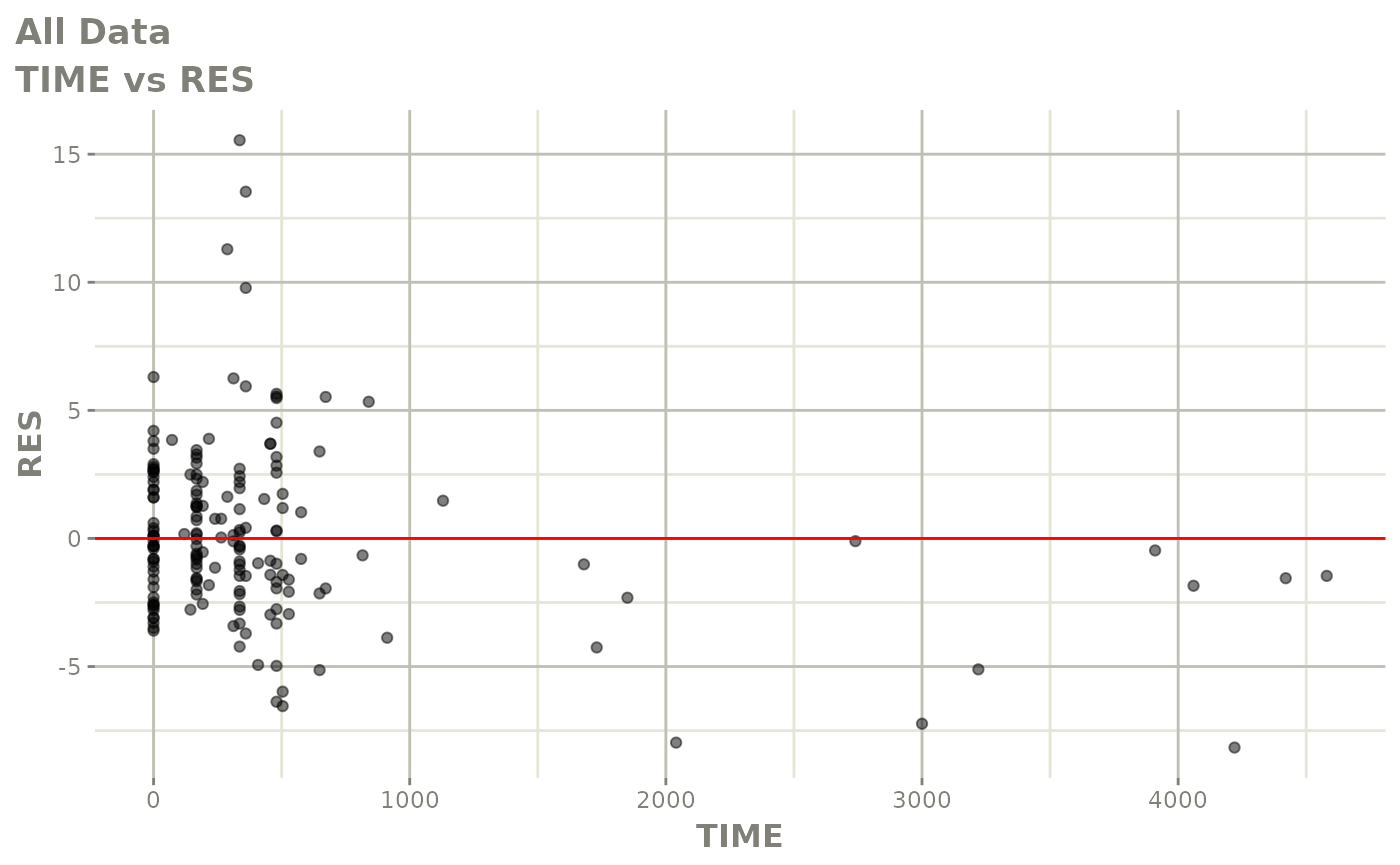
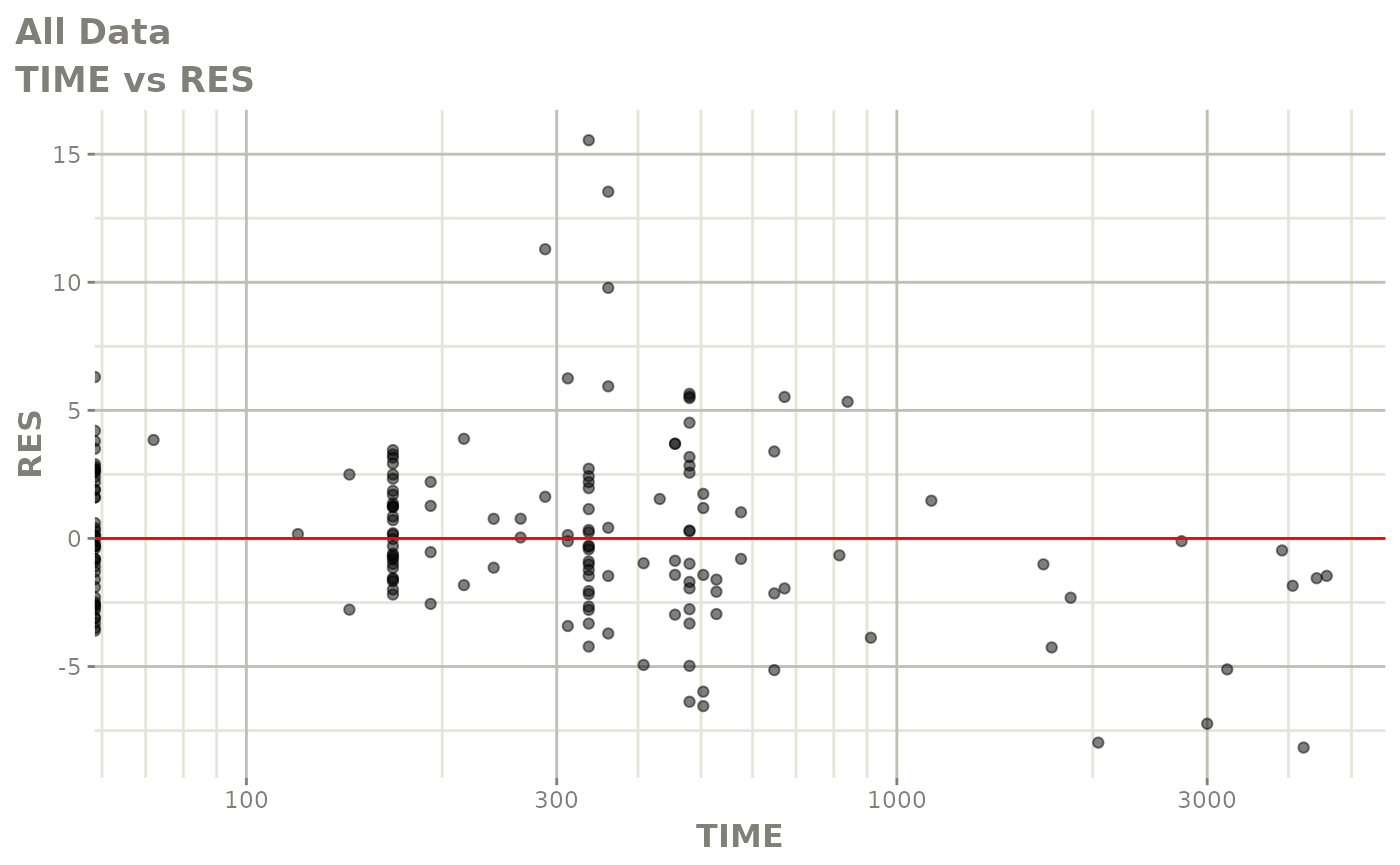
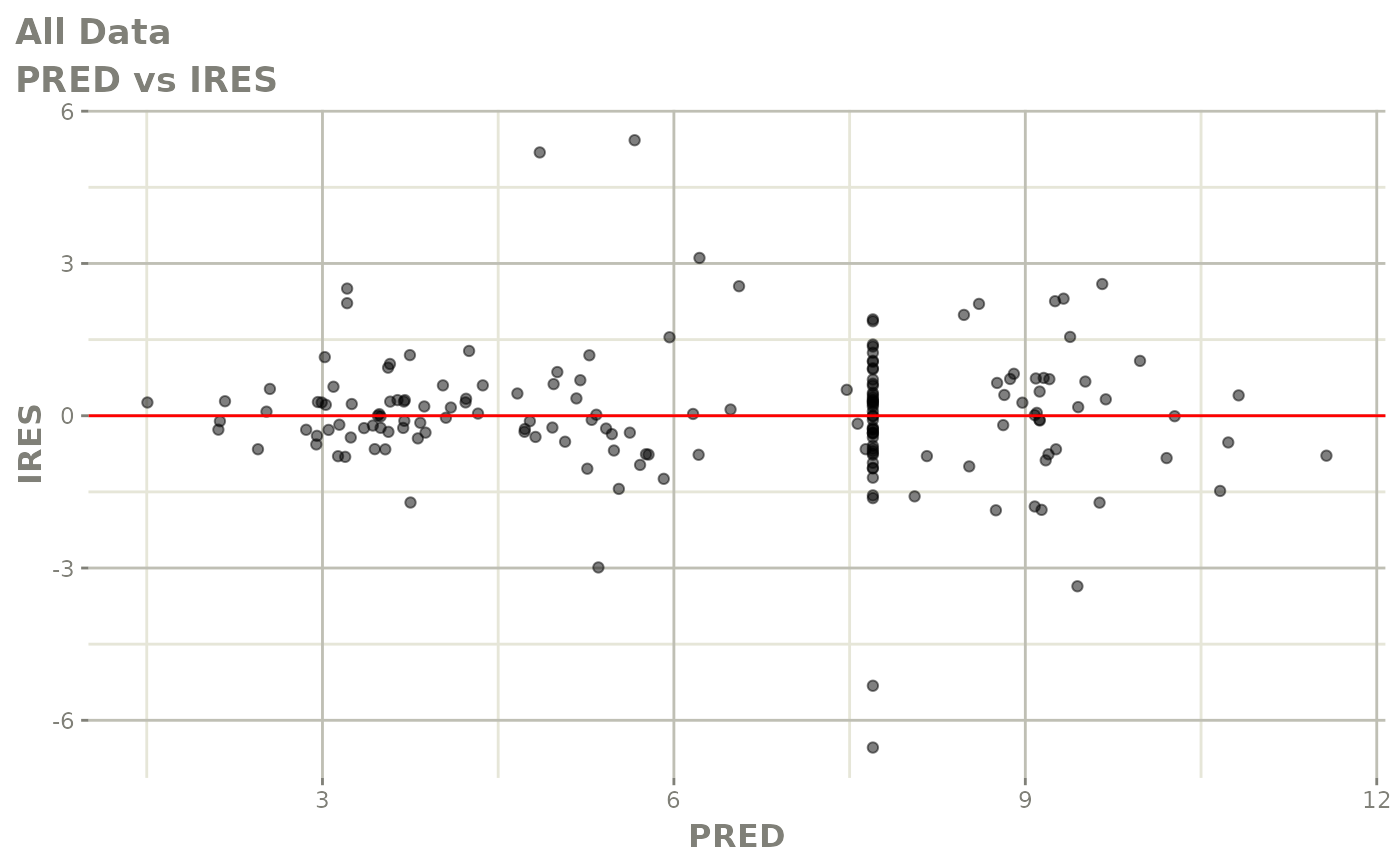
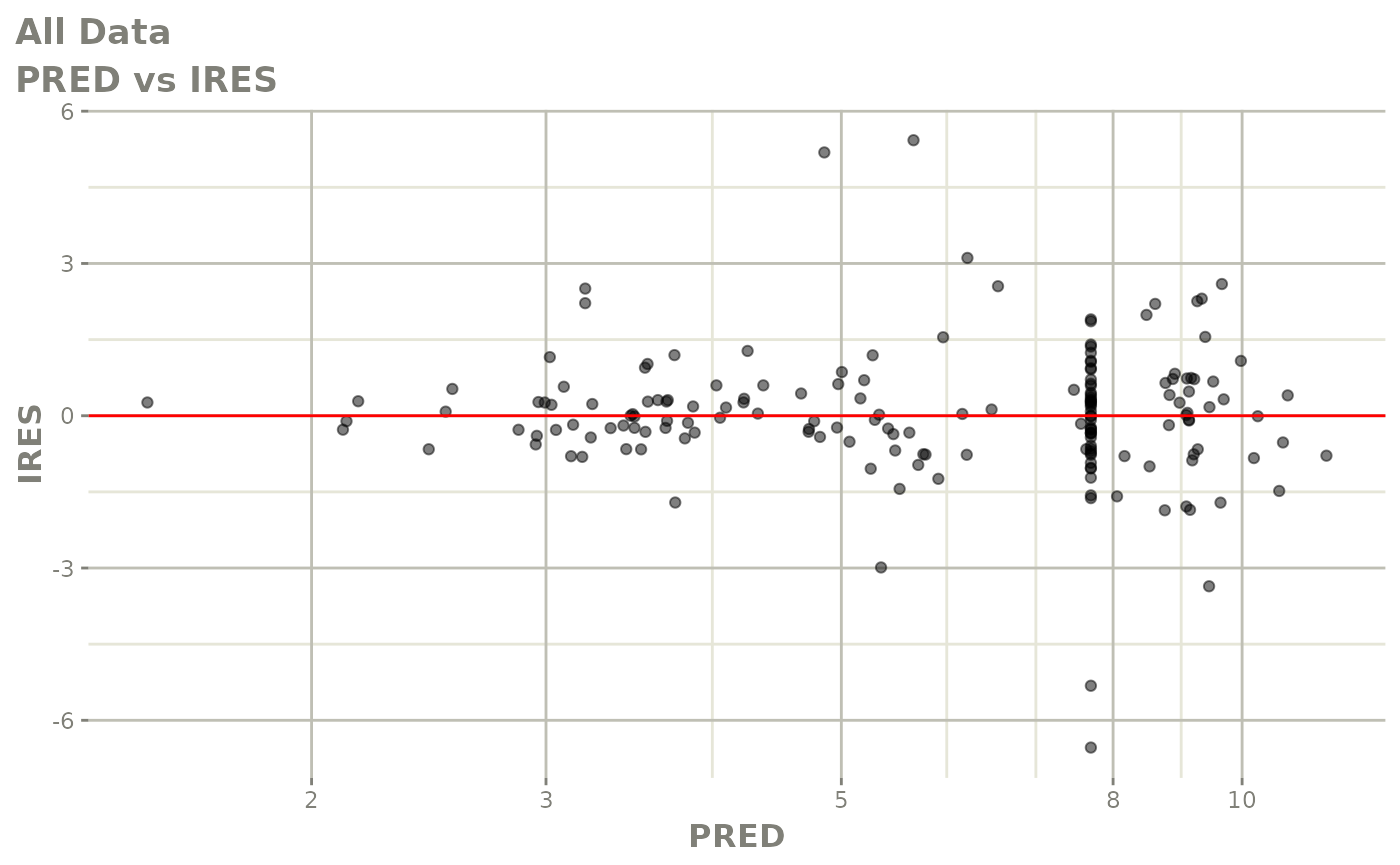
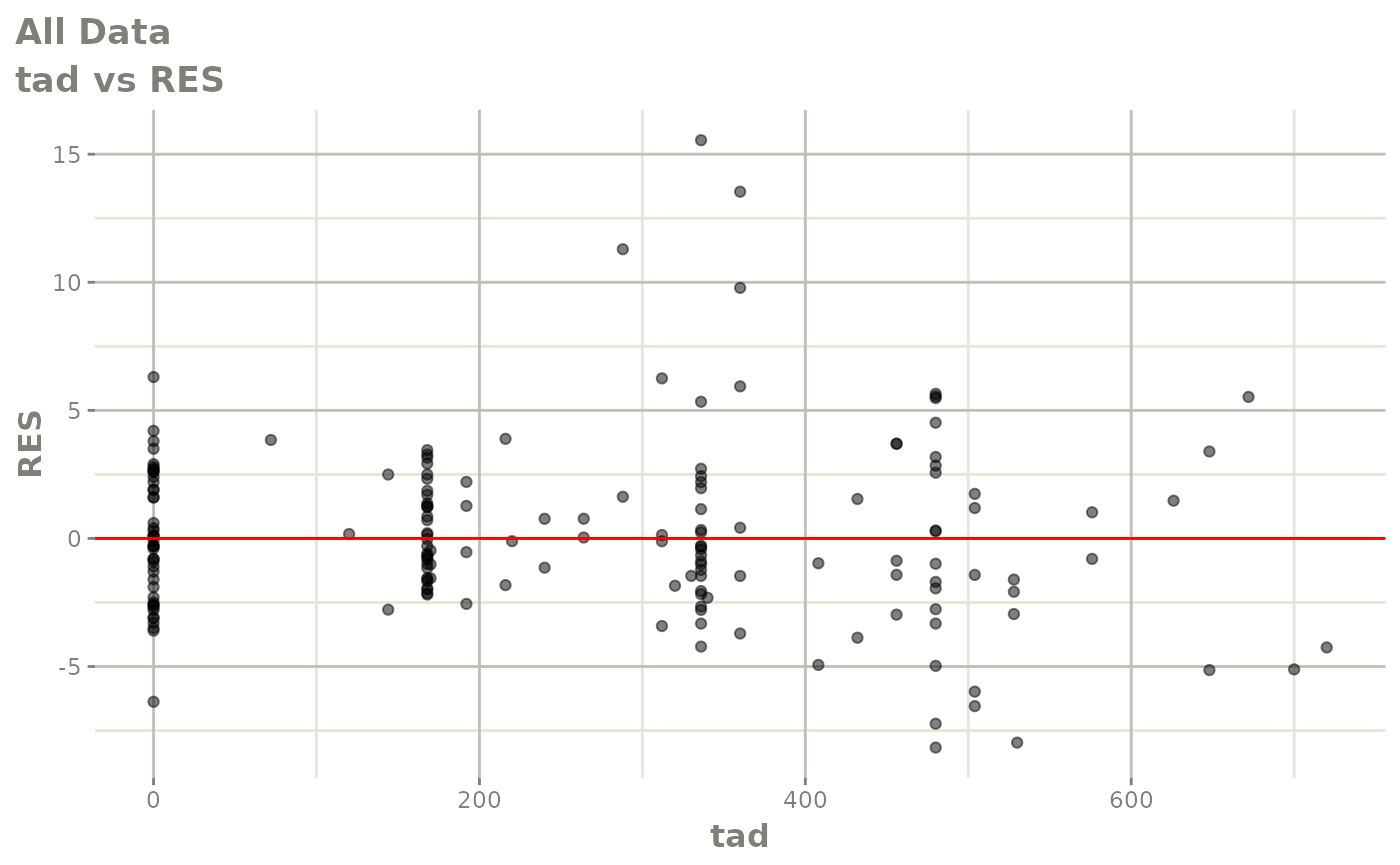
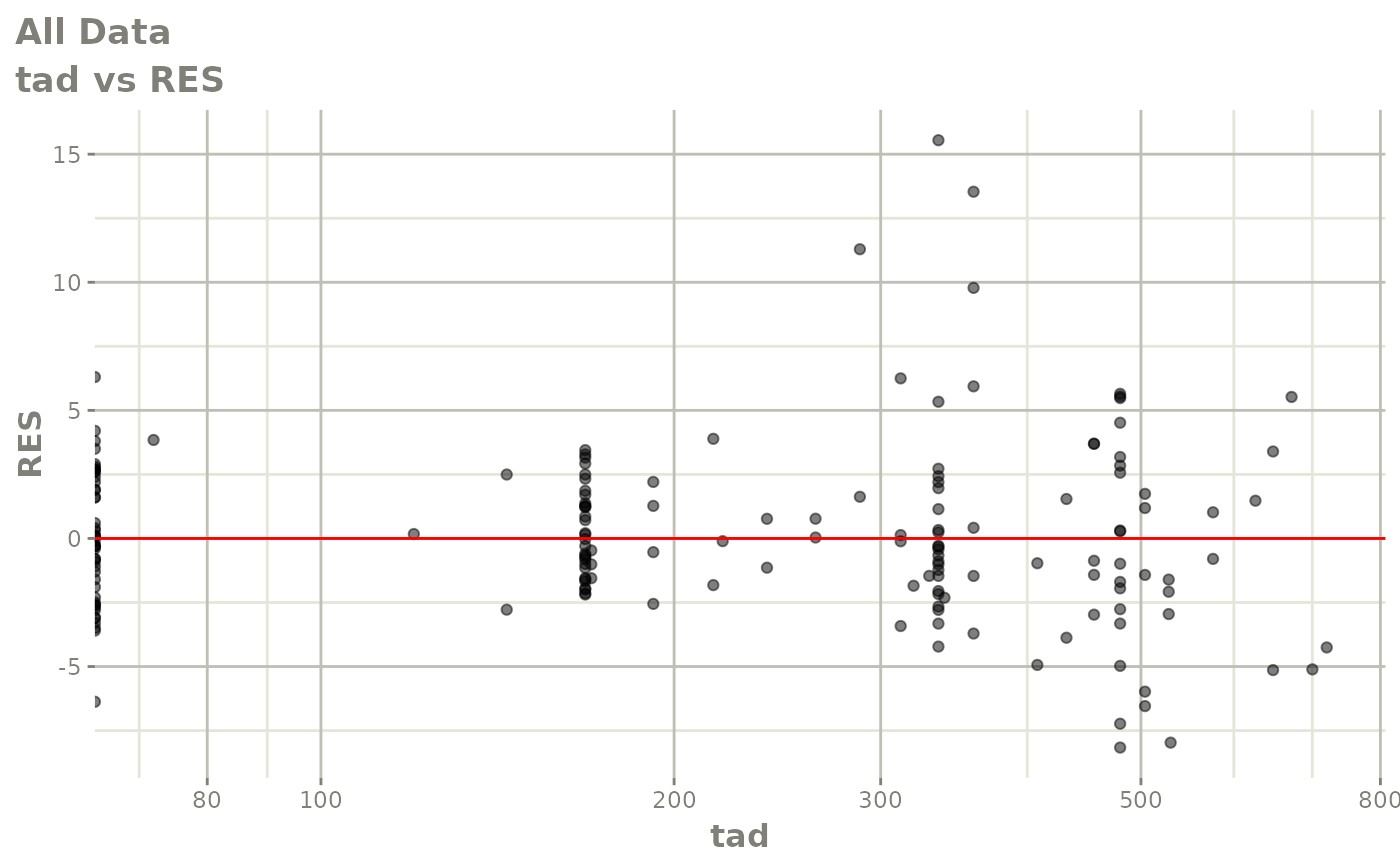
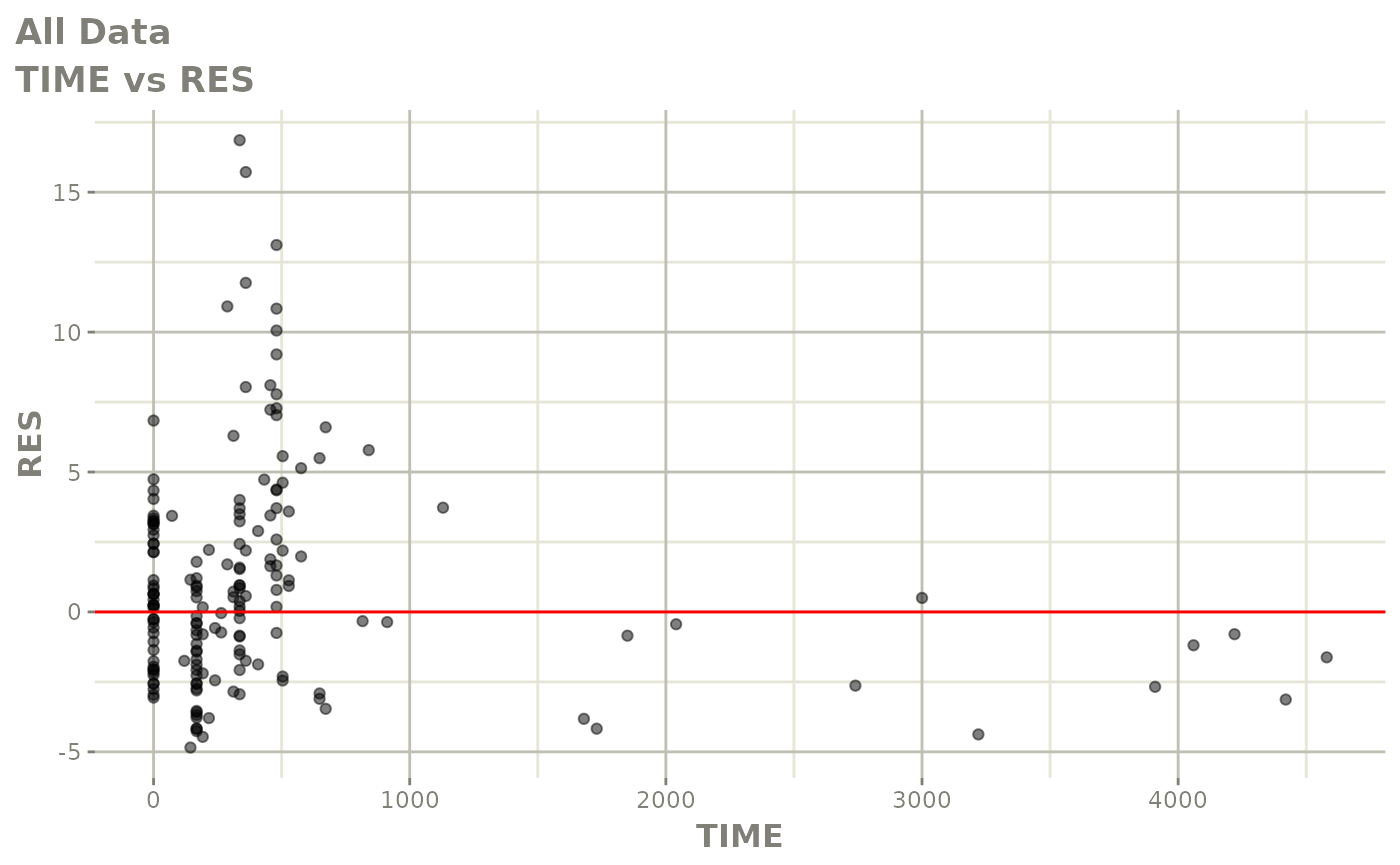
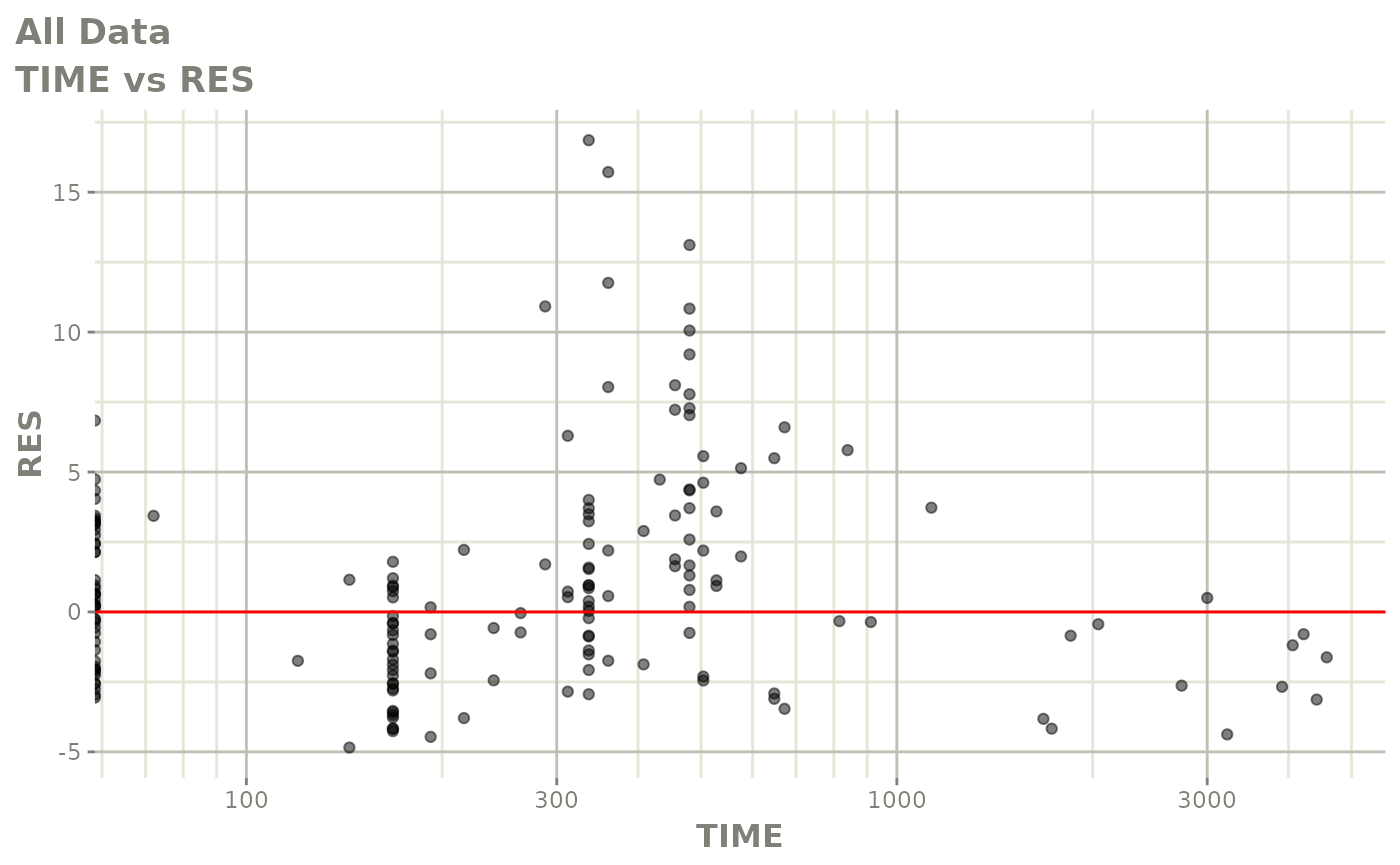
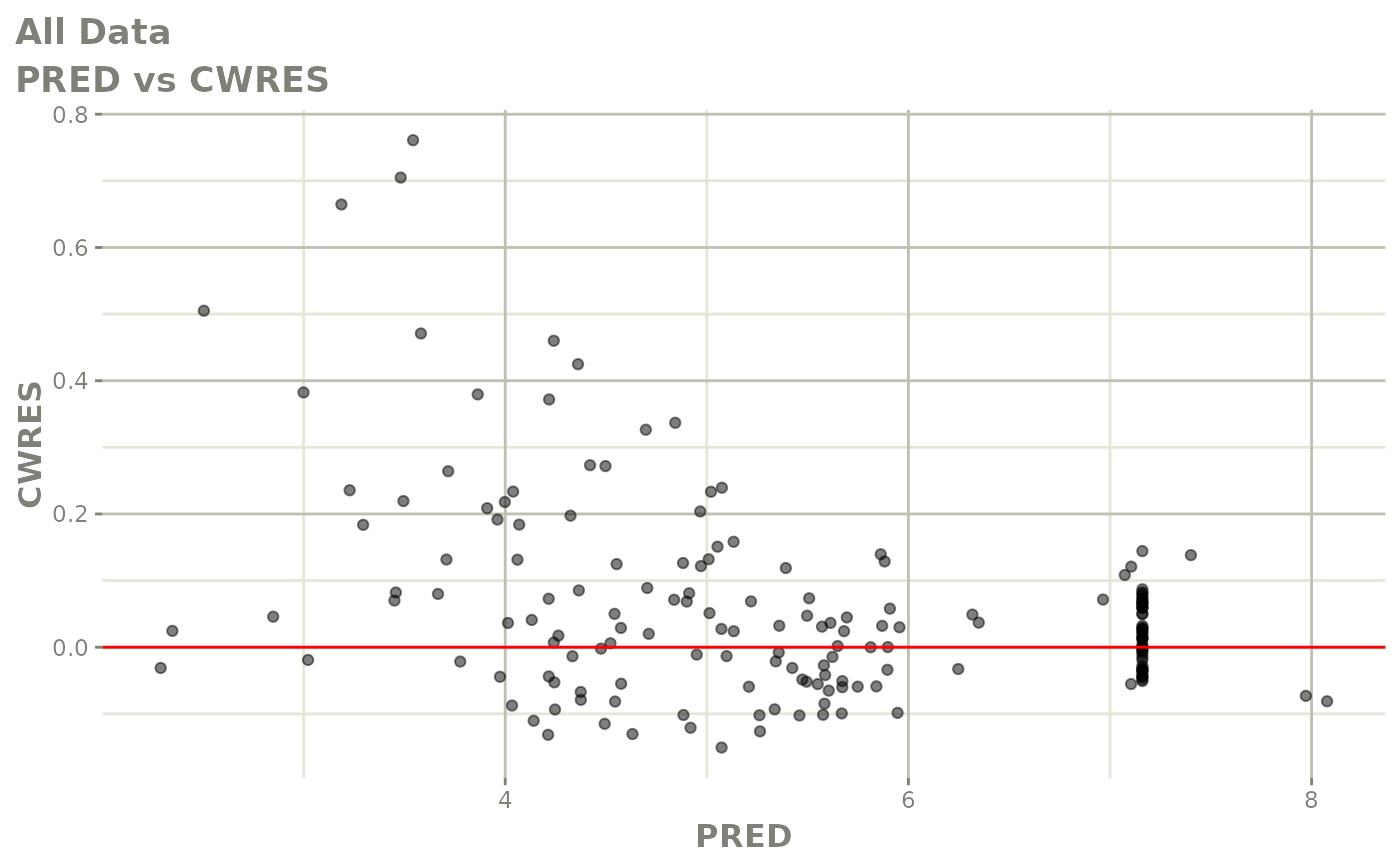
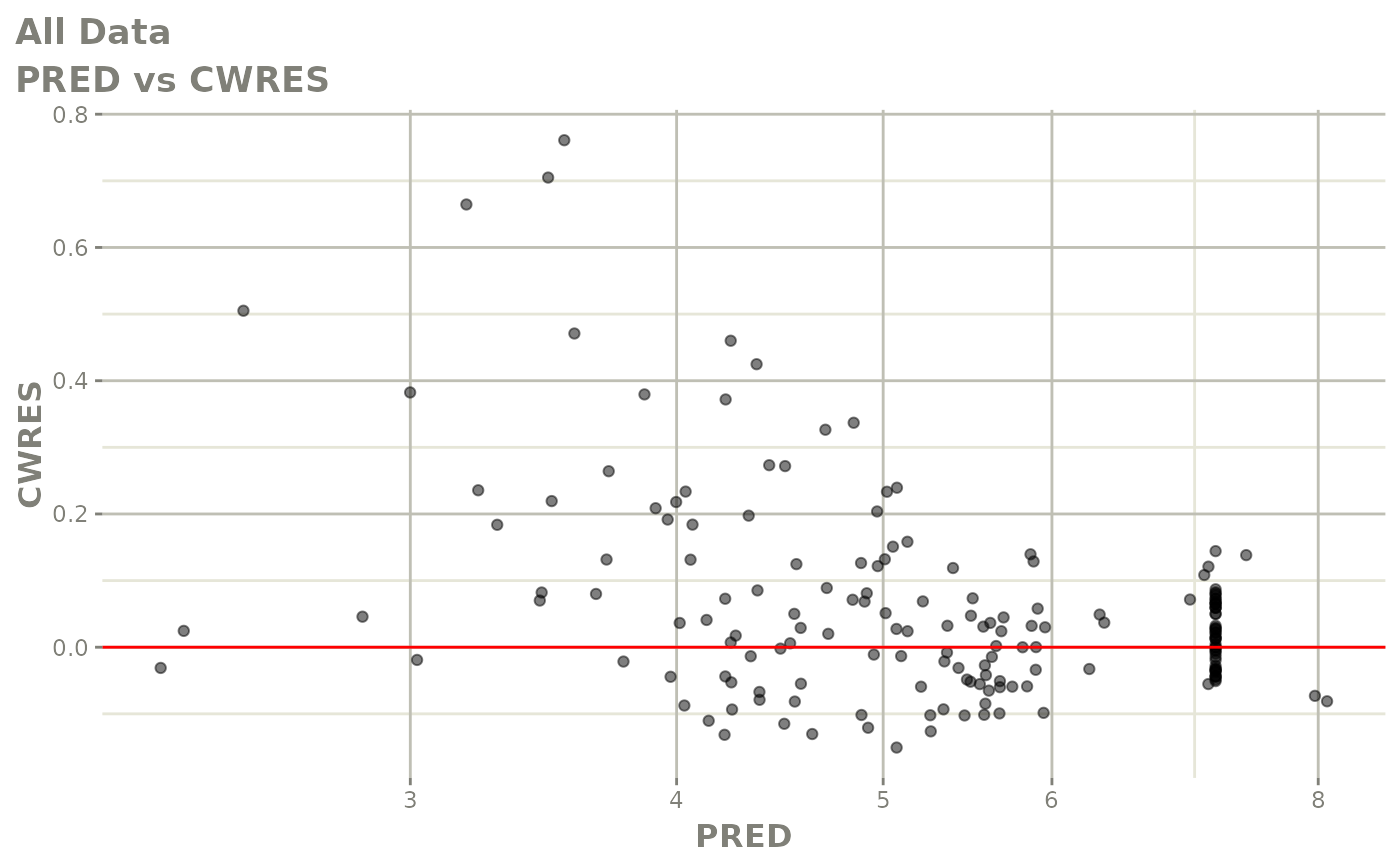
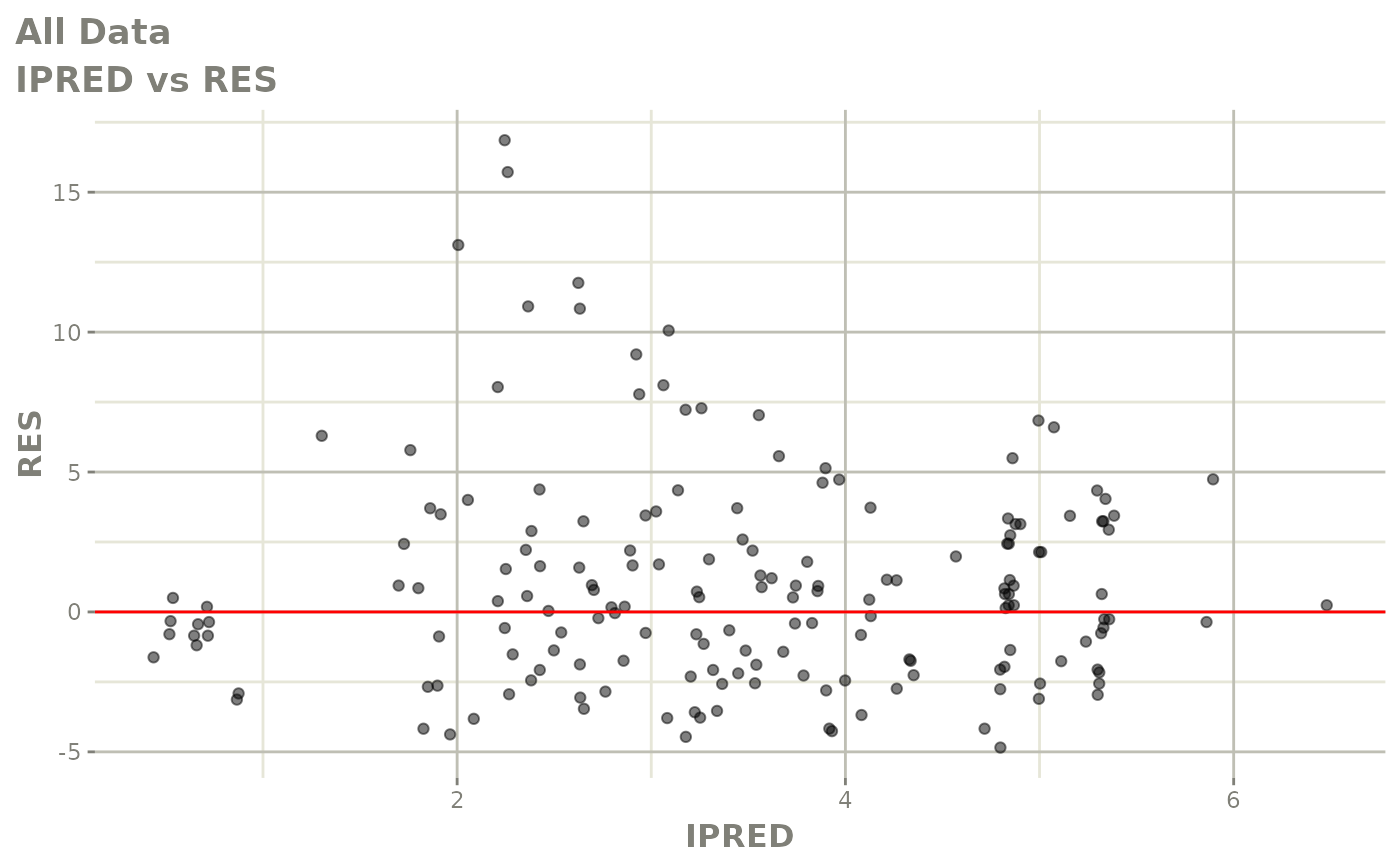
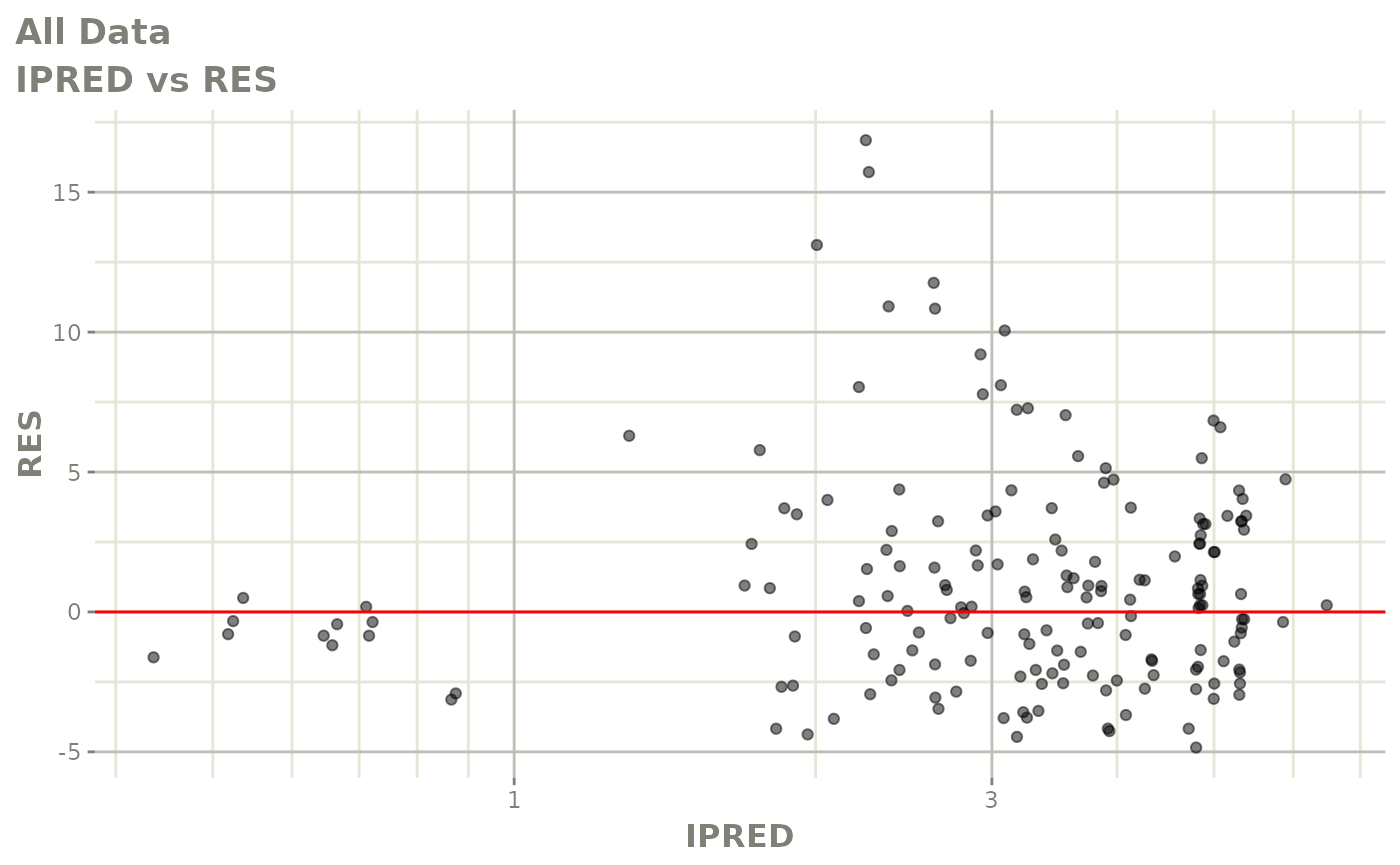
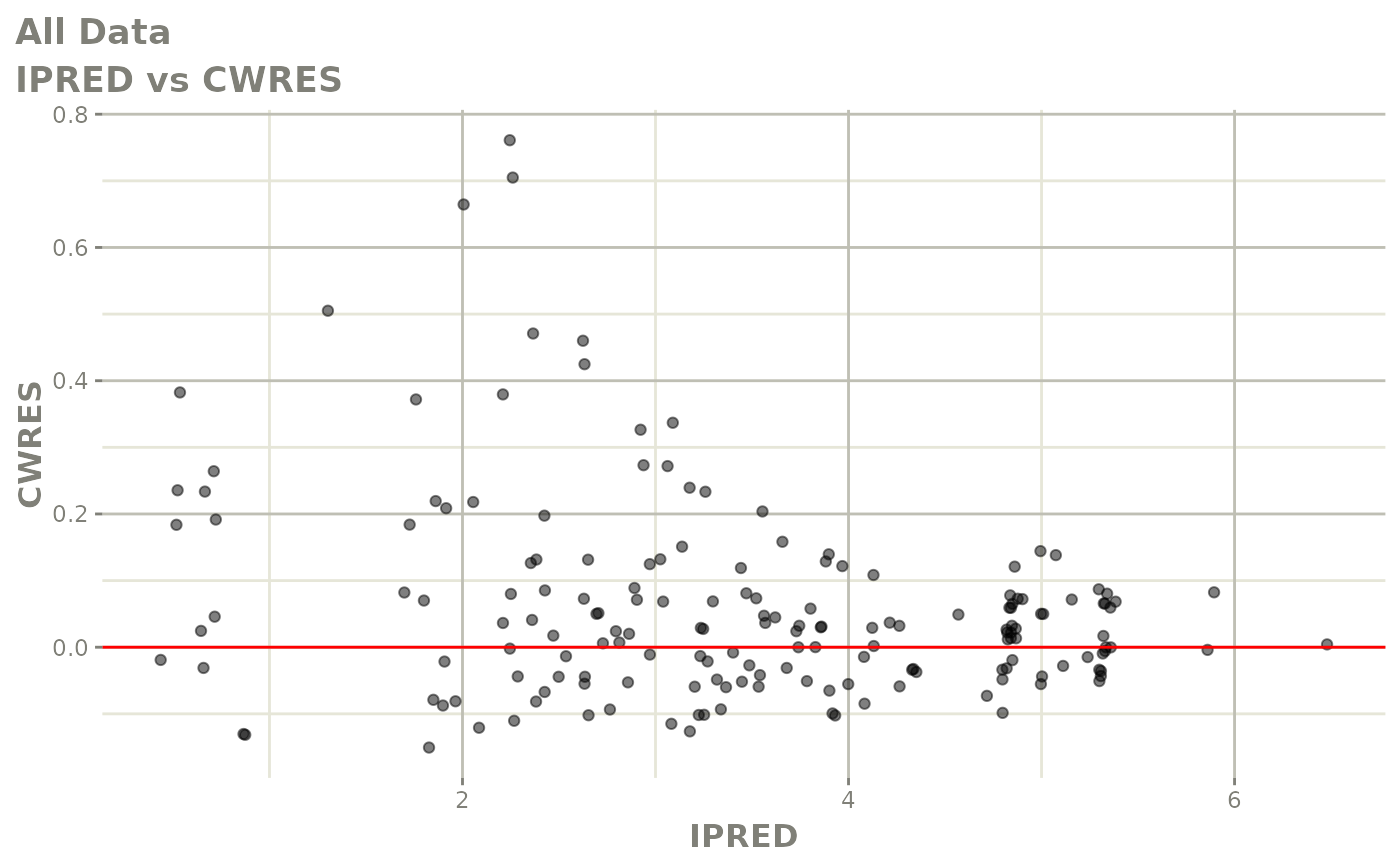
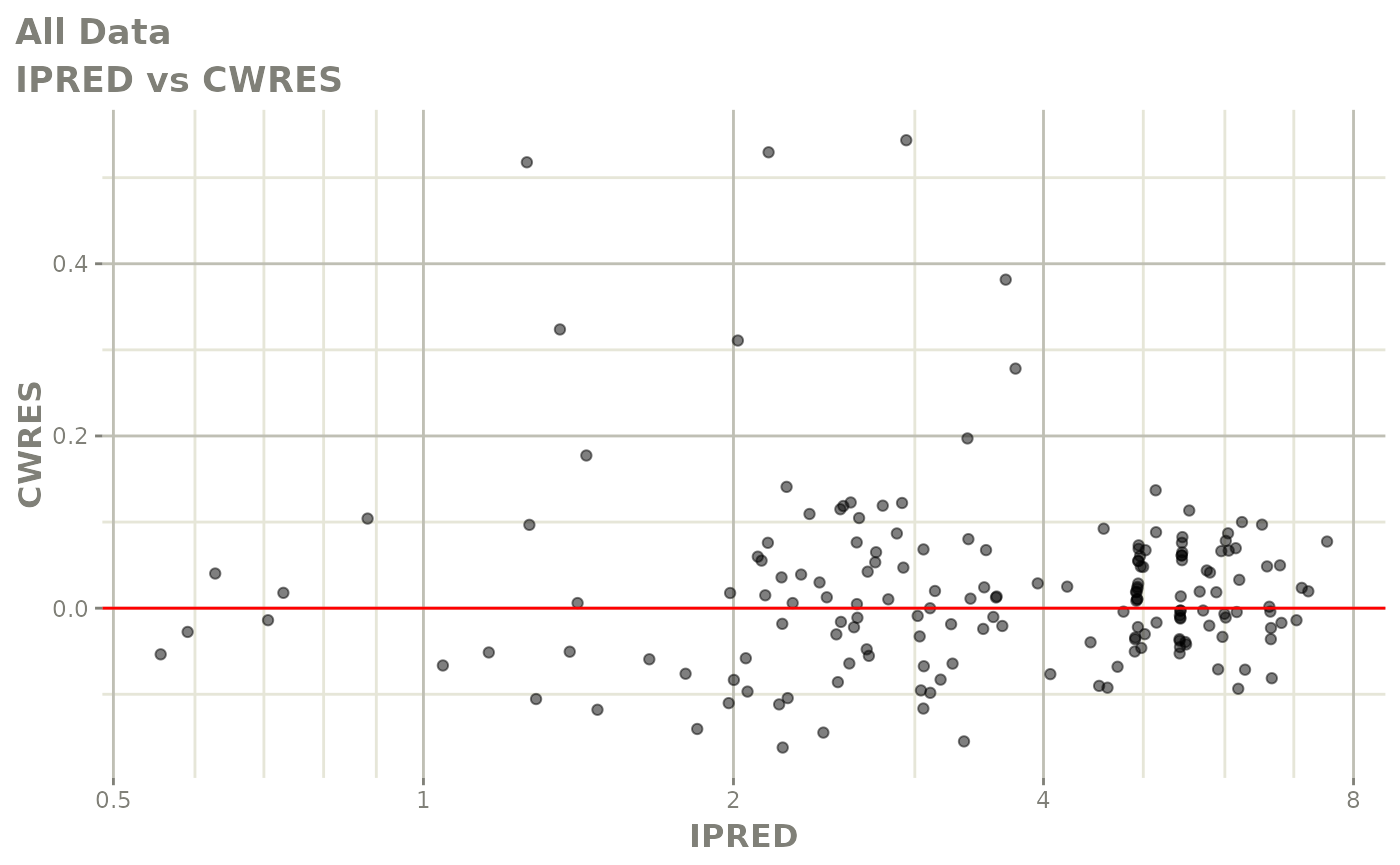
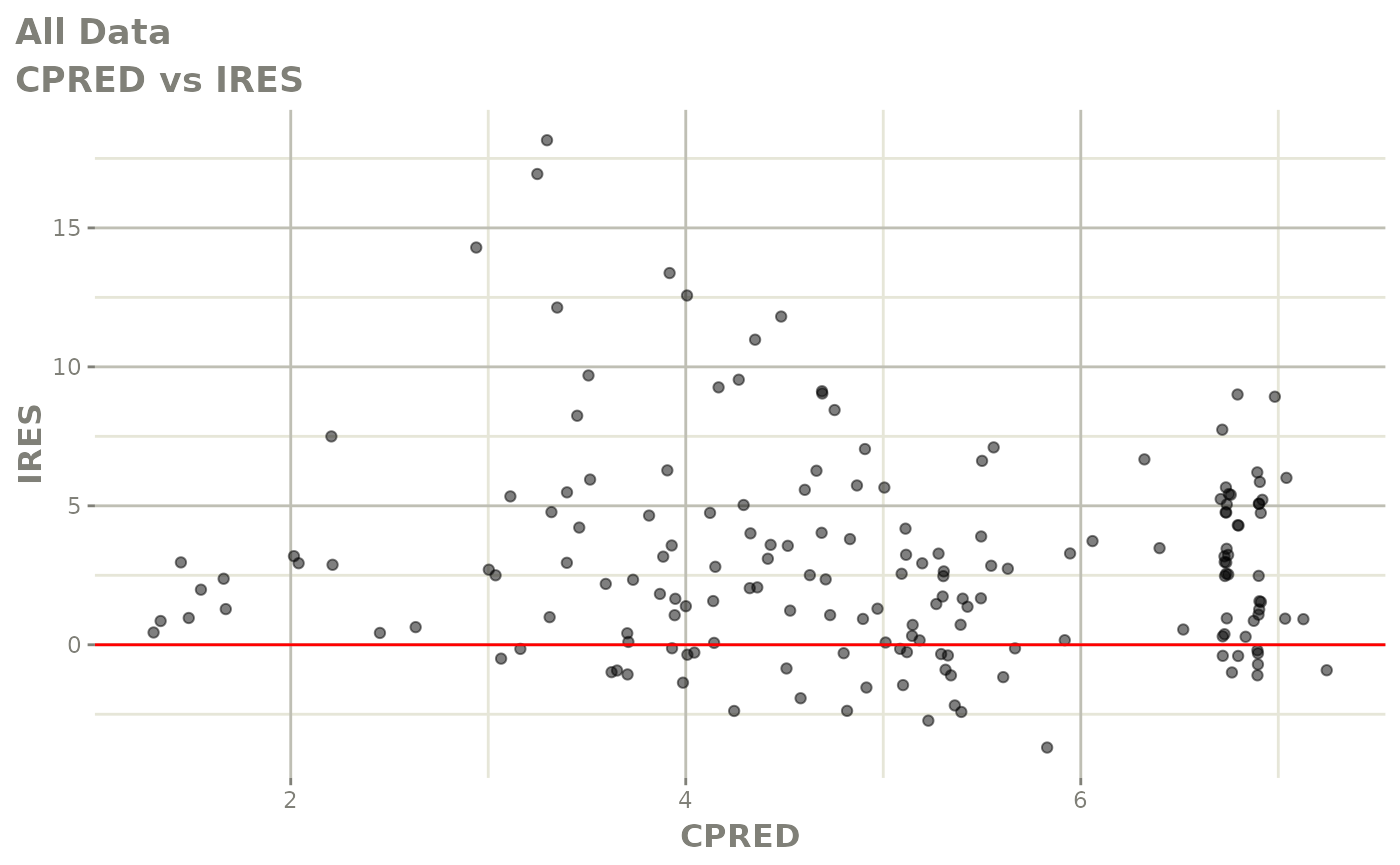
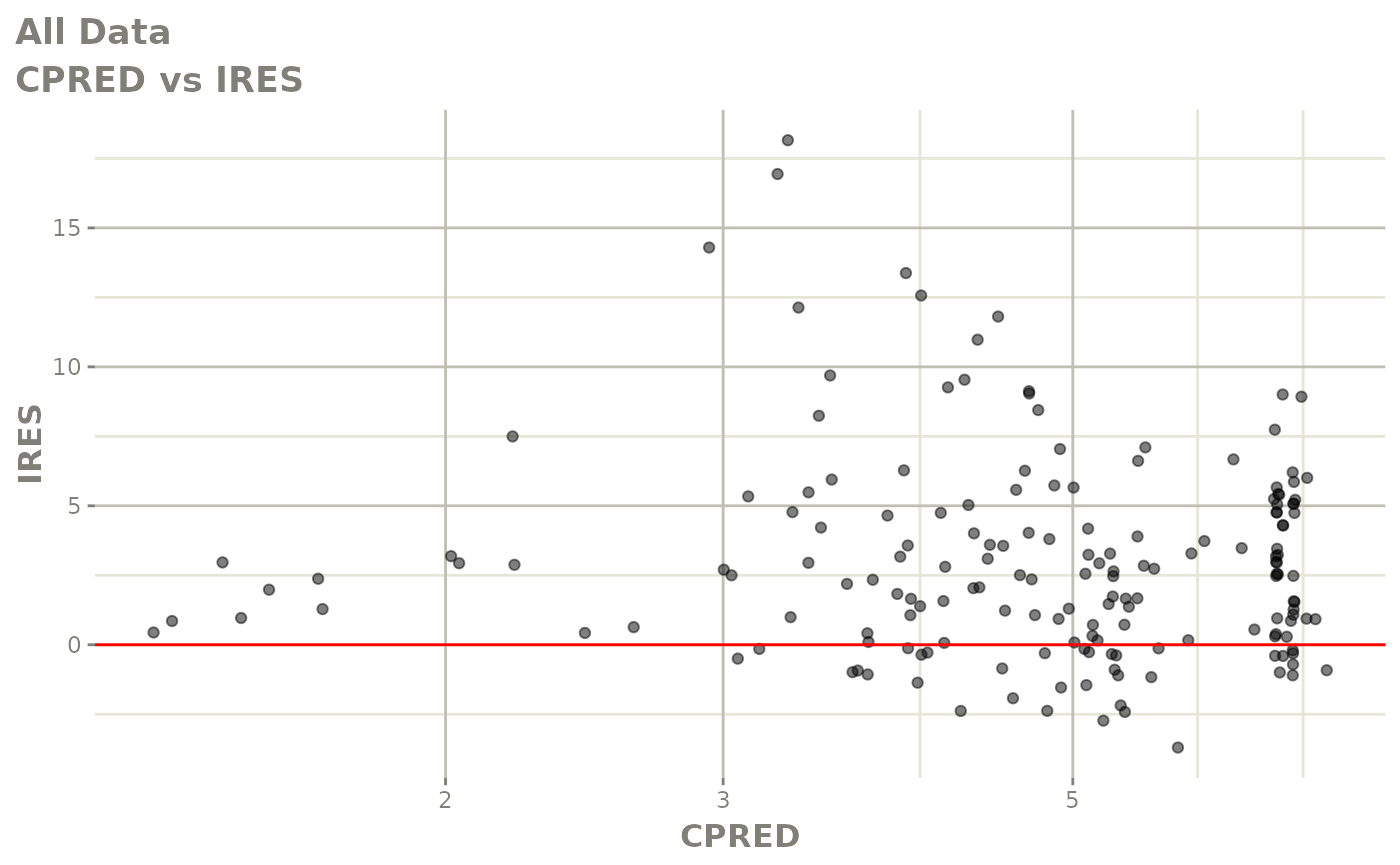
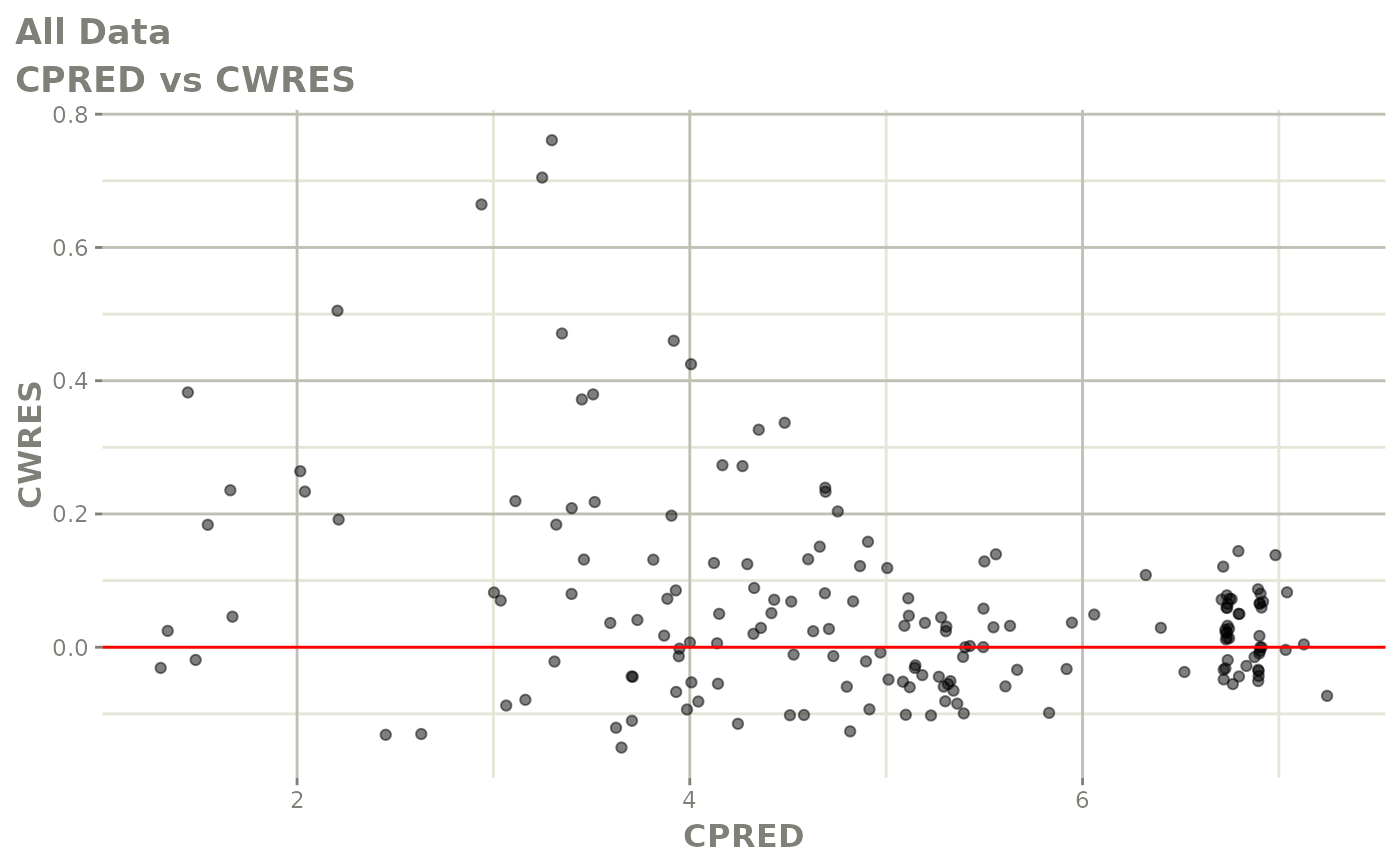
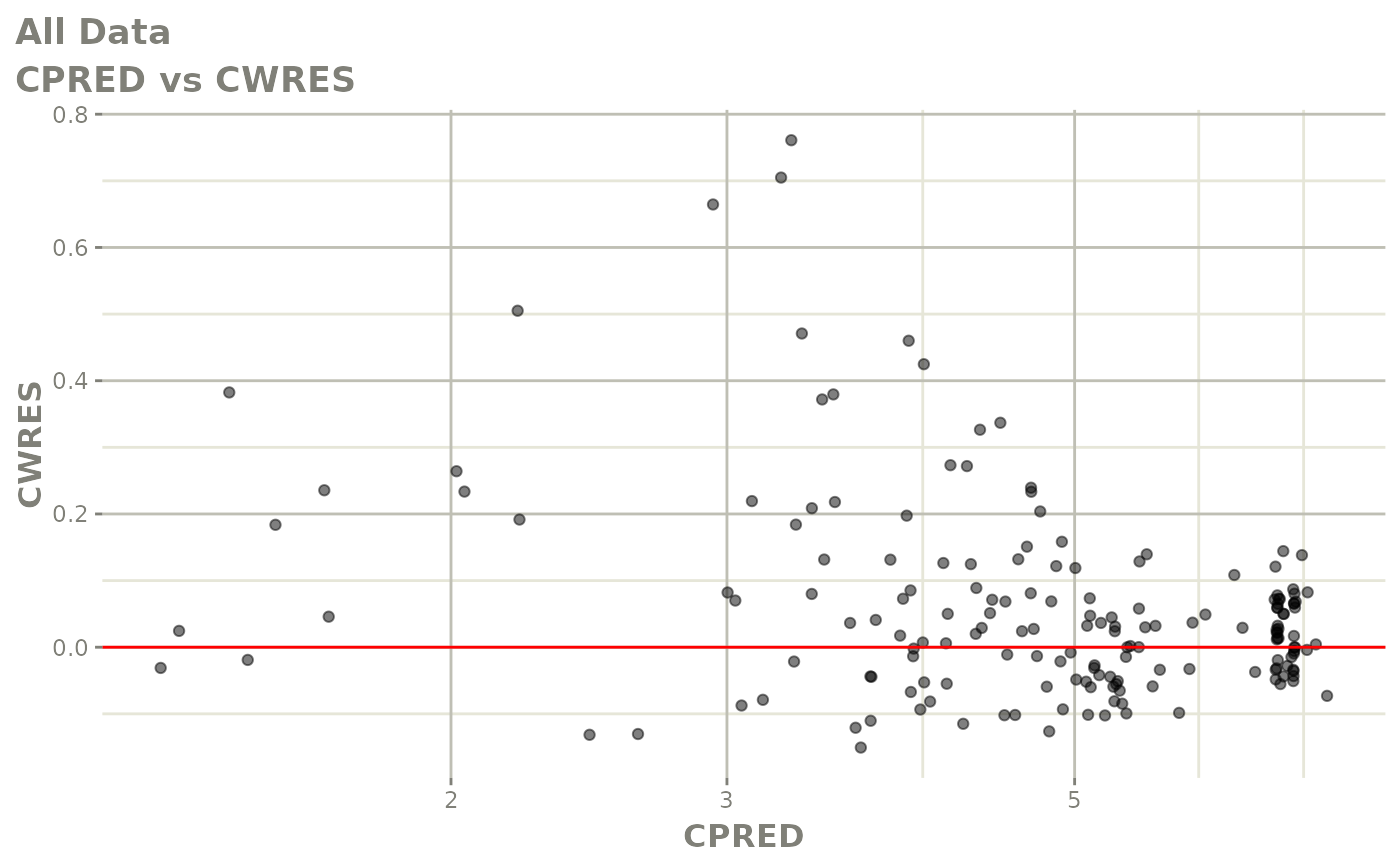
print(res_vs_pred(xpdb) +
ylab("Conditional Weighted Residuals") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))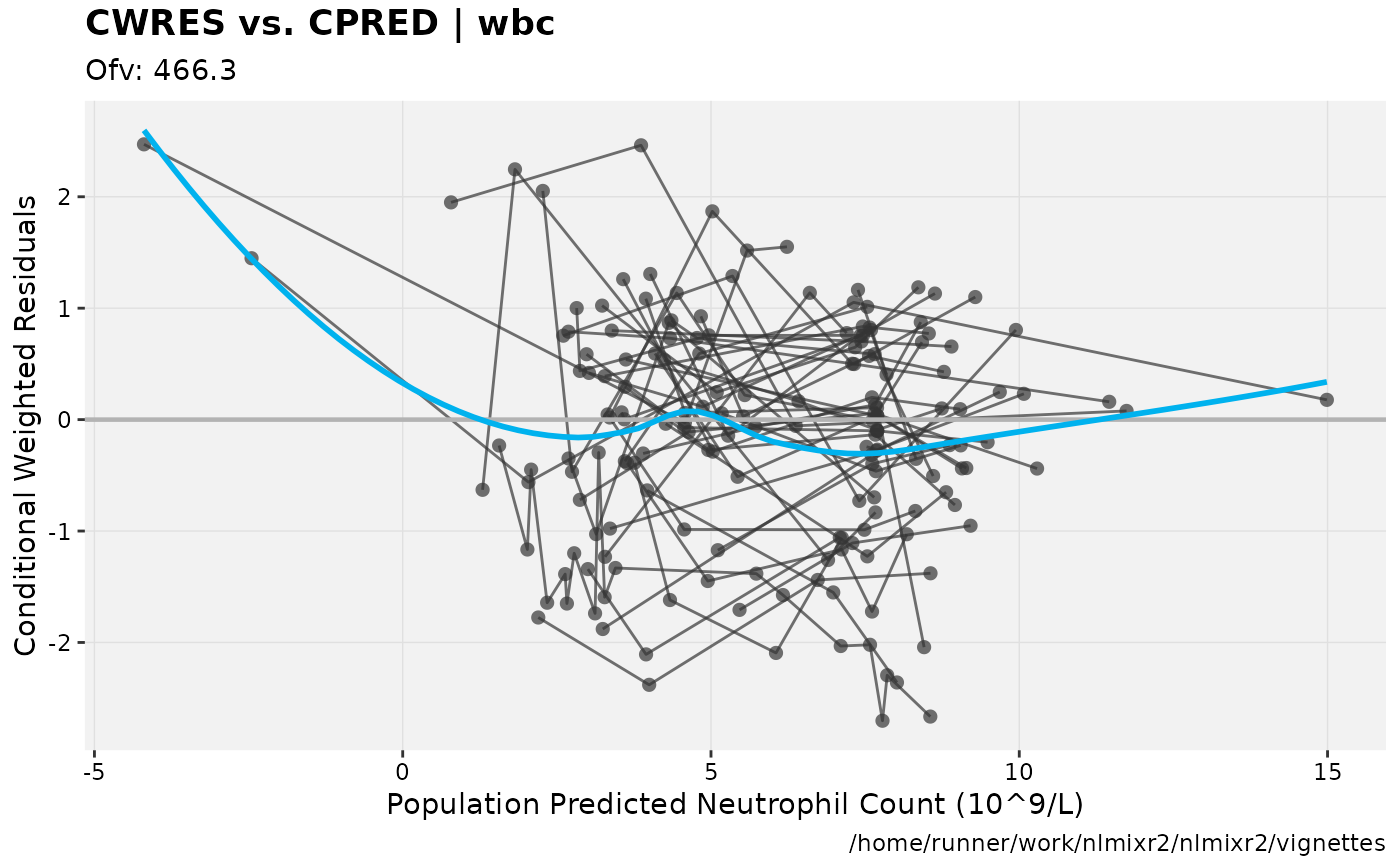
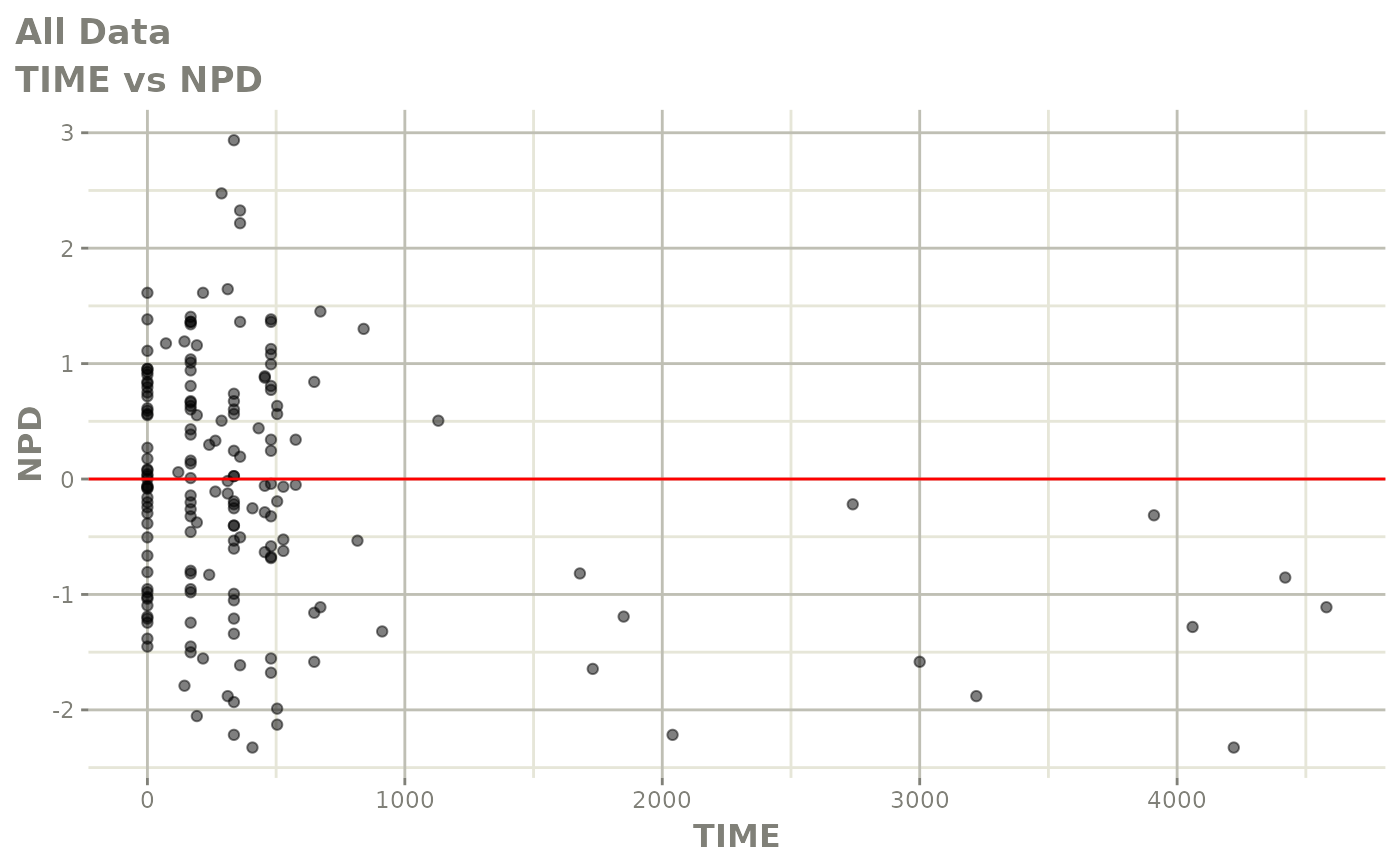
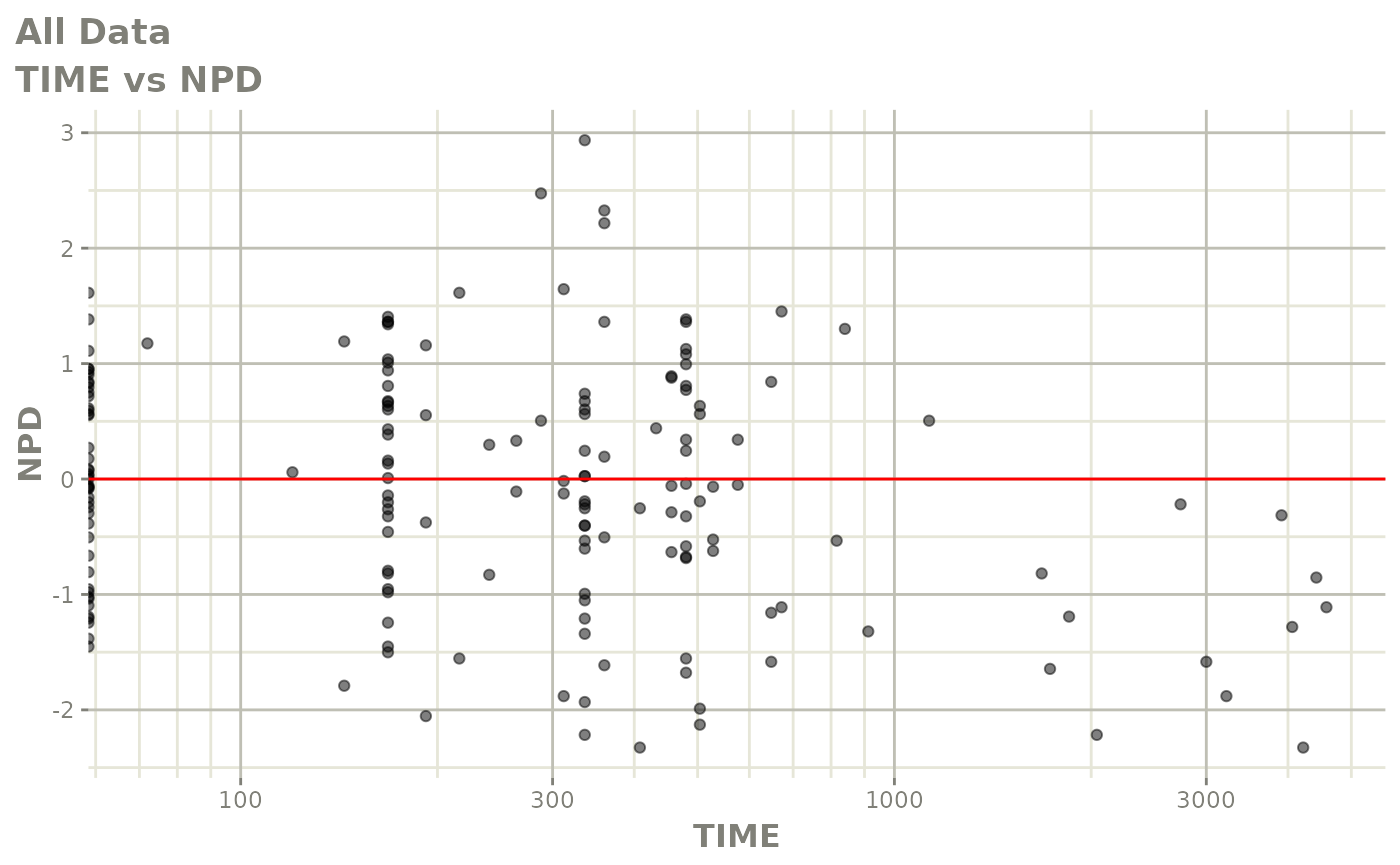
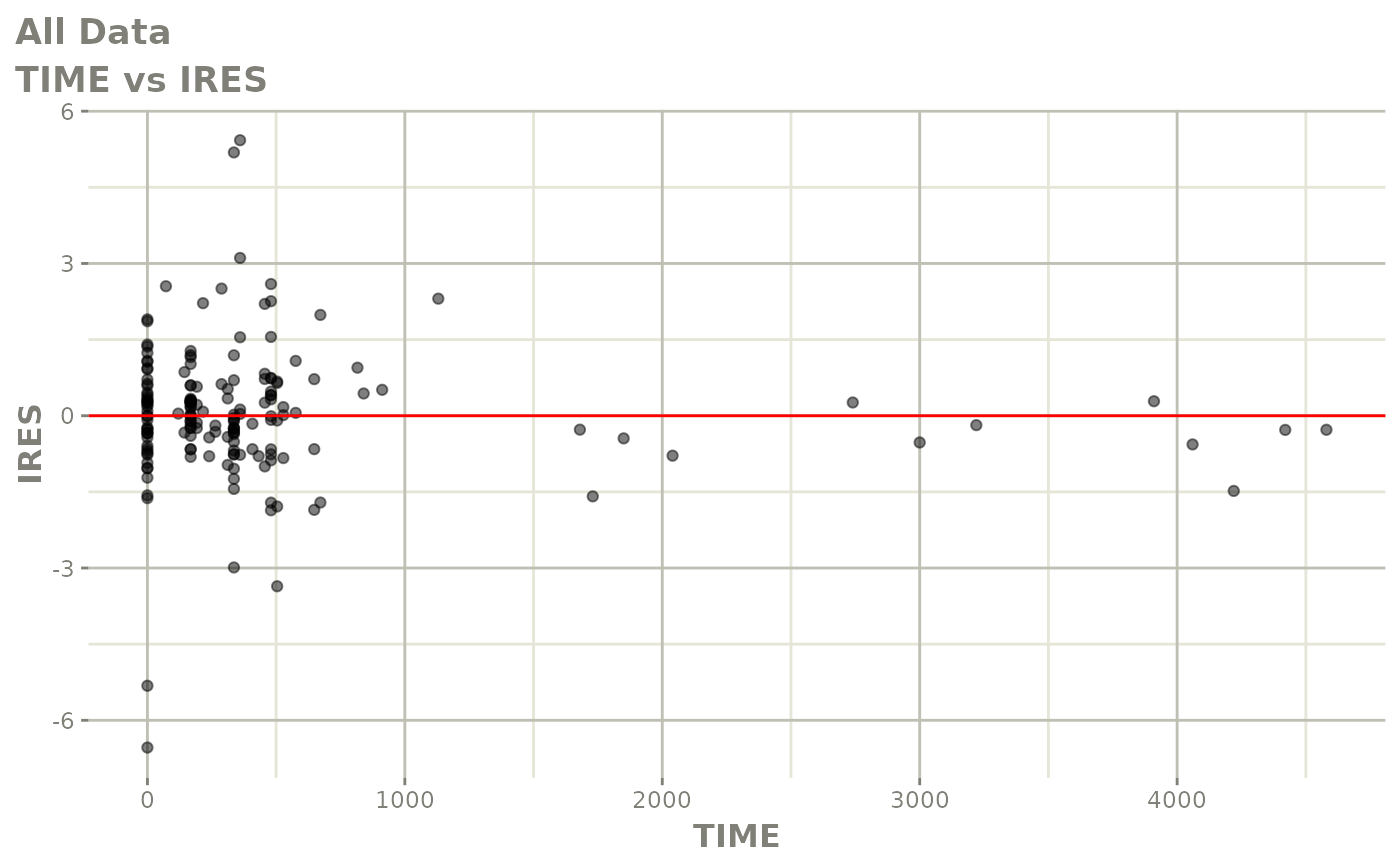
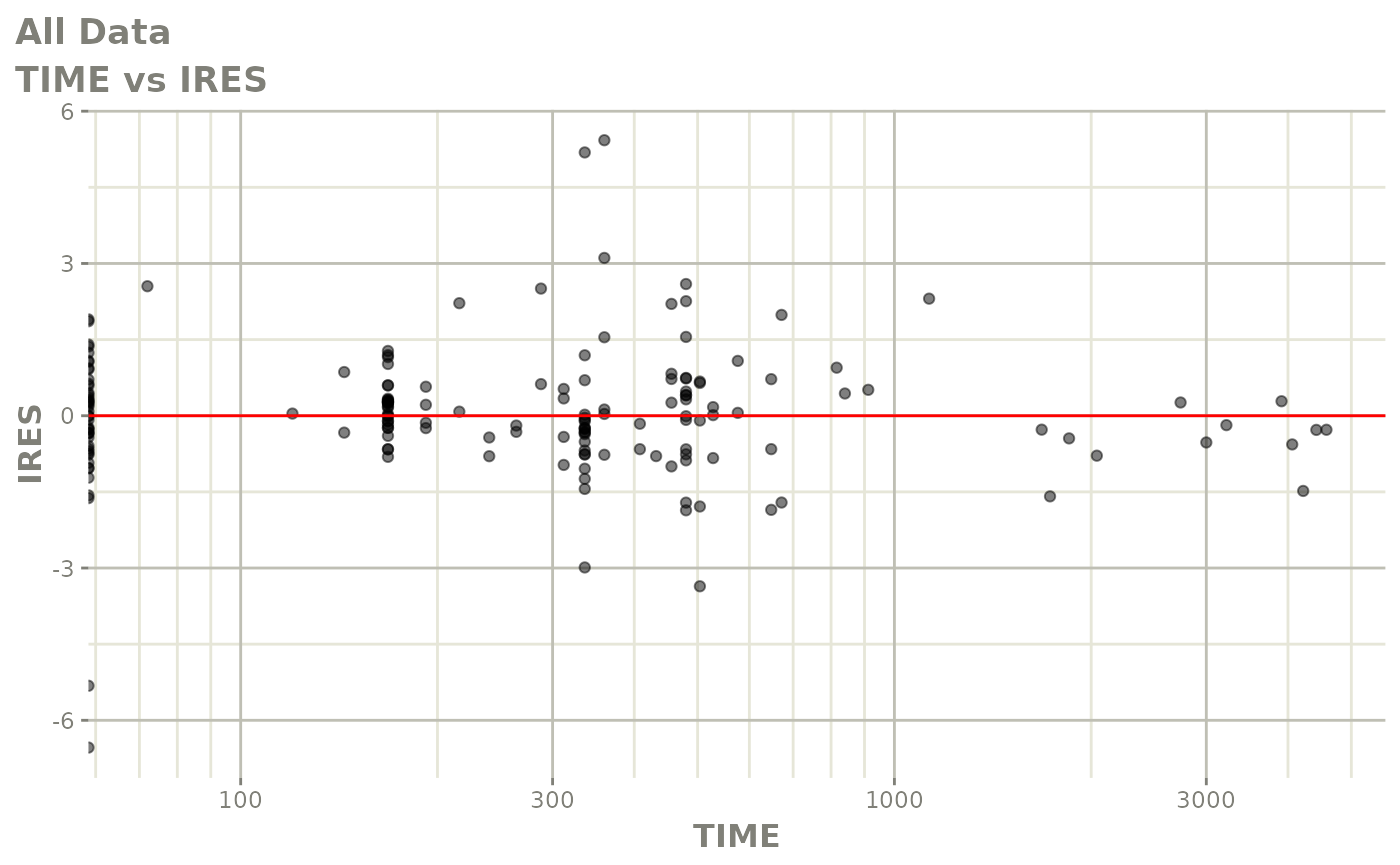
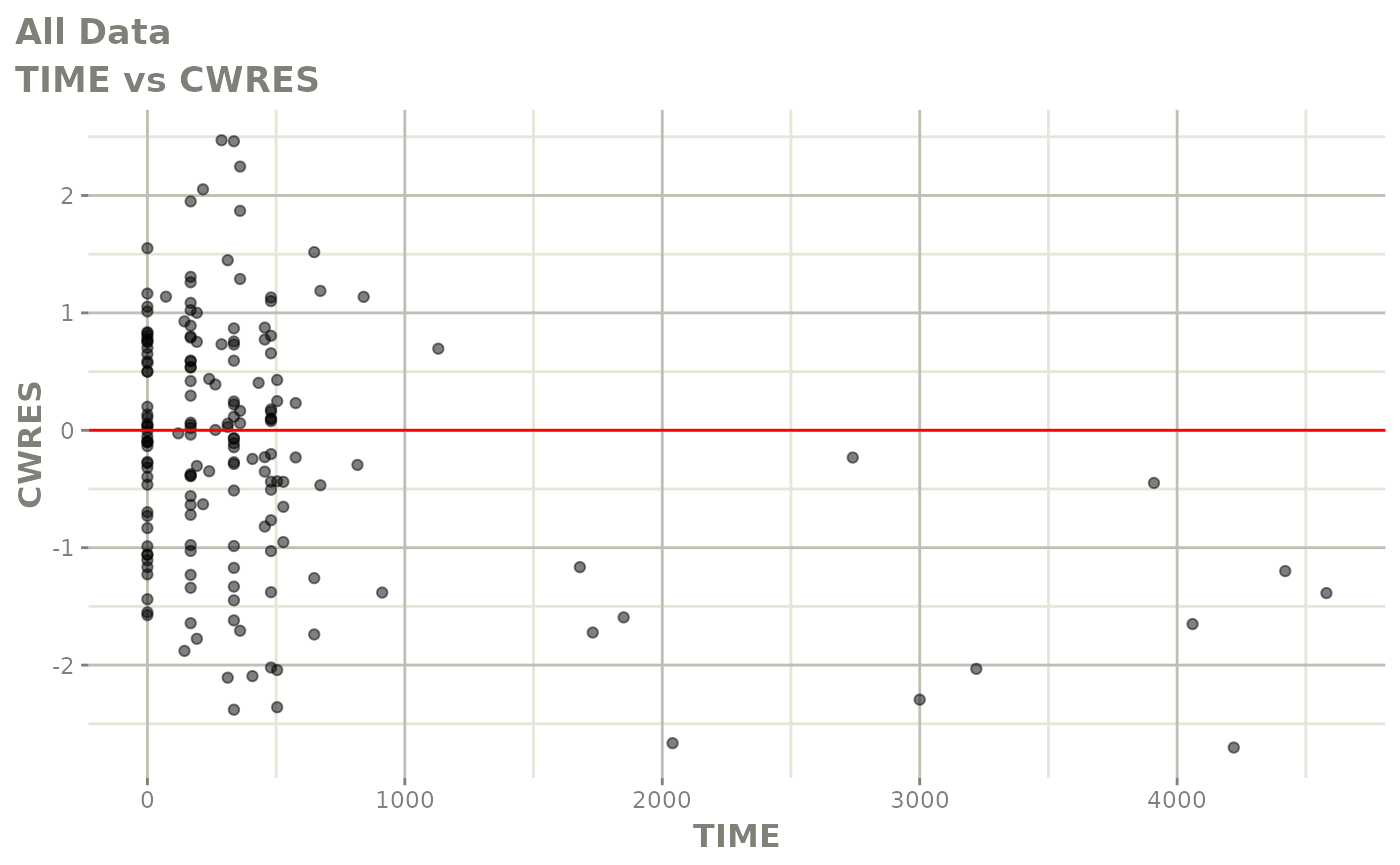
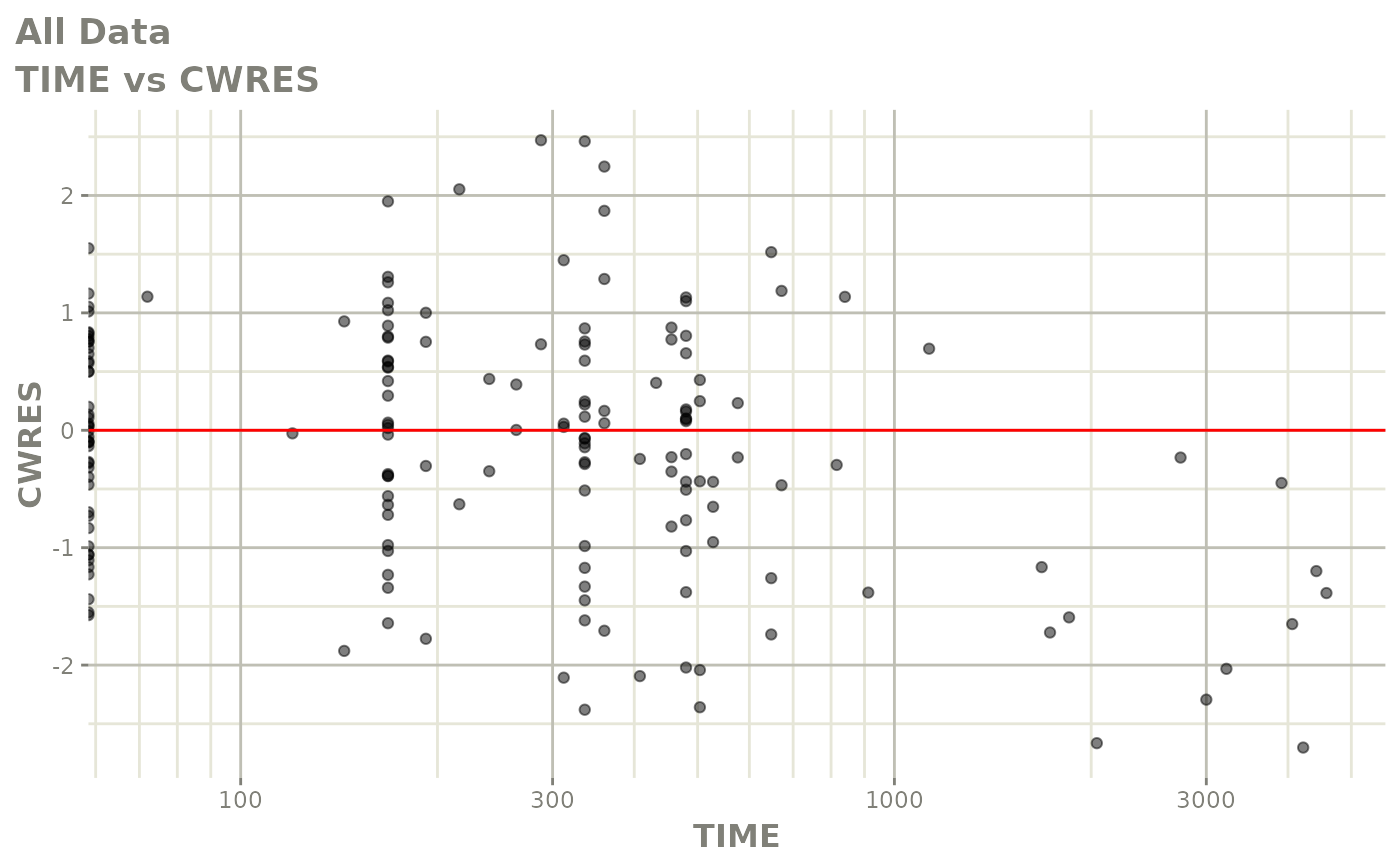
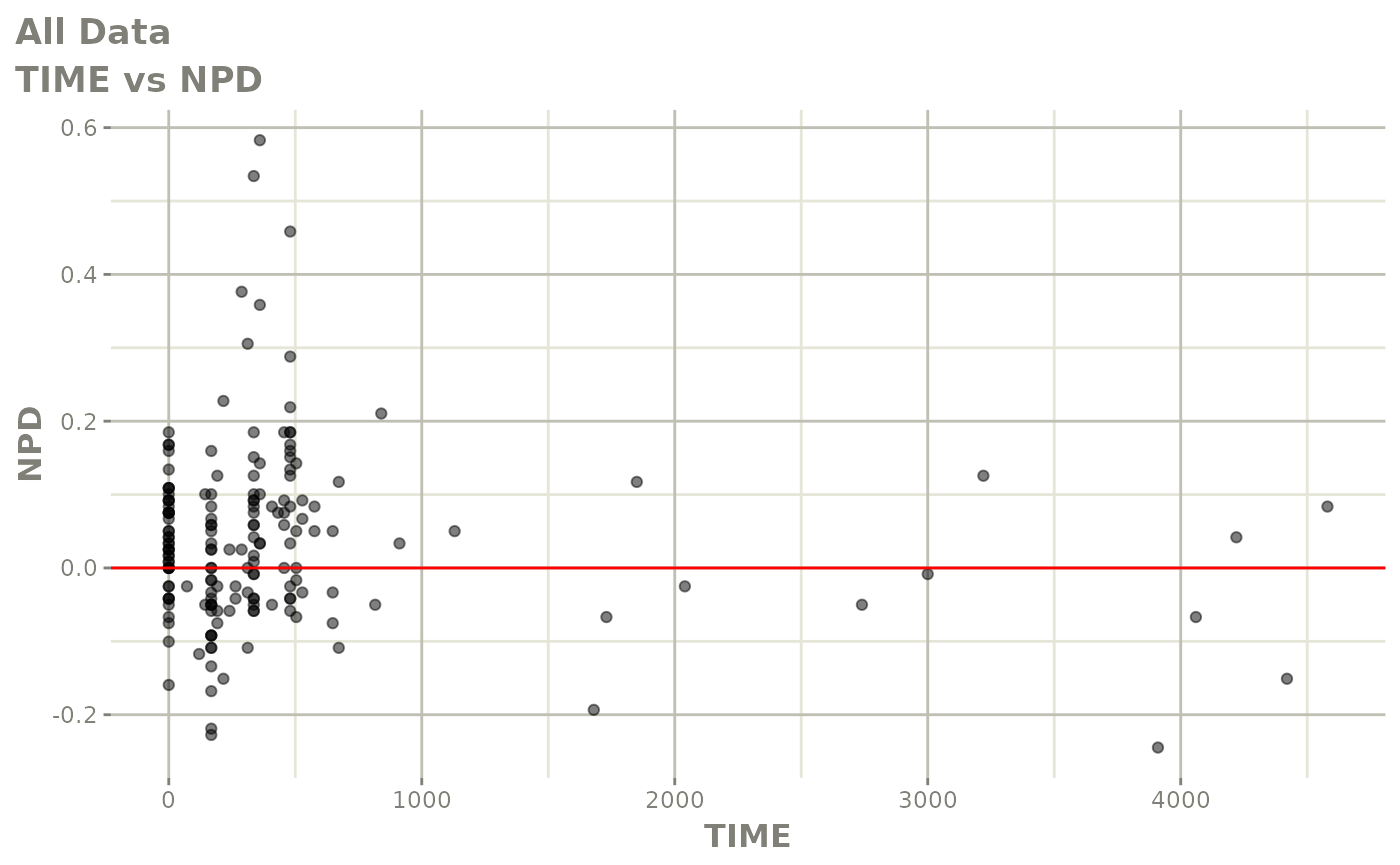
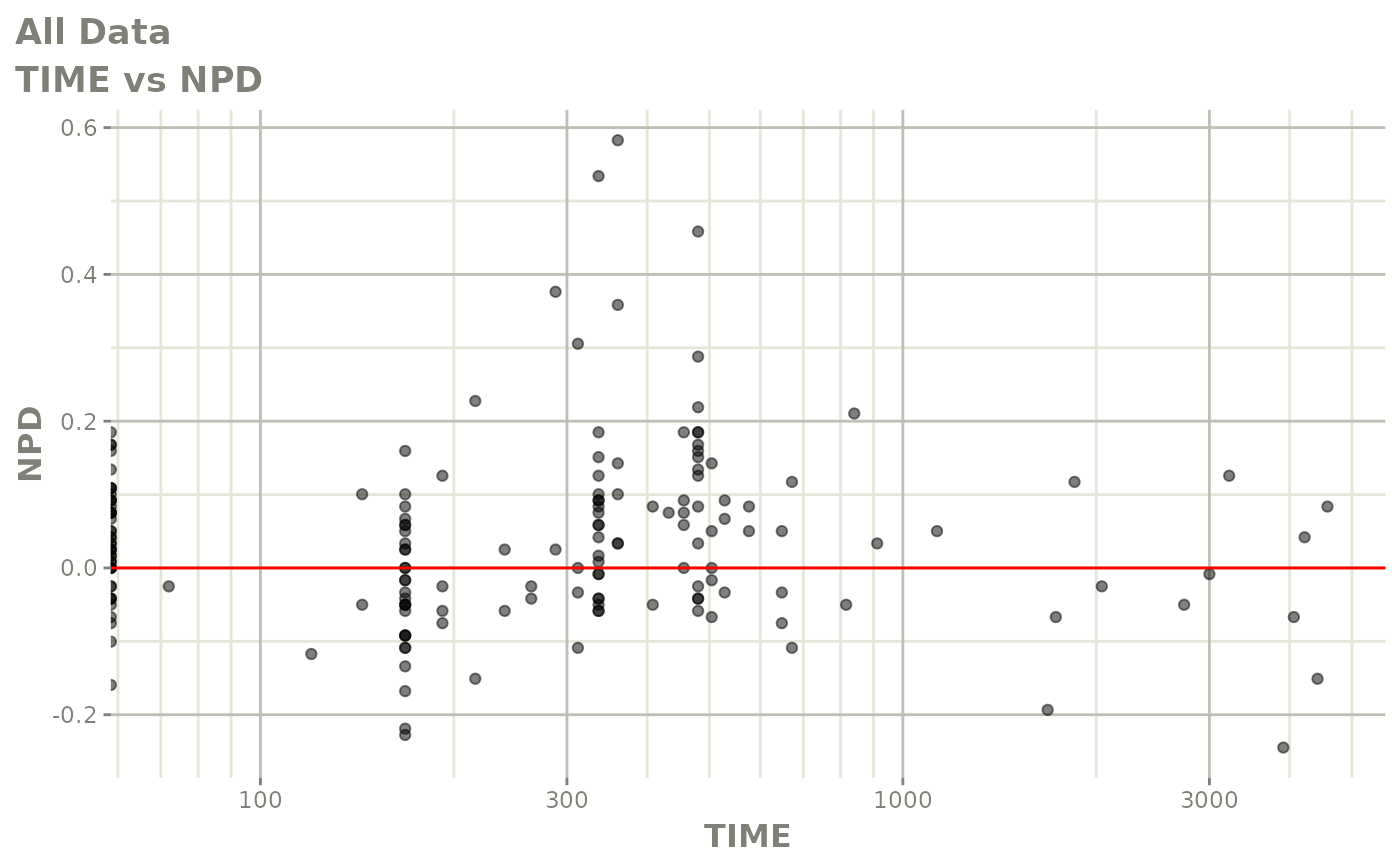
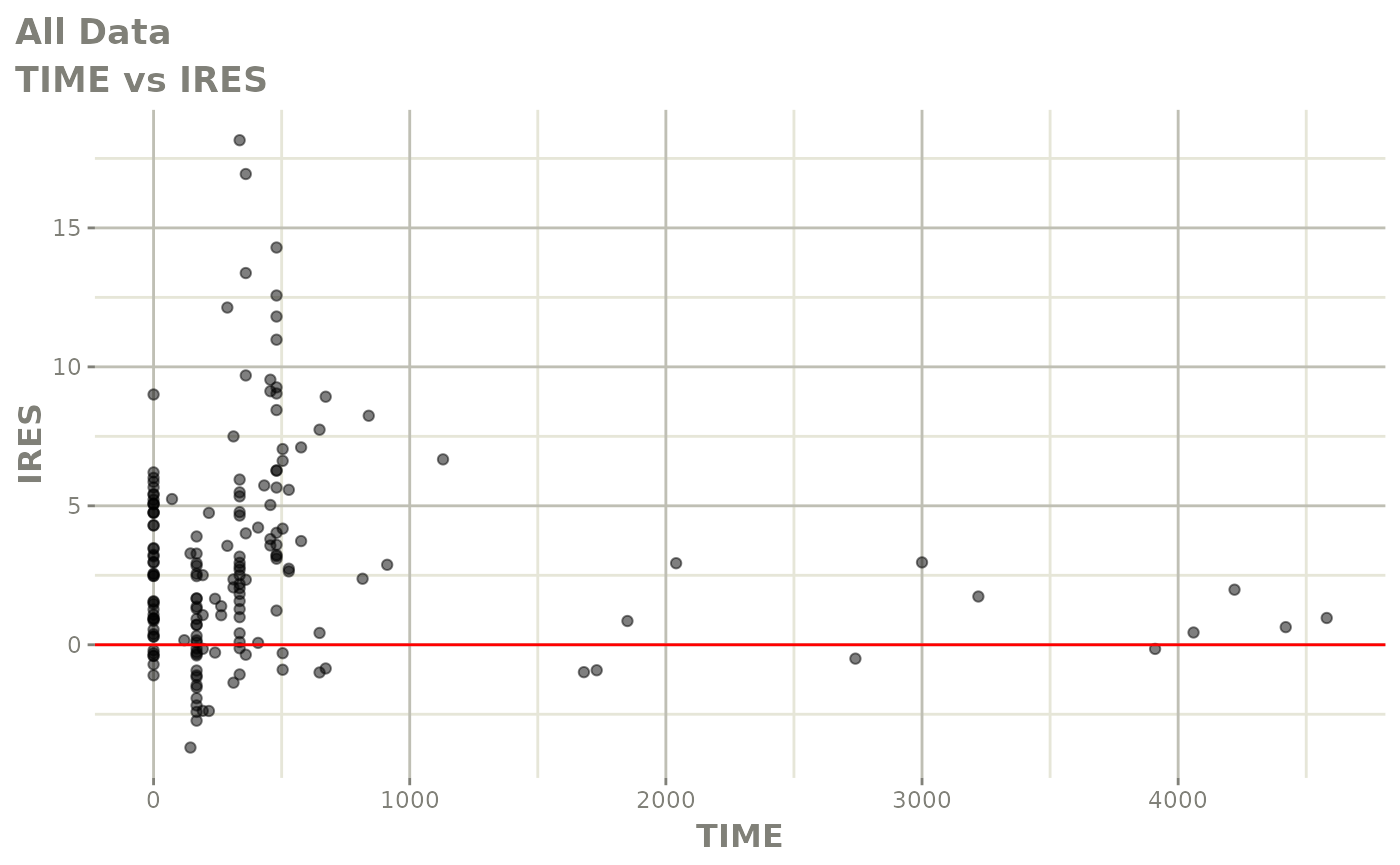
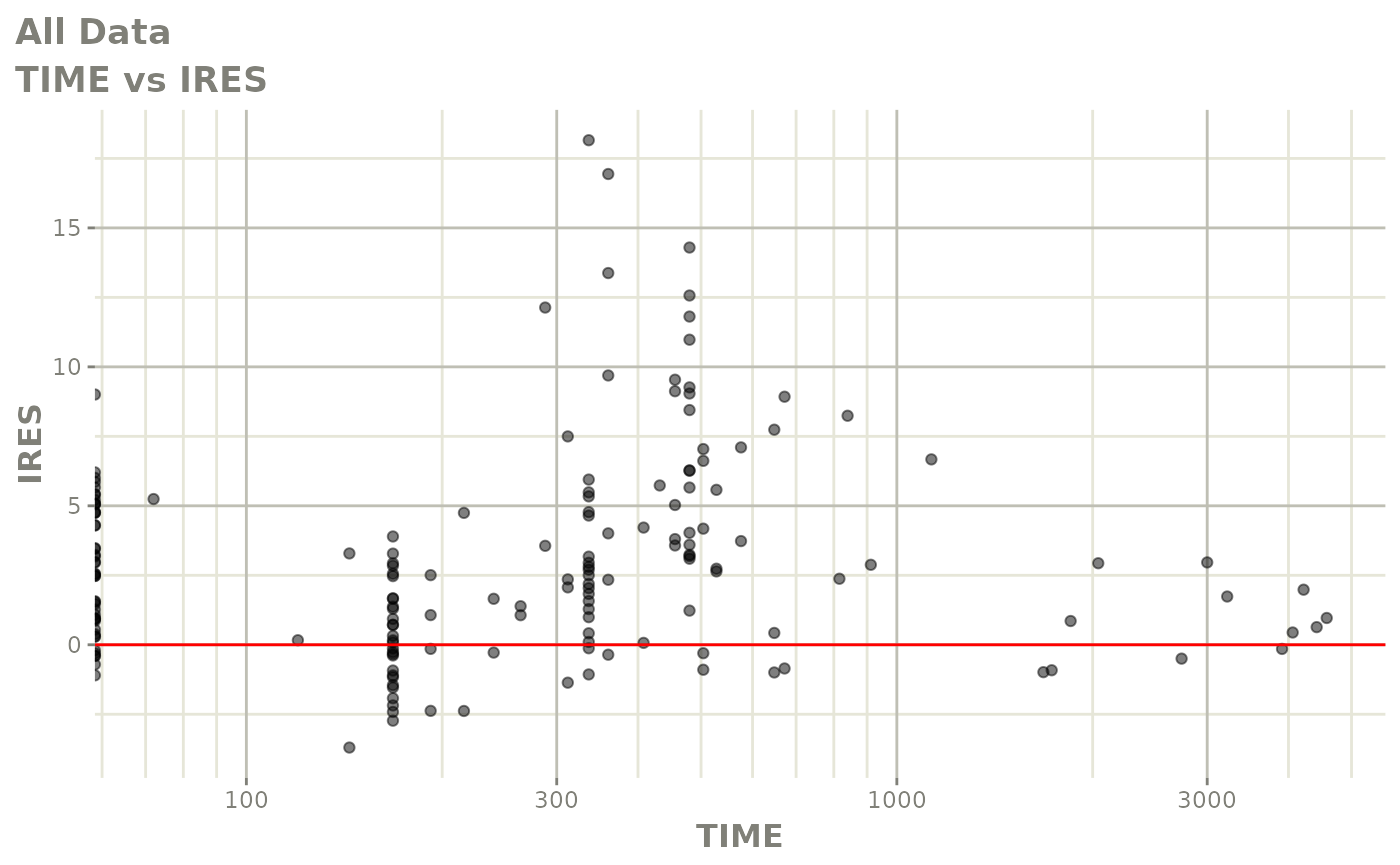
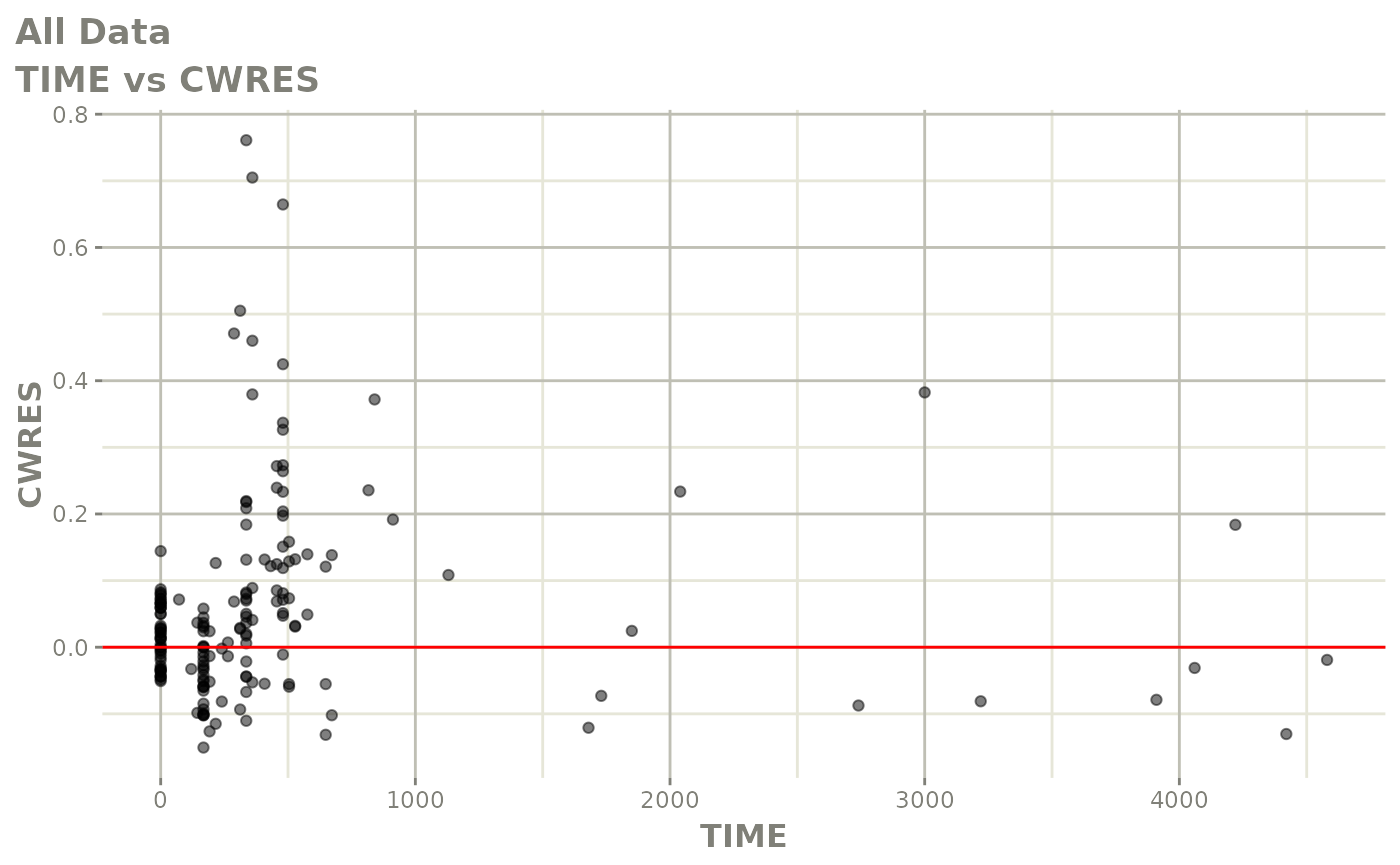
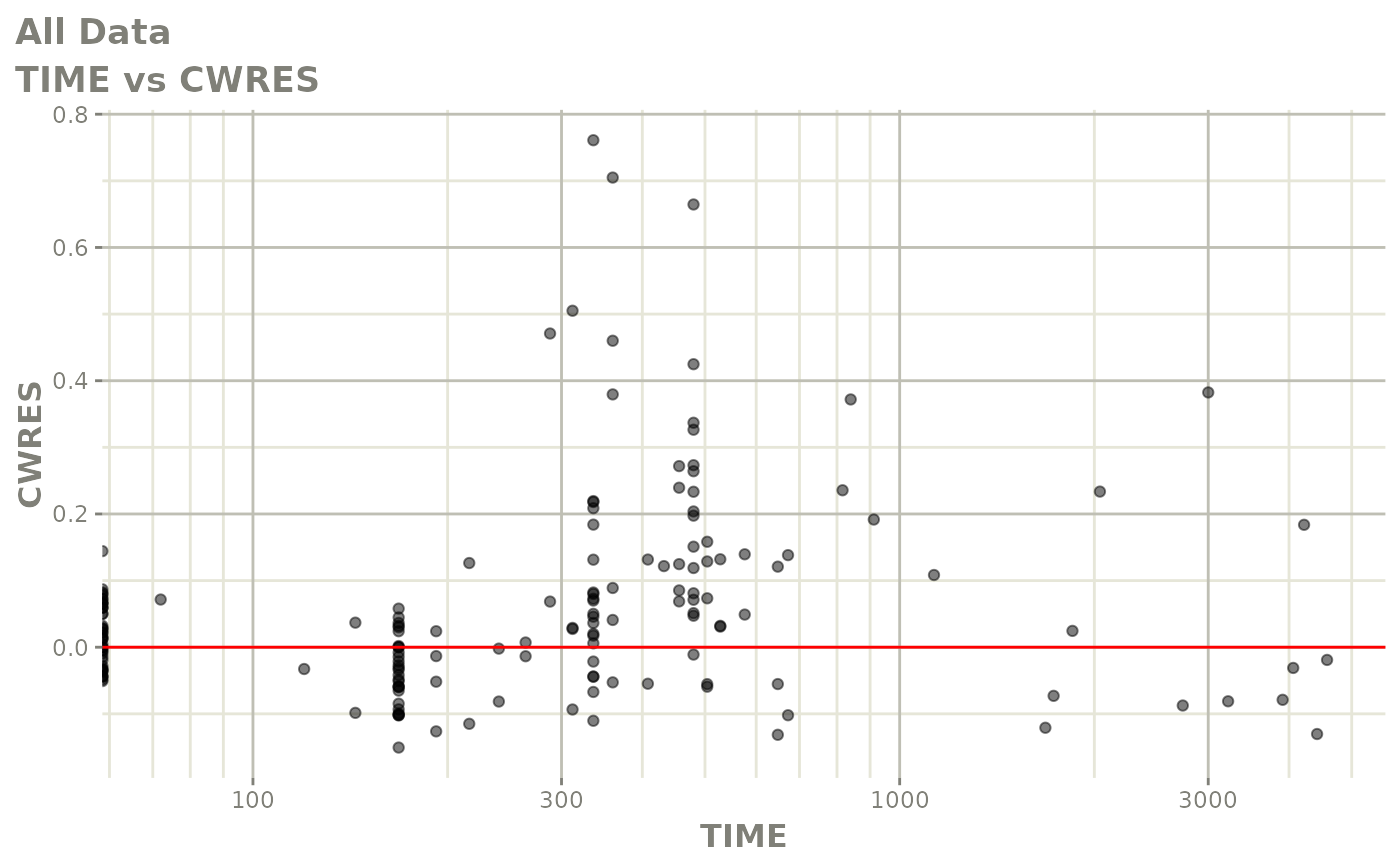
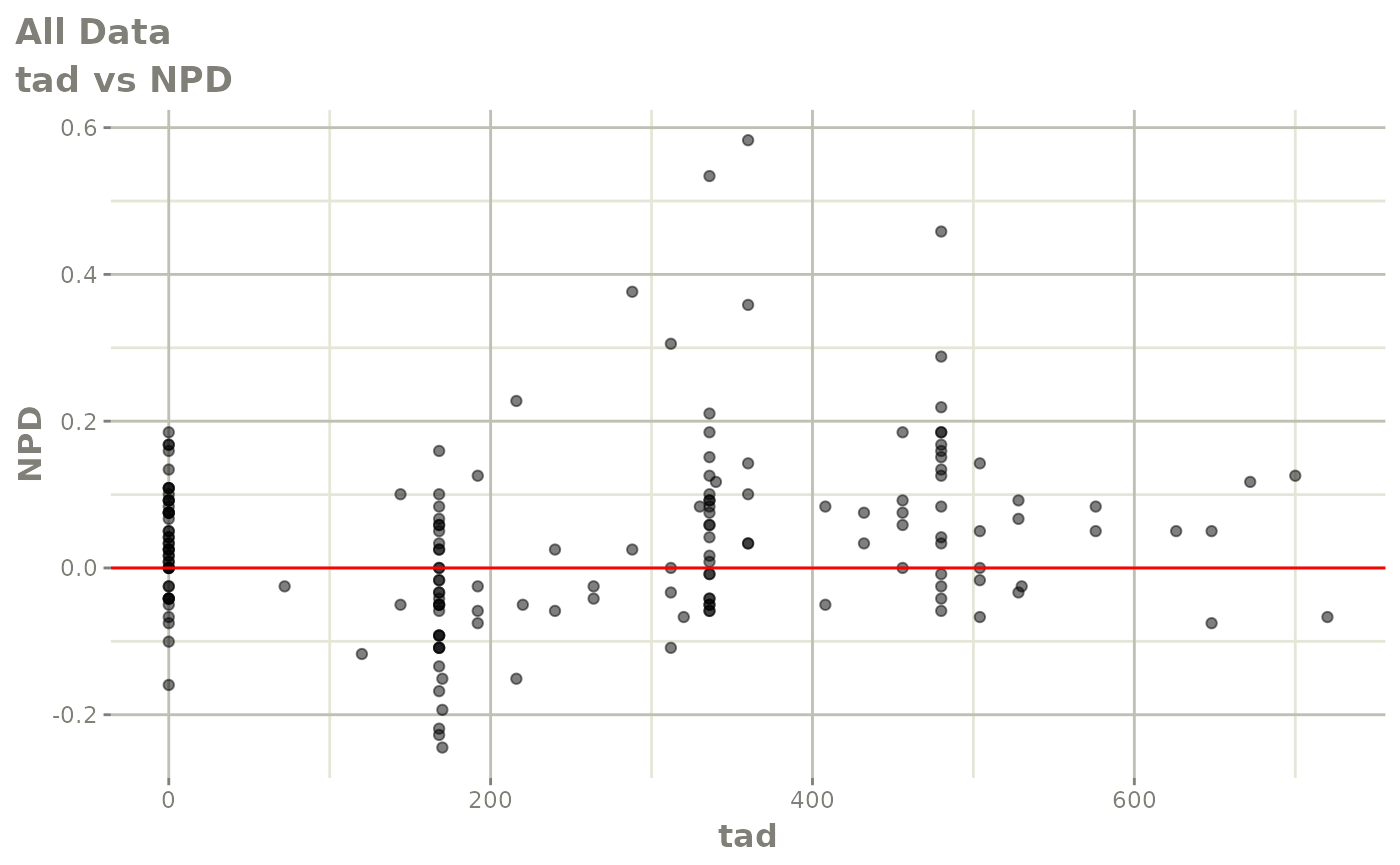
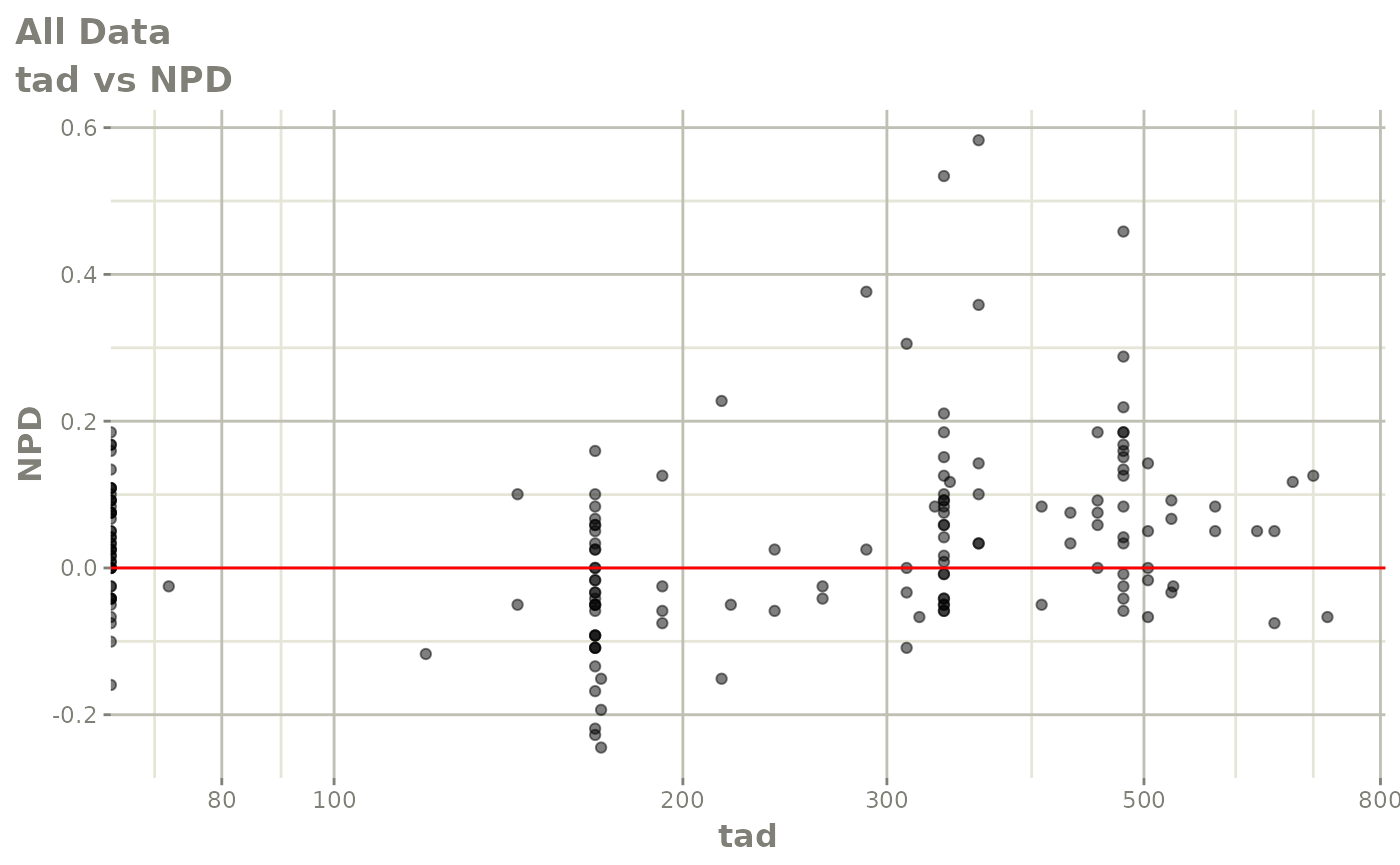
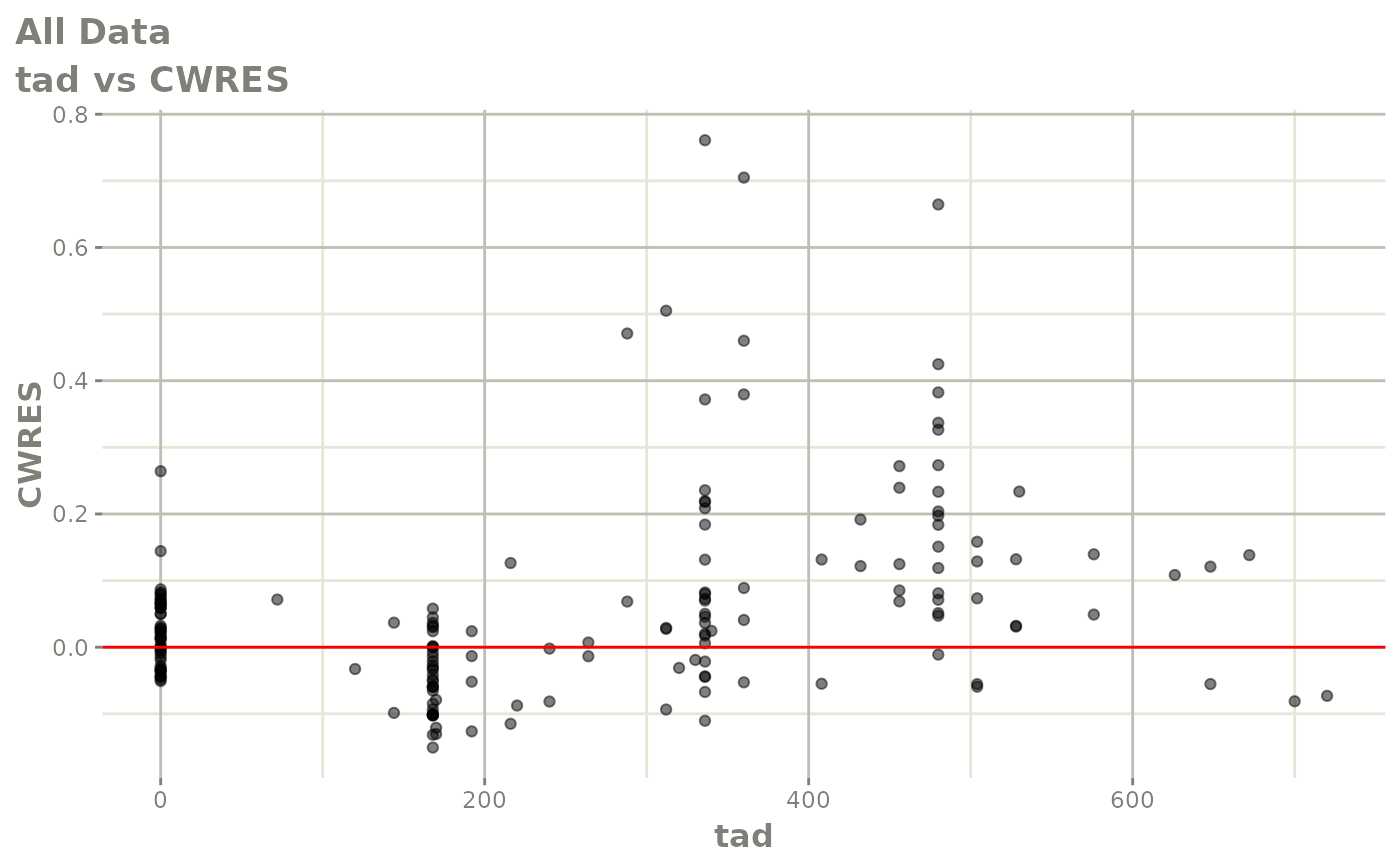
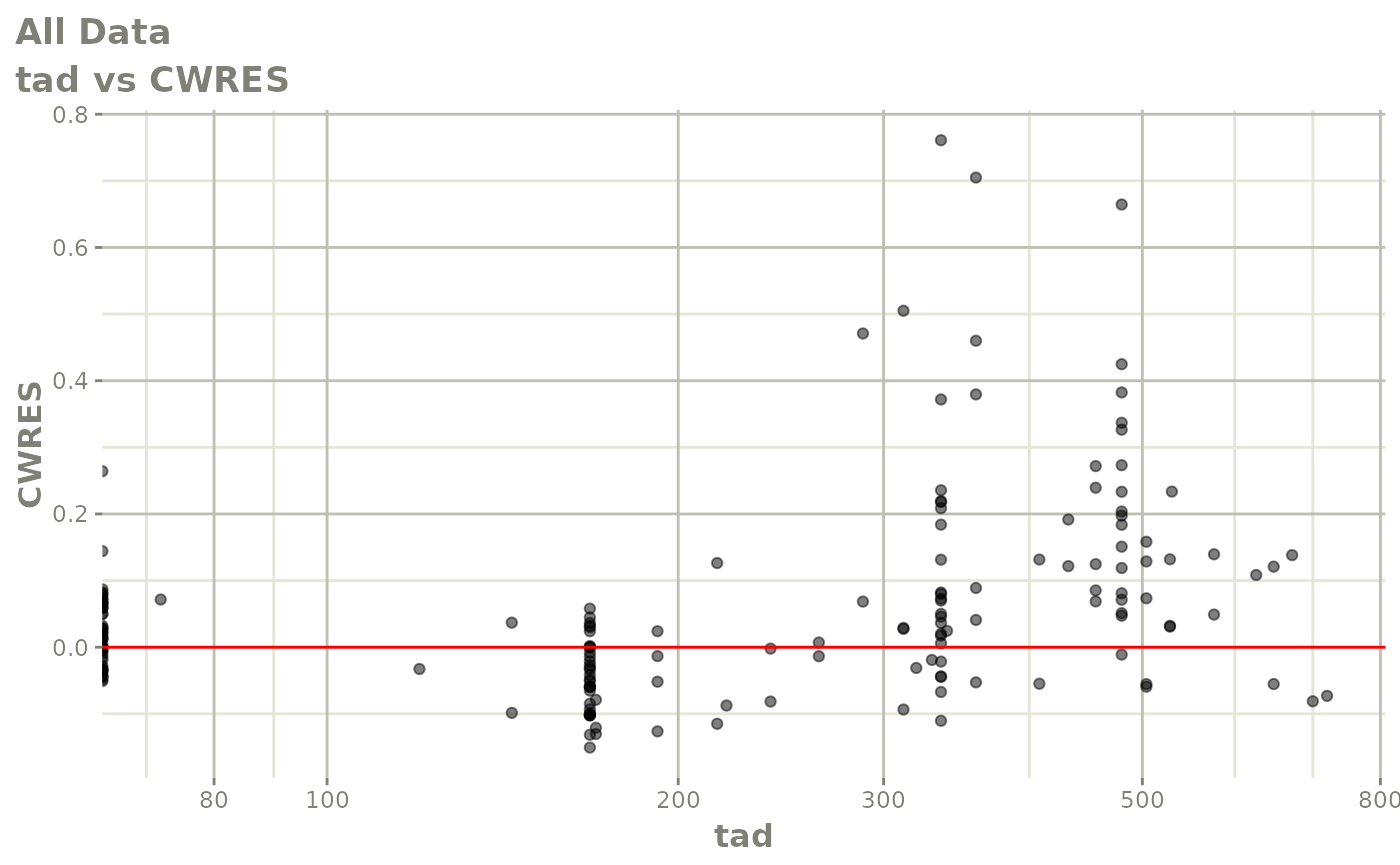
print(res_vs_idv(xpdb) +
ylab("Conditional Weighted Residuals") +
xlab("Time (h)"))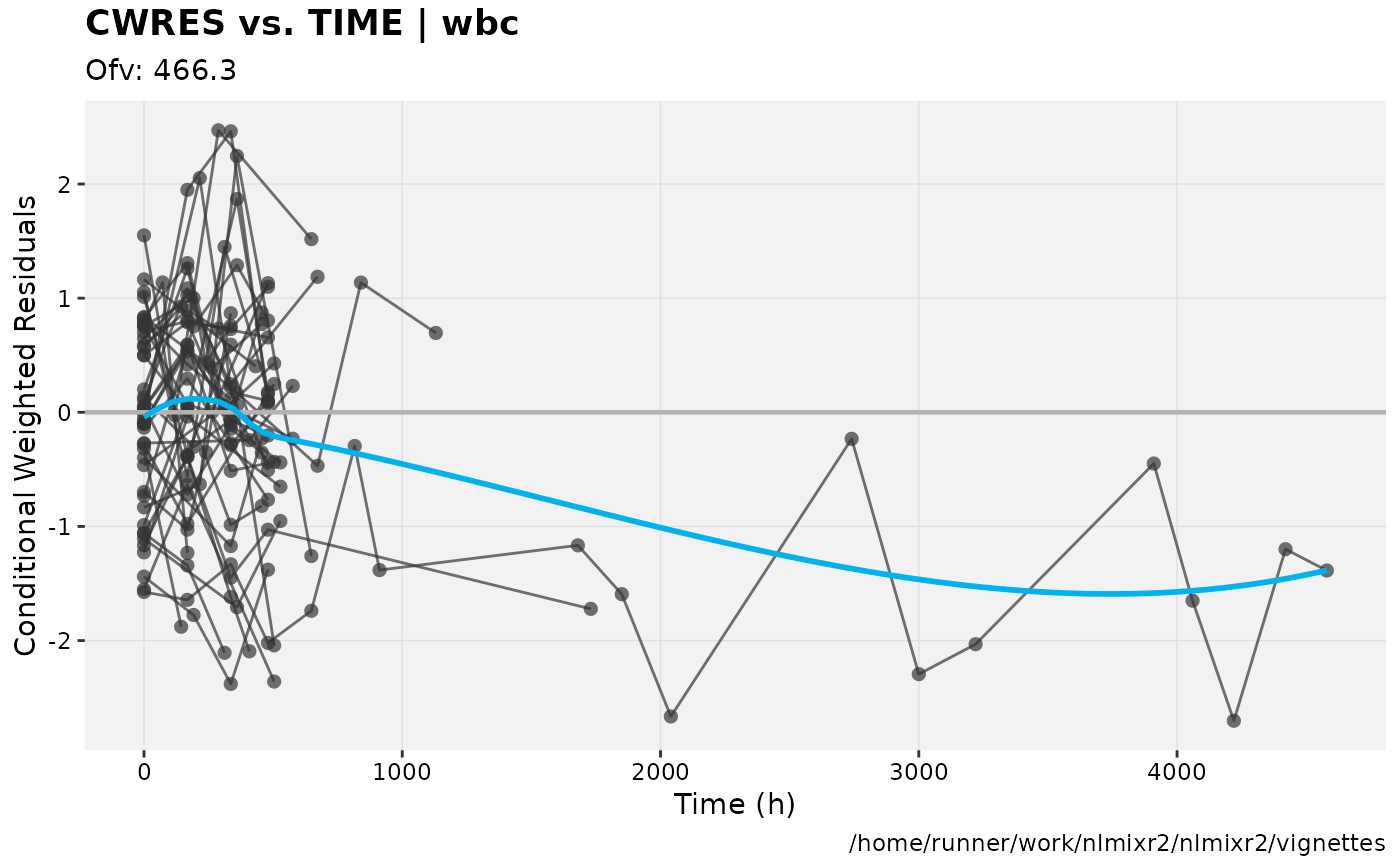
print(prm_vs_iteration(xpdb))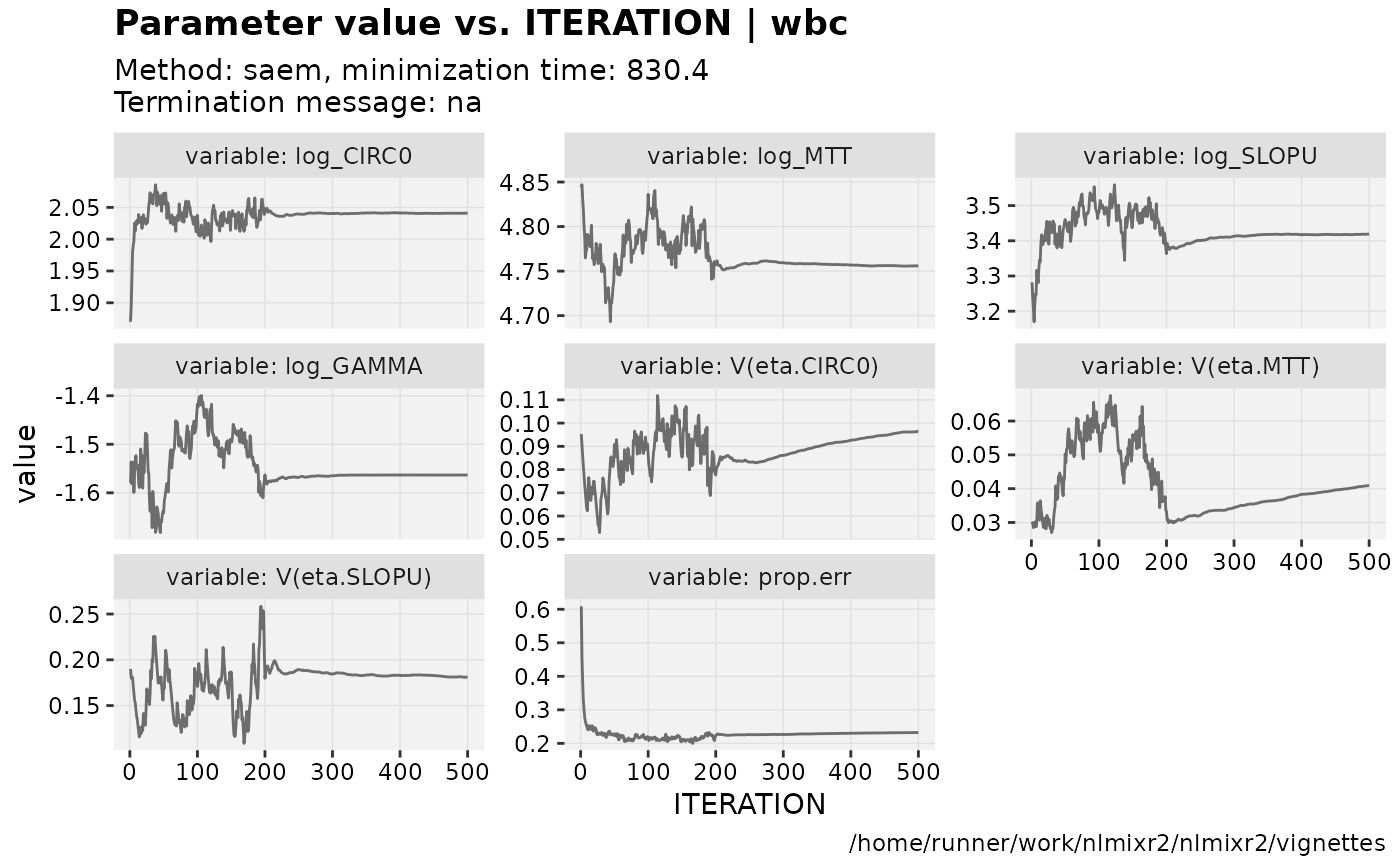
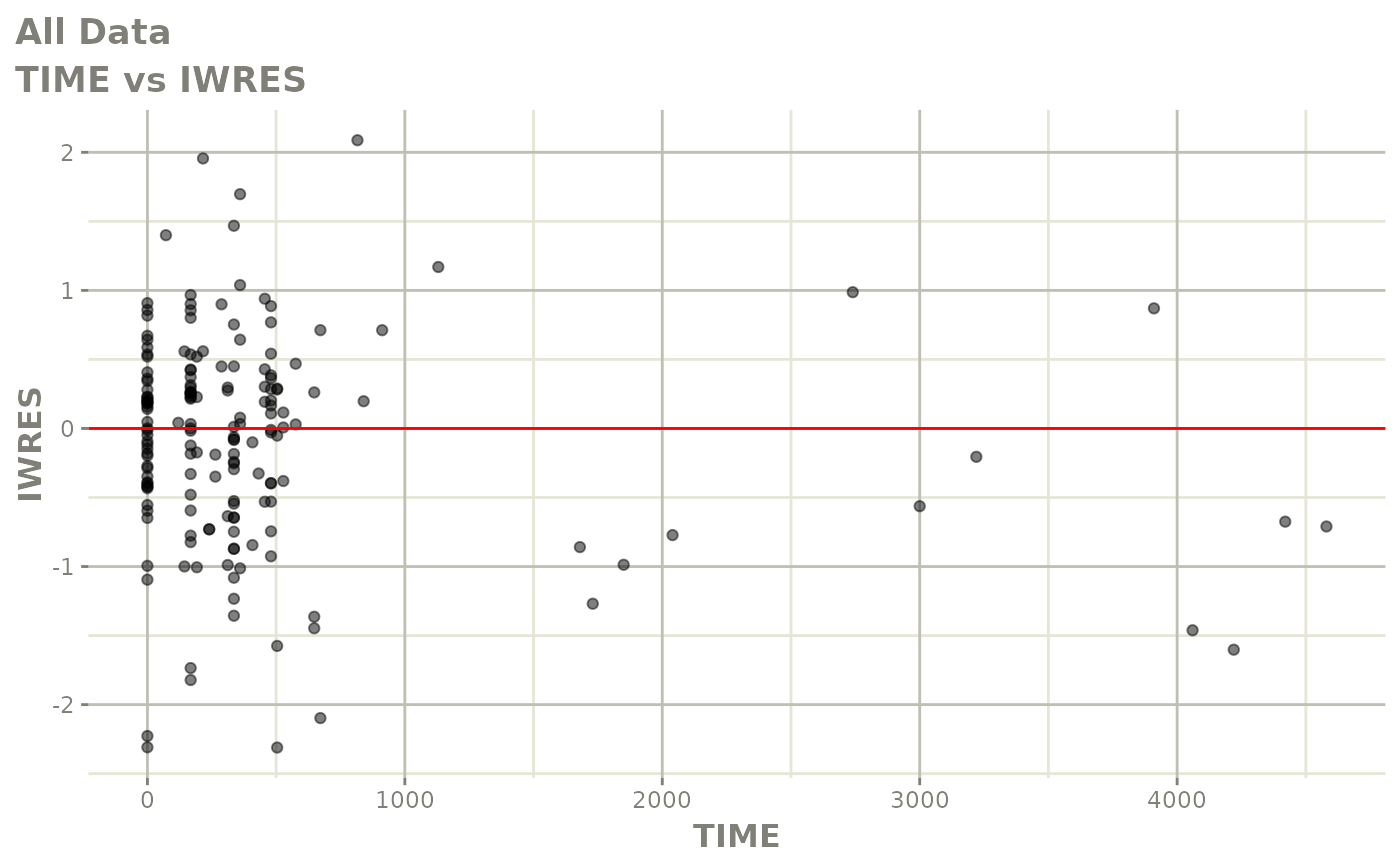
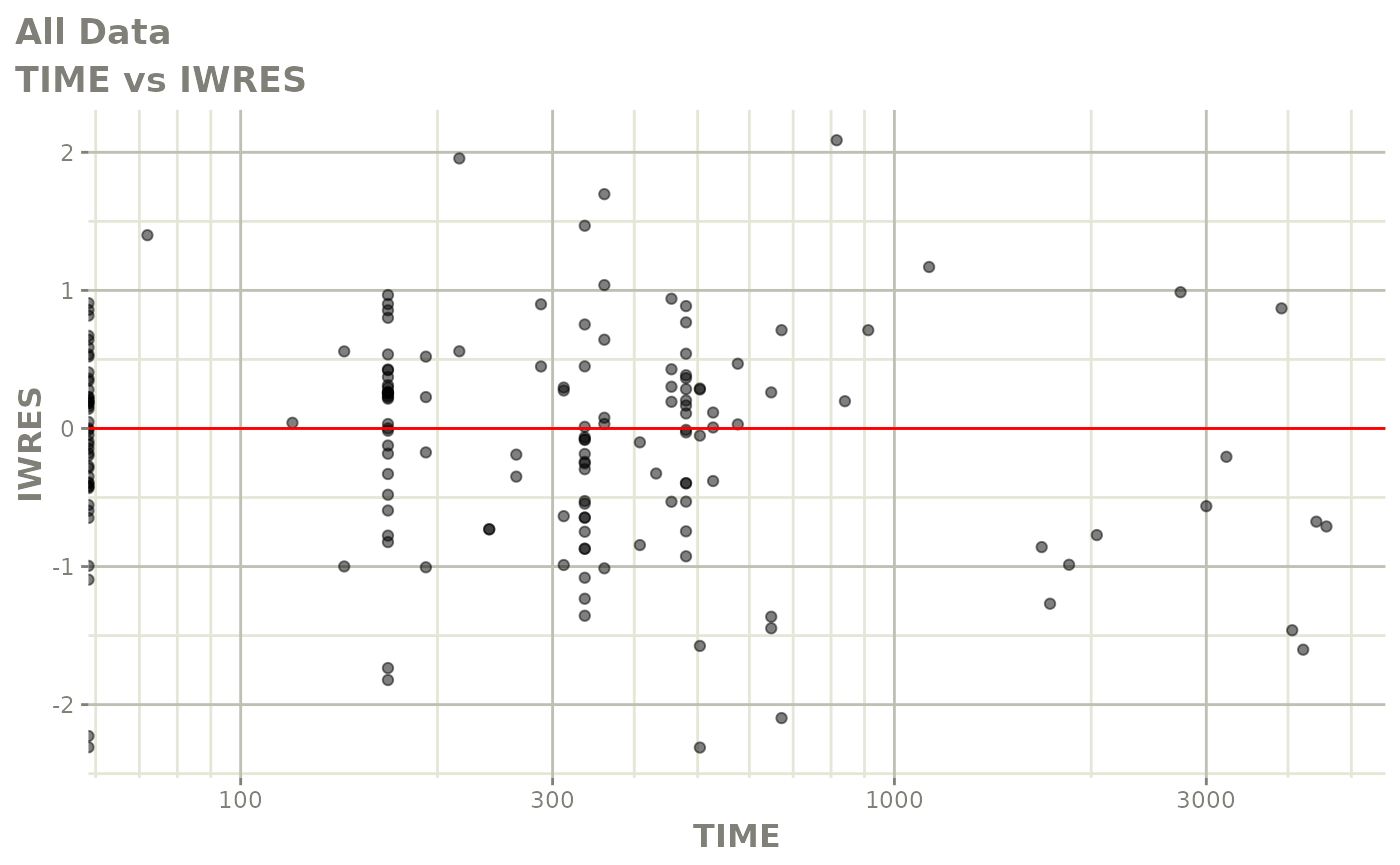
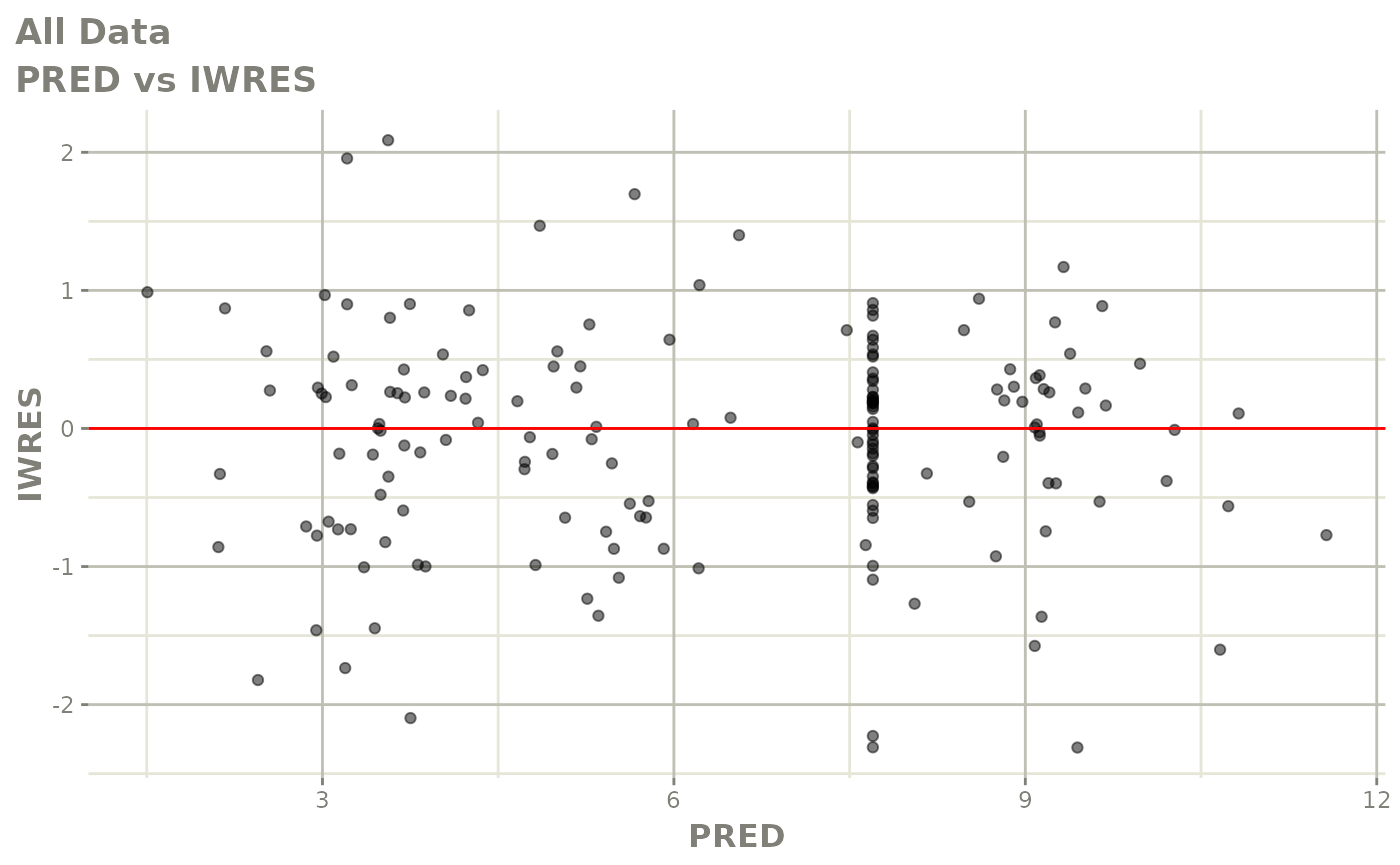
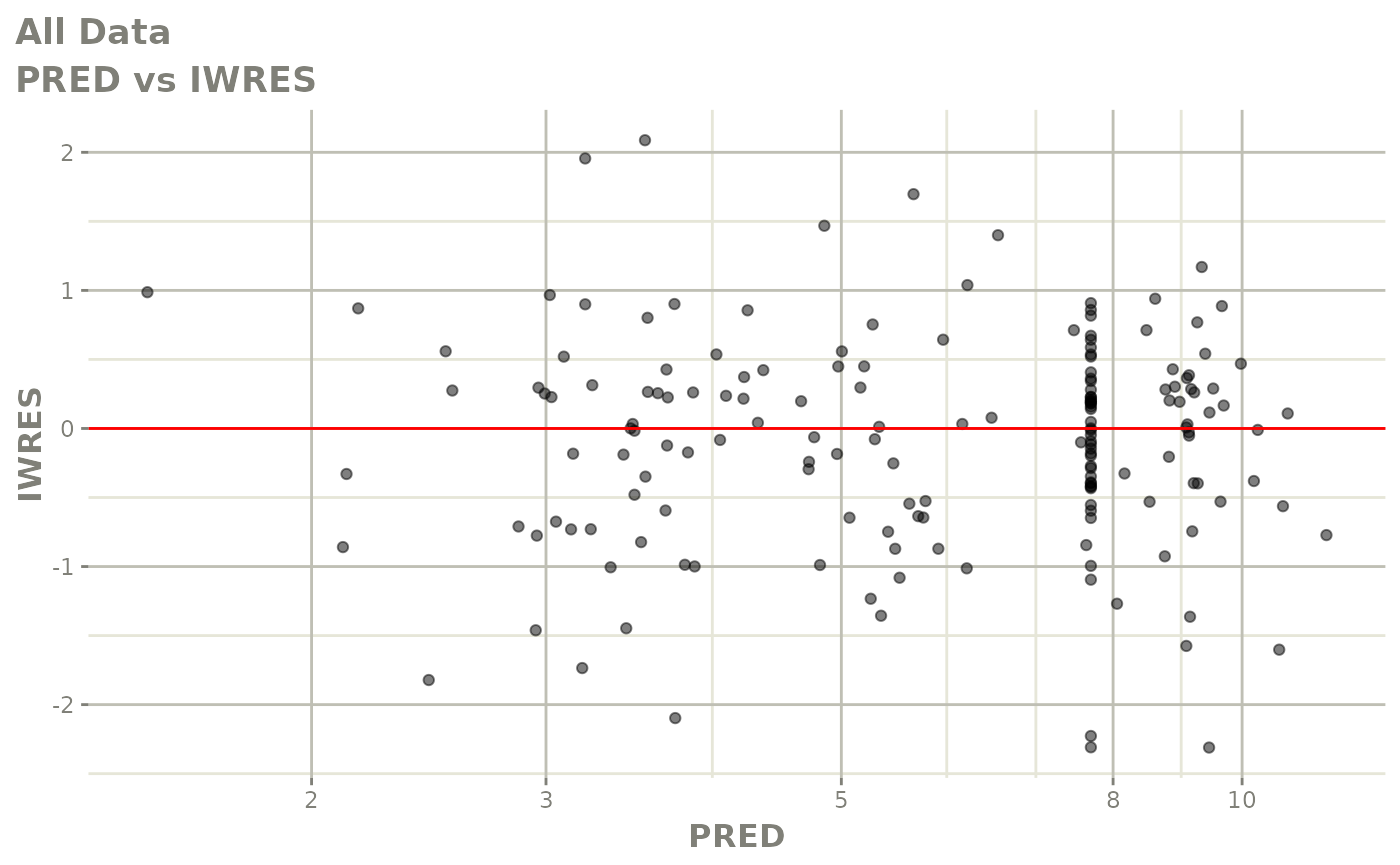
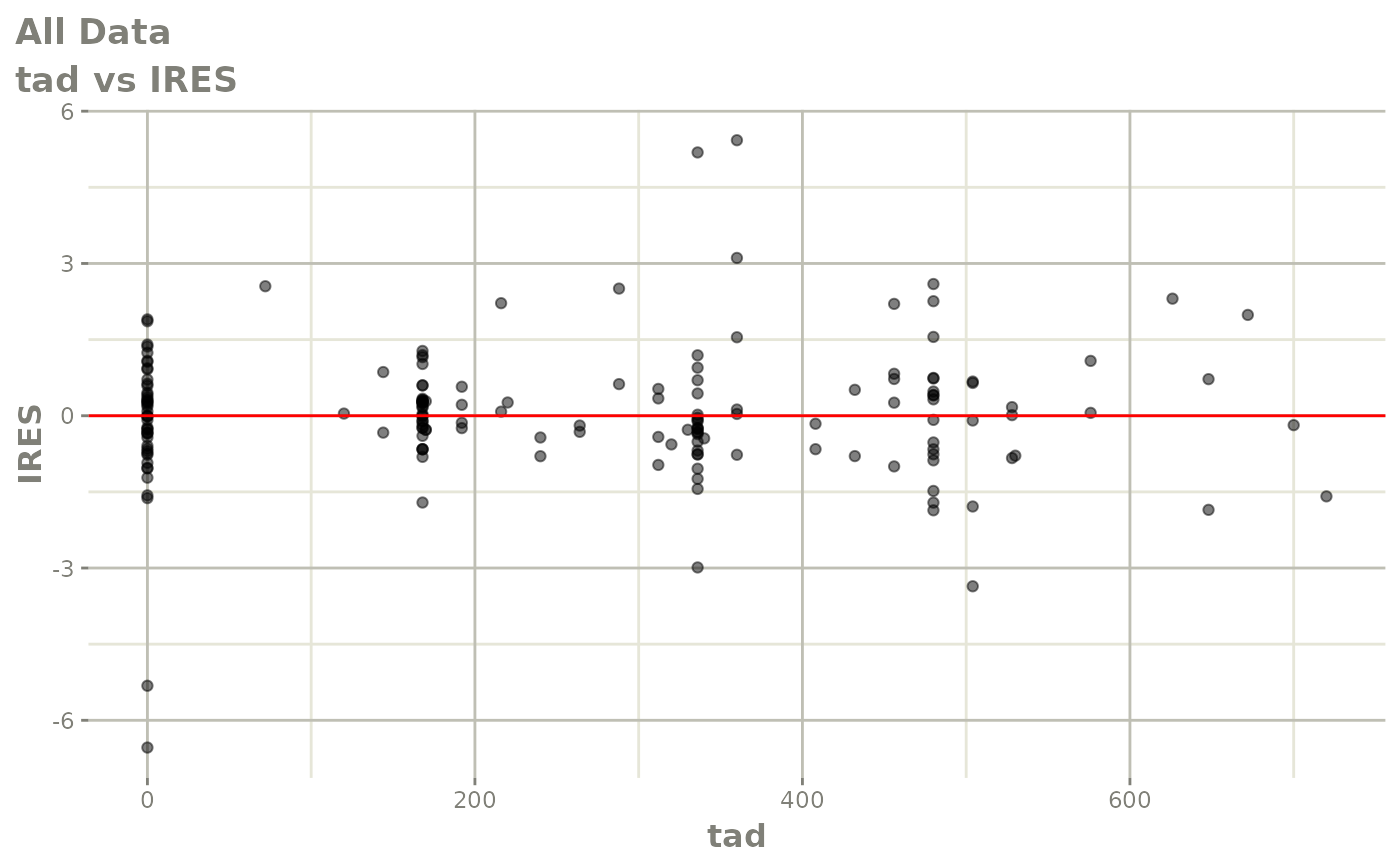
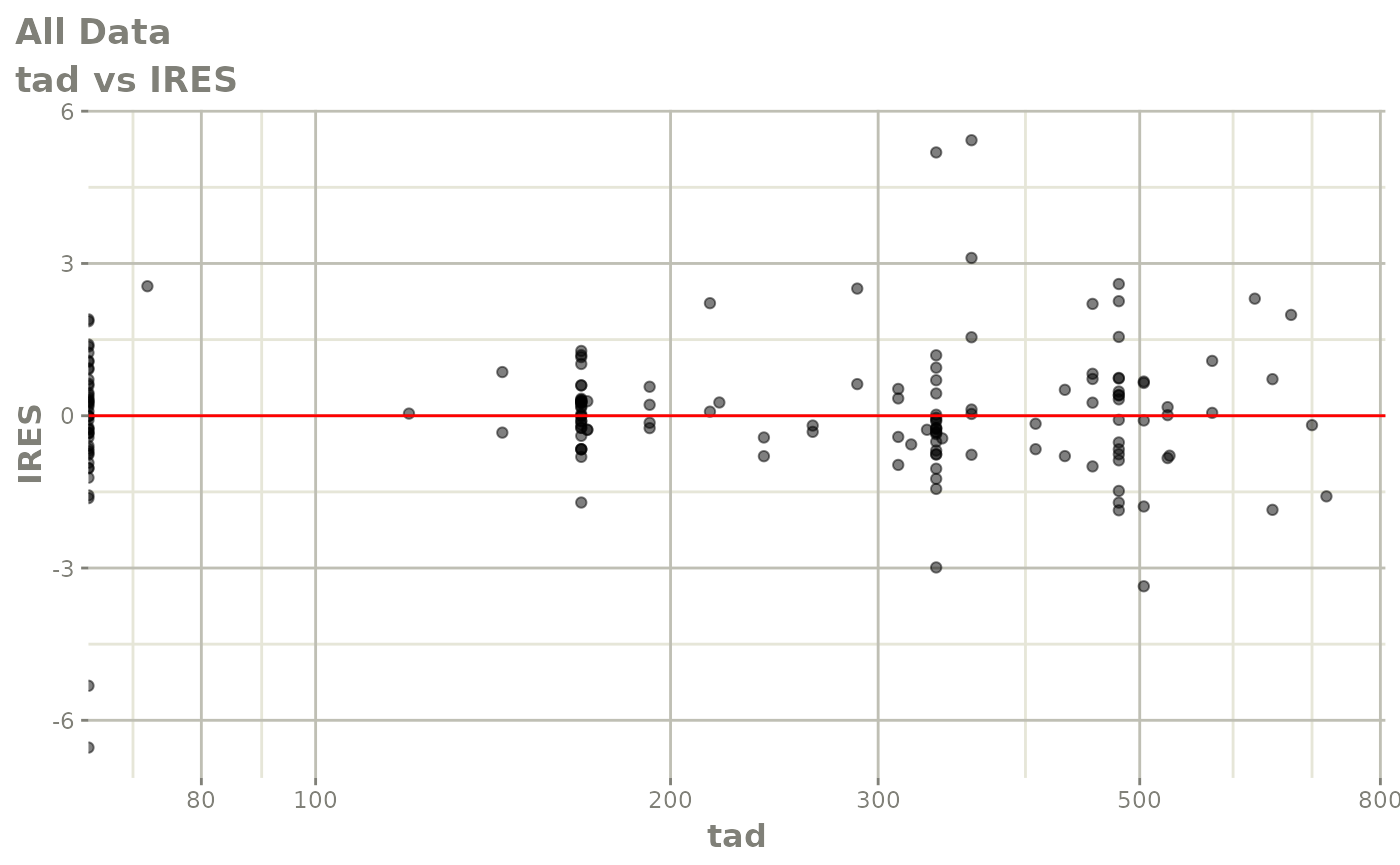
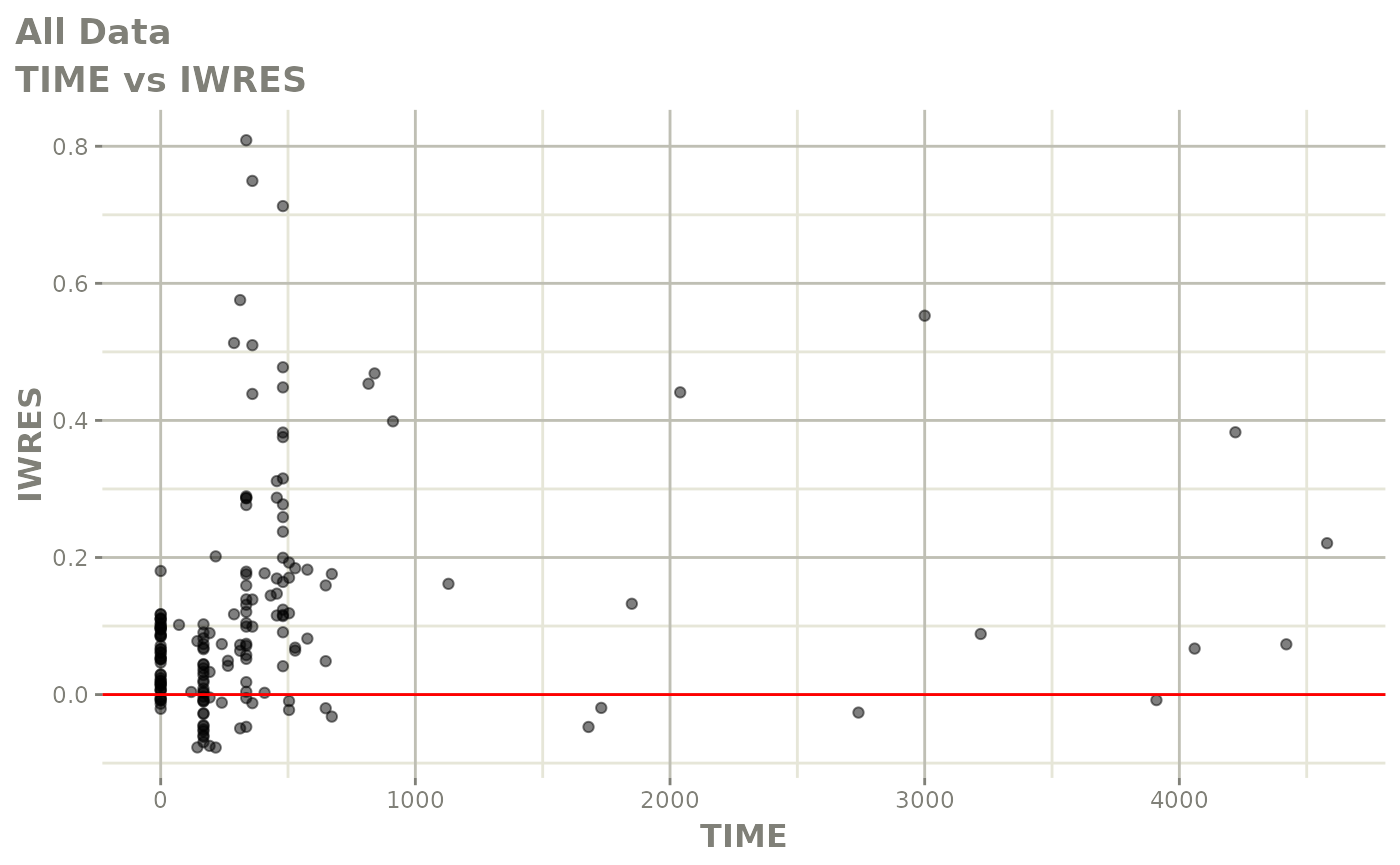
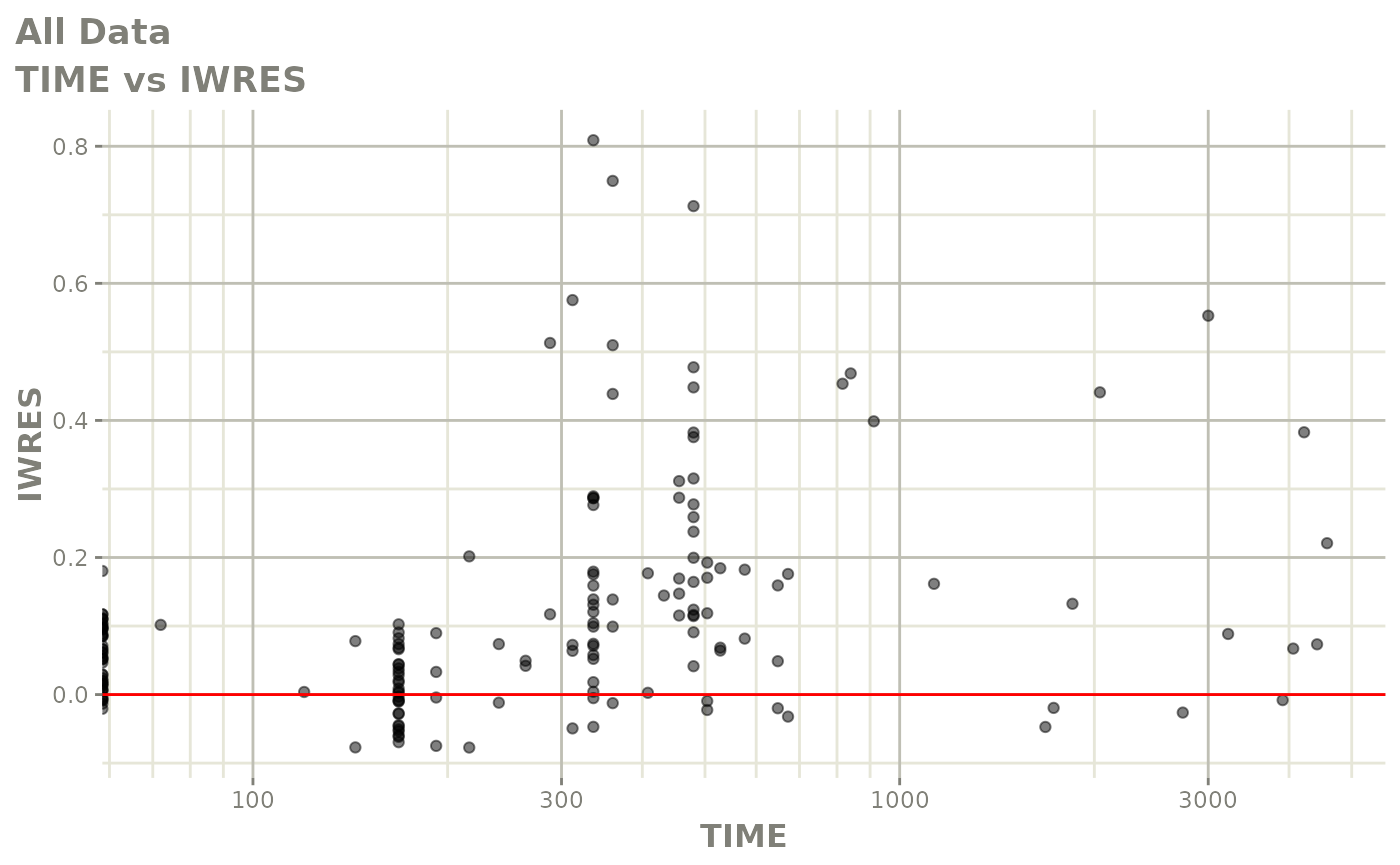
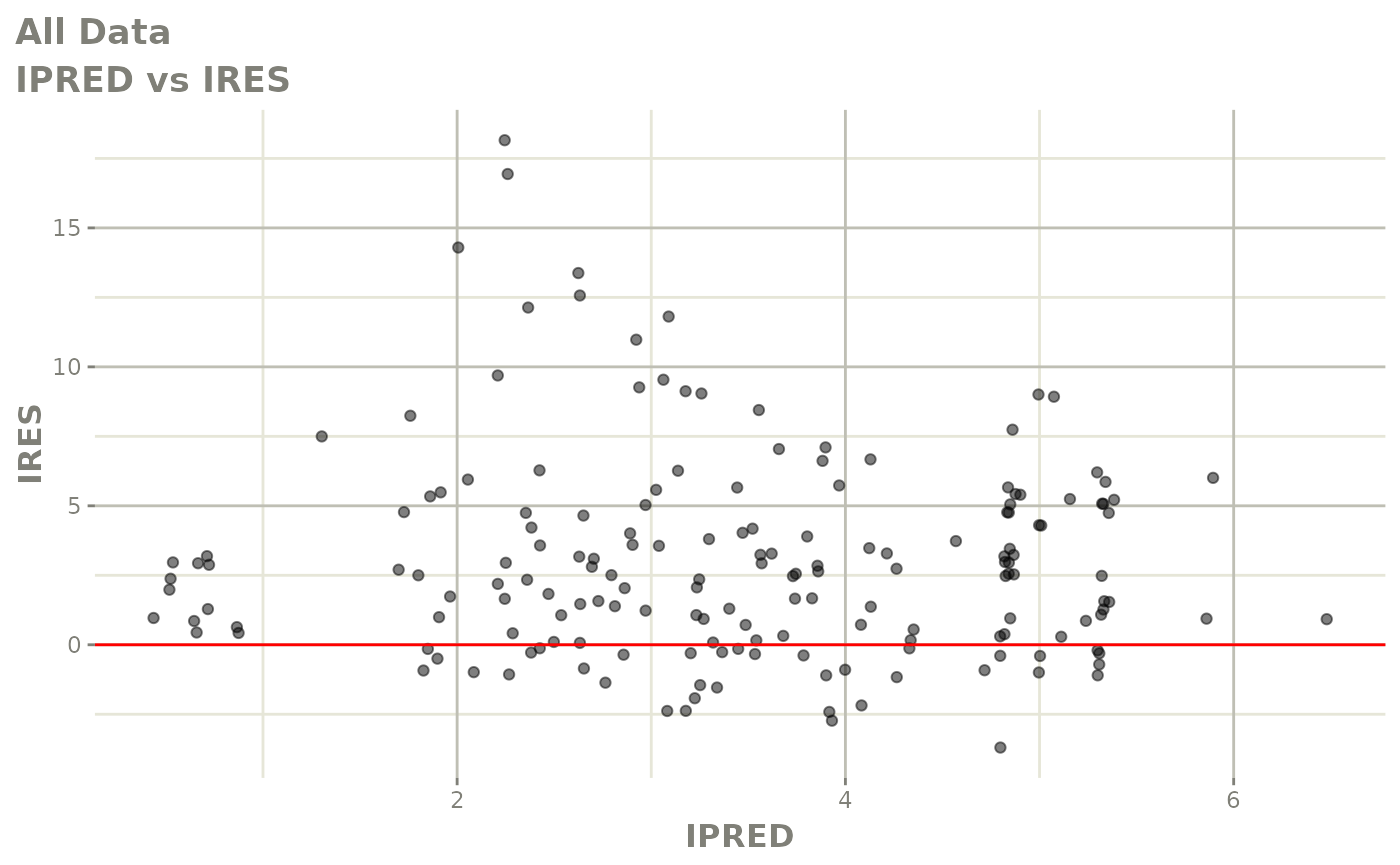
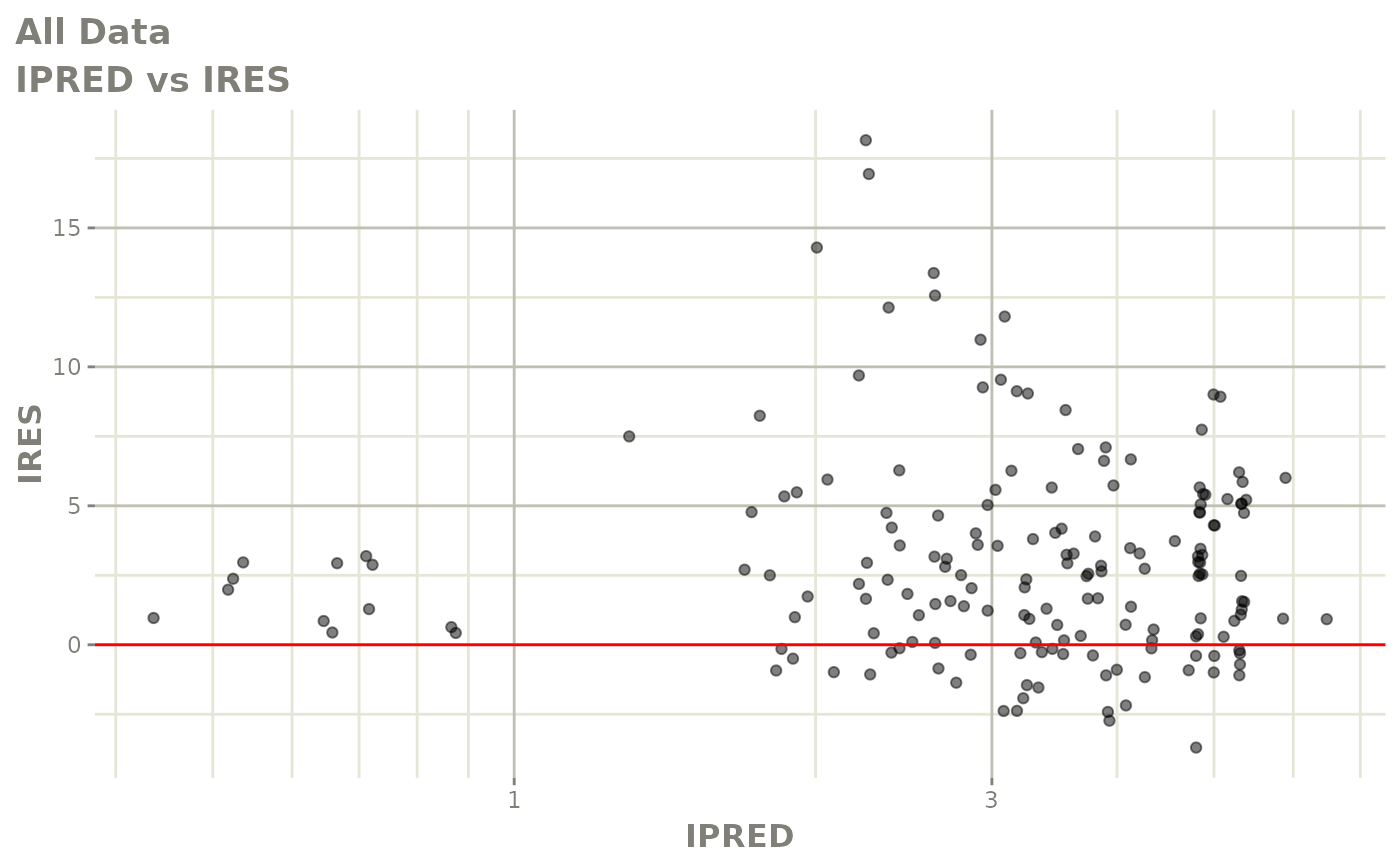
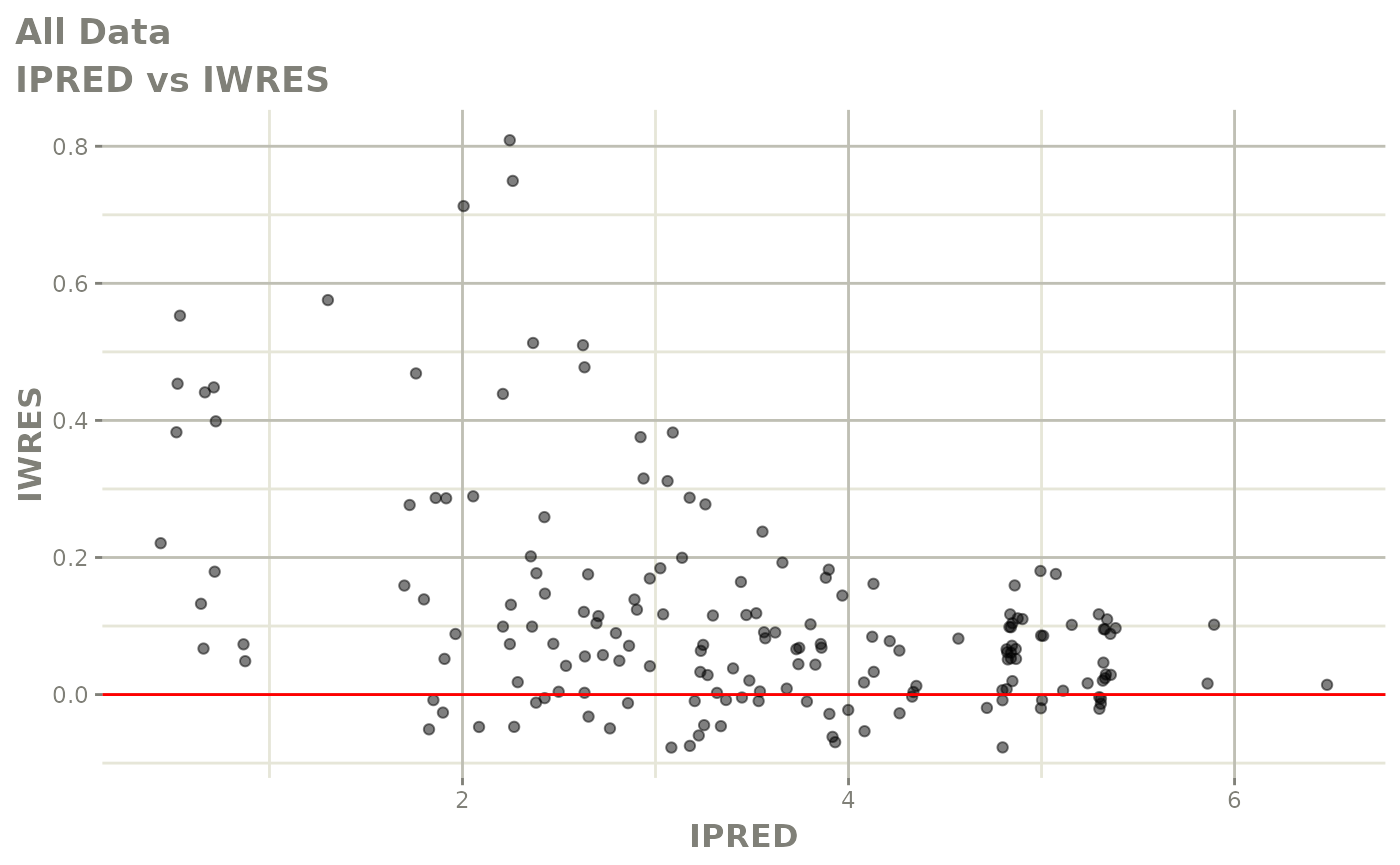
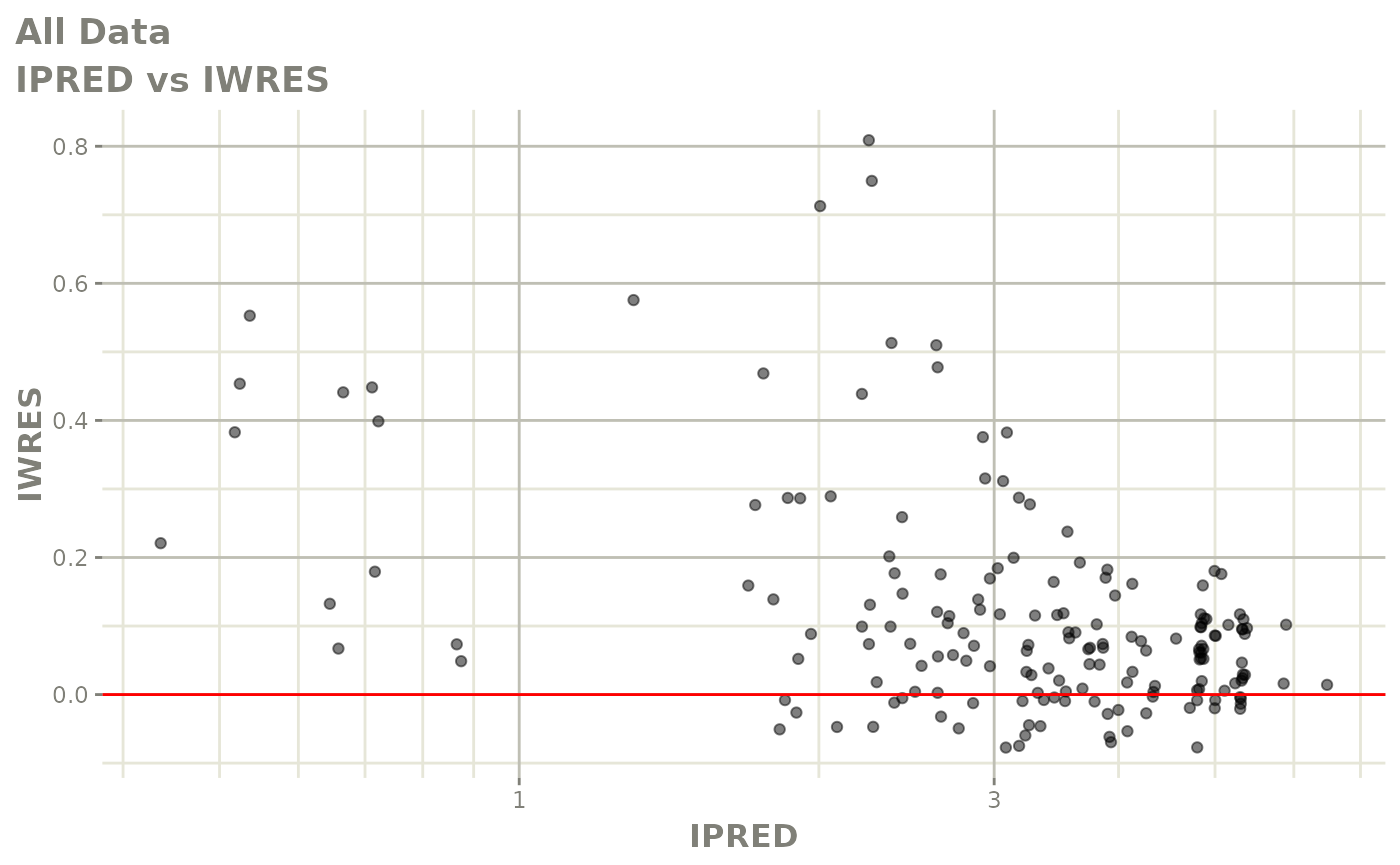
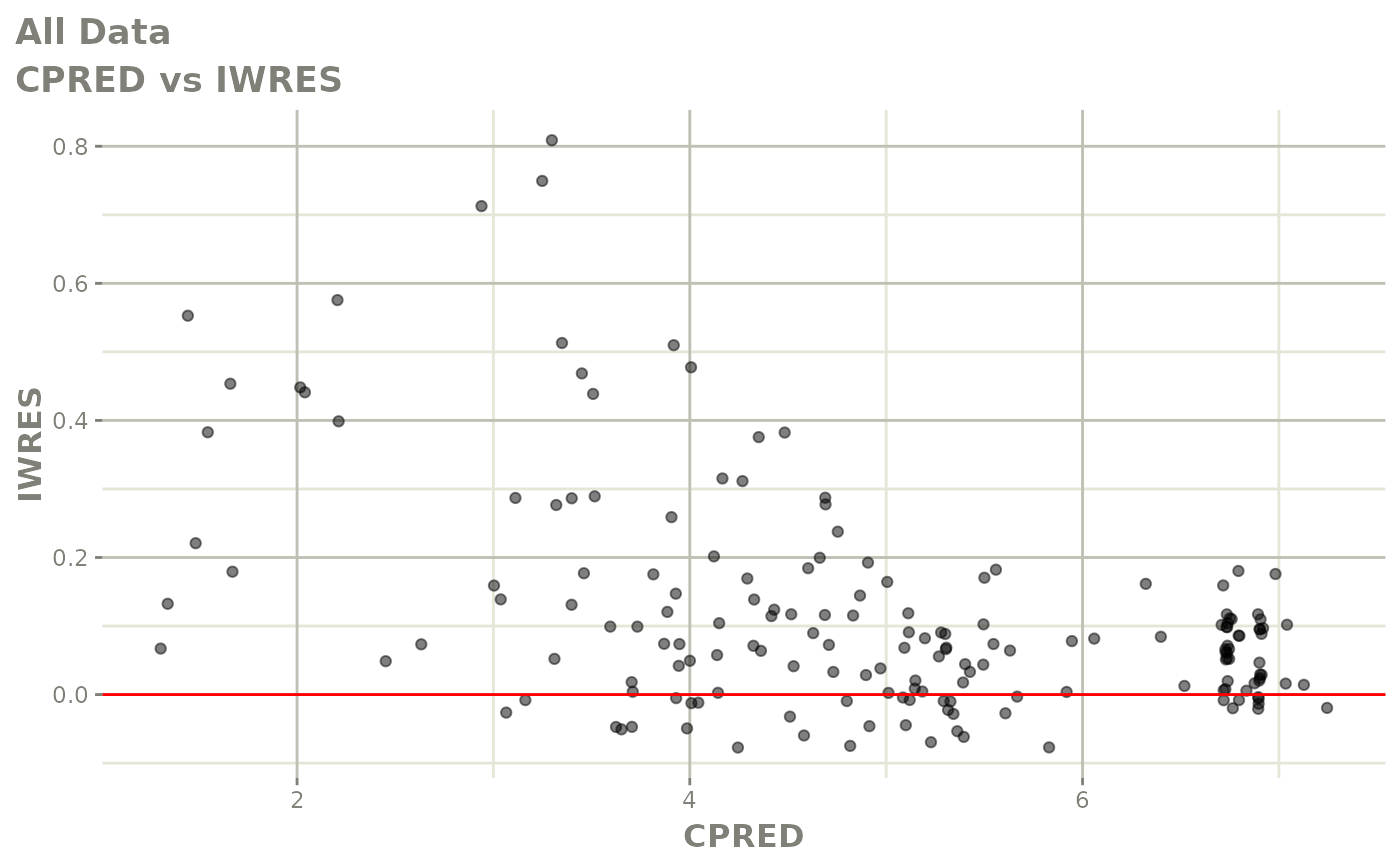
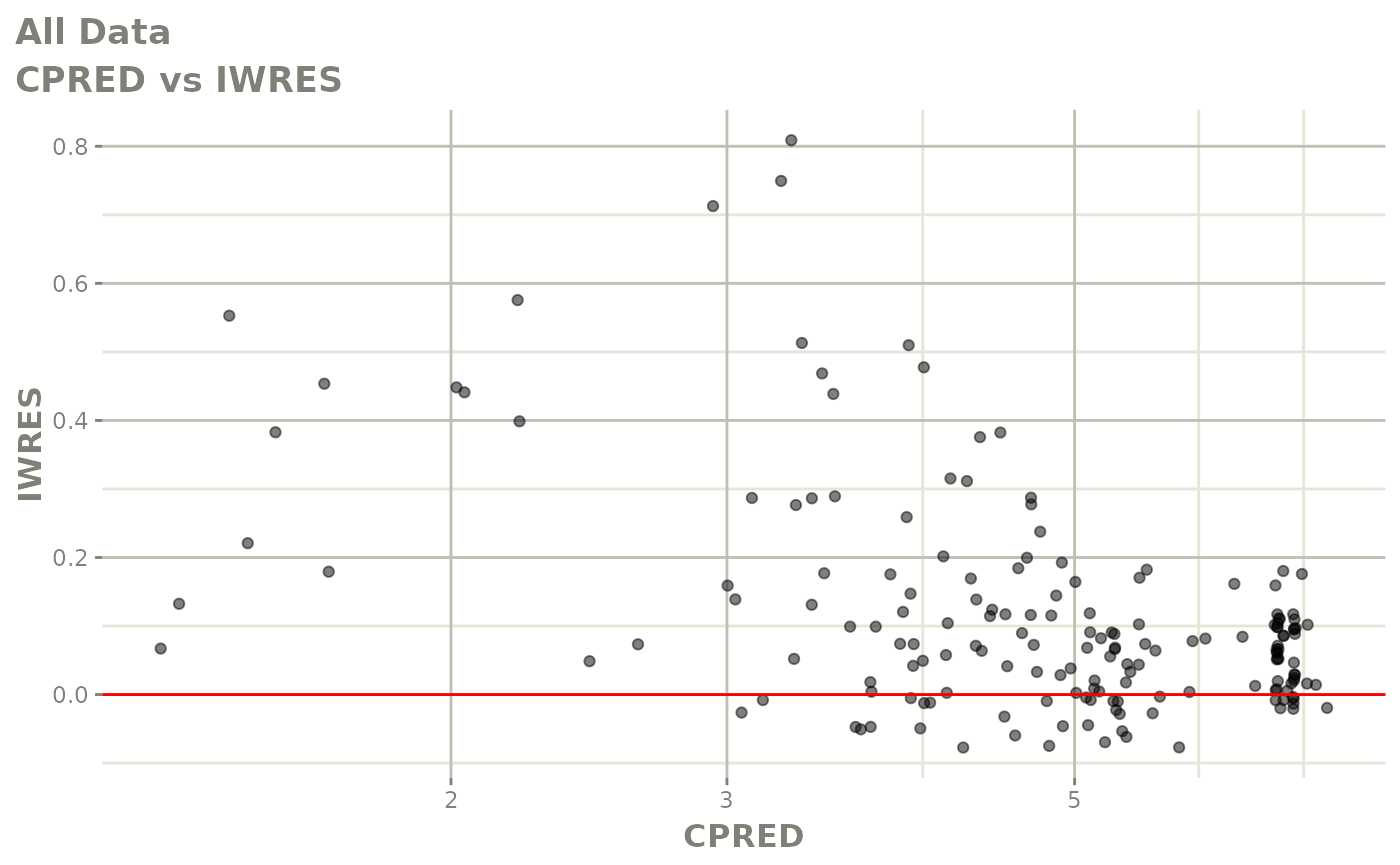
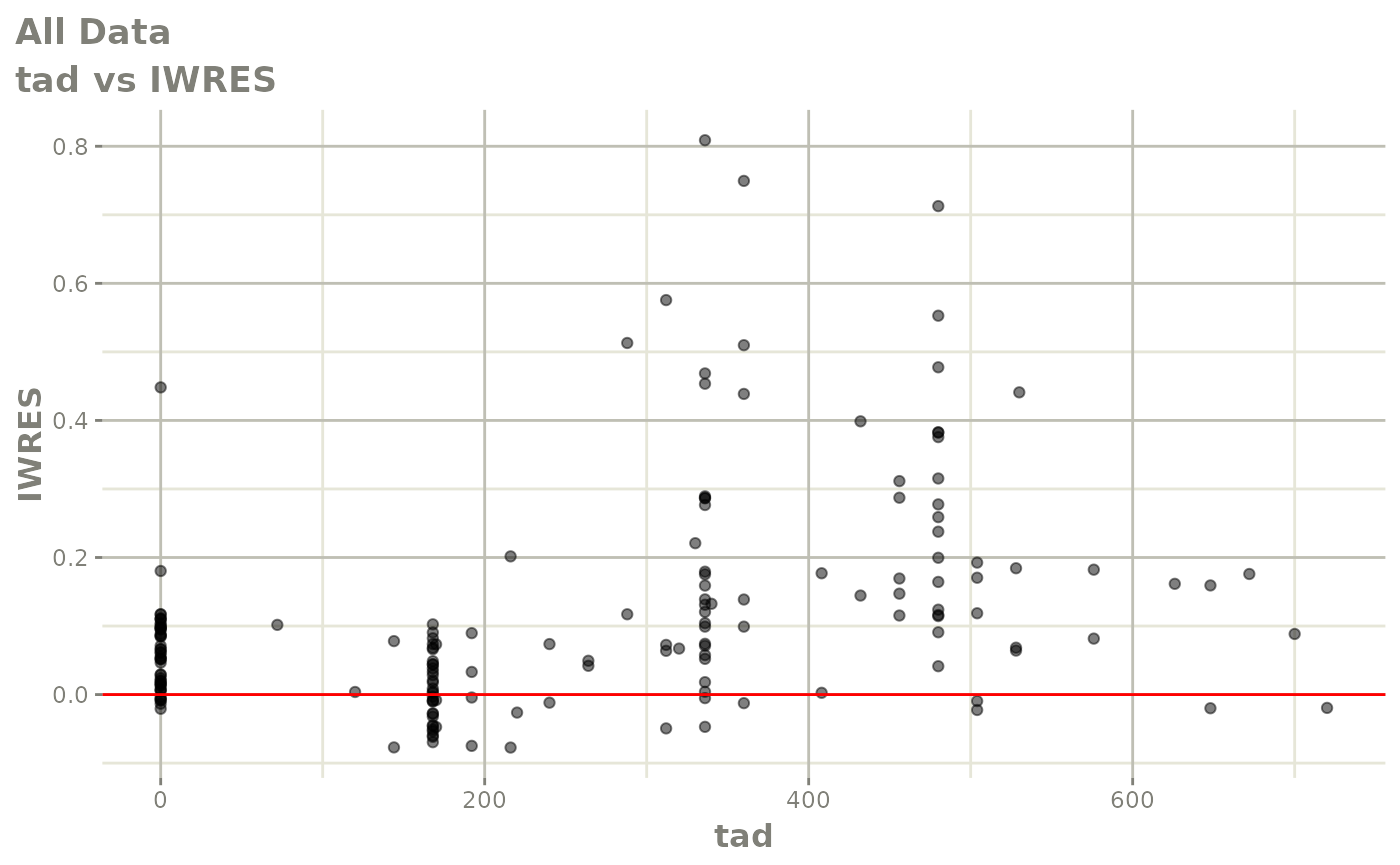
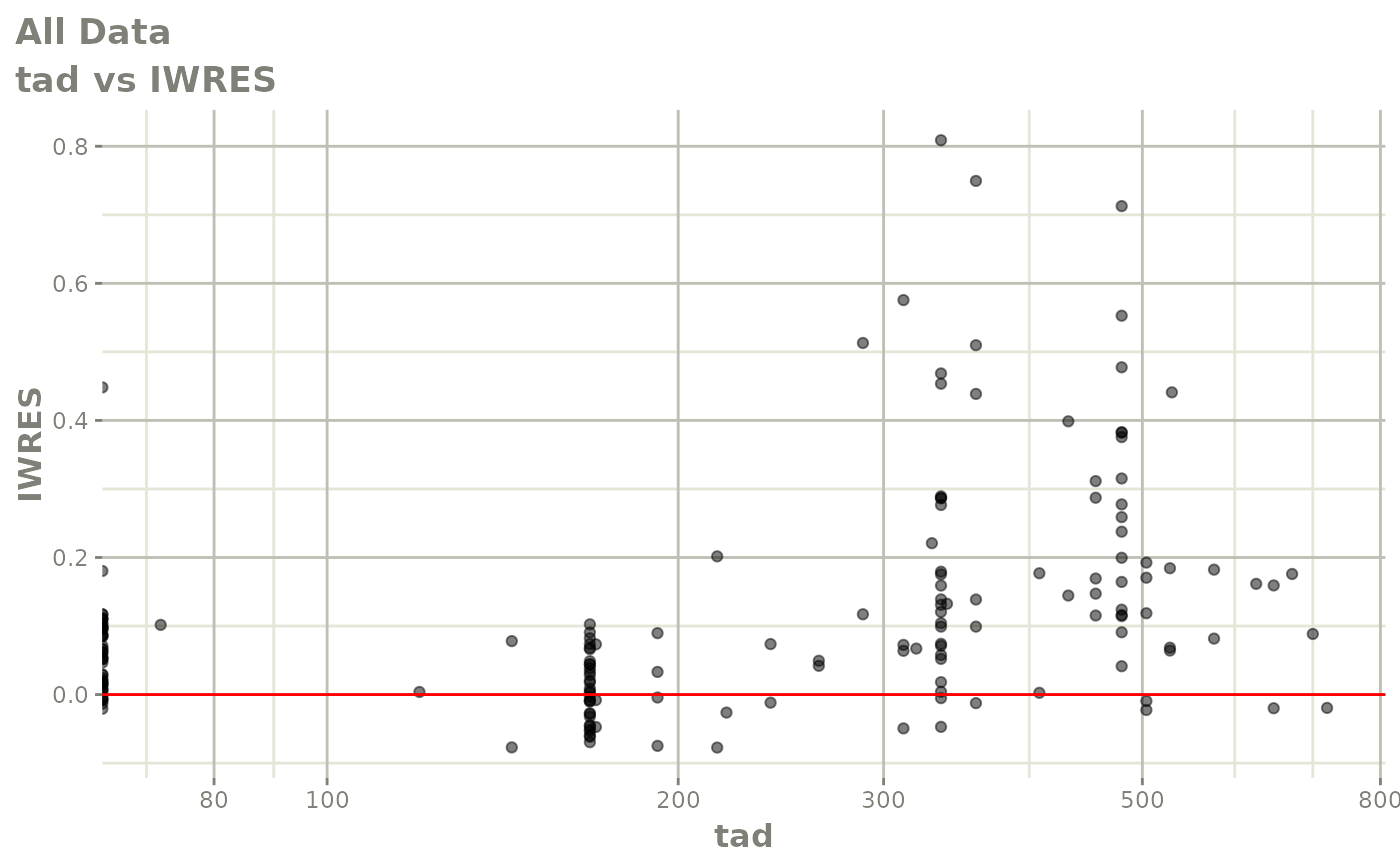
print(absval_res_vs_idv(xpdb, res = 'IWRES') +
ylab("Individual Weighted Residuals") +
xlab("Time (h)"))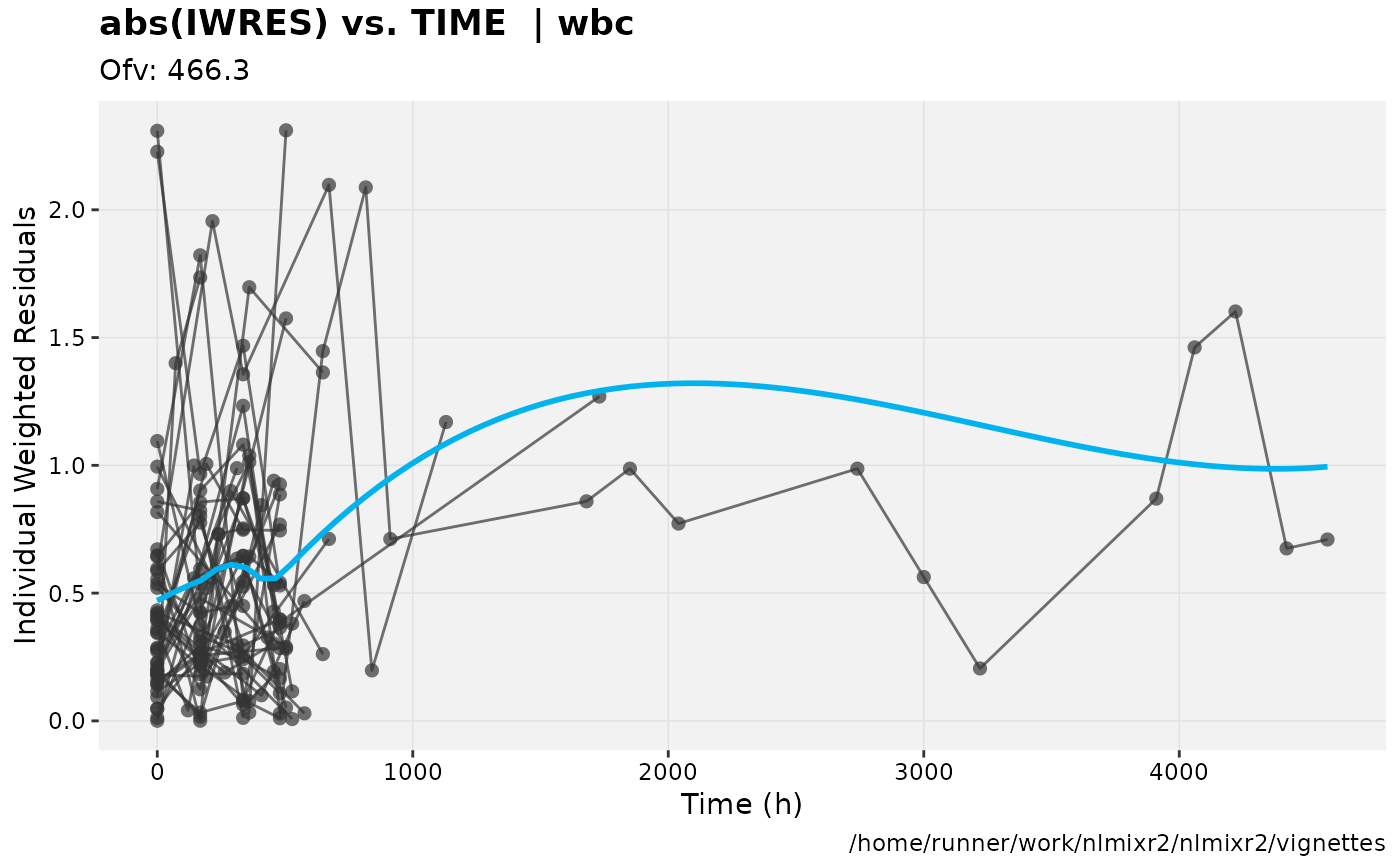
print(absval_res_vs_pred(xpdb, res = 'IWRES') +
ylab("Individual Weighted Residuals") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))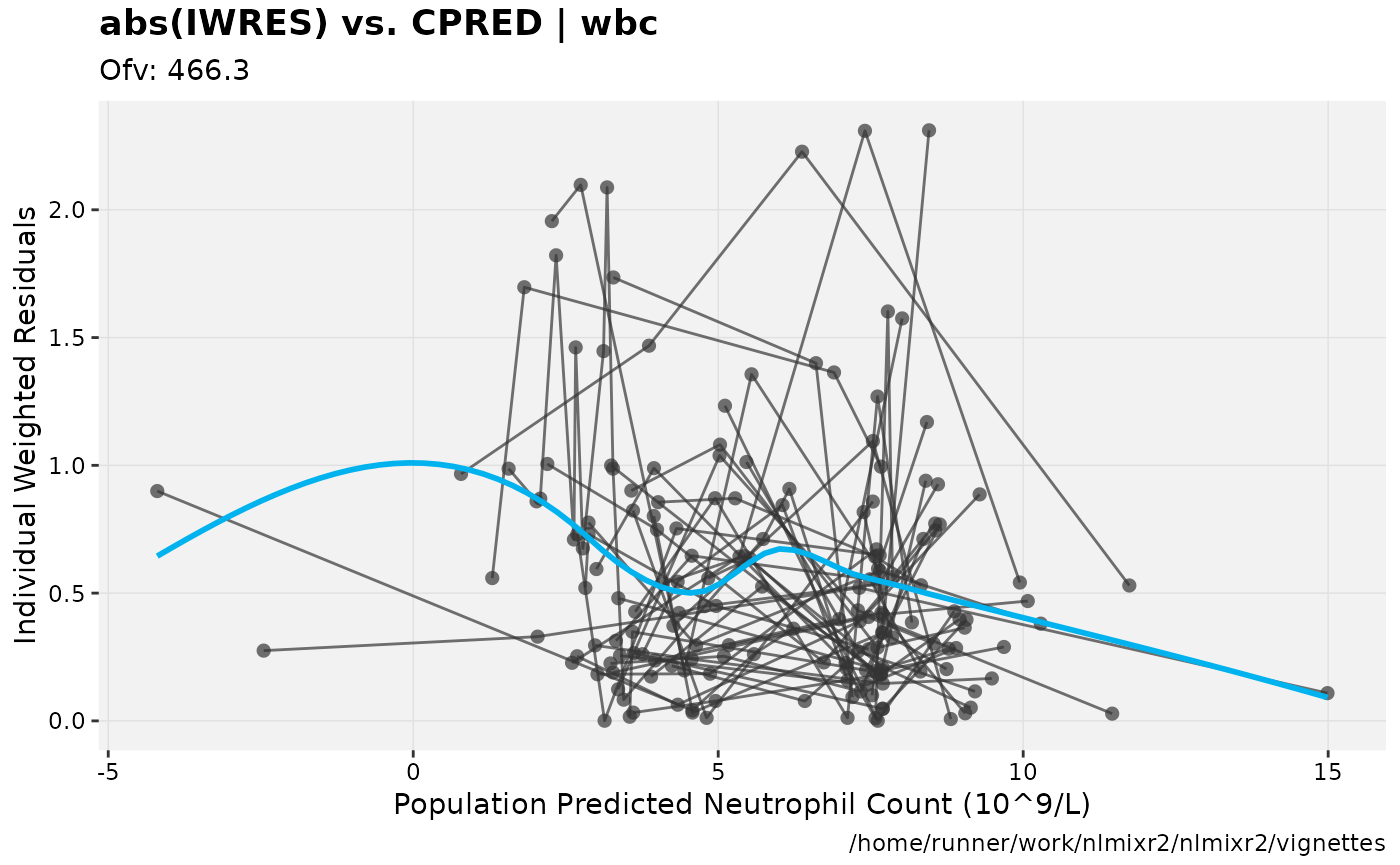
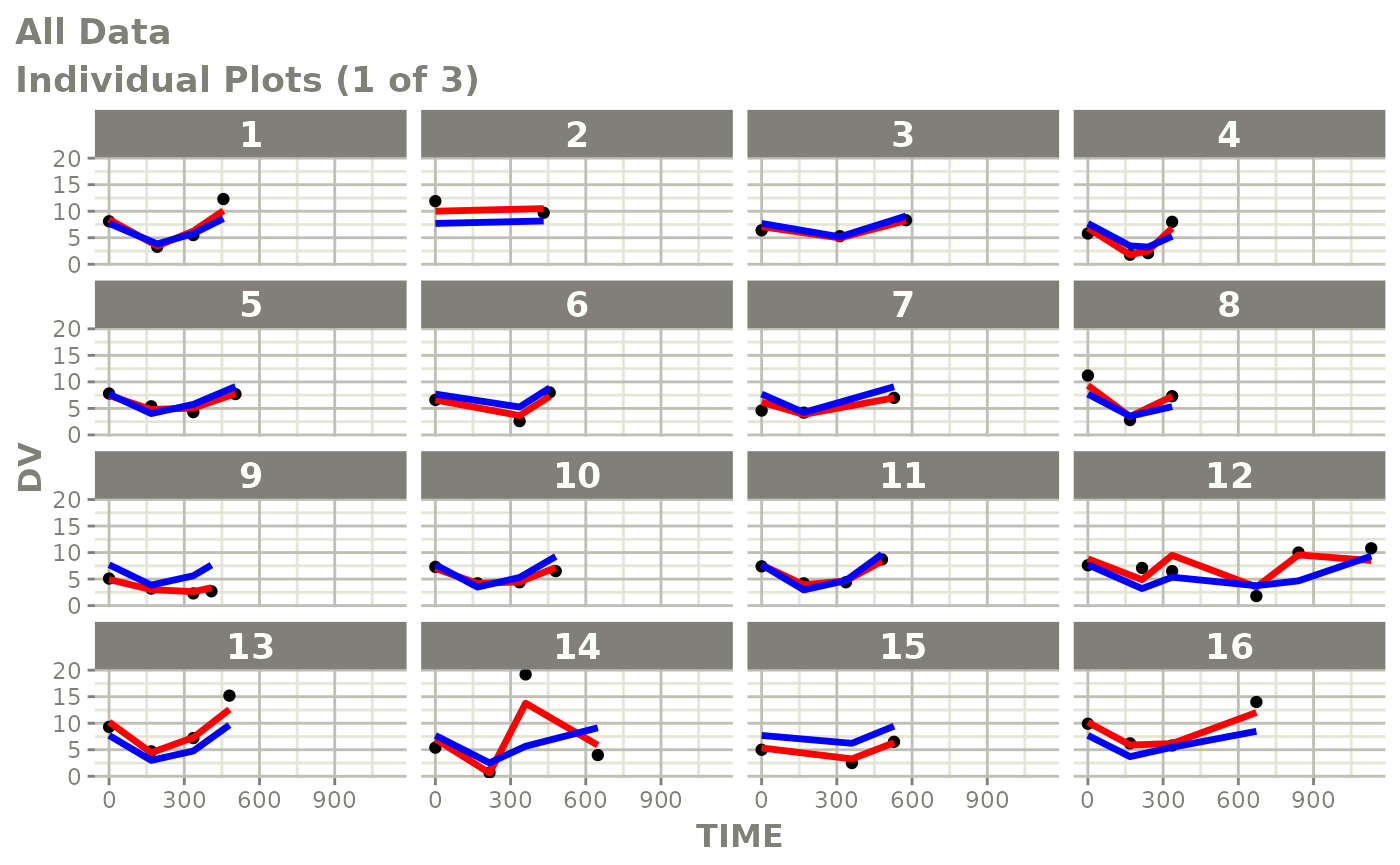
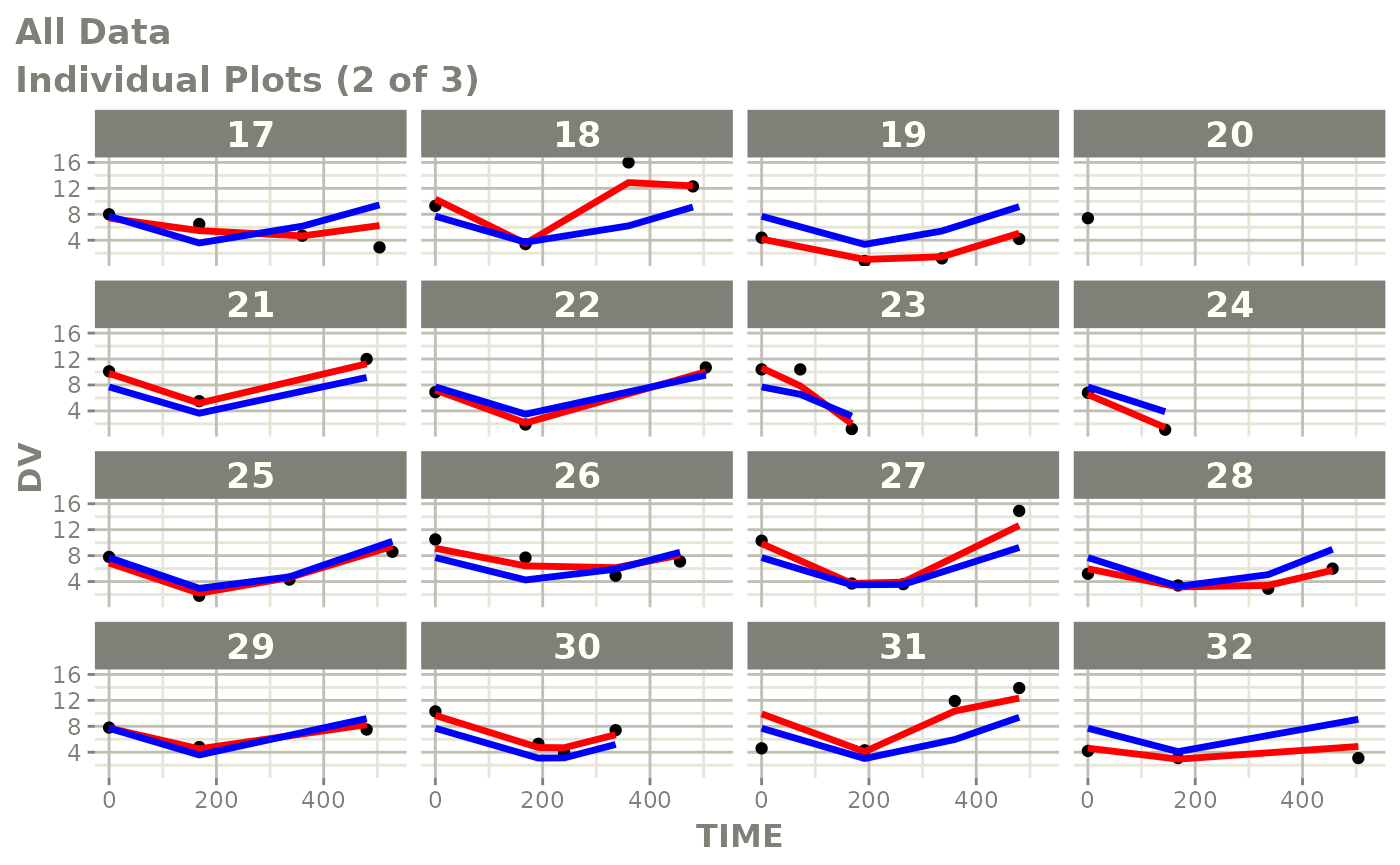
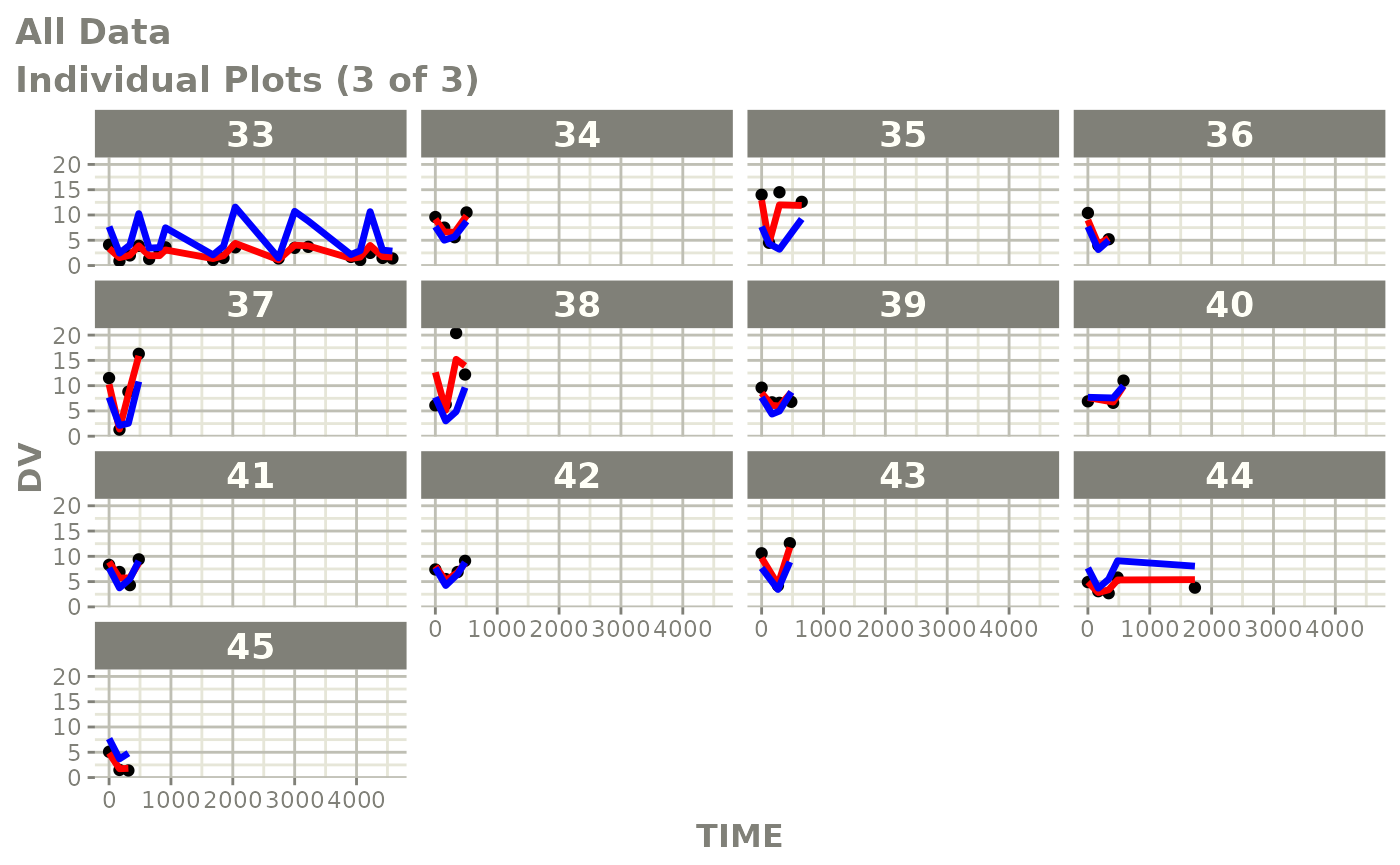
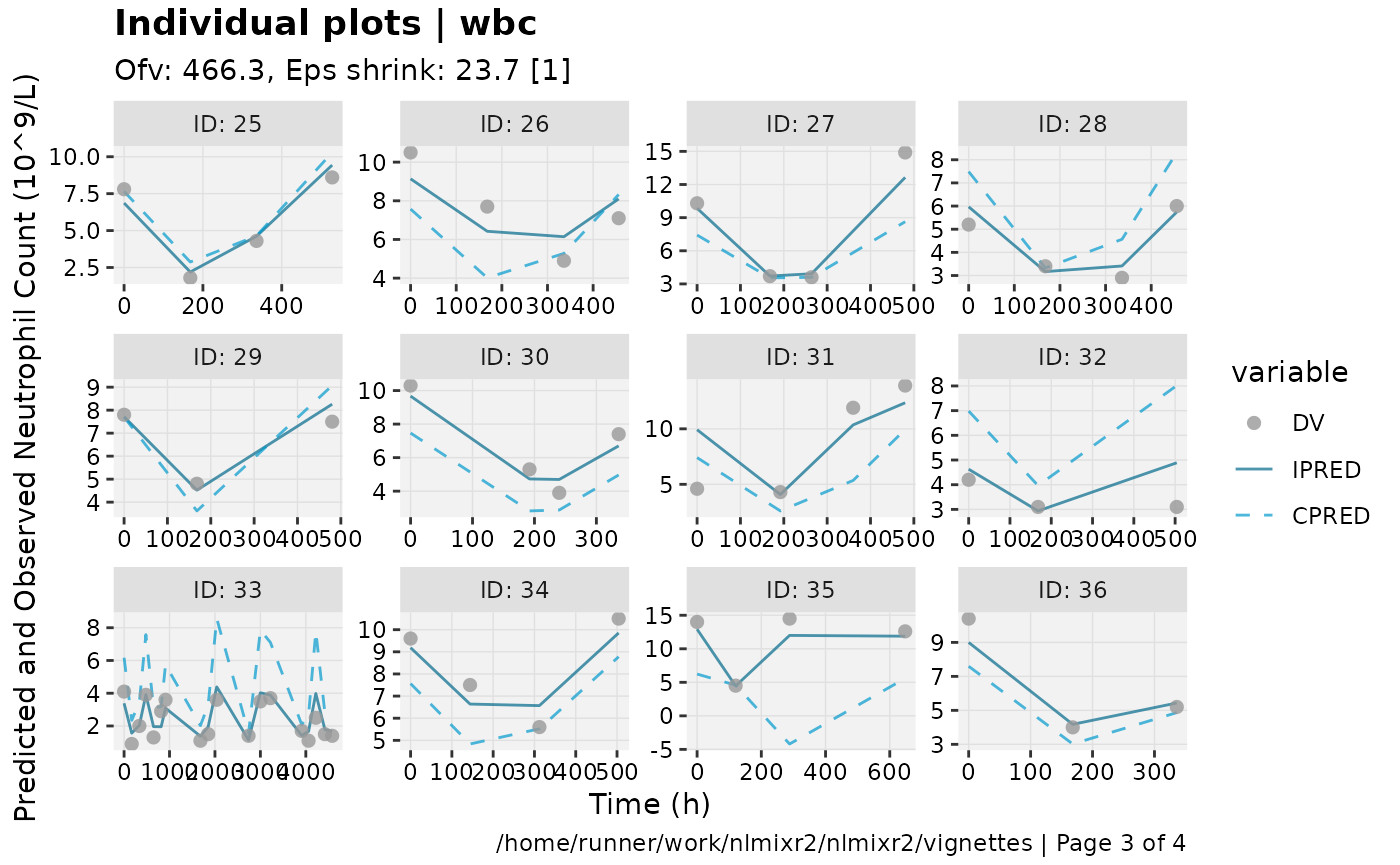
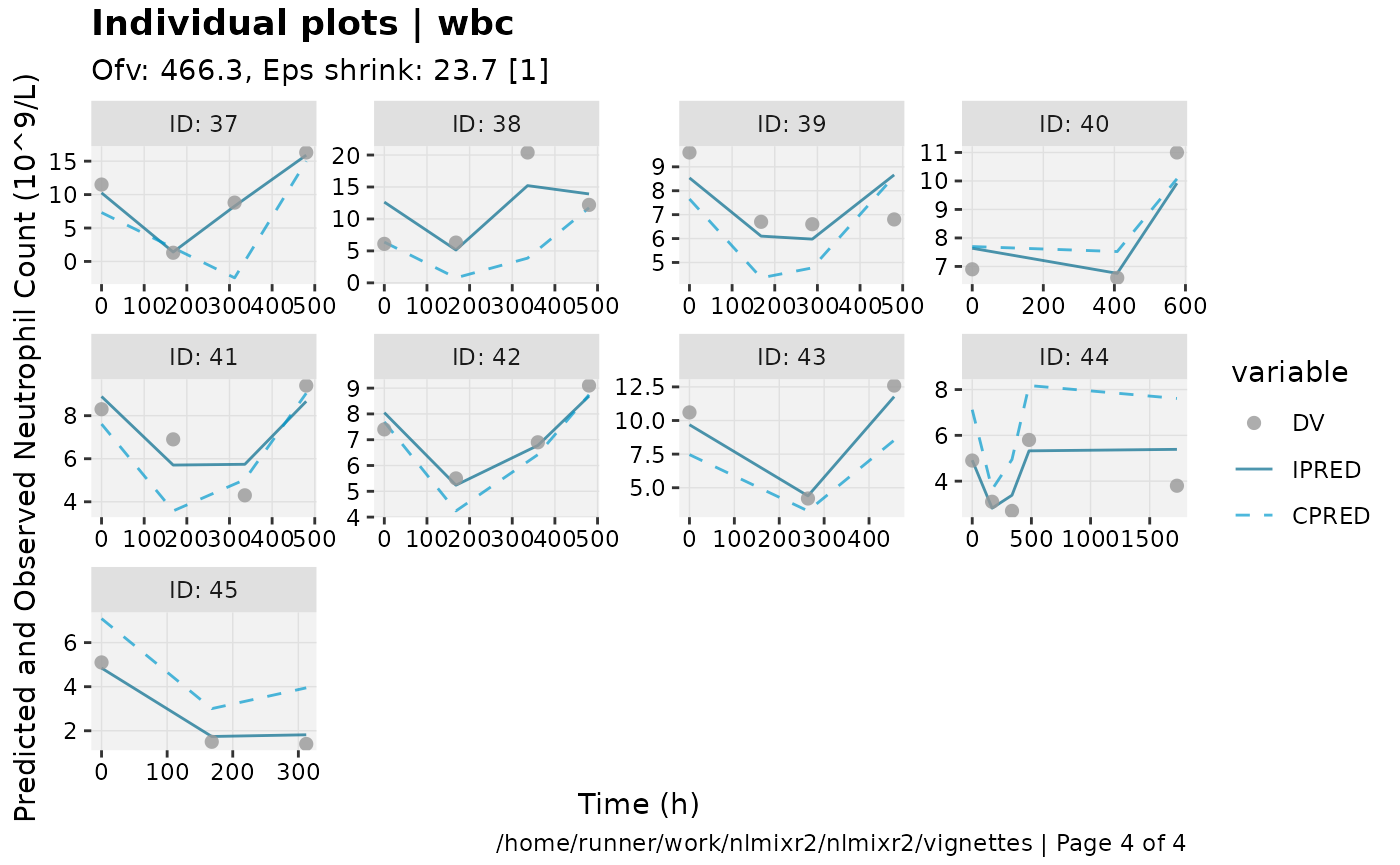
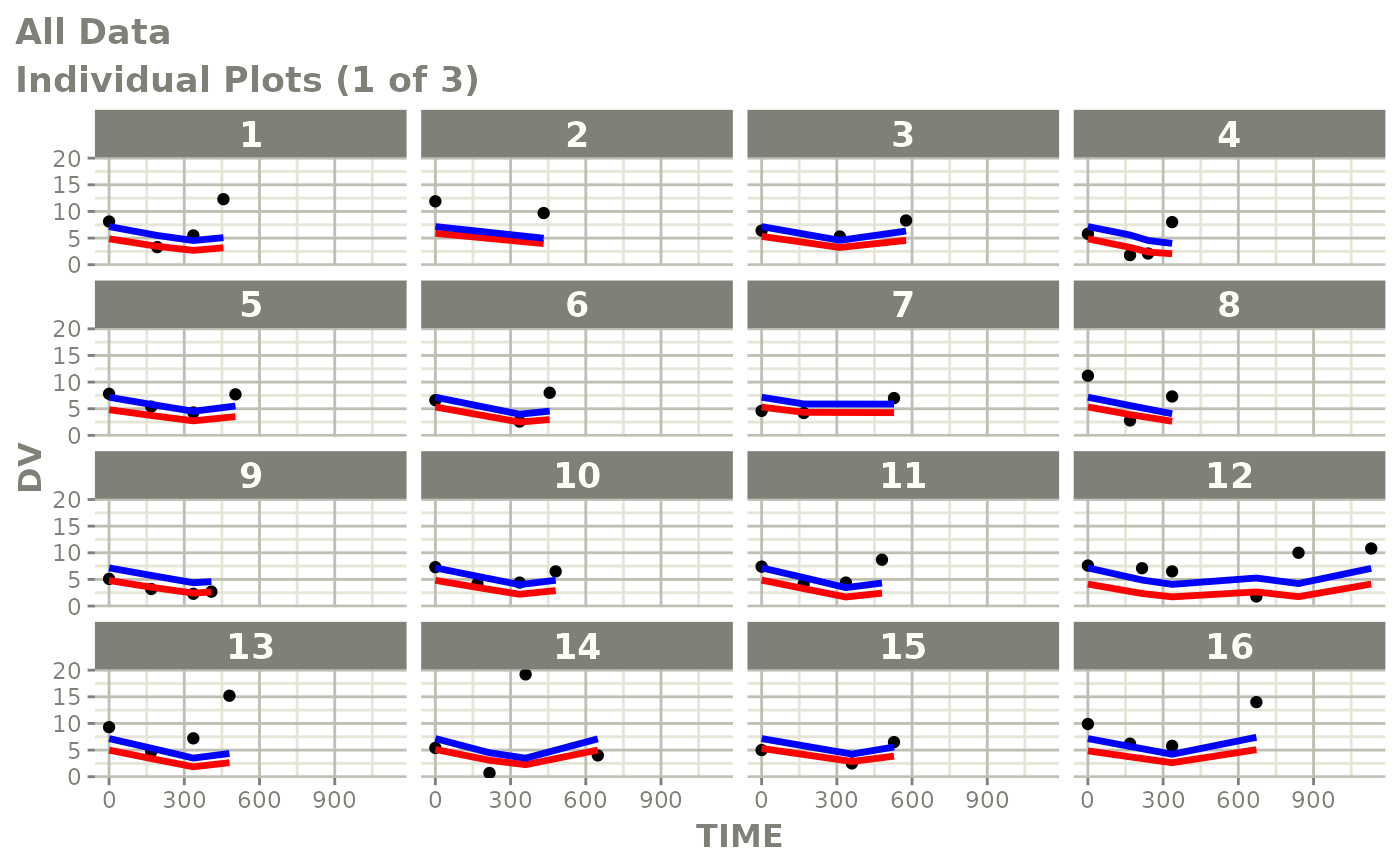
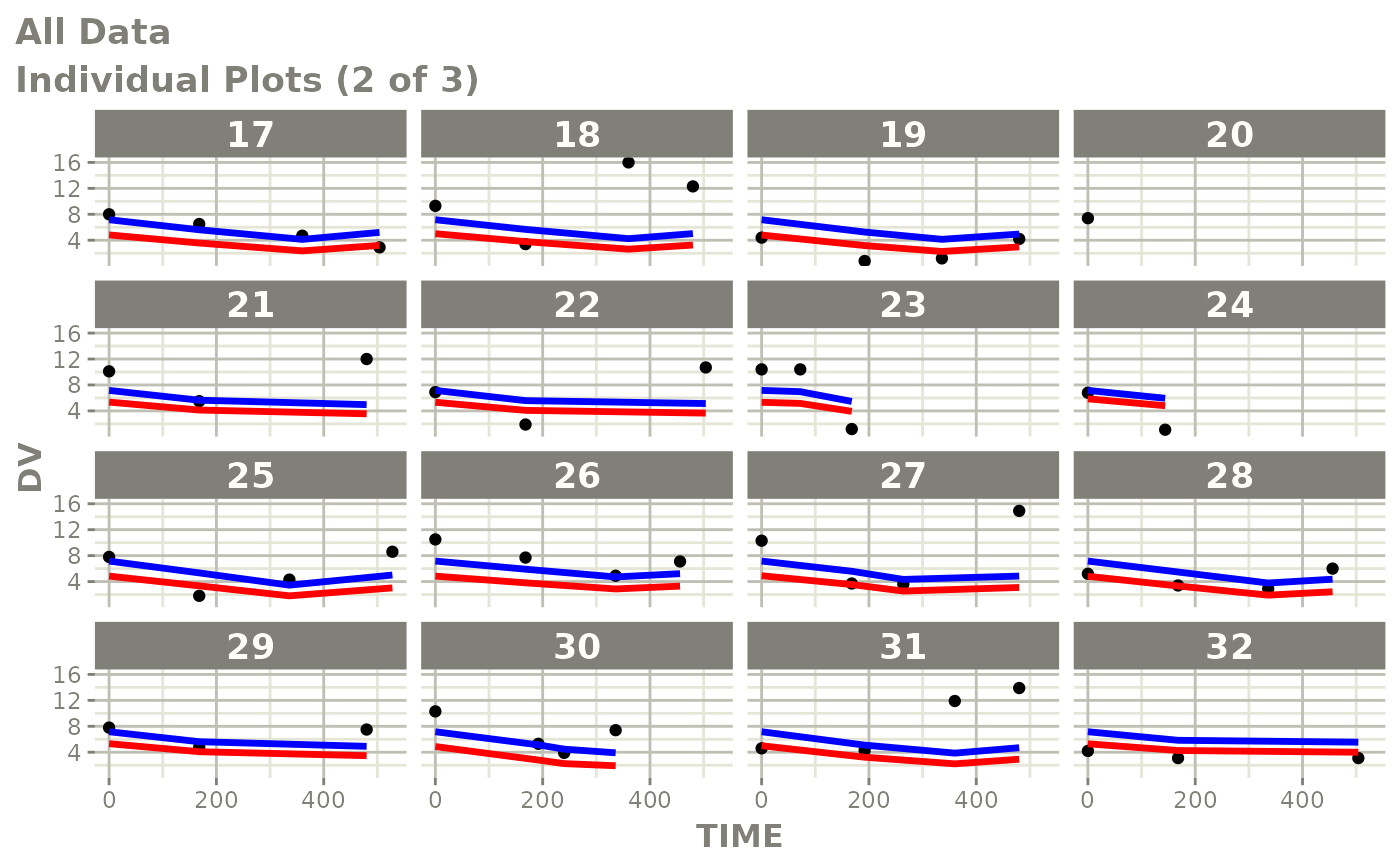
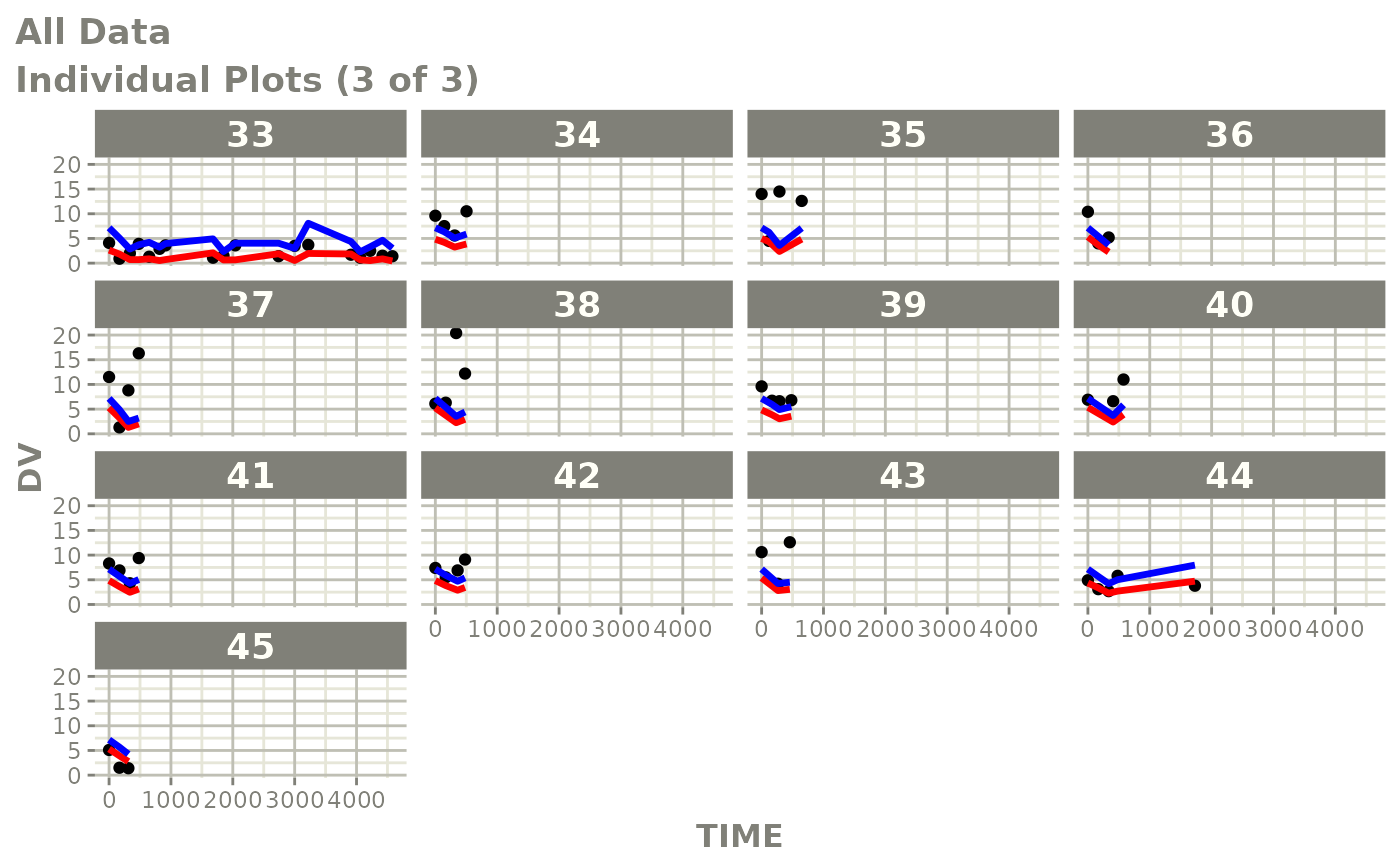
print(ind_plots(xpdb, nrow=3, ncol=4) +
ylab("Predicted and Observed Neutrophil Count (10^9/L)") +
xlab("Time (h)"))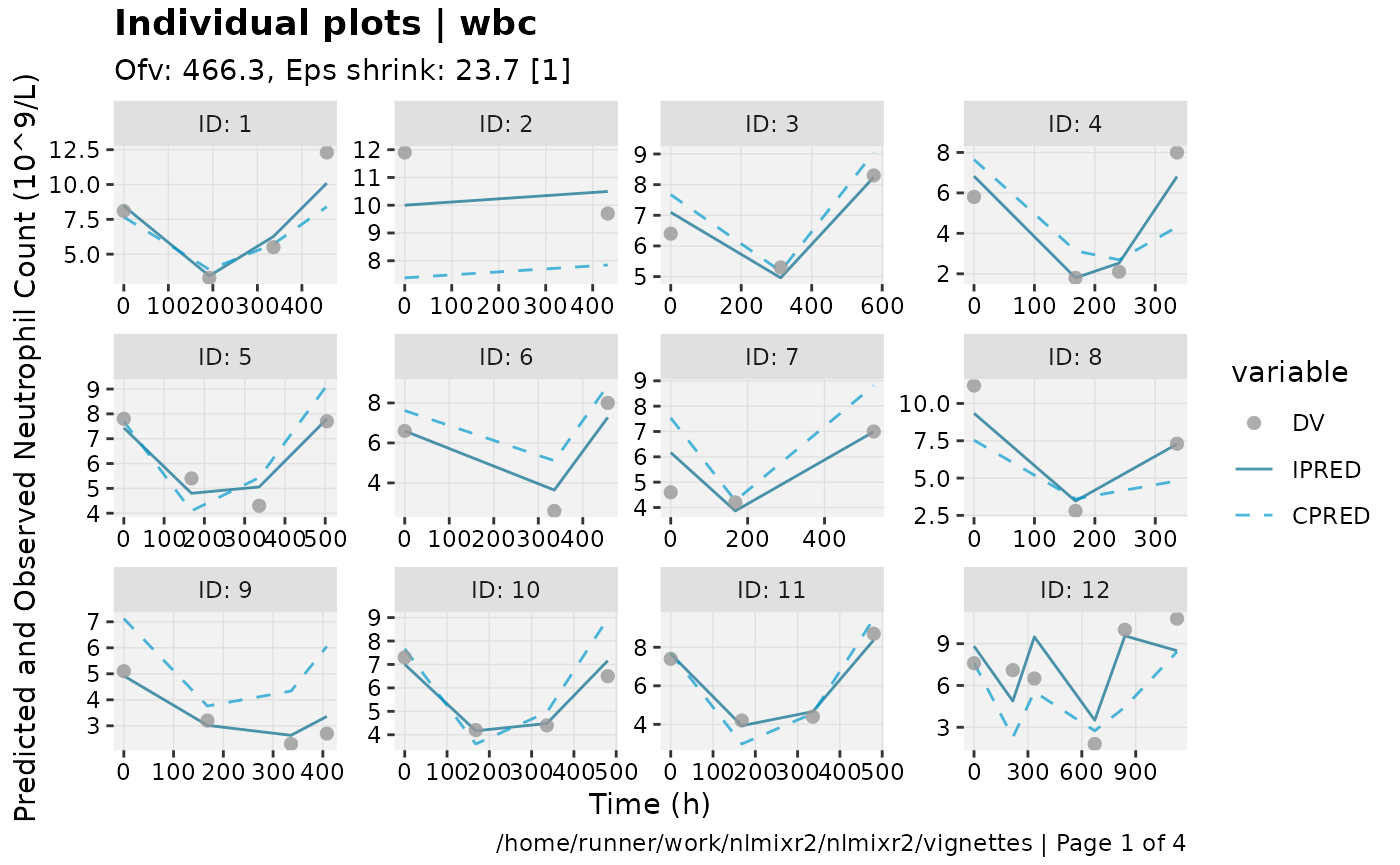
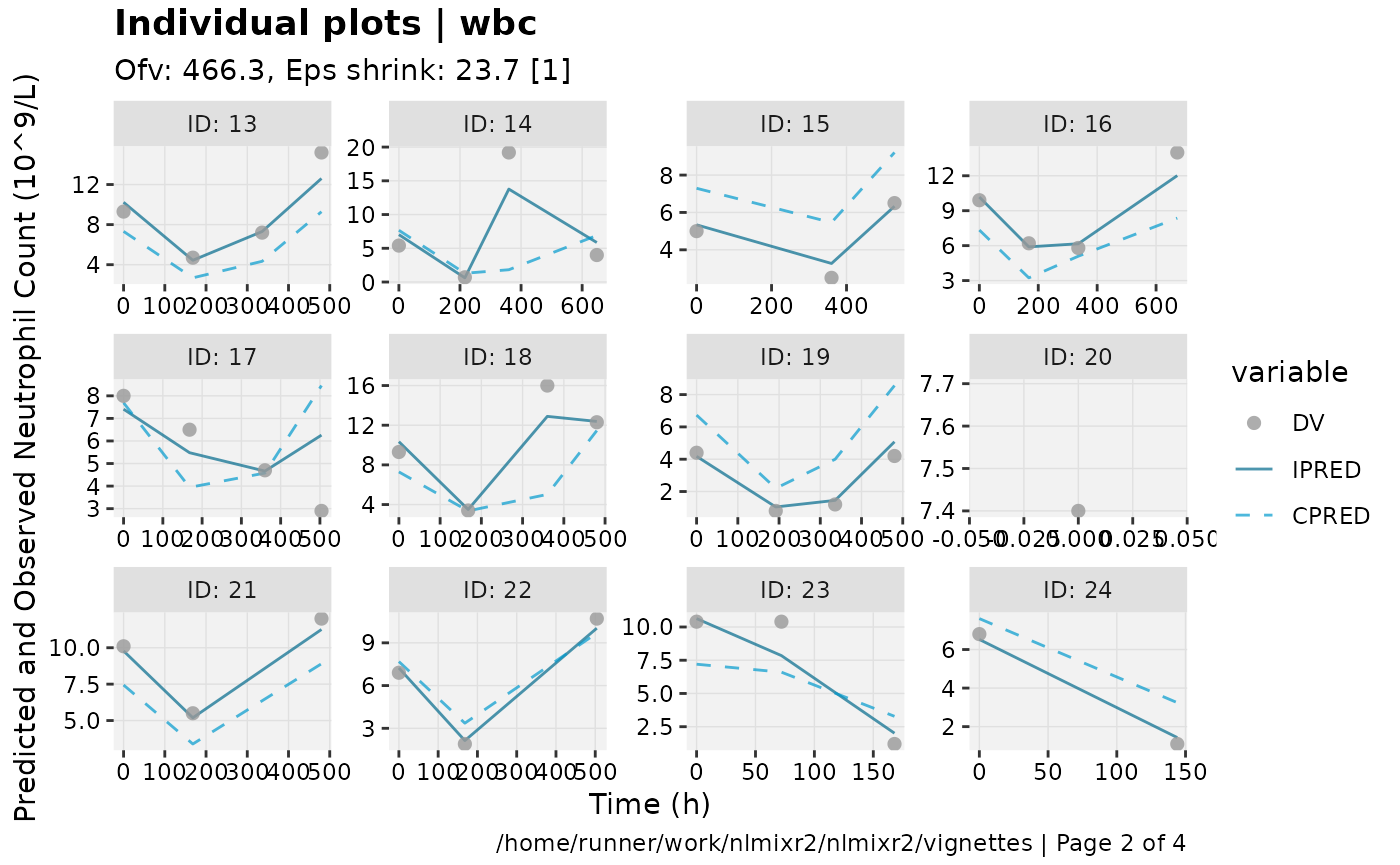
print(res_distrib(xpdb) +
ylab("Density") +
xlab("Conditional Weighted Residuals"))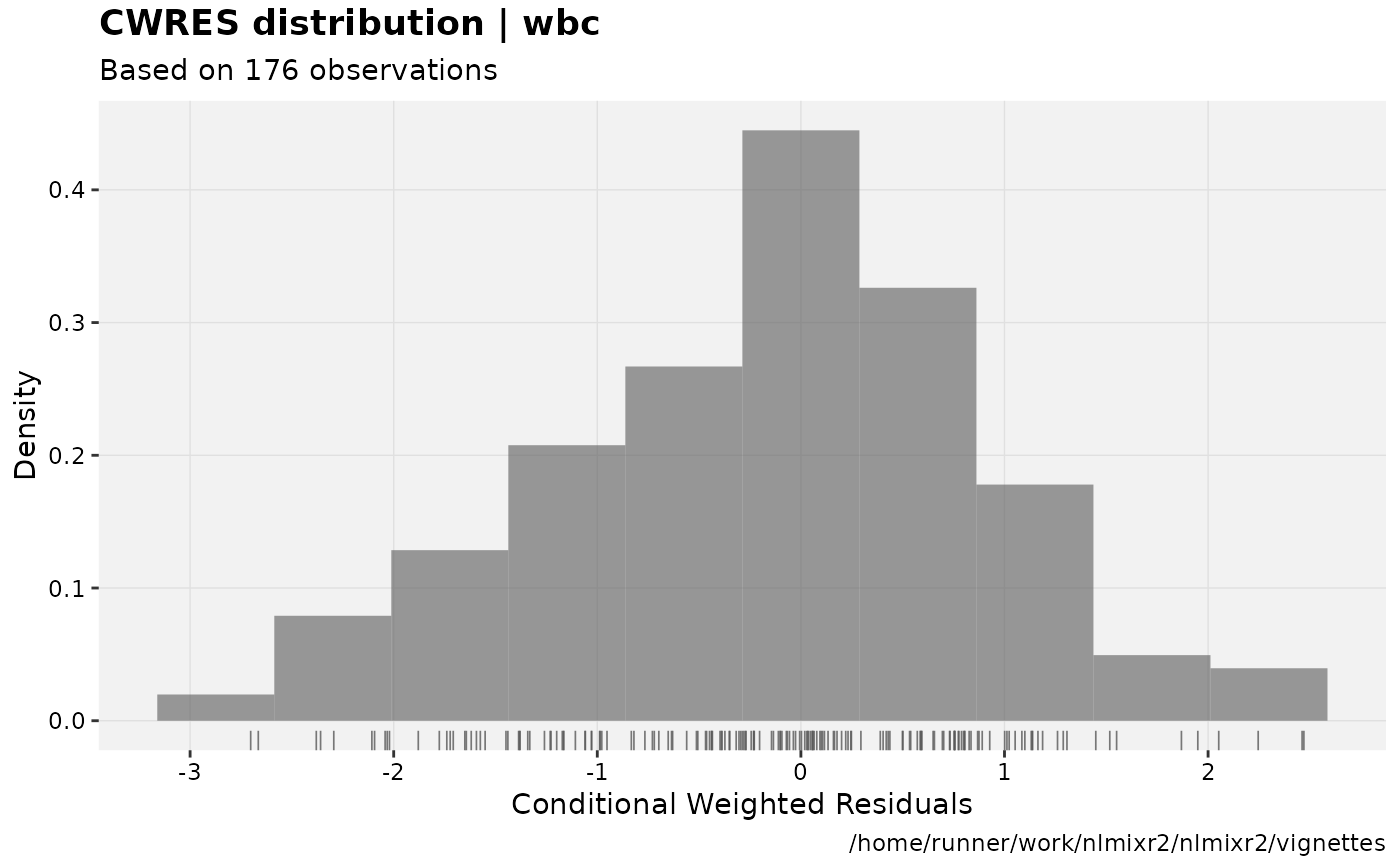
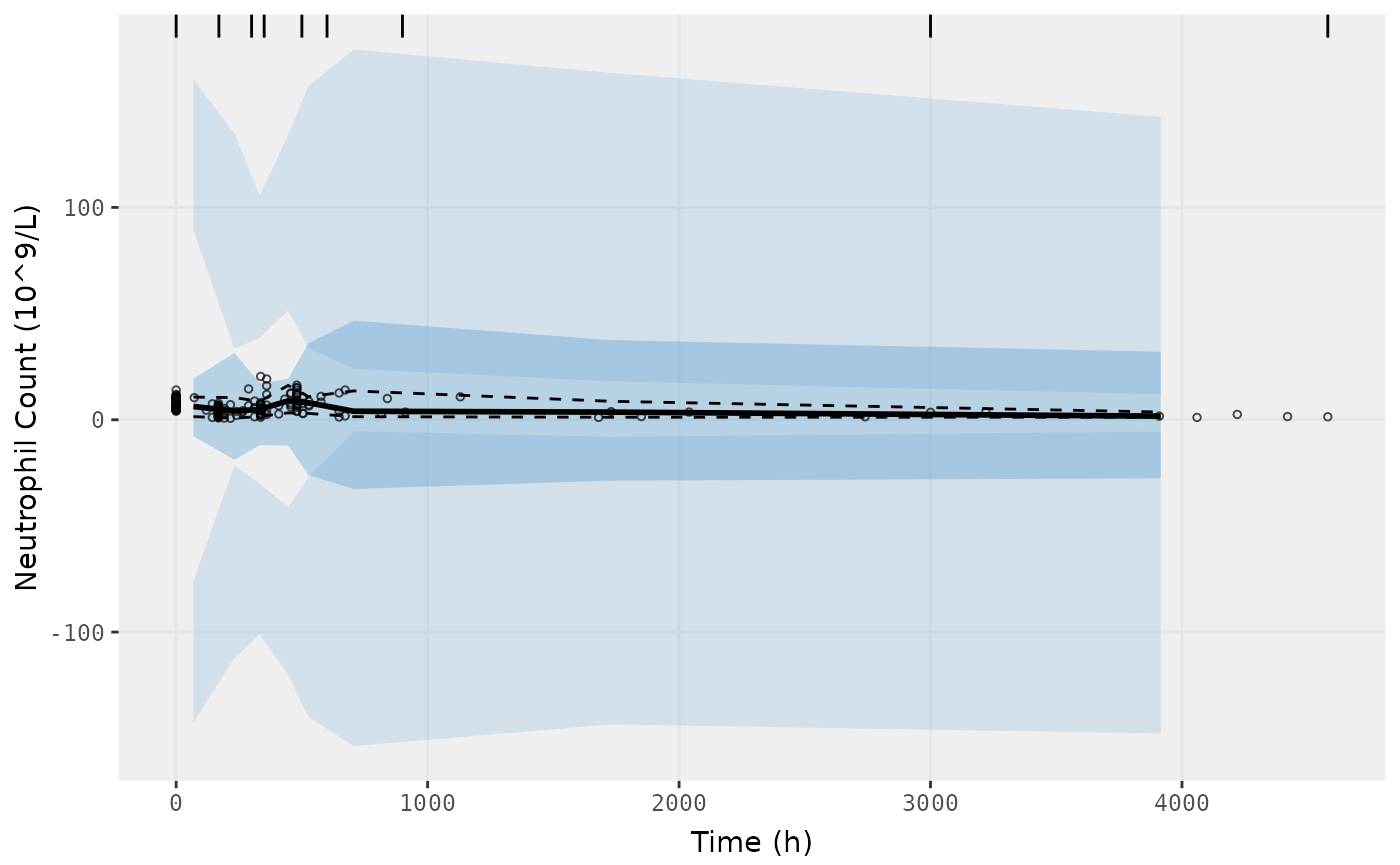
vpcPlot(fit.S, n=500, n_bins = 10, show=list(obs_dv=TRUE),
ylab = "Neutrophil Count (10^9/L)", xlab = "Time (h)")
#> [====|====|====|====|====|====|====|====|====|====] 0:00:03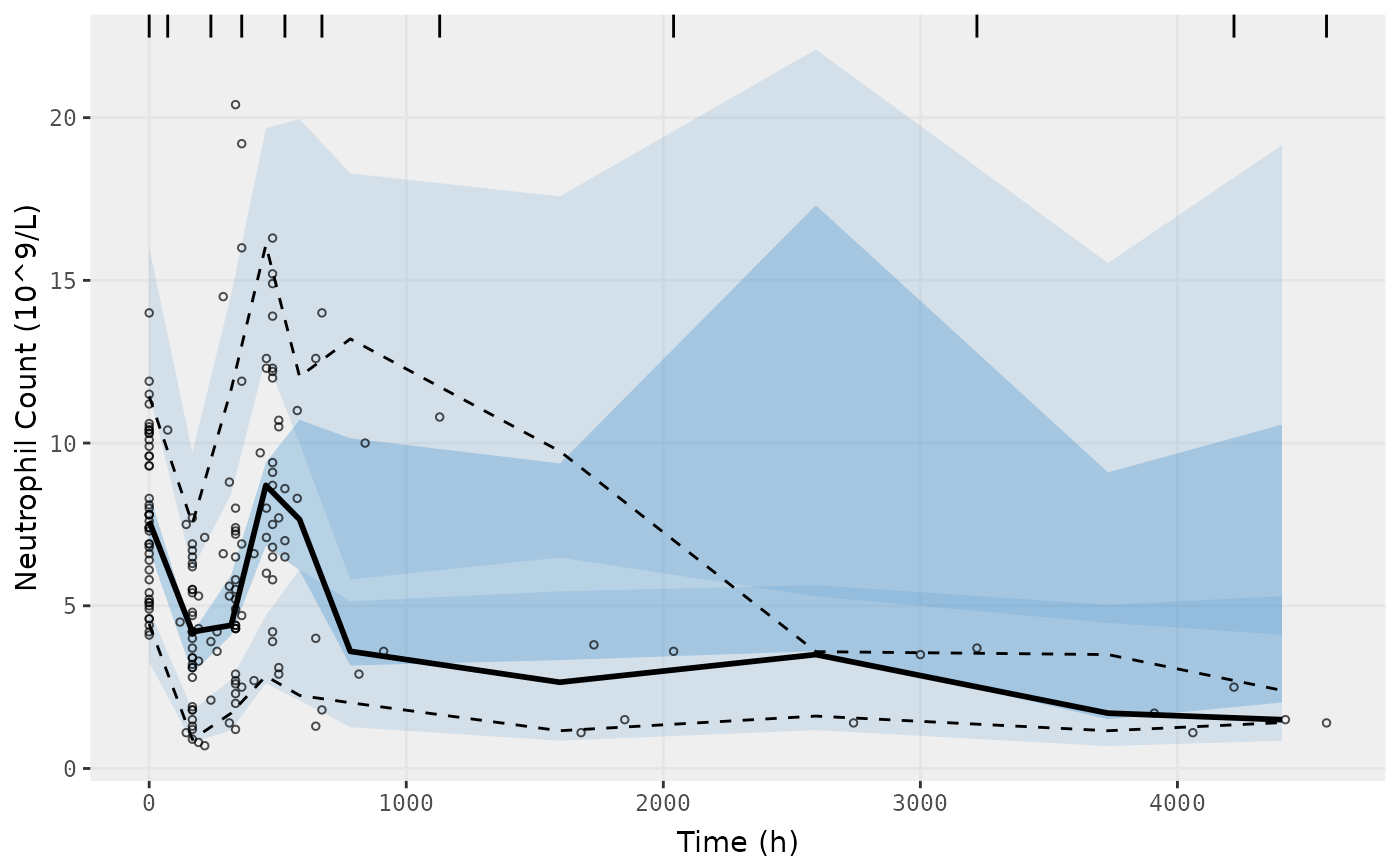
vpcPlot(fit.S, n=500, bins = c(0,170,300,350,500,600,900,3000,4580),
show=list(obs_dv=TRUE), ylab = "Neutrophil Count (10^9/L)", xlab = "Time (h)")
#> [====|====|====|====|====|====|====|====|====|====] 0:00:03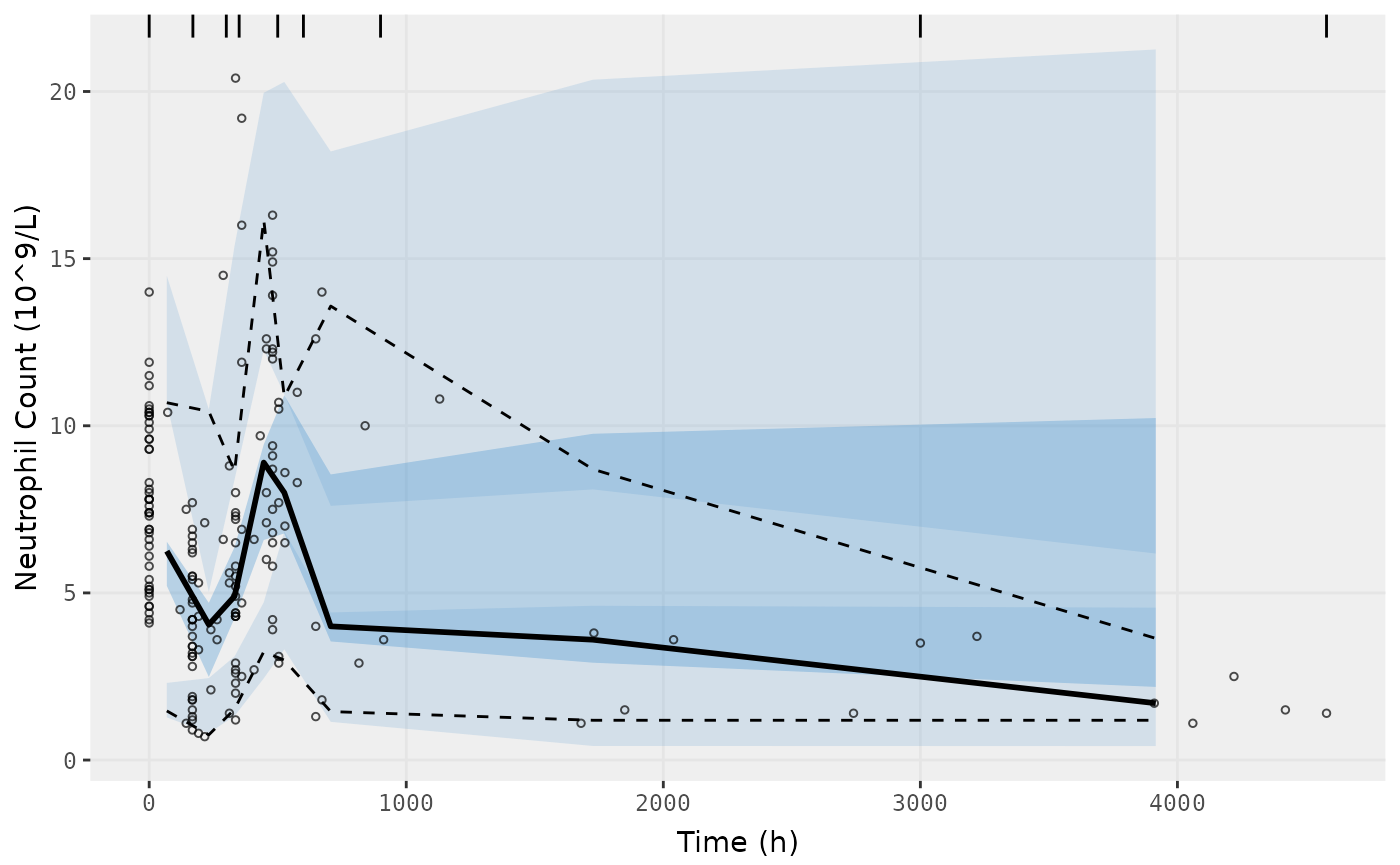
Fit model using FOCEi
fit.F <- nlmixr(wbc, d3, est="focei", list(print=0), table=list(cwres=TRUE, npde=TRUE))
#> calculating covariance matrix
#> [====|====|====|====|====|====|====|====|====|====] 0:00:23
#> done
#> [====|====|====|====|====|====|====|====|====|====] 0:00:02FOCEi goodness of fit plots
xpdb <- xpose_data_nlmixr(fit.F)
plot(fit.F)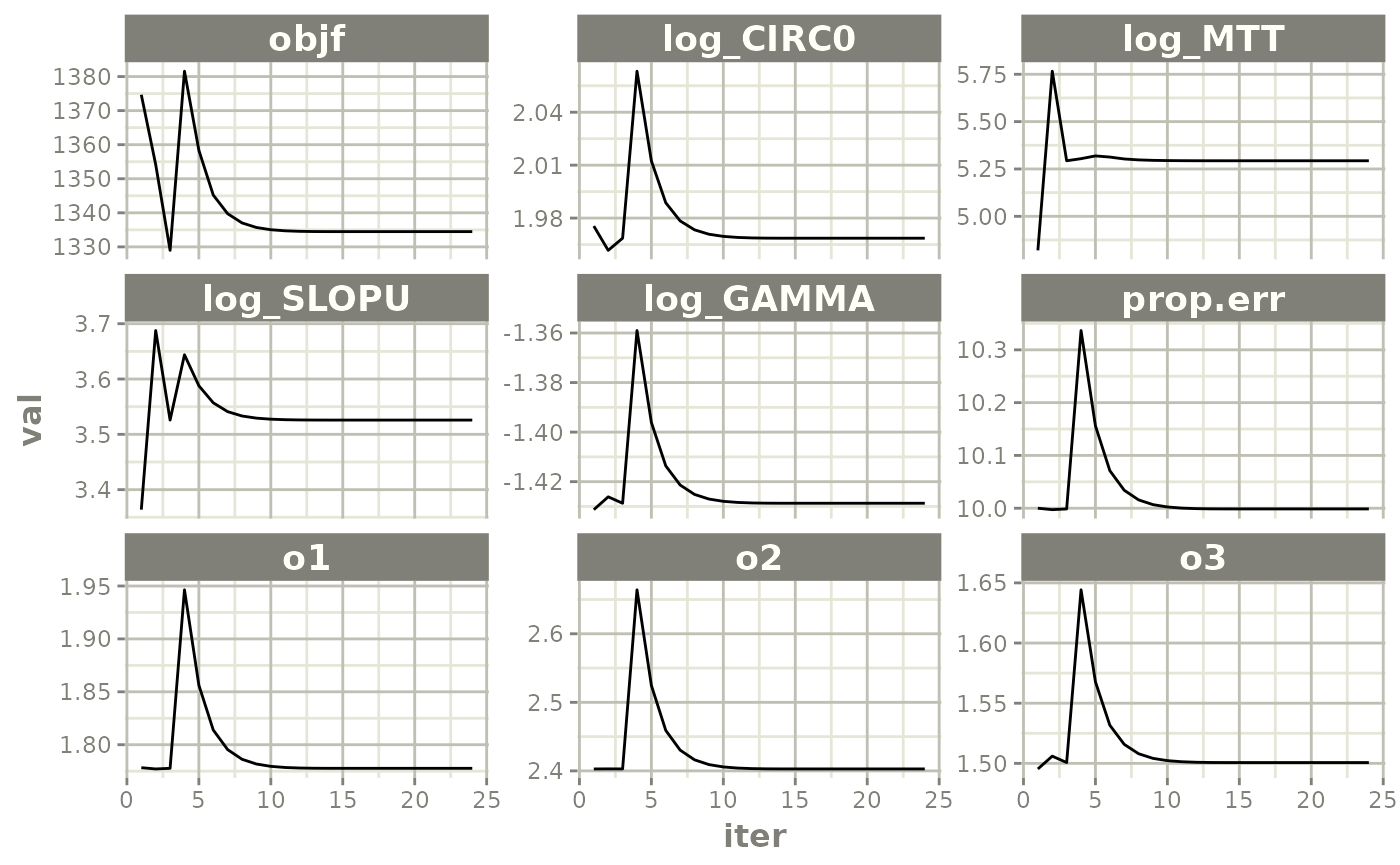
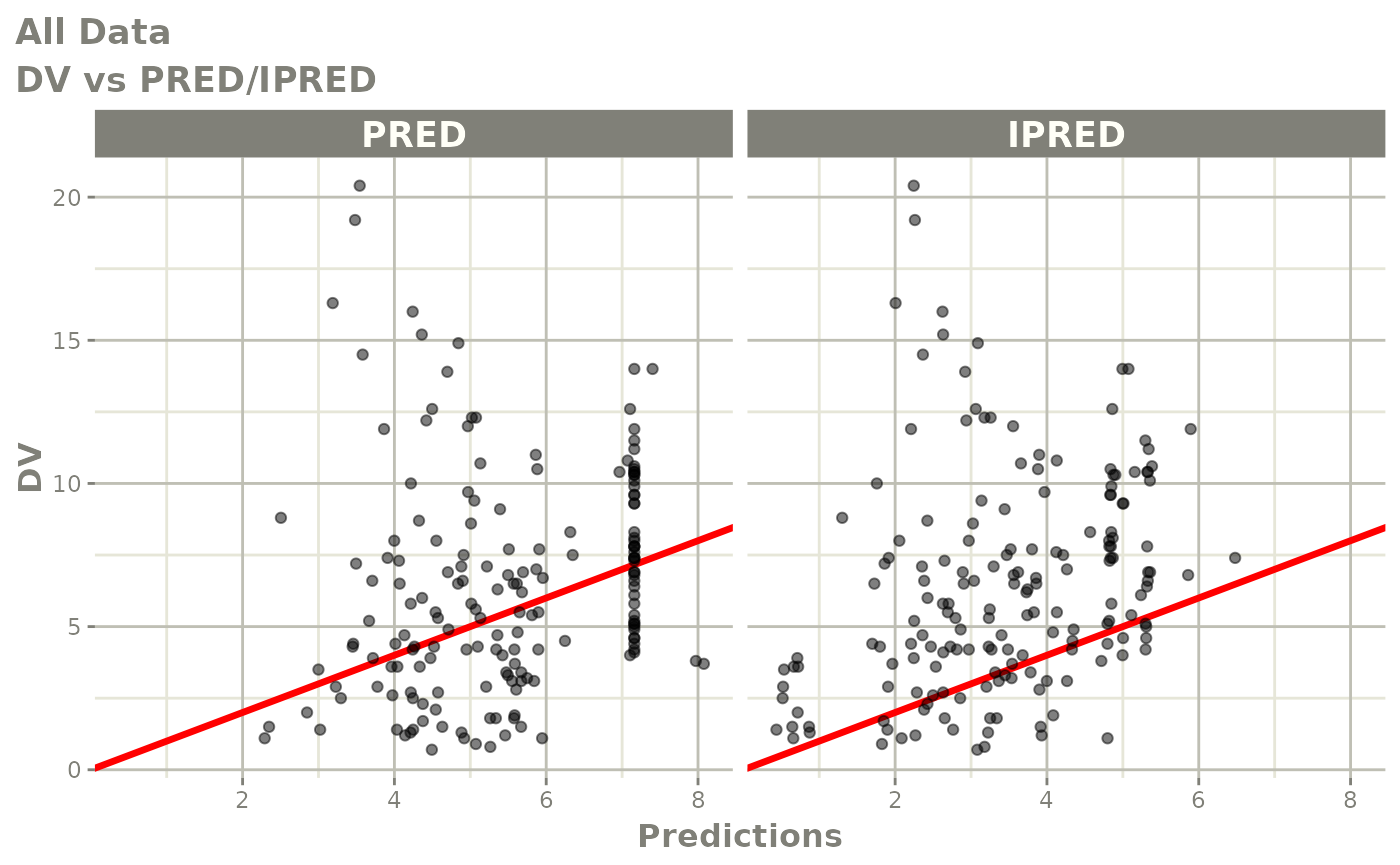
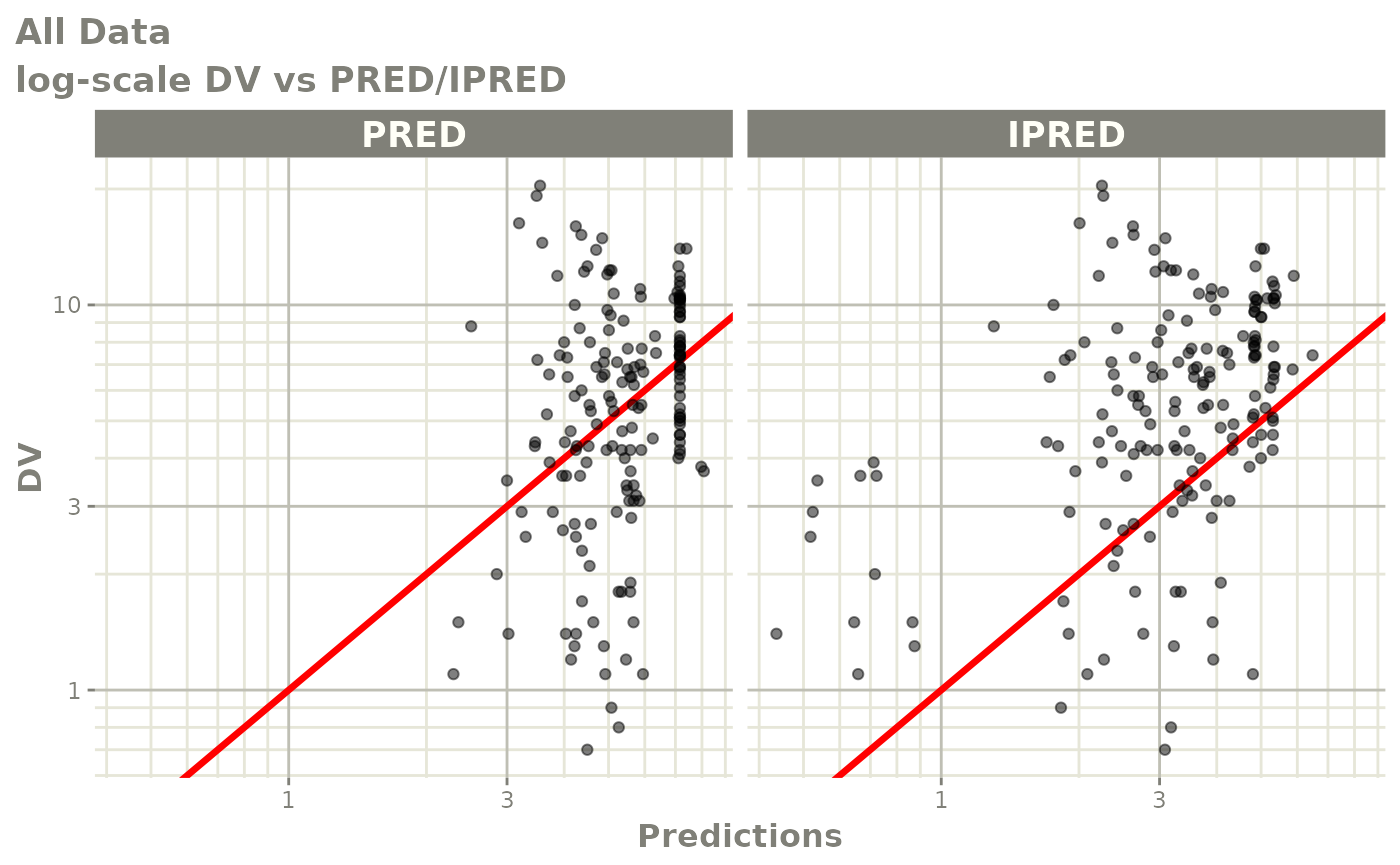
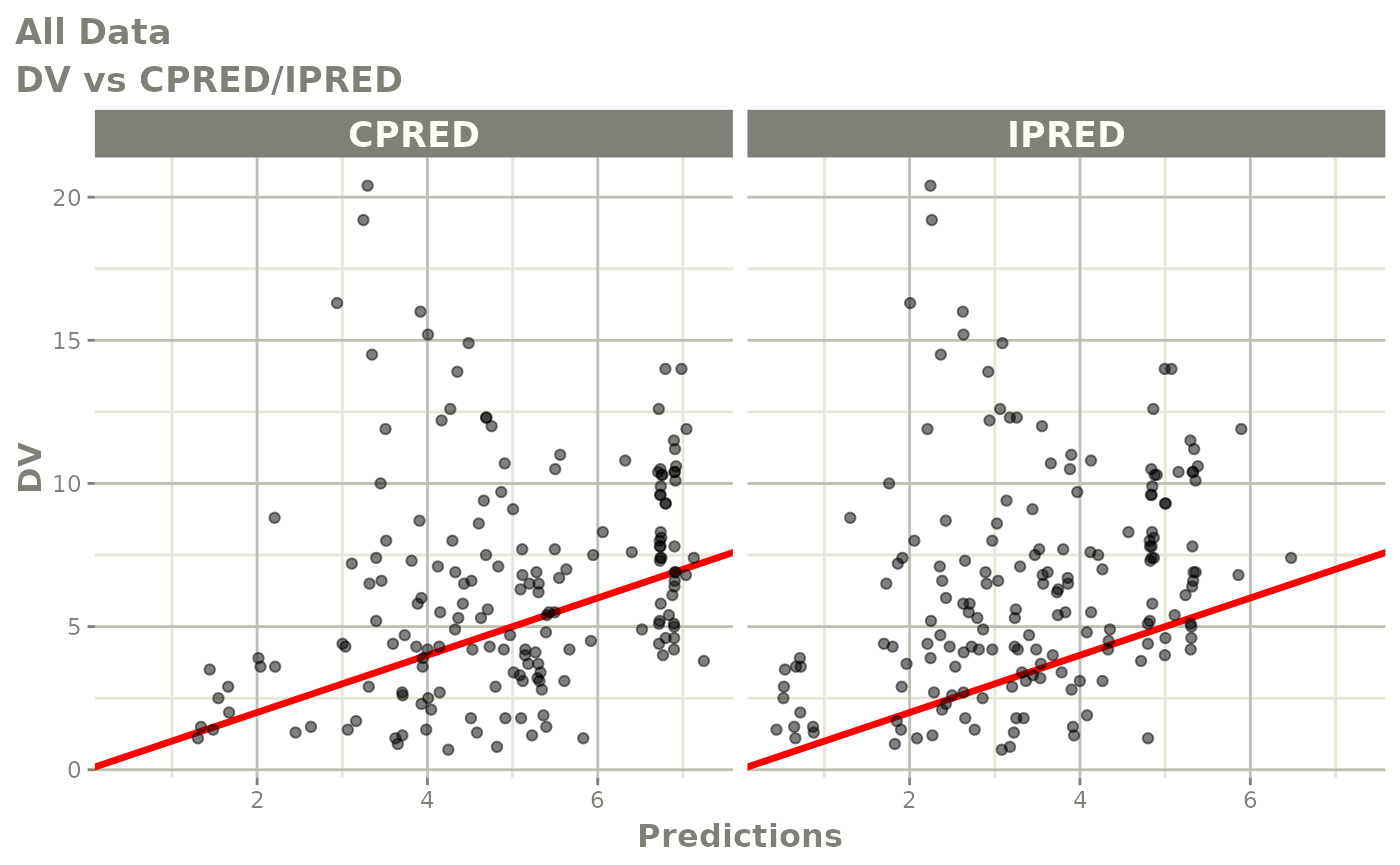
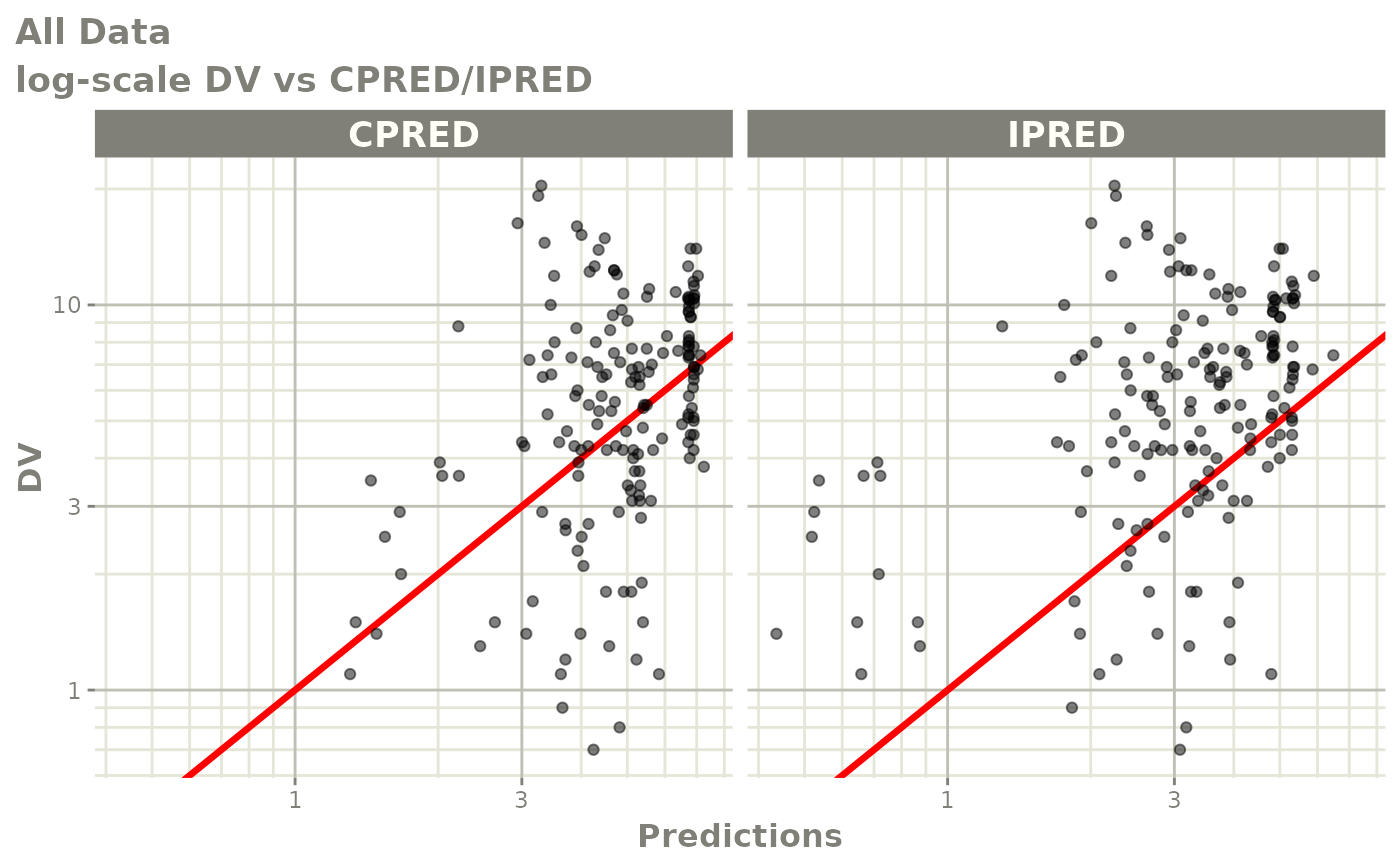
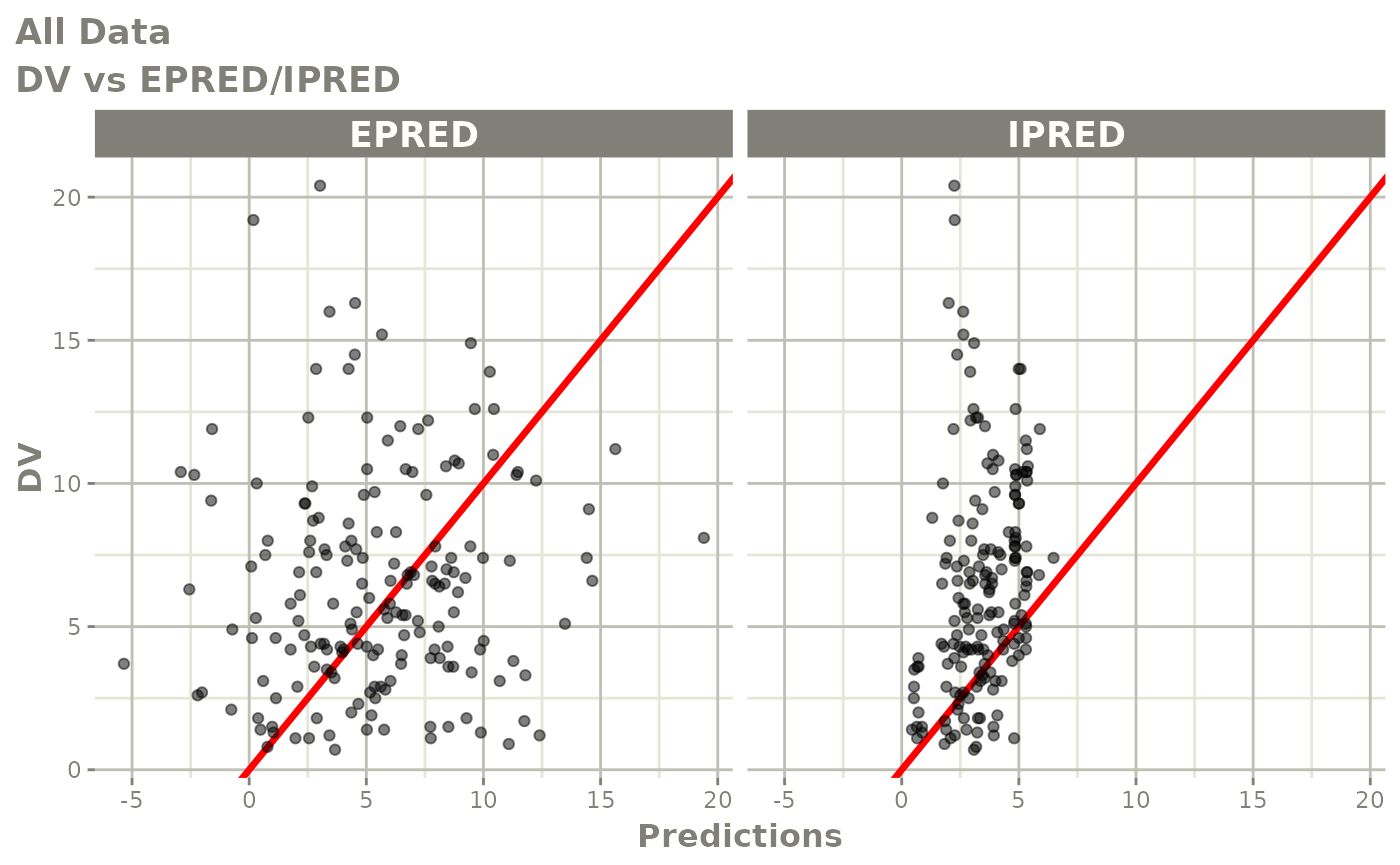
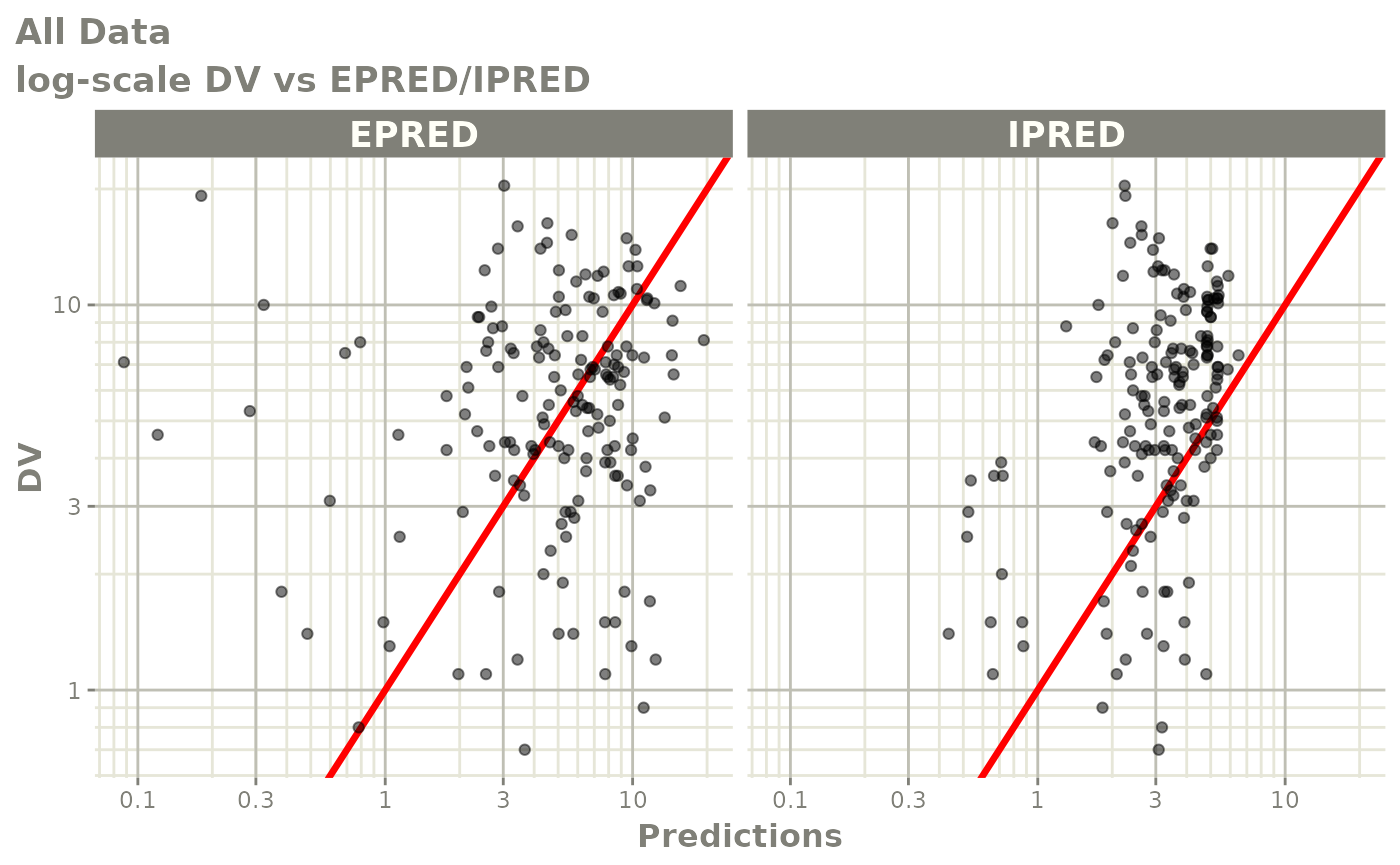
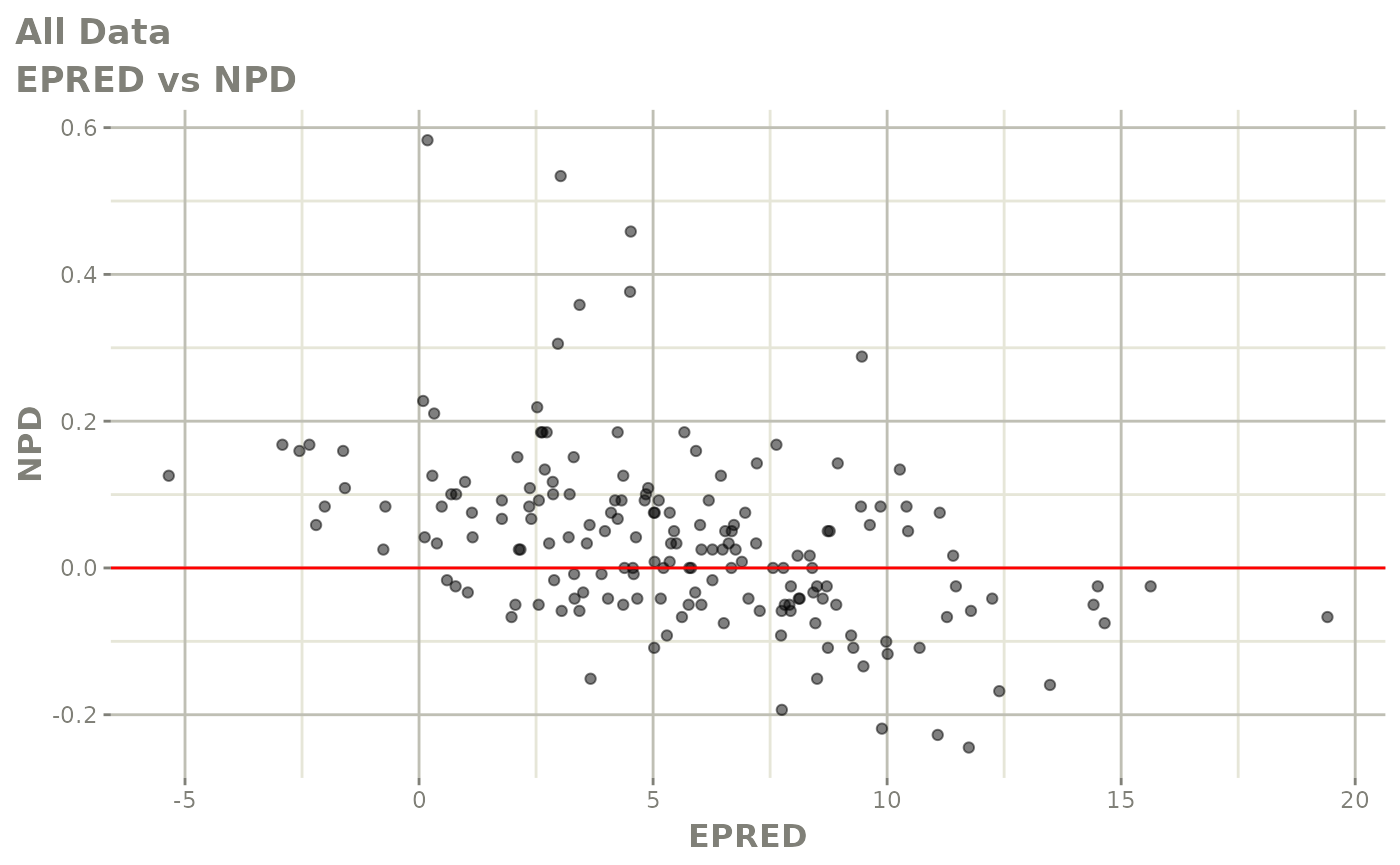
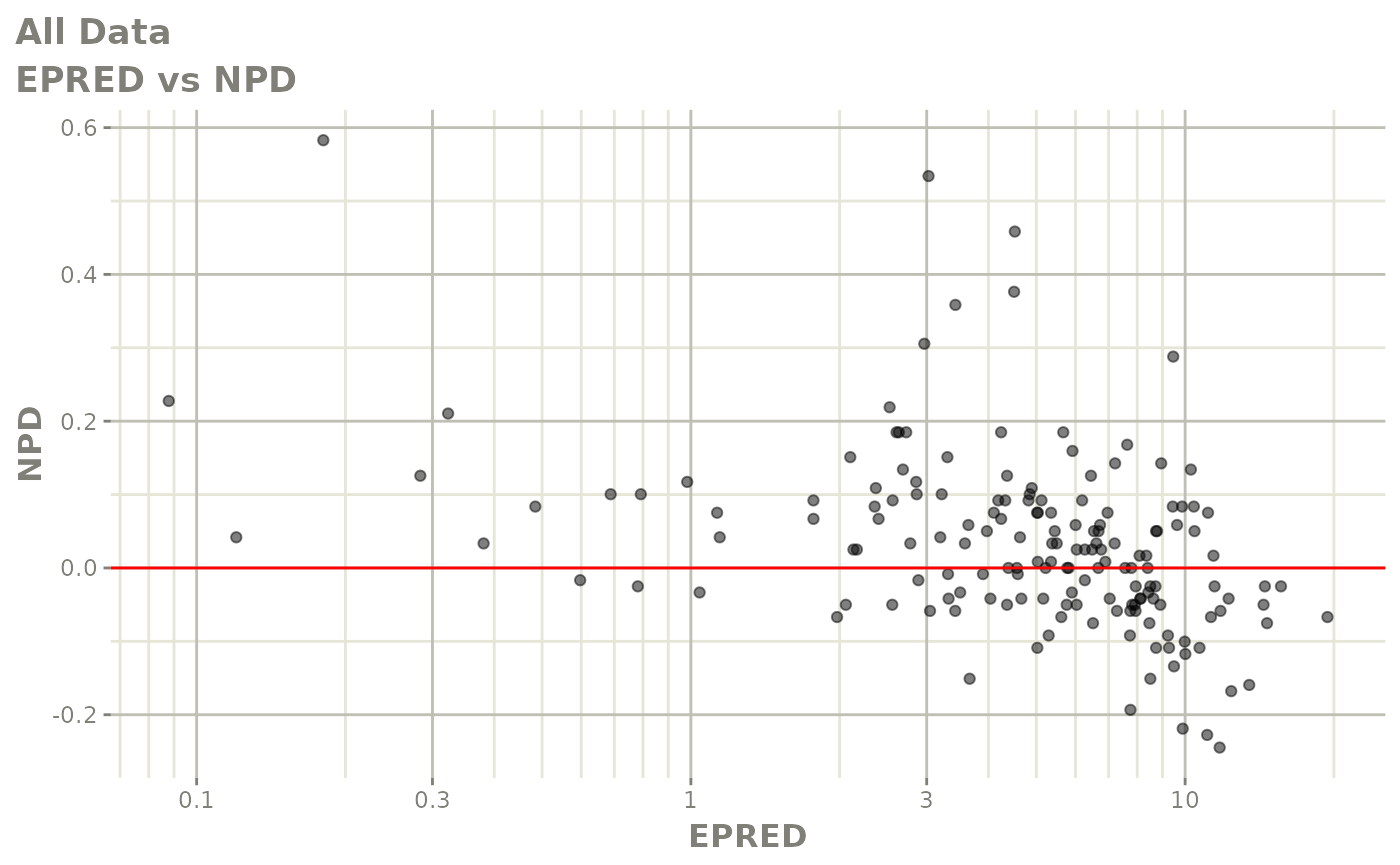
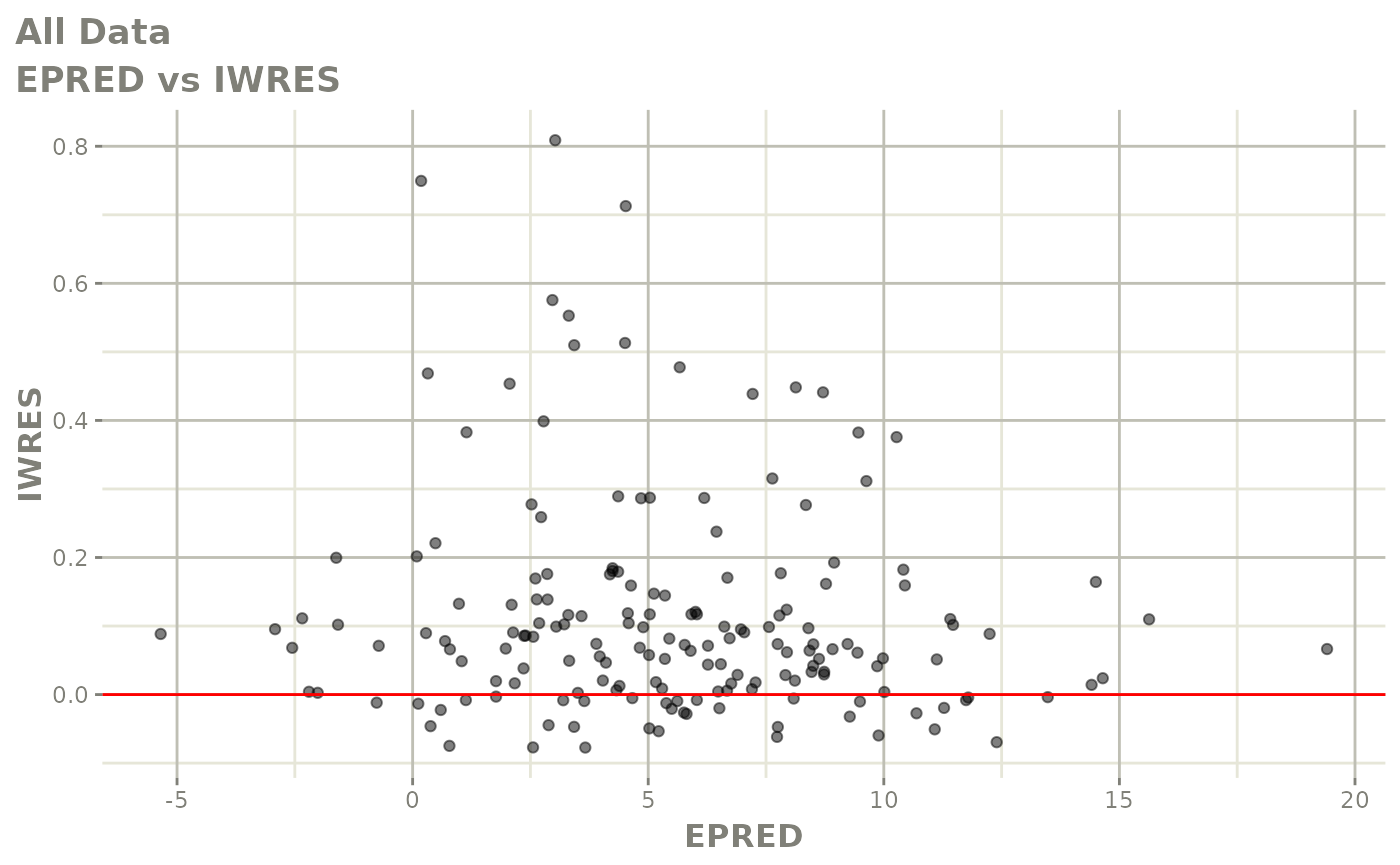
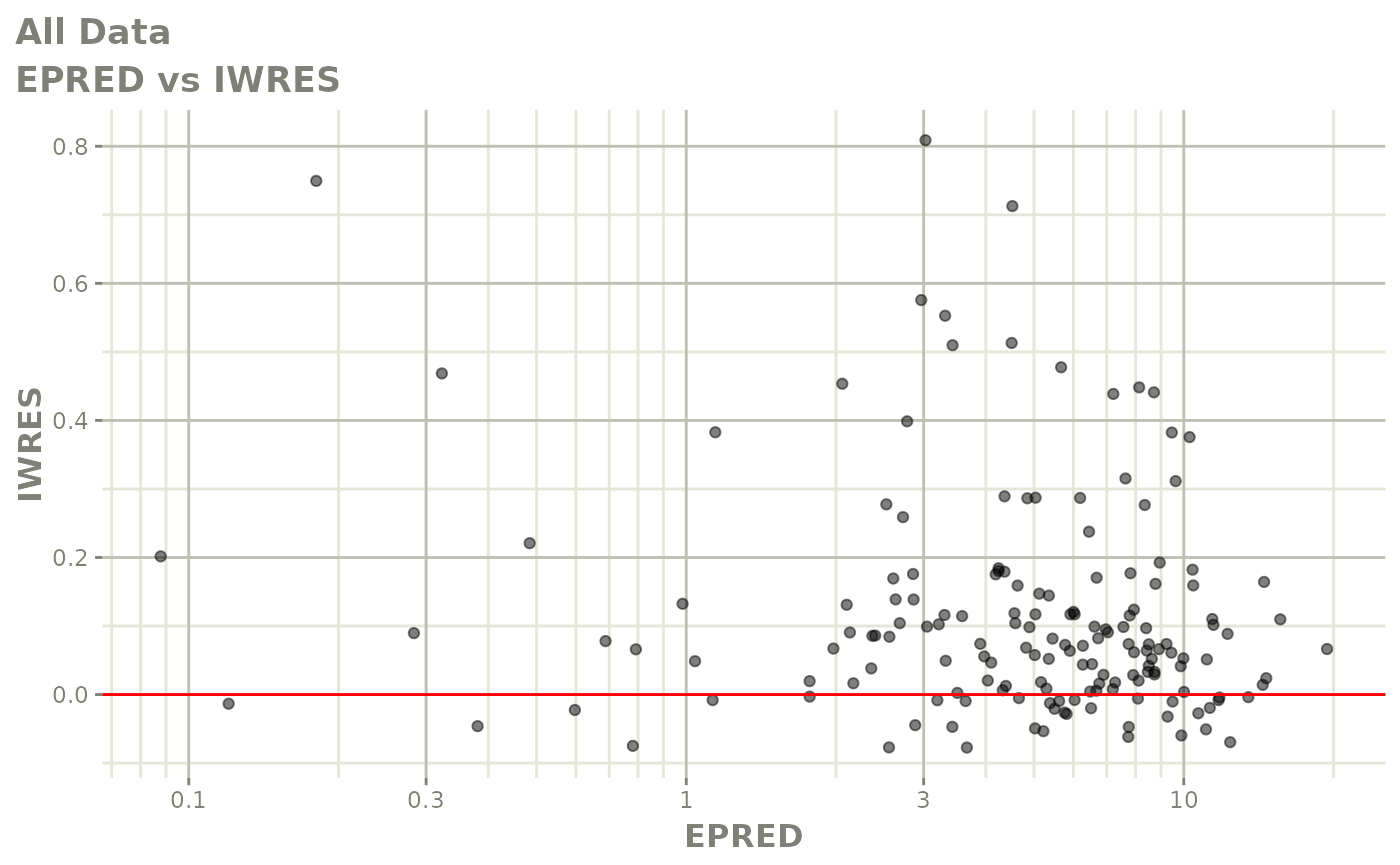
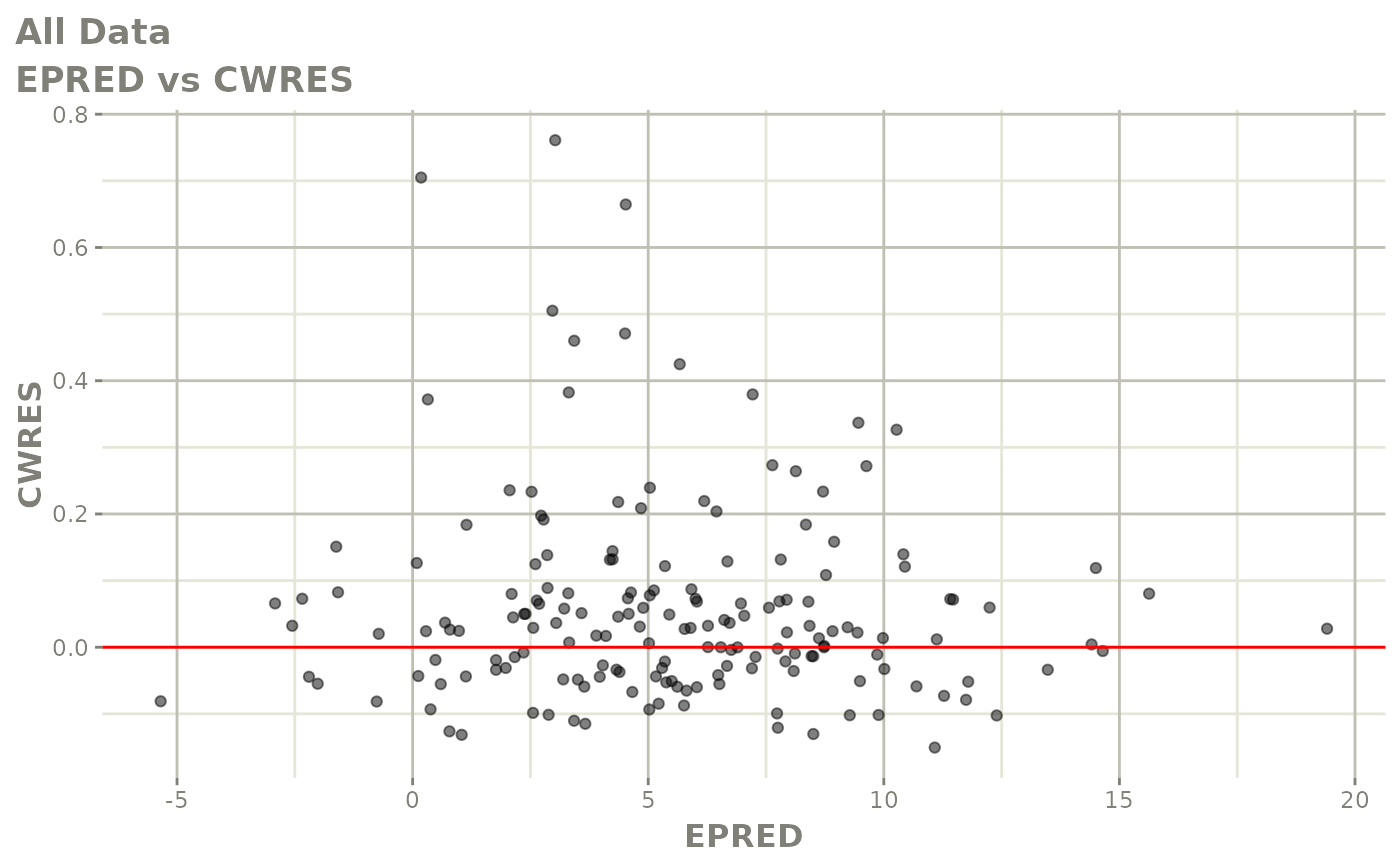
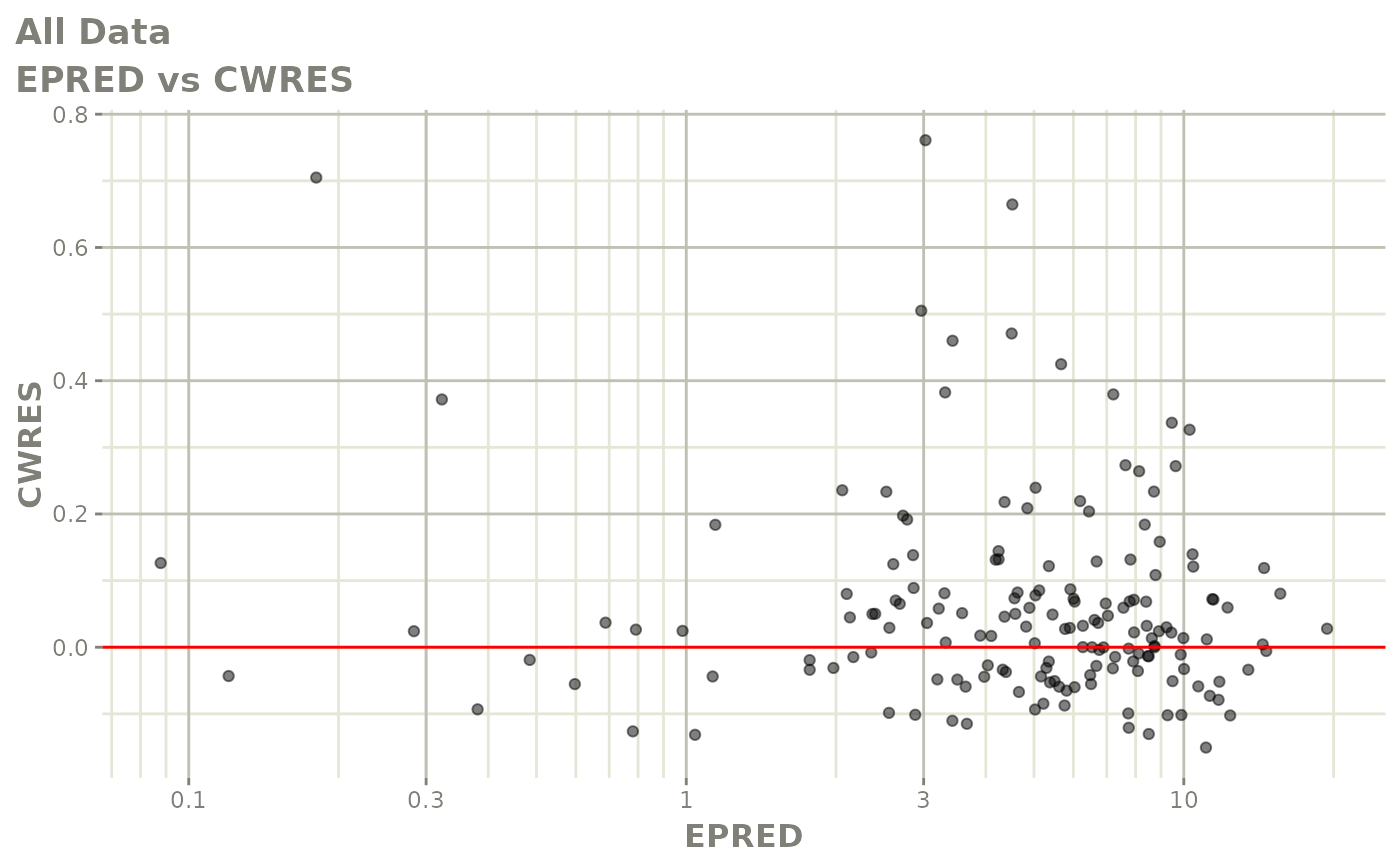
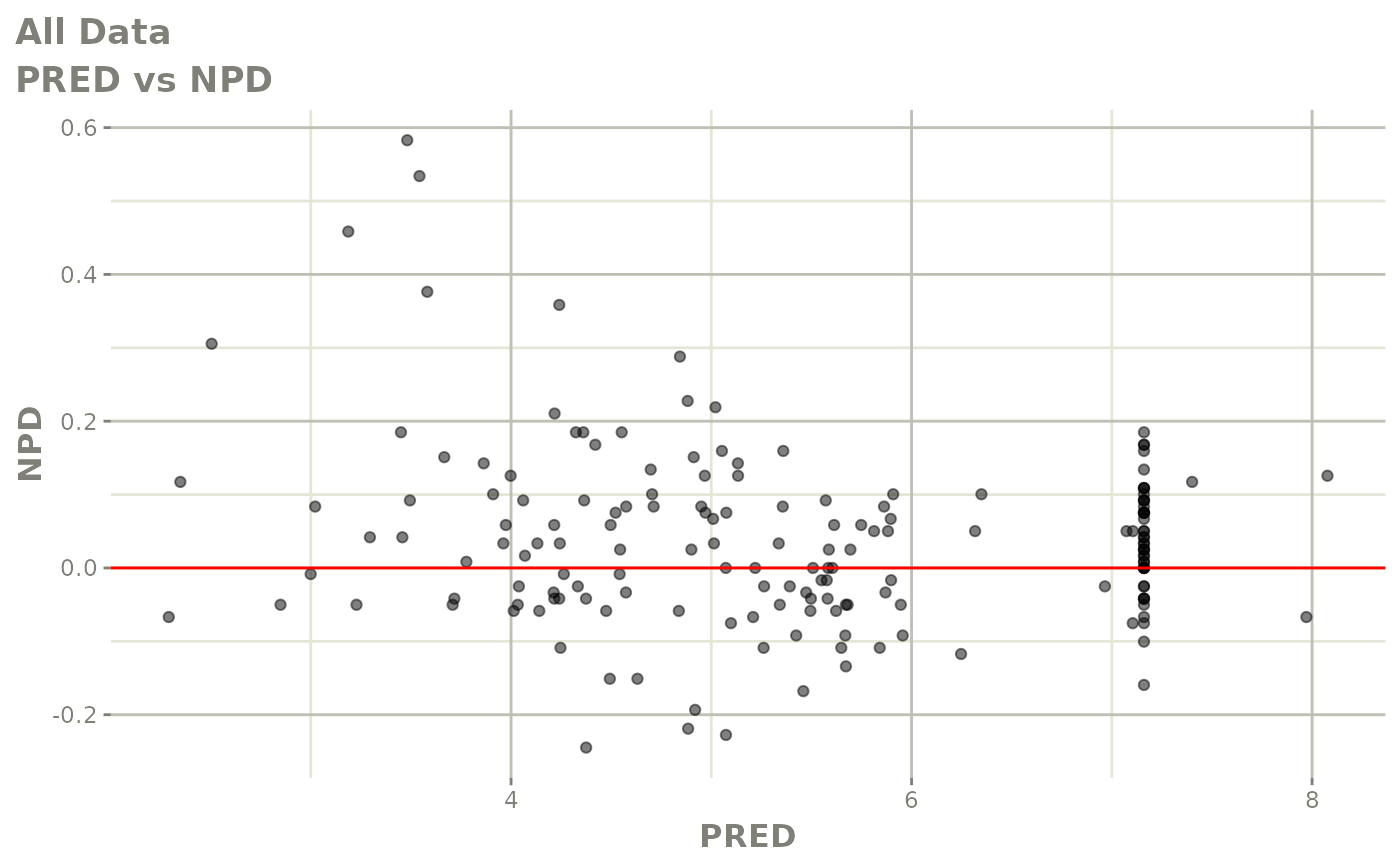
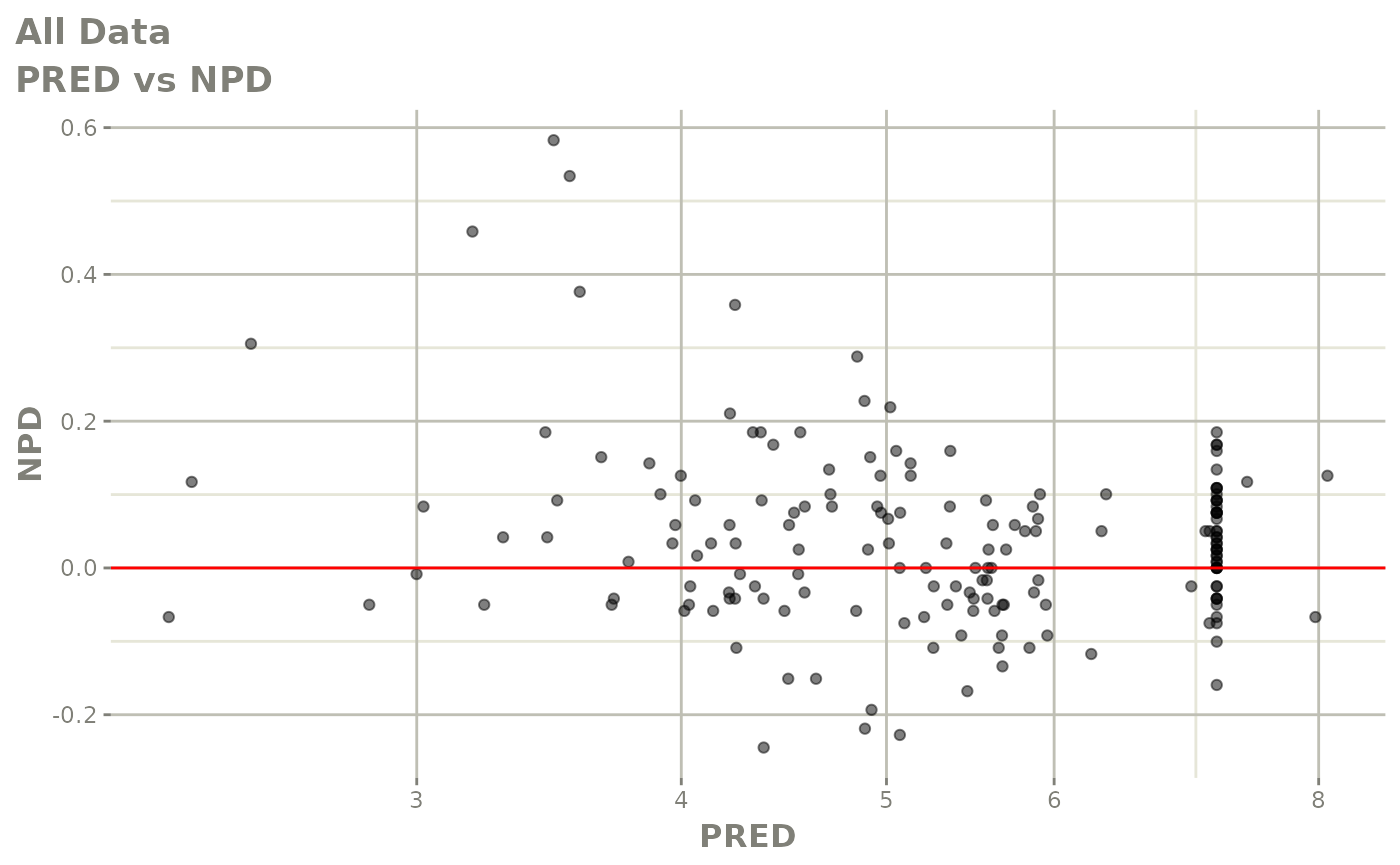
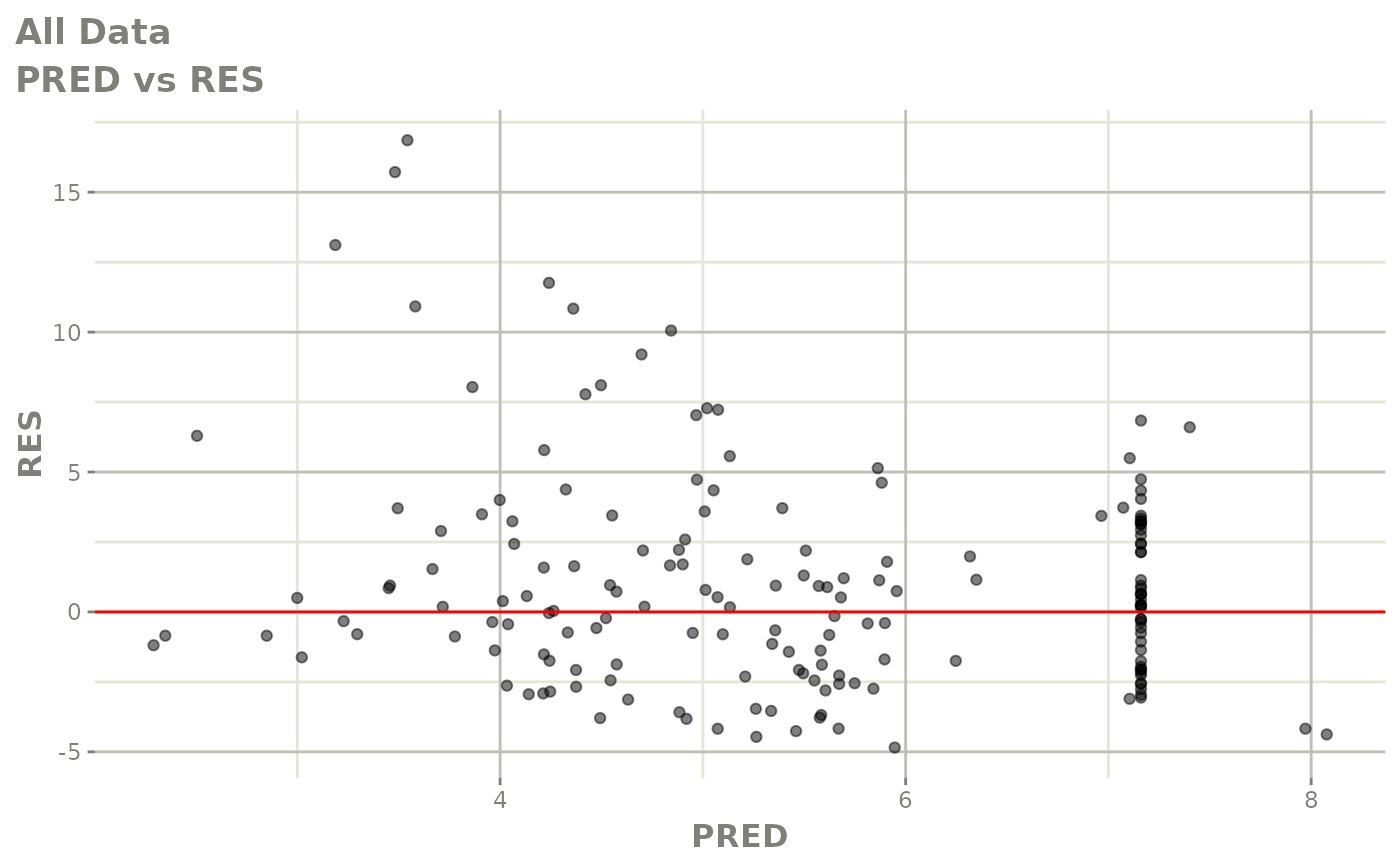
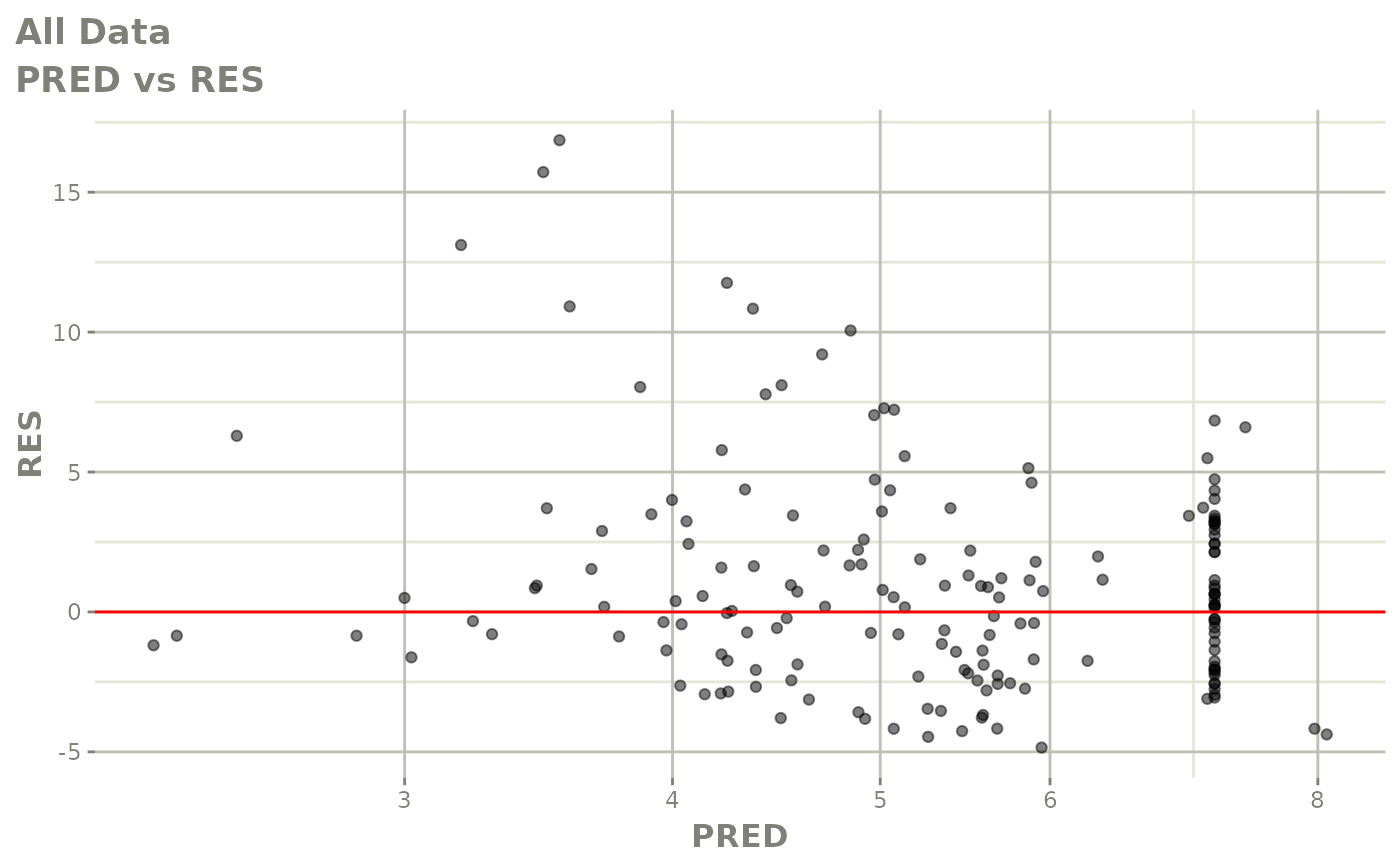
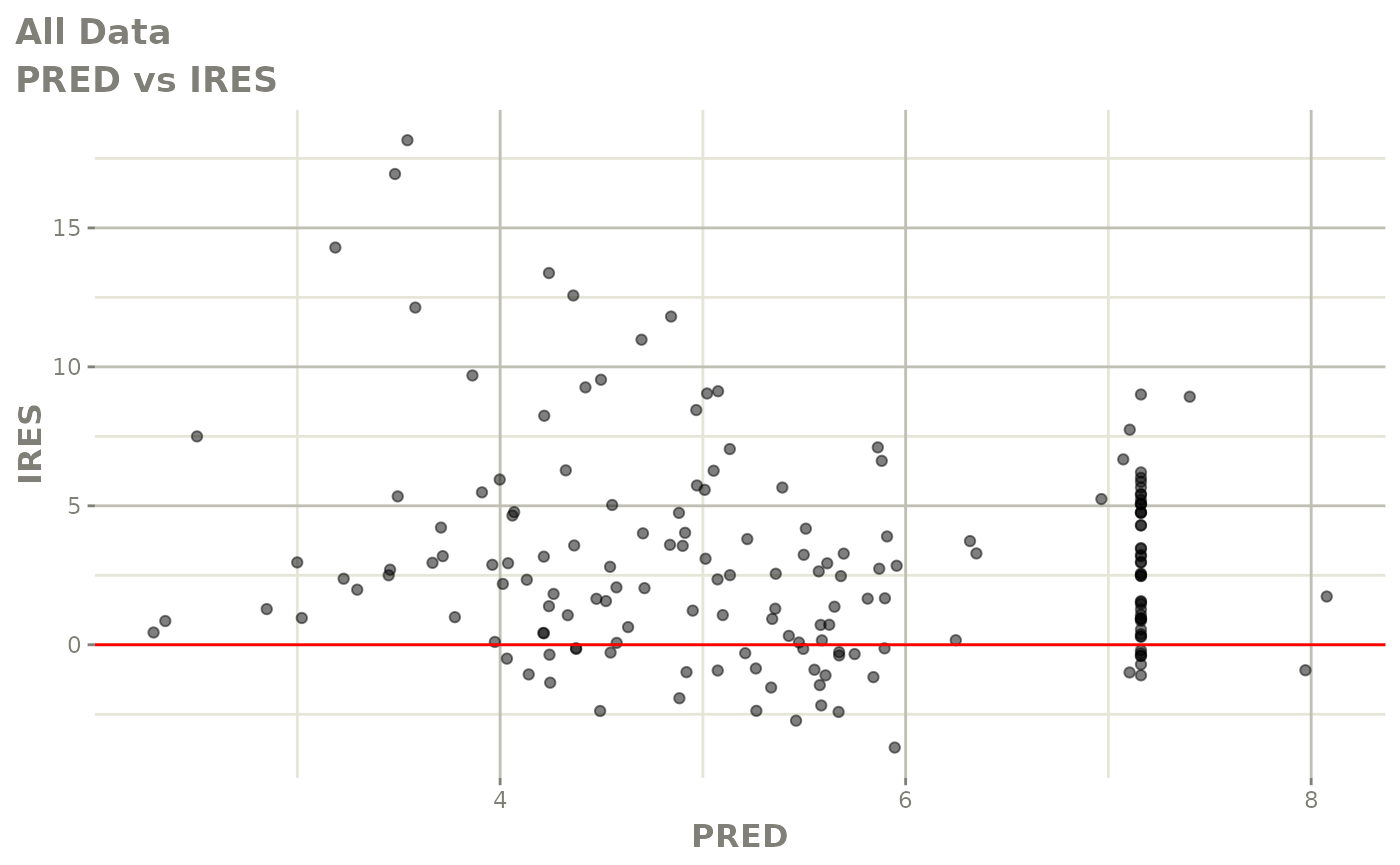
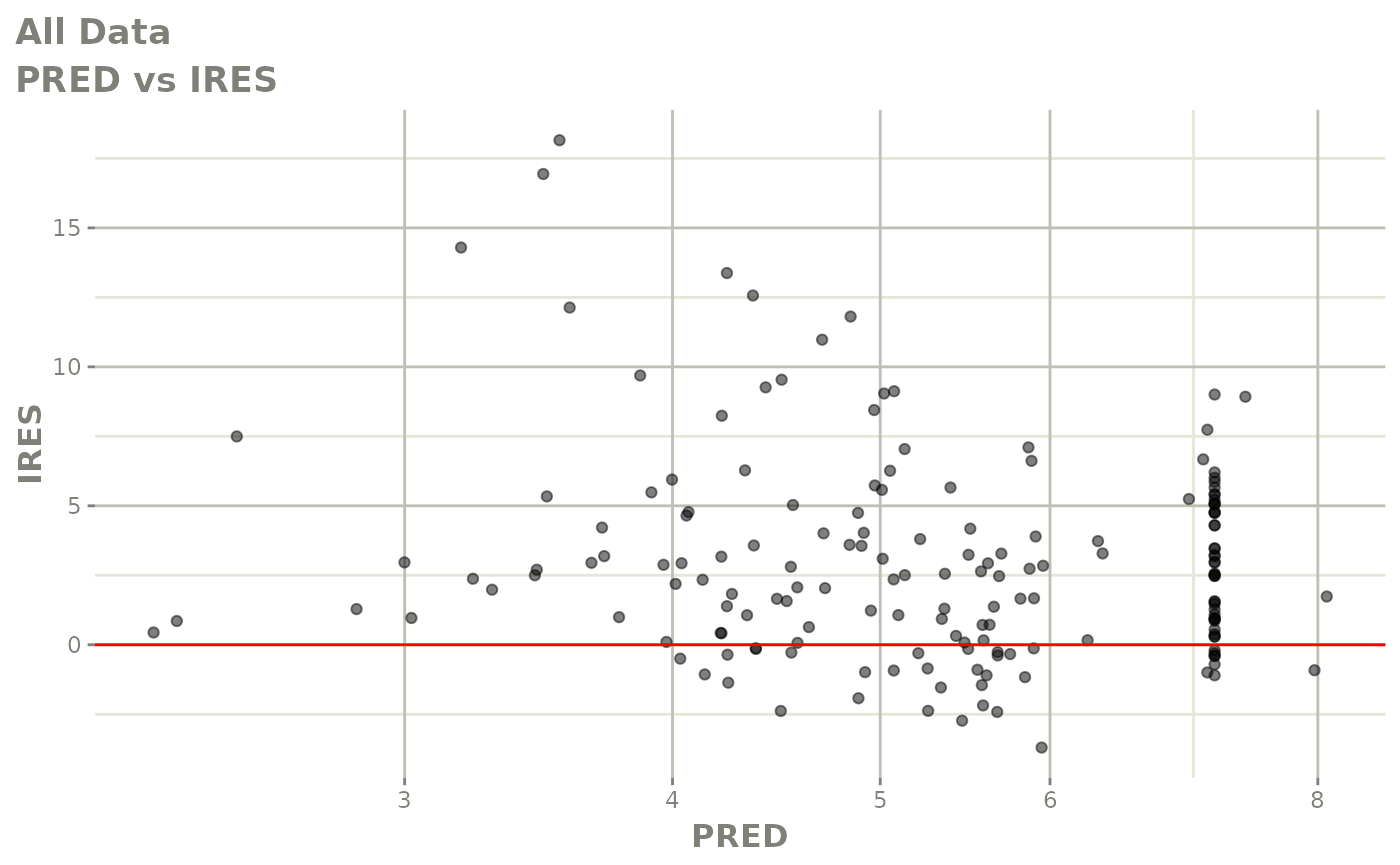
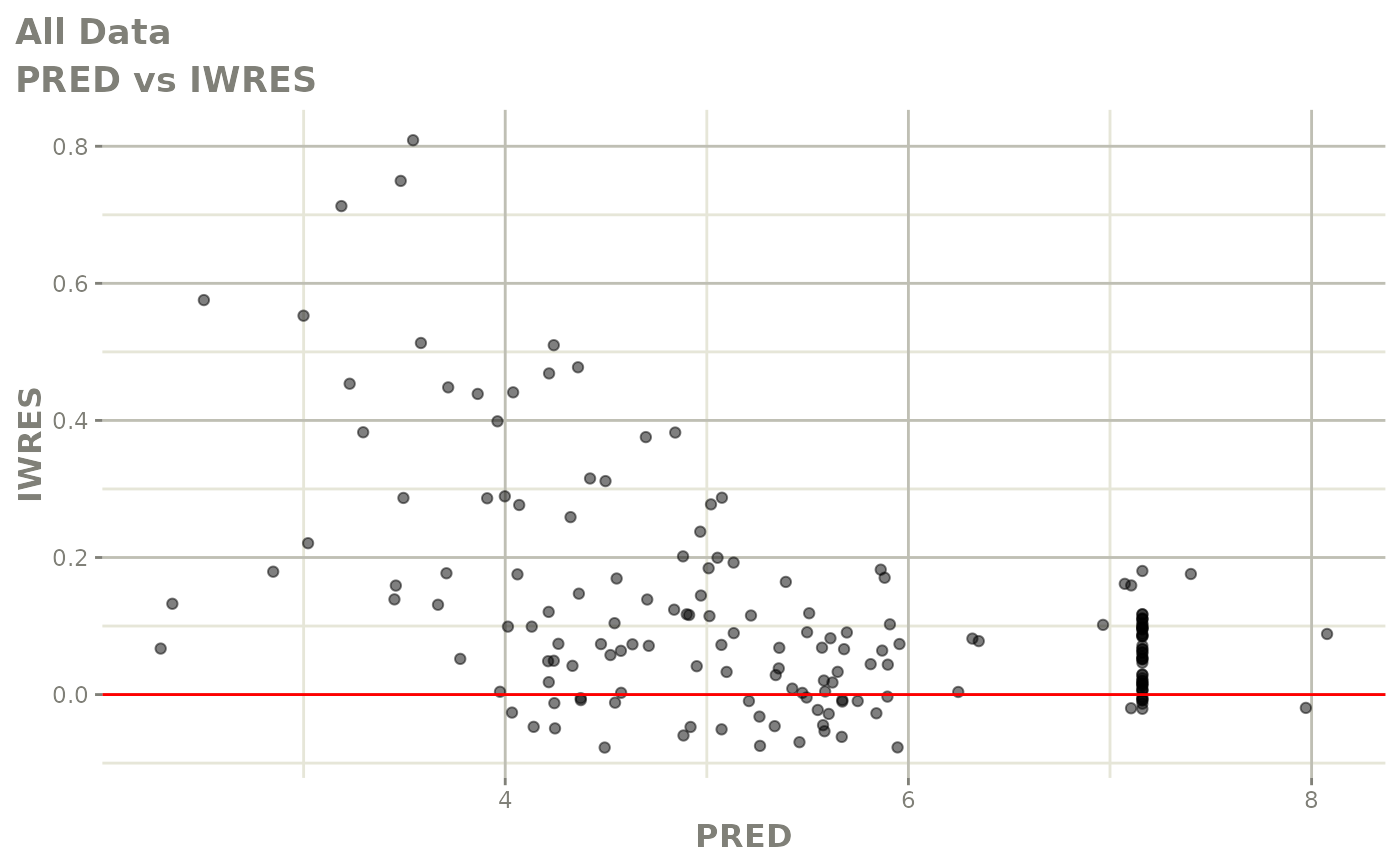
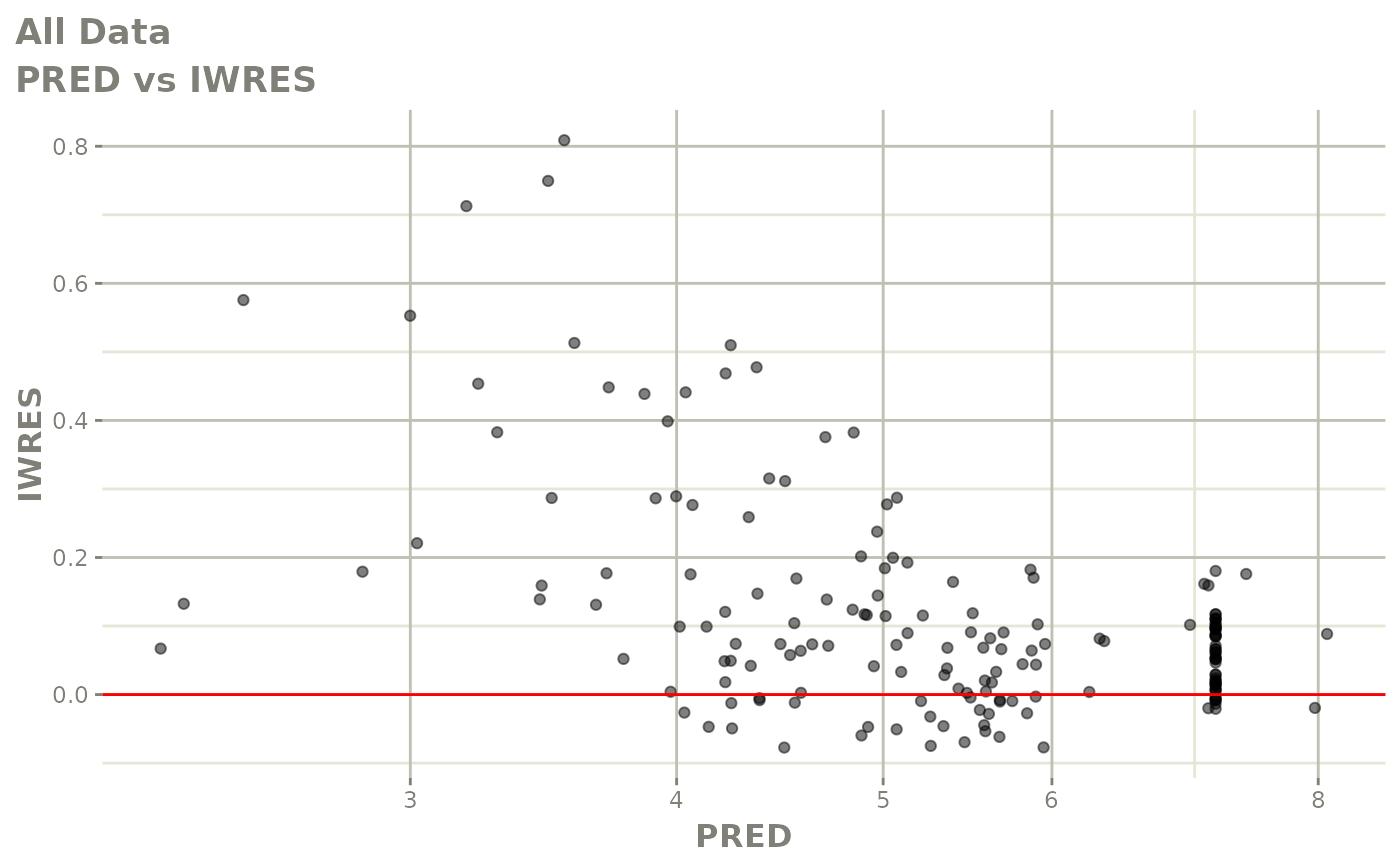
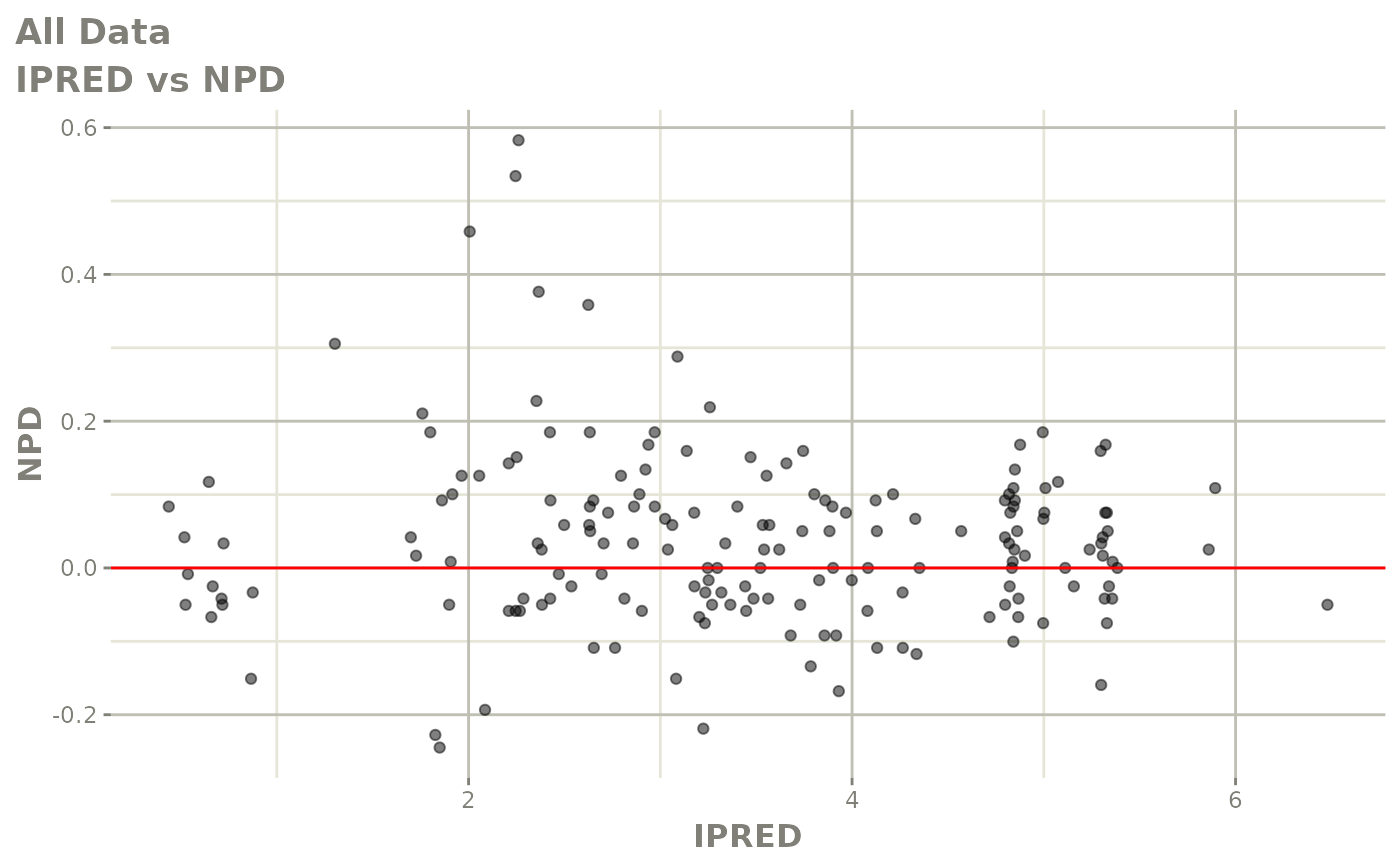
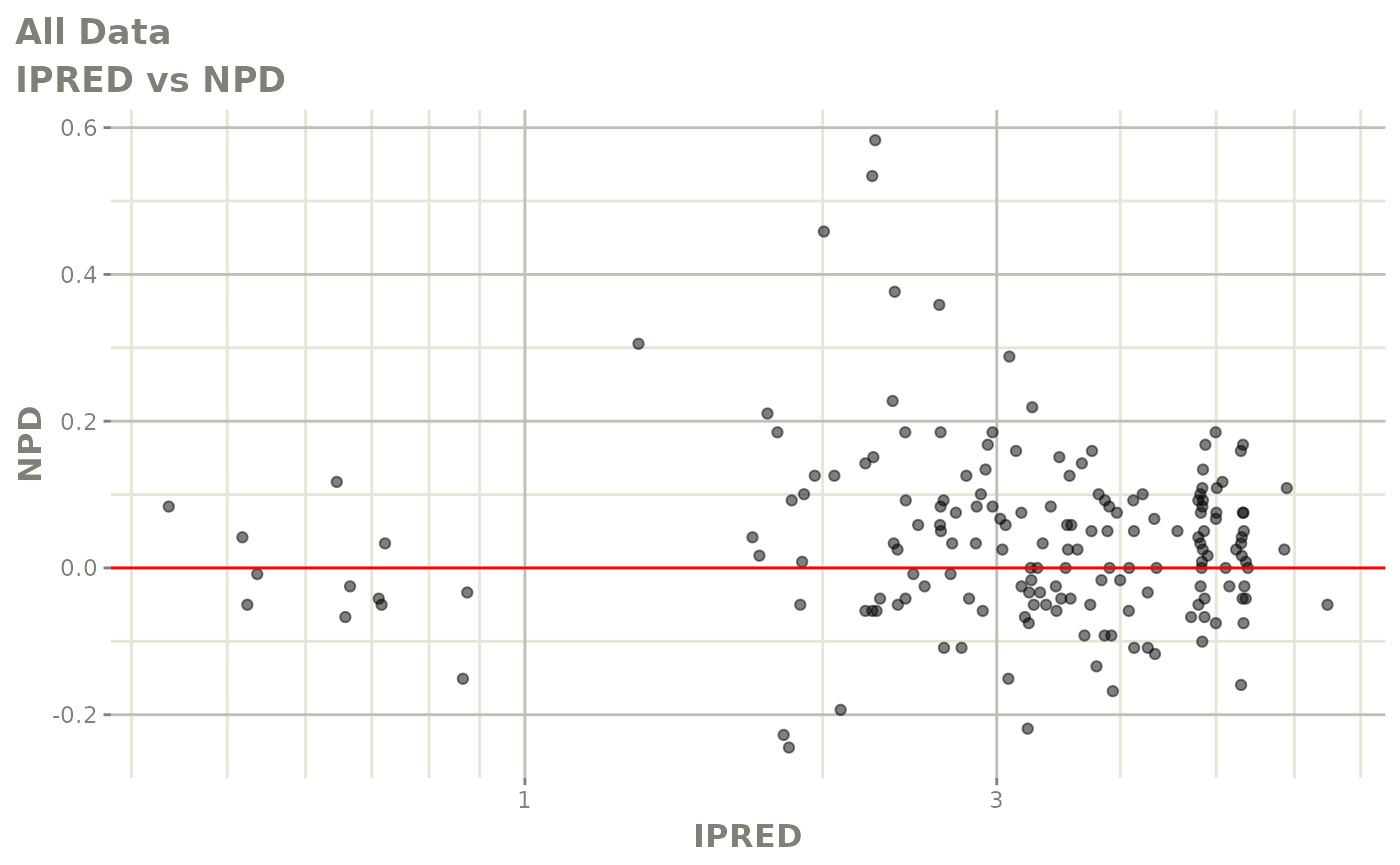
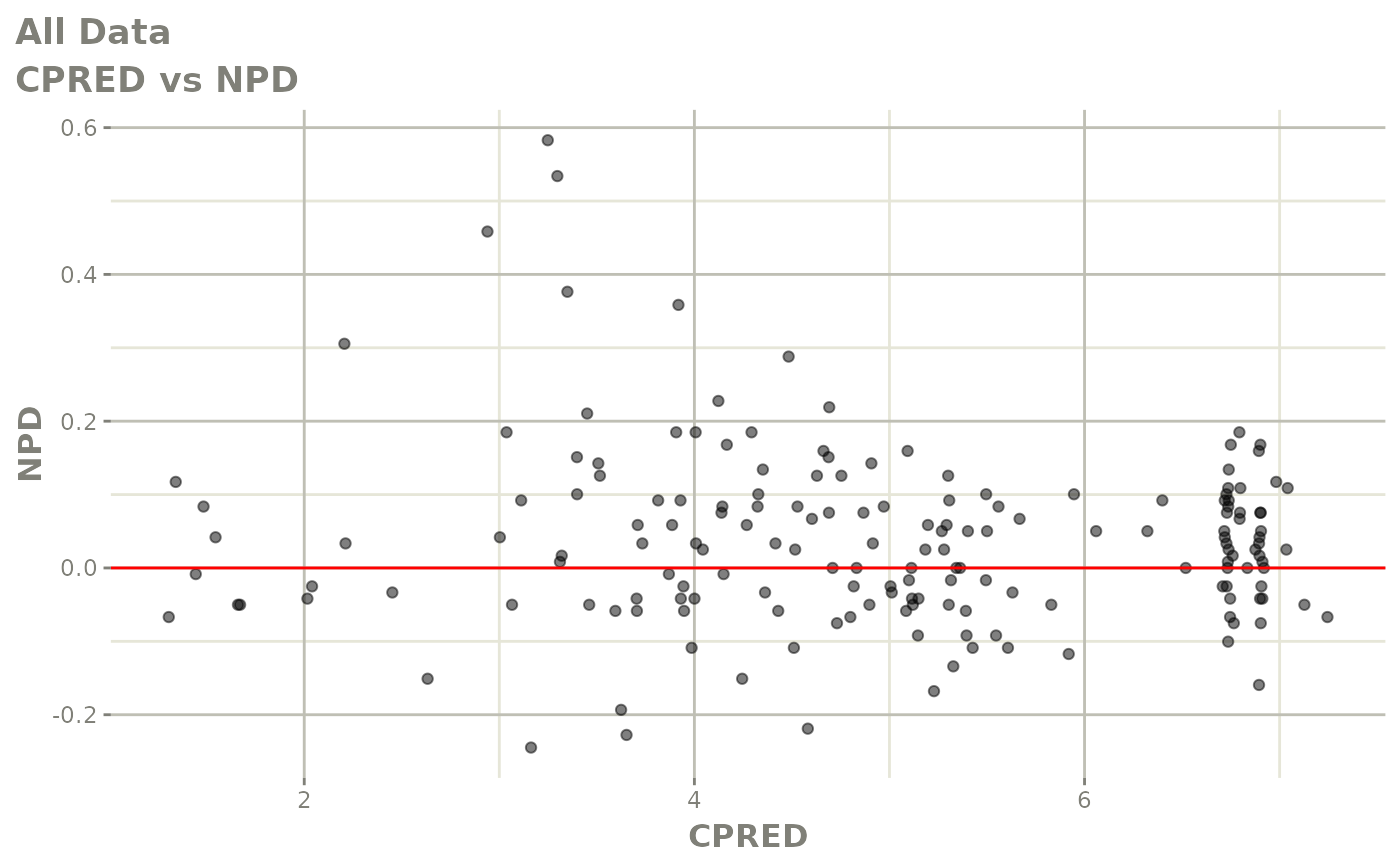
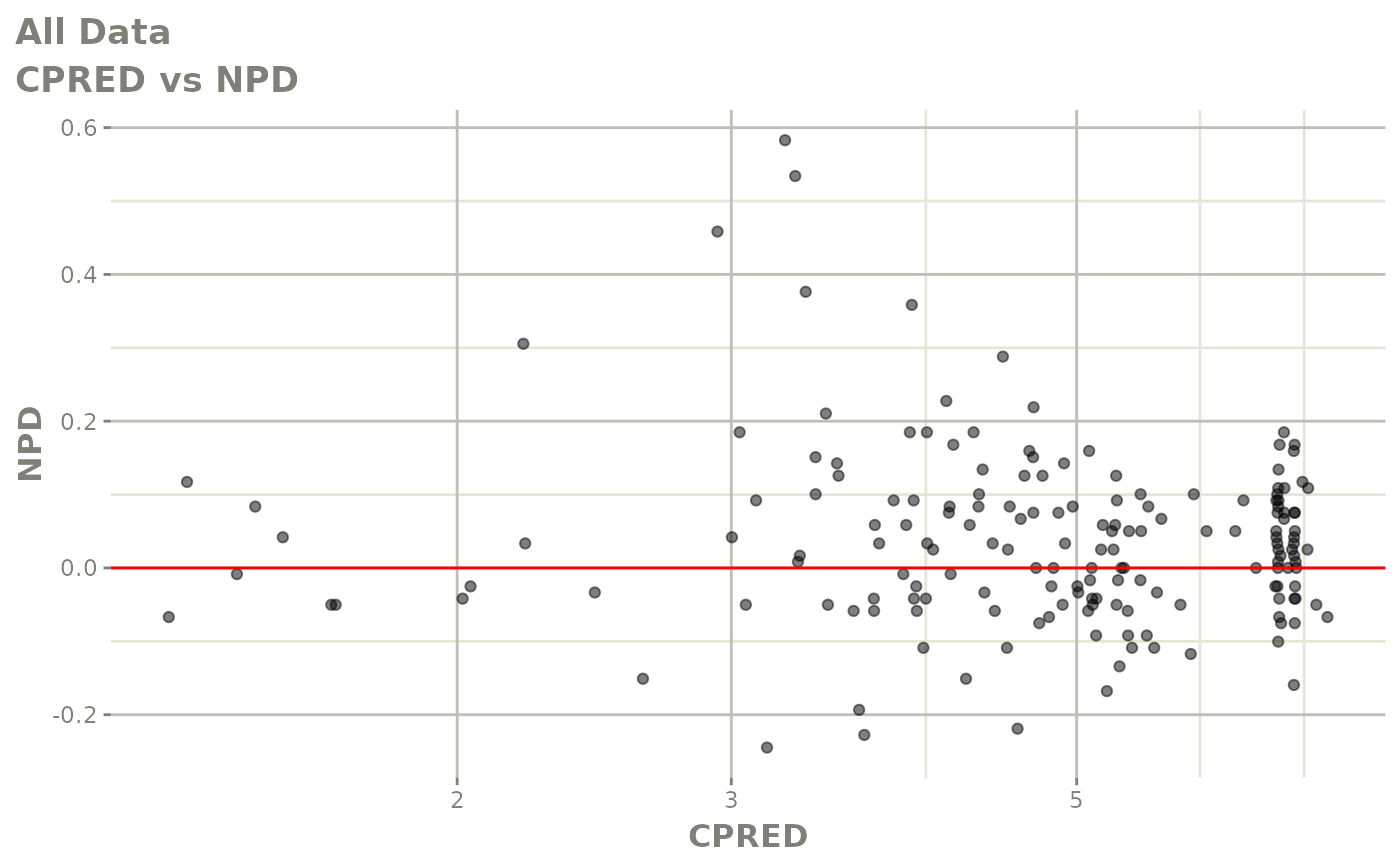
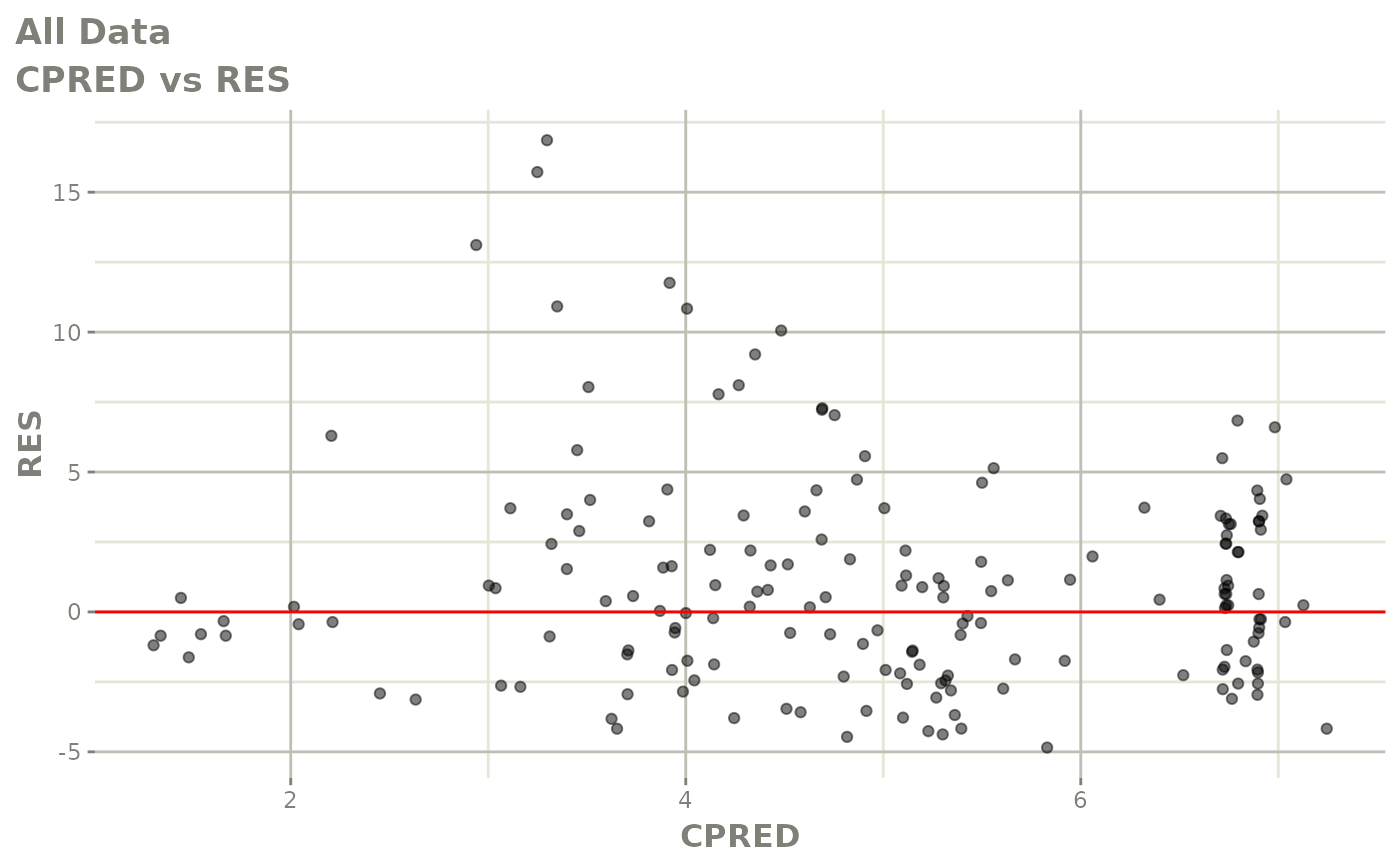
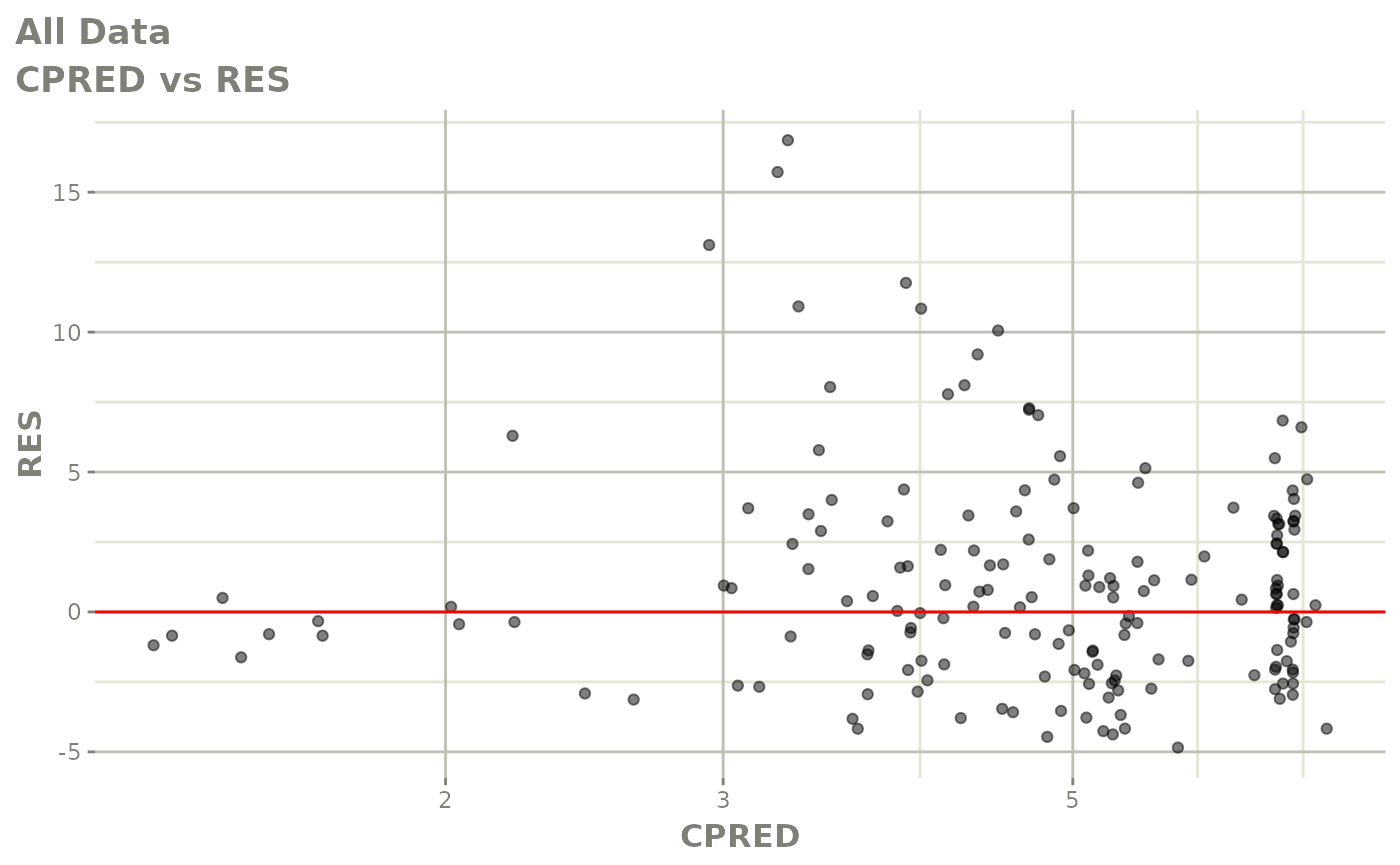
print(dv_vs_pred(xpdb) +
ylab("Observed Neutrophil Count (10^9/L)") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))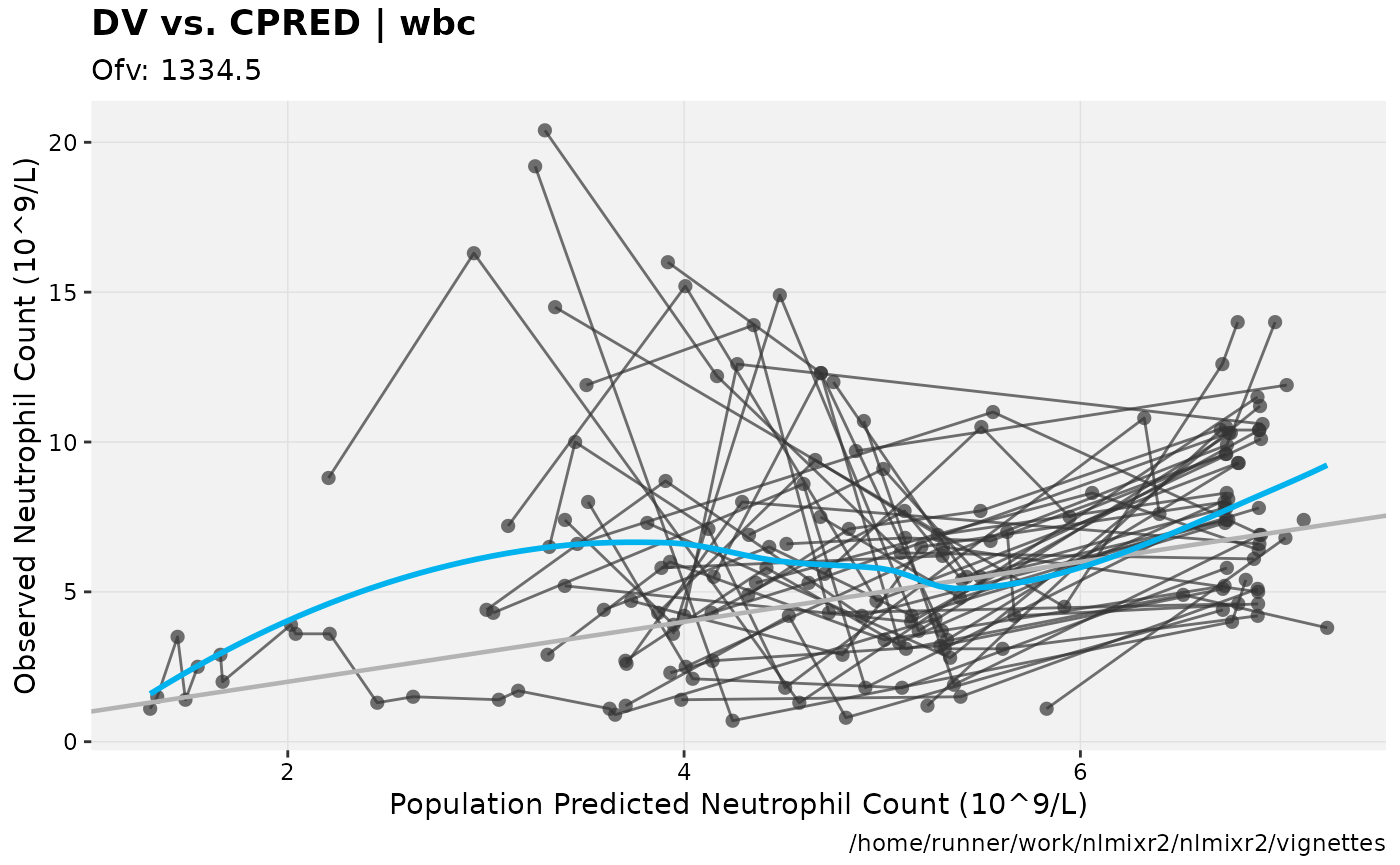
print(dv_vs_ipred(xpdb) +
ylab("Observed Neutrophil Count (10^9/L)") +
xlab("Individual Predicted Neutrophil Count (10^9/L)"))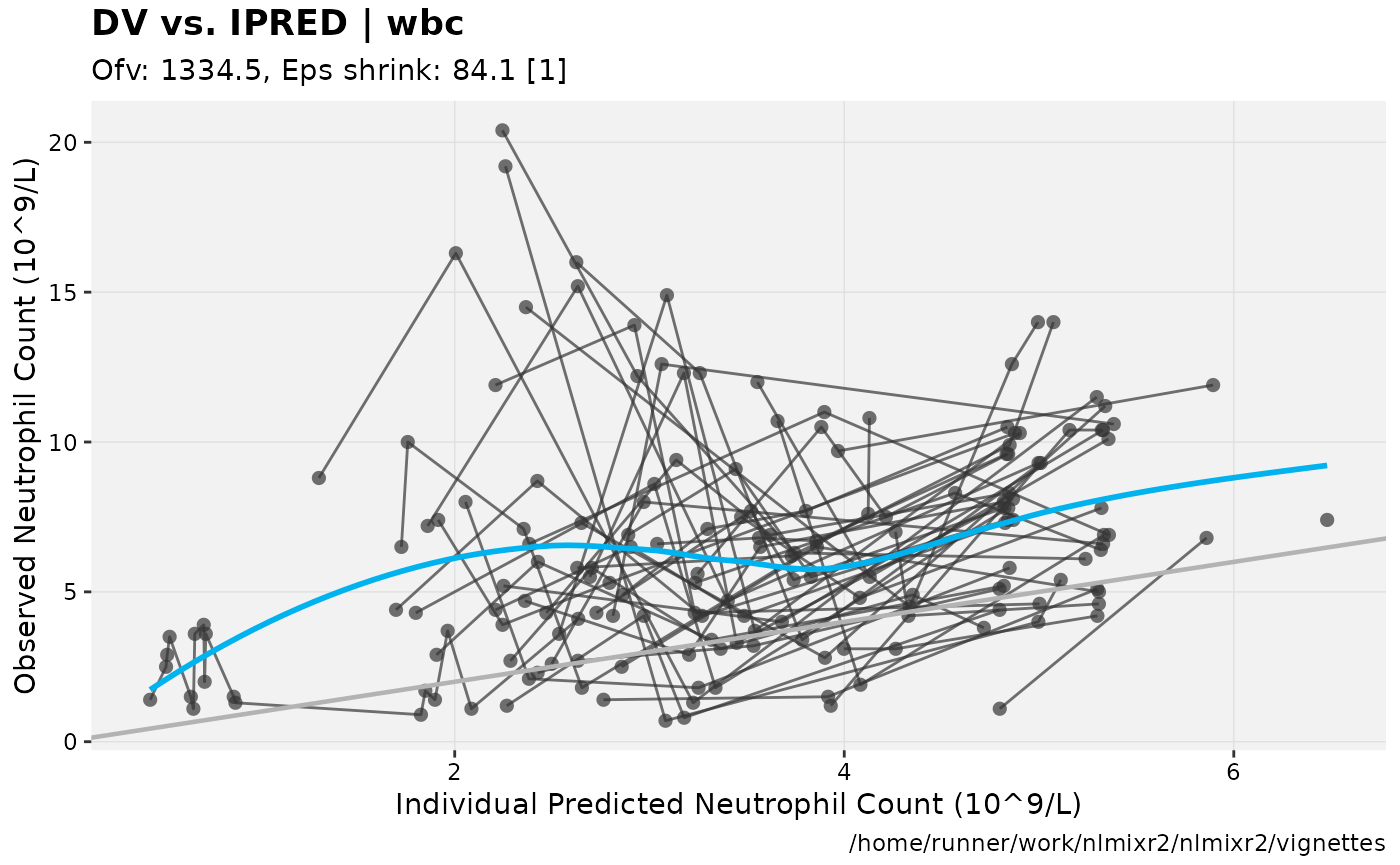
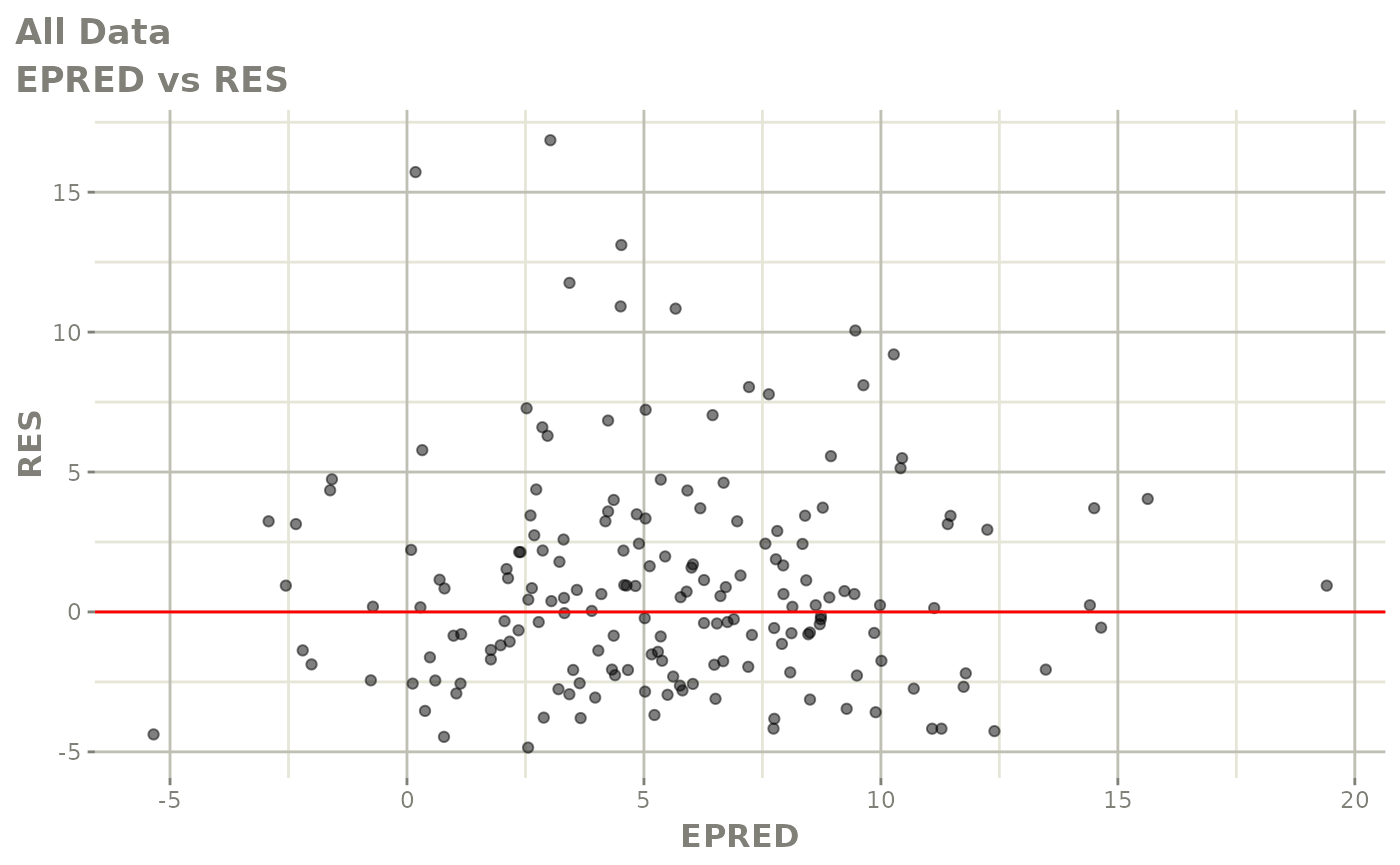
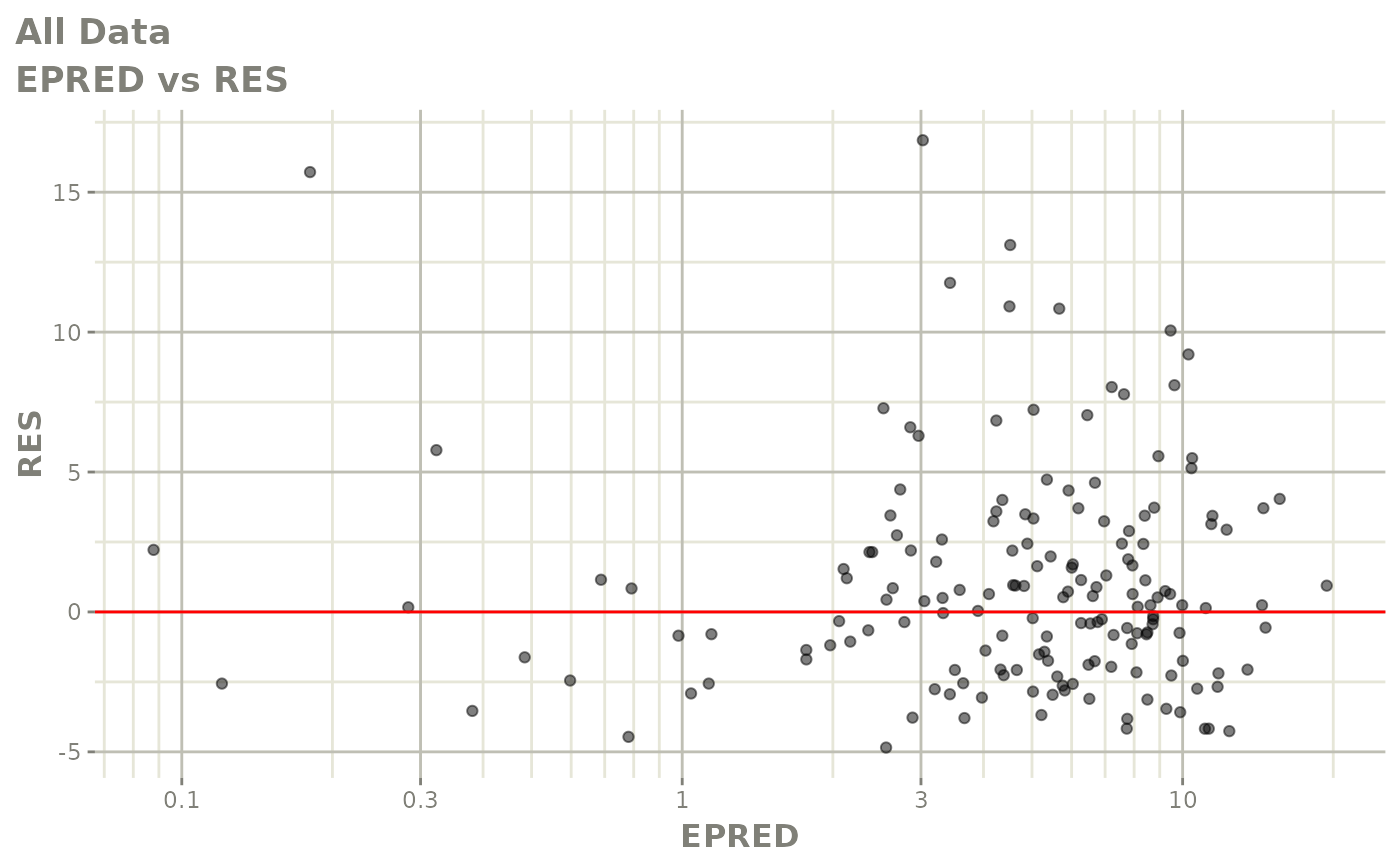
print(res_vs_pred(xpdb) +
ylab("Conditional Weighted Residuals") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))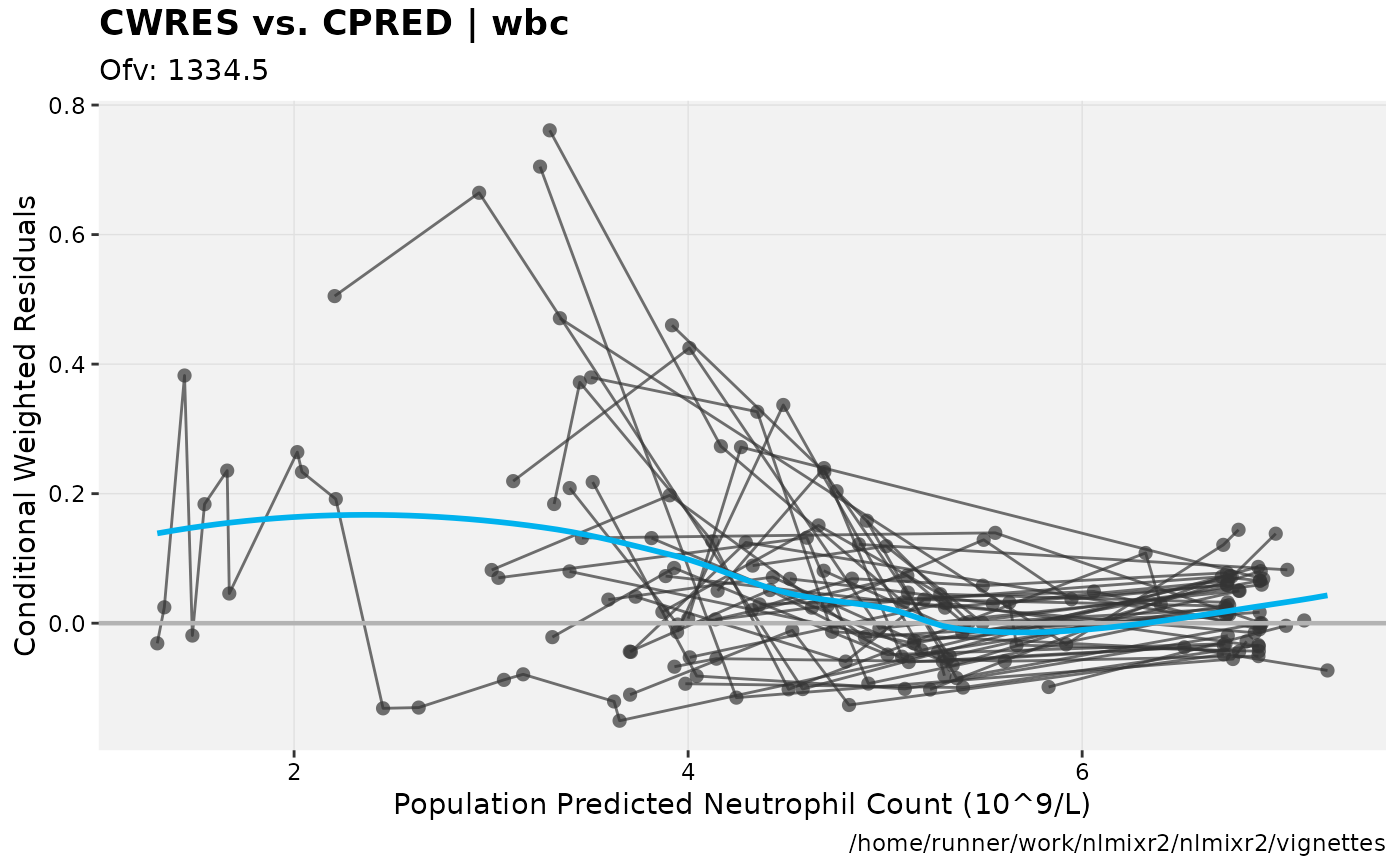
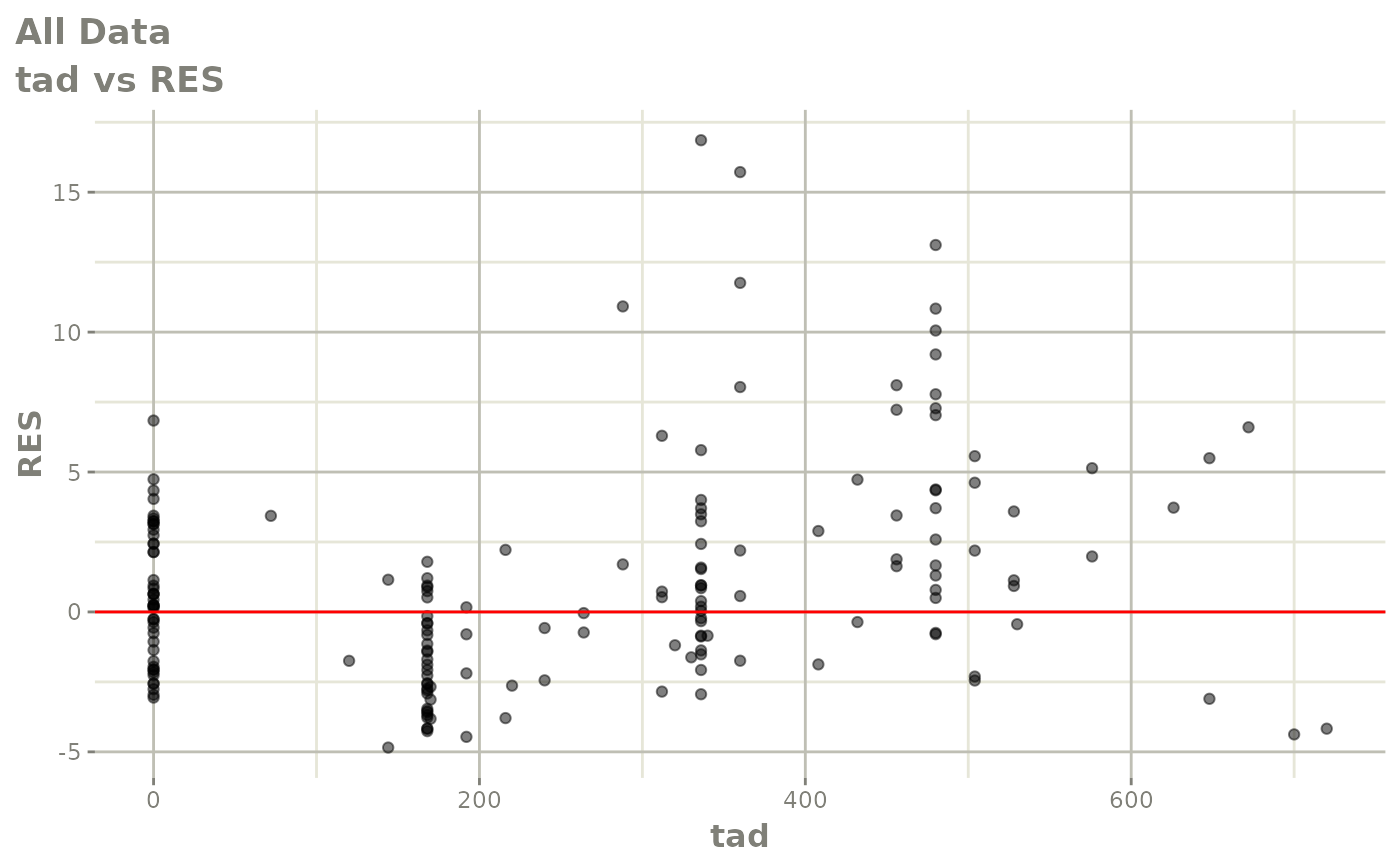
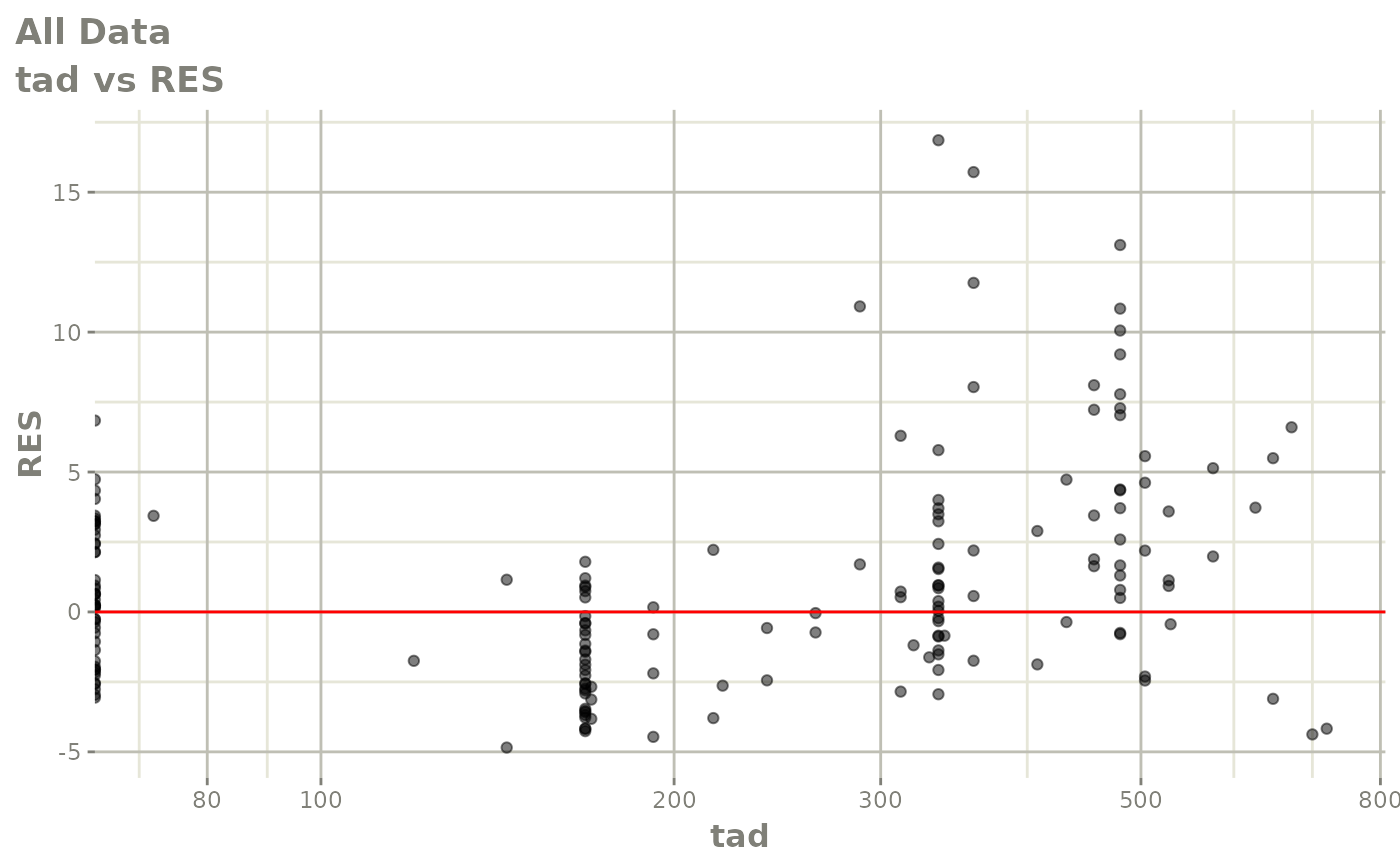
print(res_vs_idv(xpdb) +
ylab("Conditional Weighted Residuals") +
xlab("Time (h)"))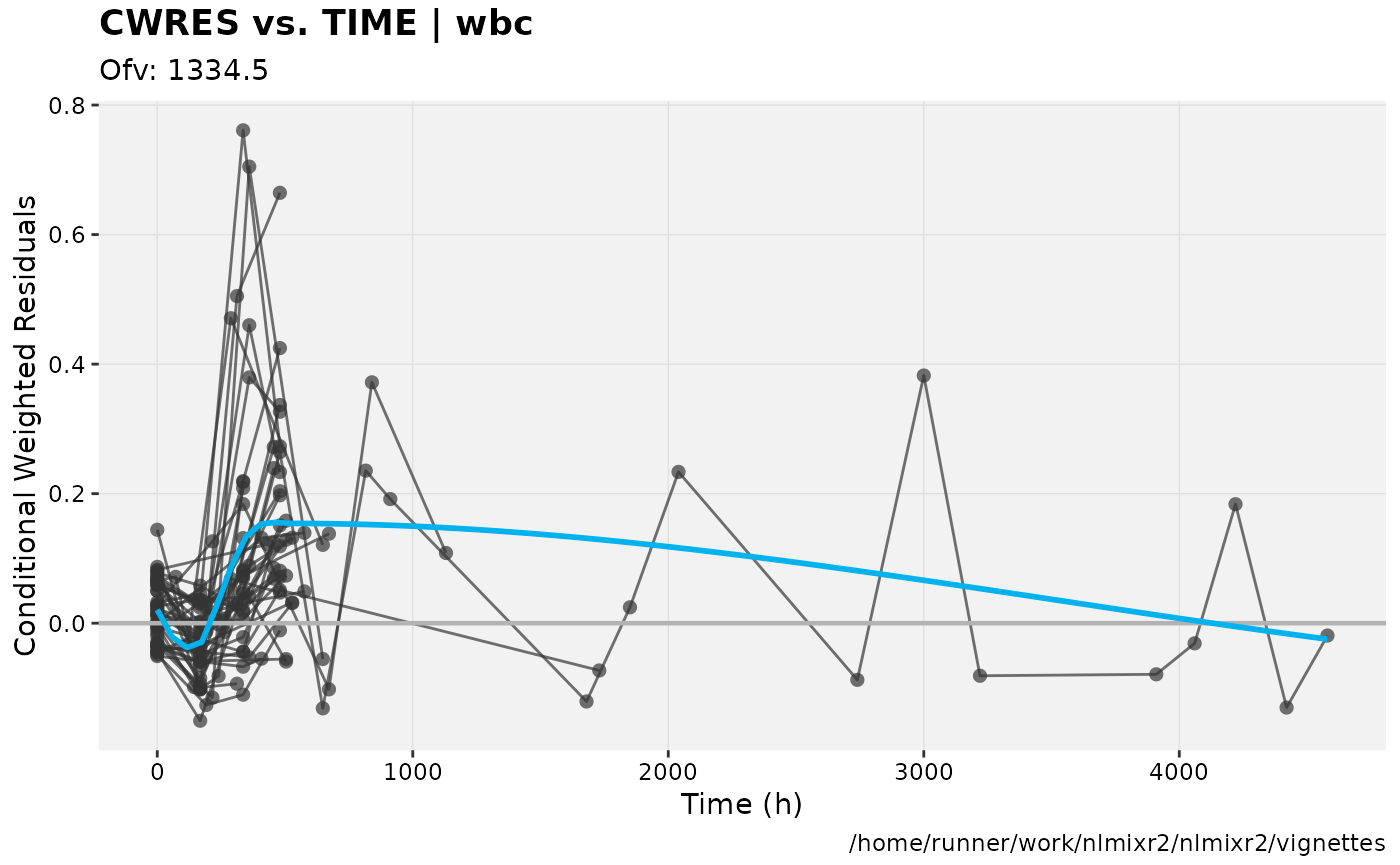
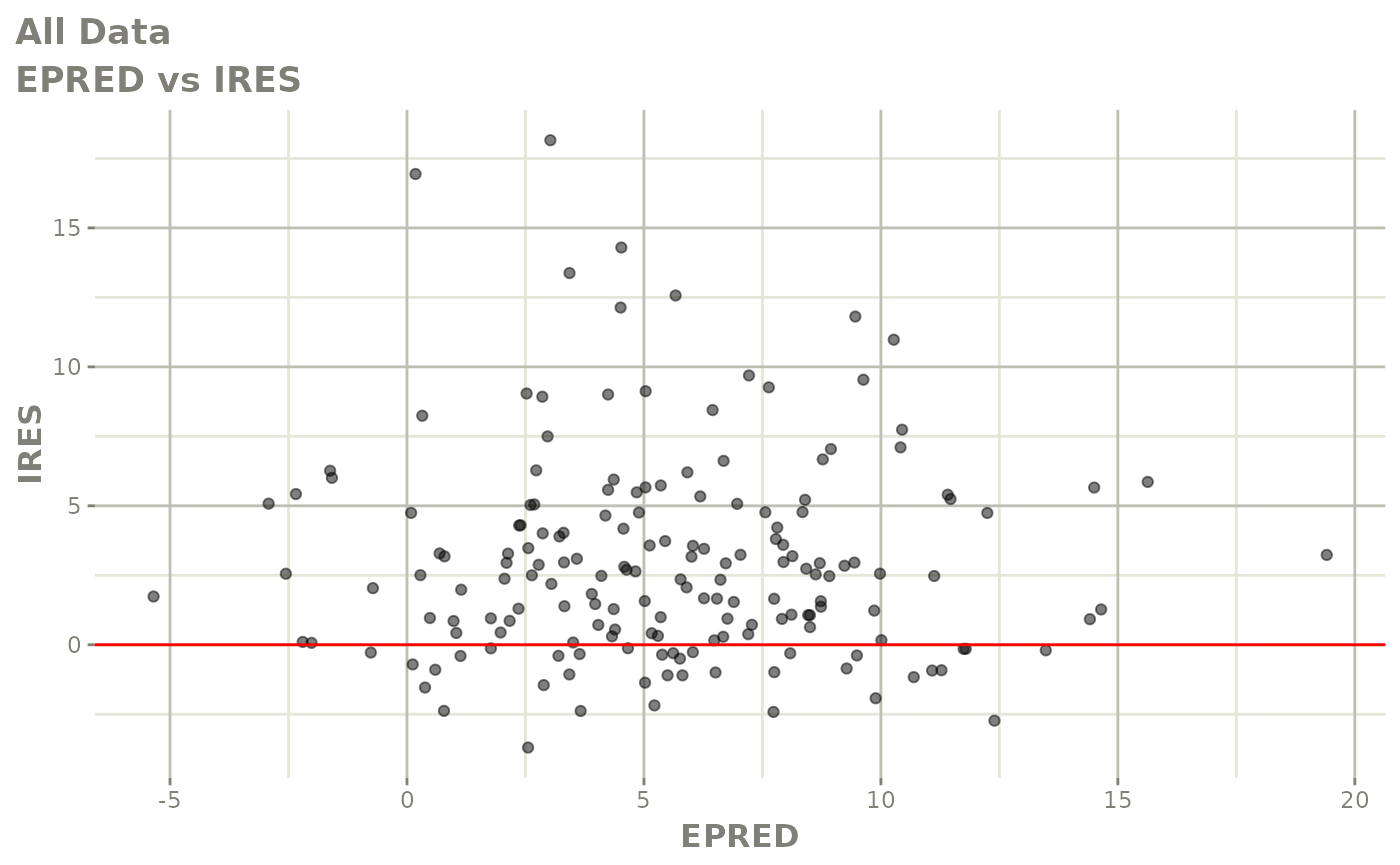
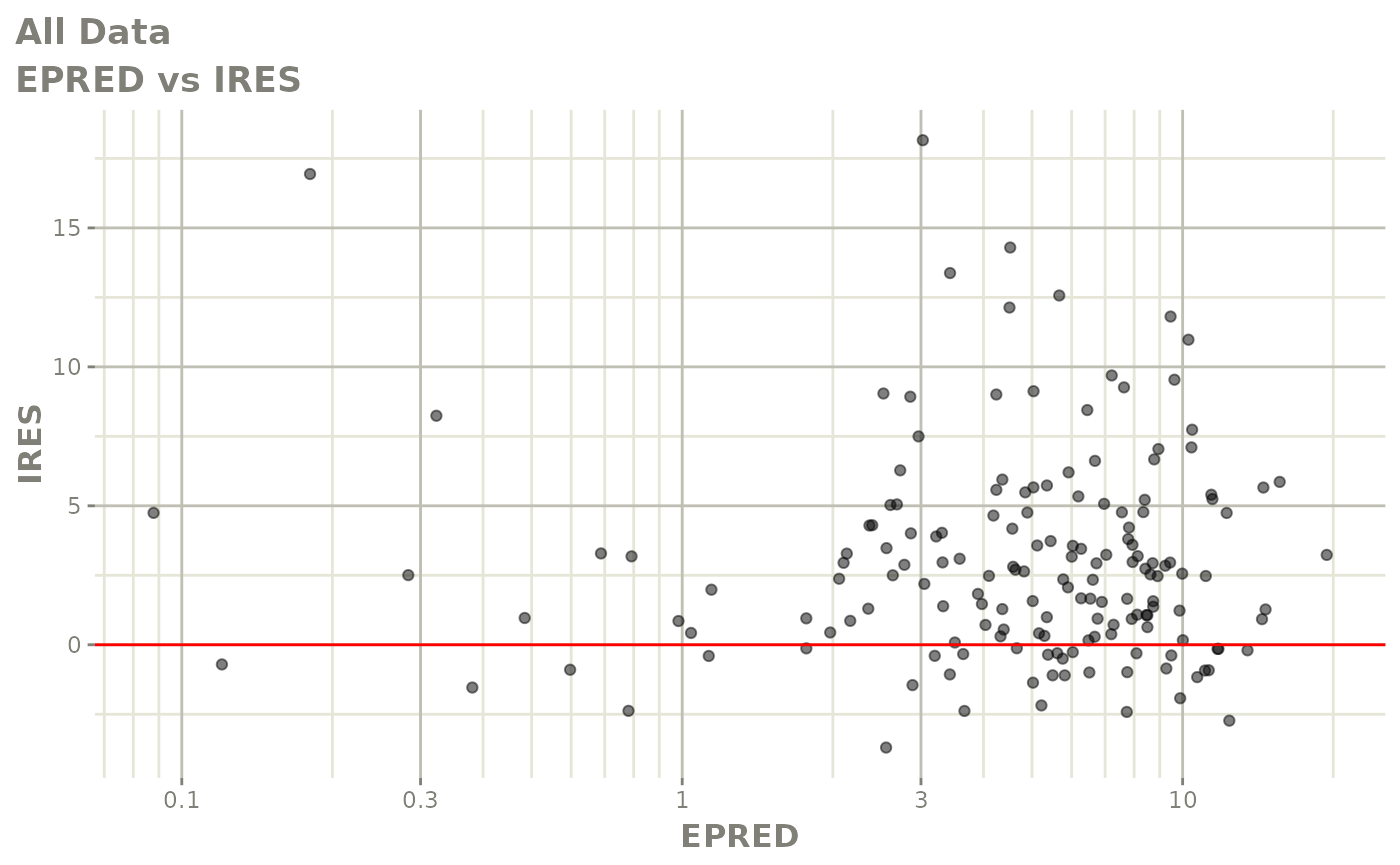
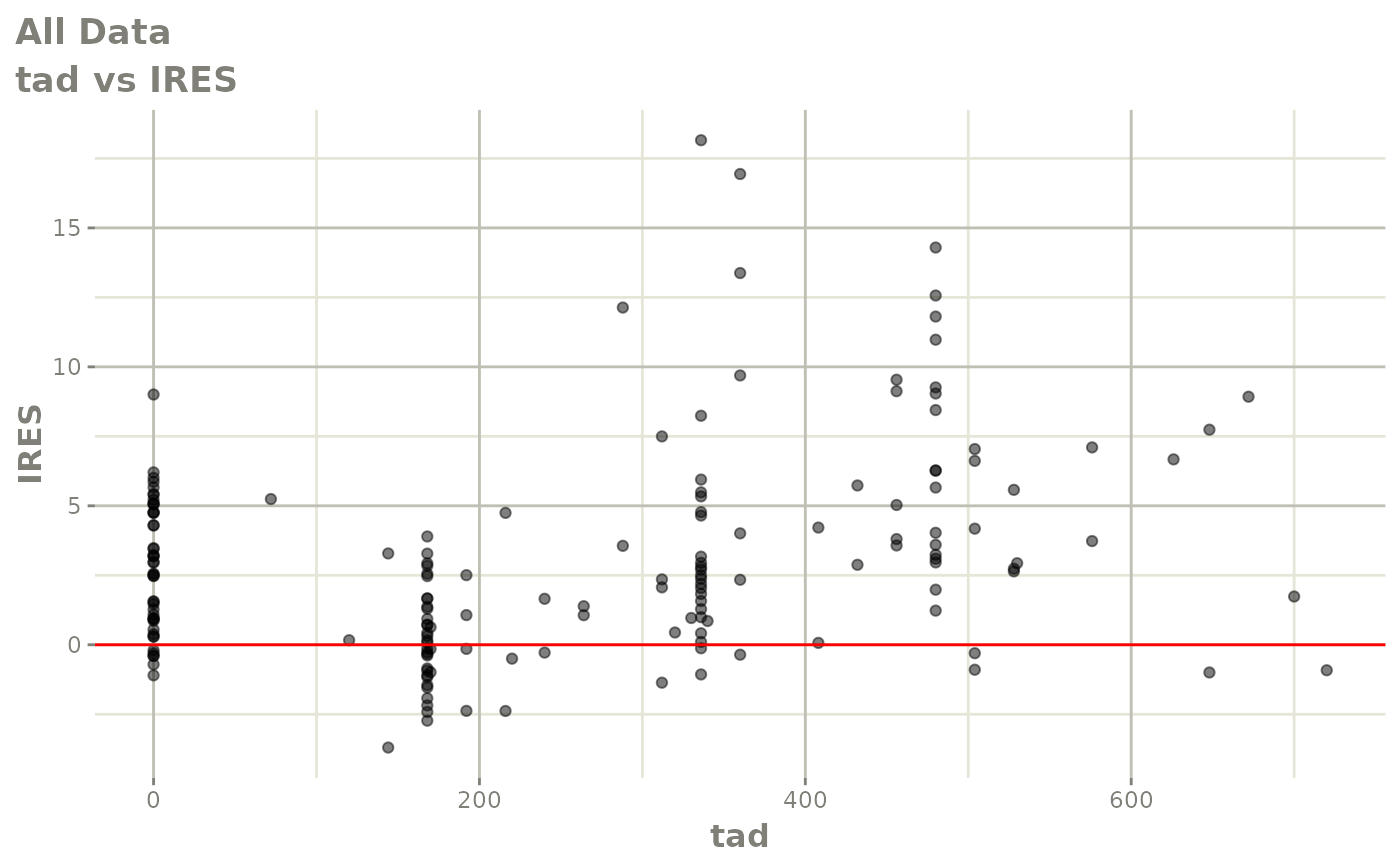
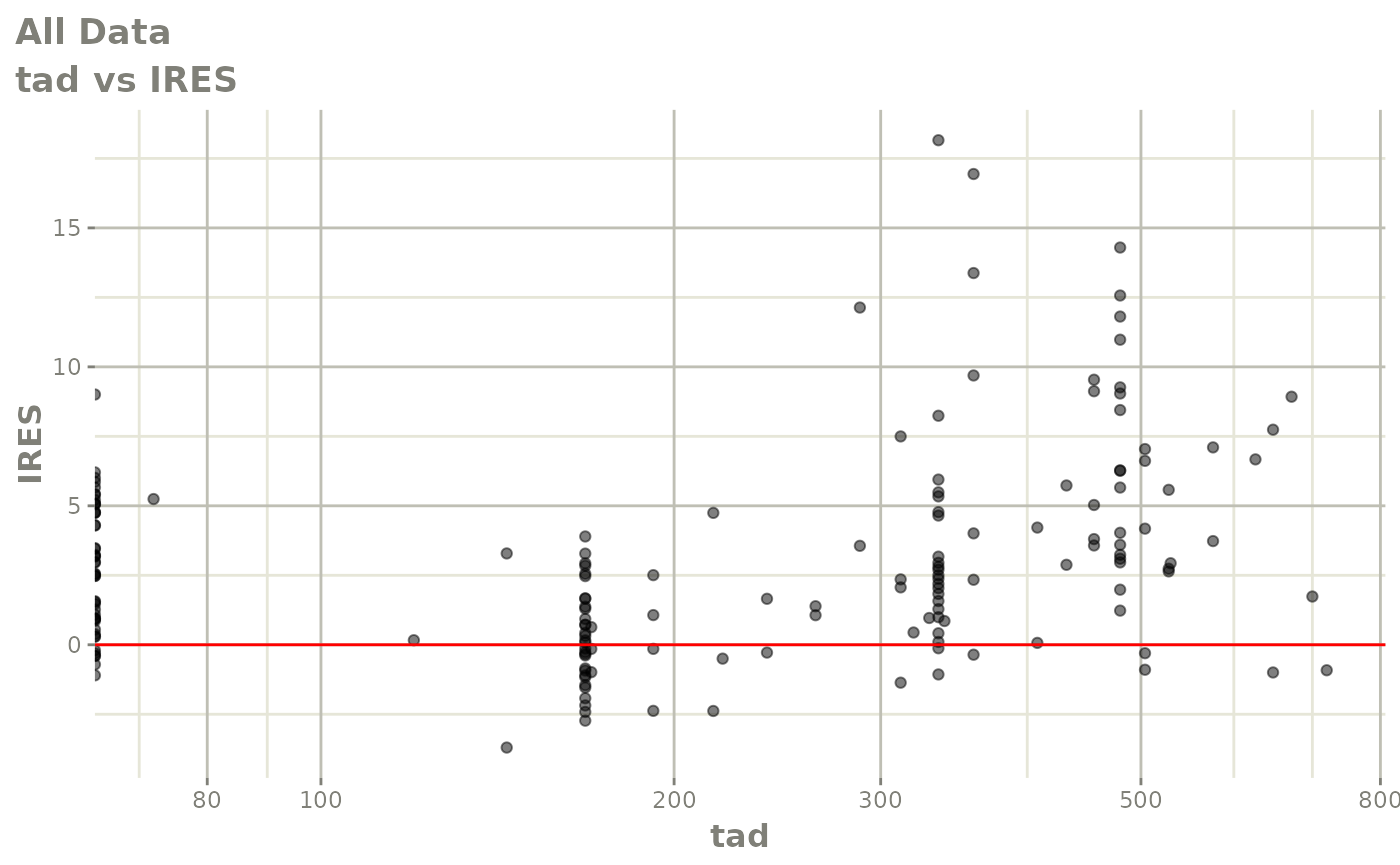
print(absval_res_vs_idv(xpdb, res = 'IWRES') +
ylab("Individual Weighted Residuals") +
xlab("Time (h)"))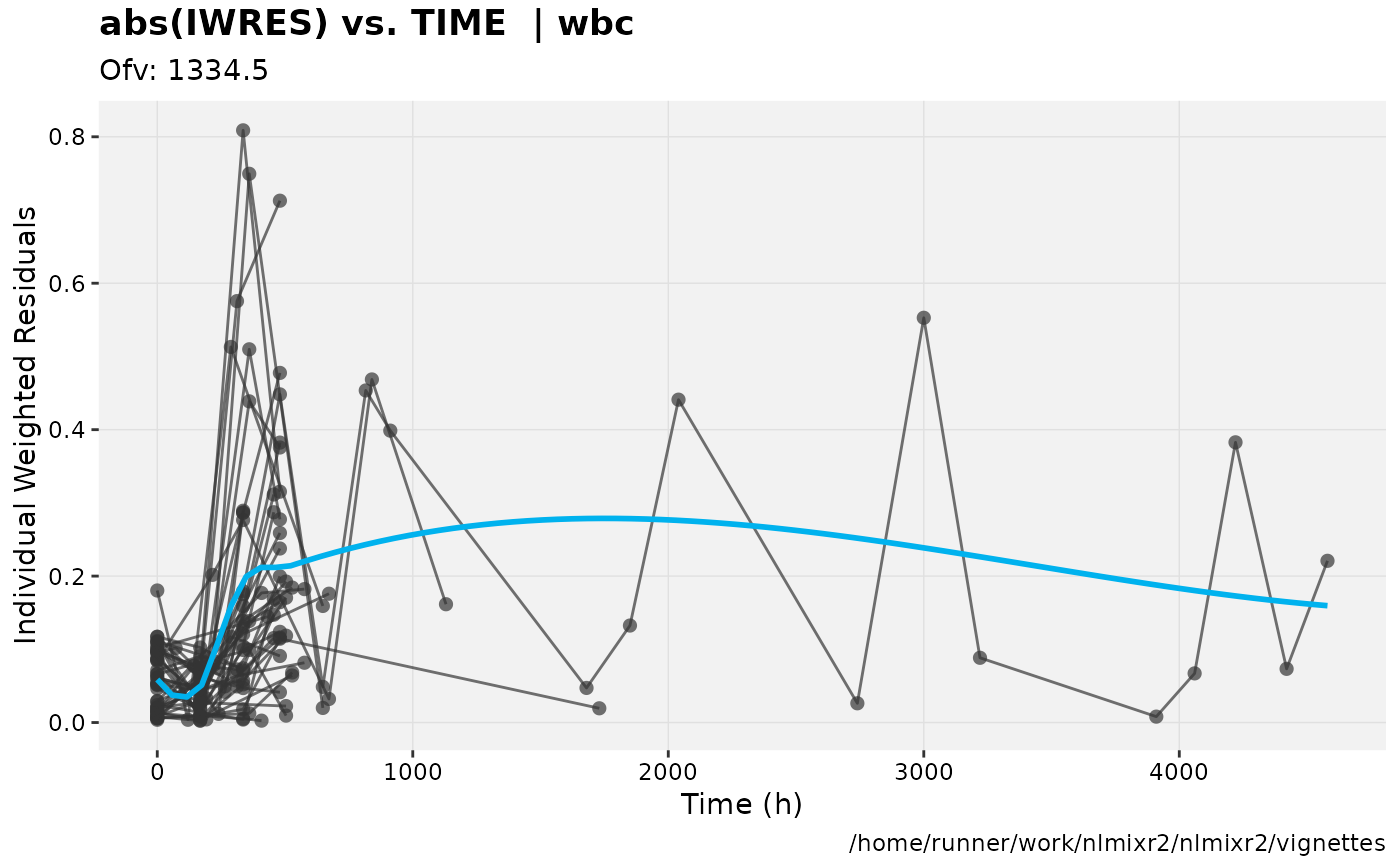
print(absval_res_vs_pred(xpdb, res = 'IWRES') +
ylab("Individual Weighted Residuals") +
xlab("Population Predicted Neutrophil Count (10^9/L)"))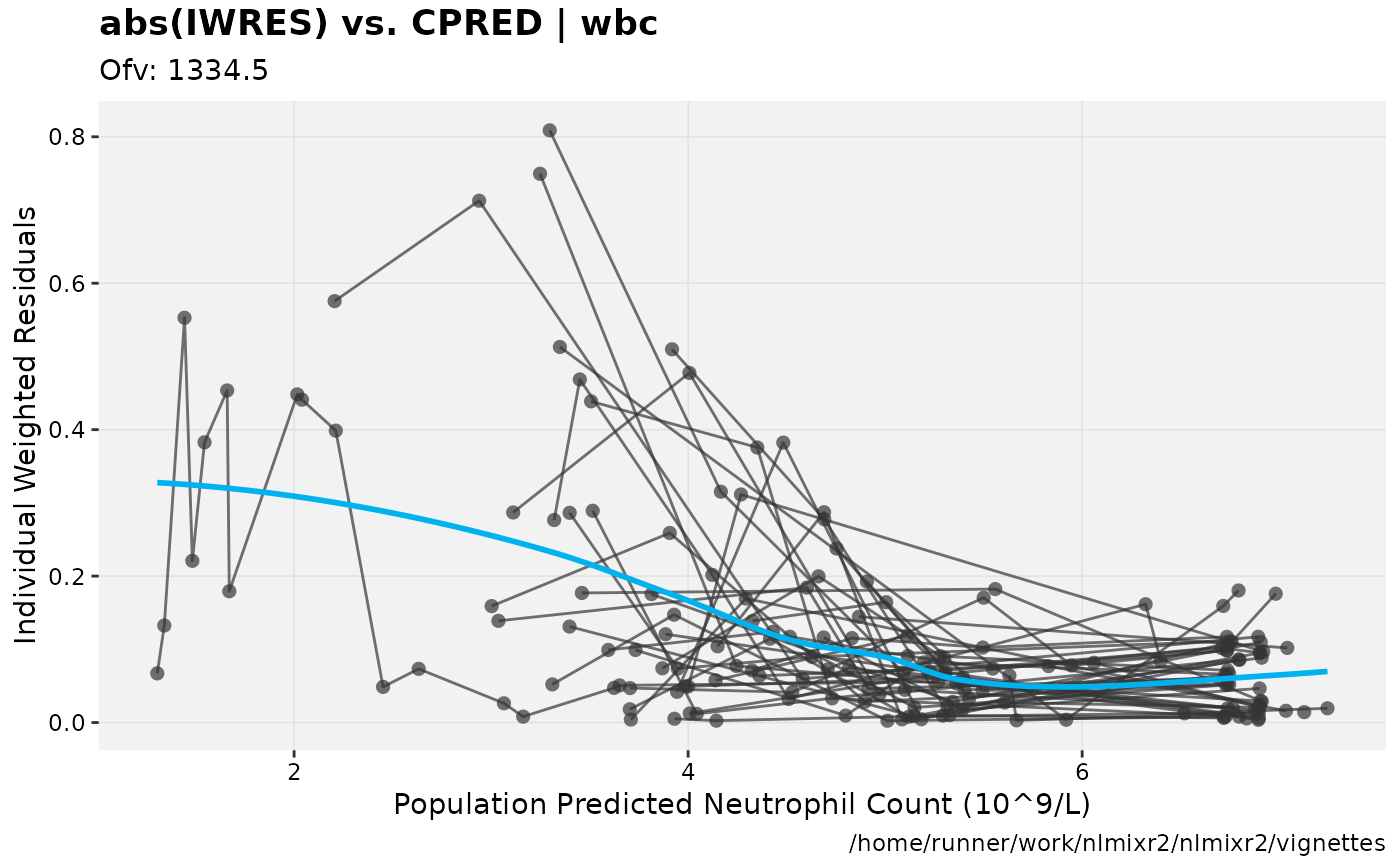
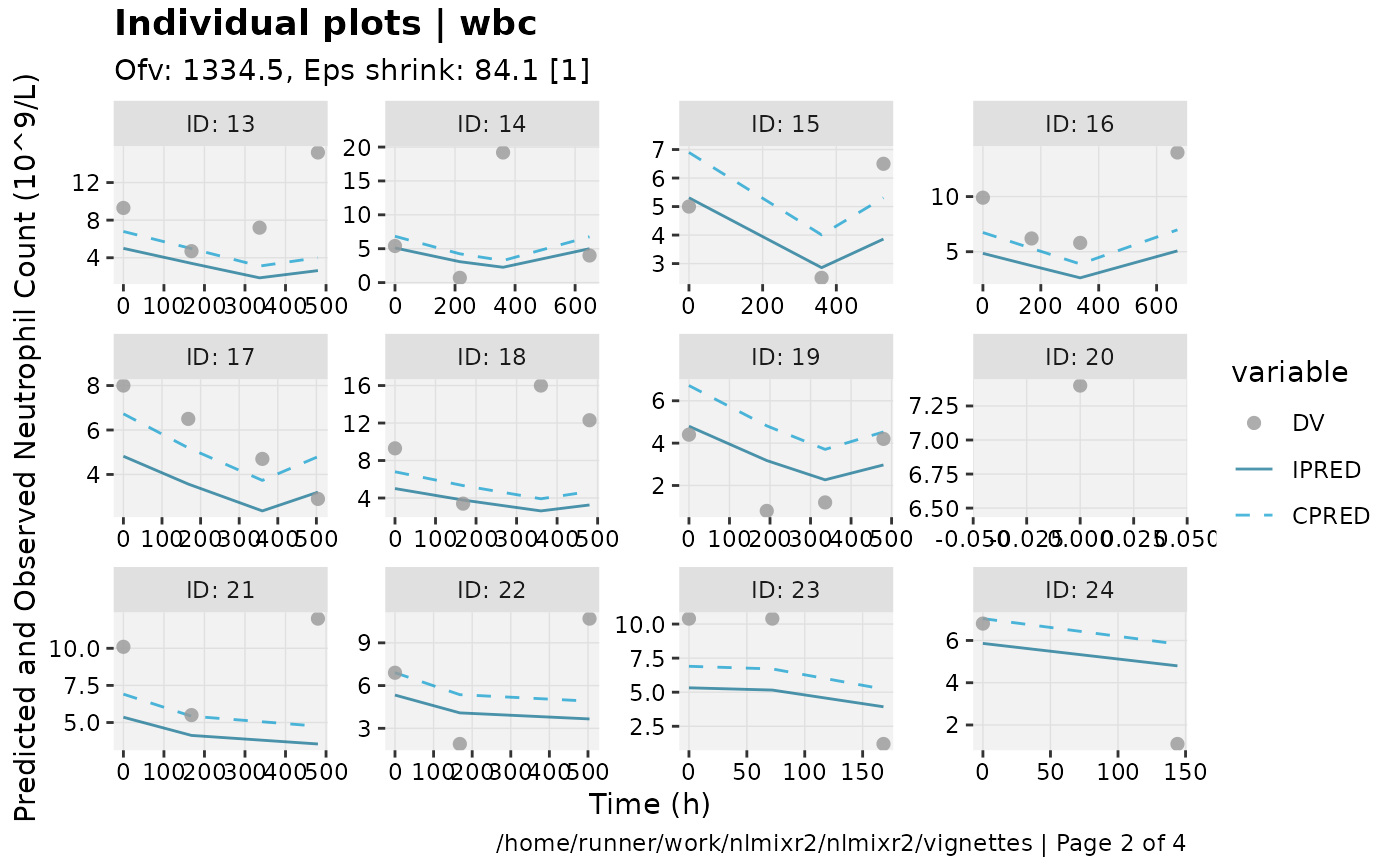
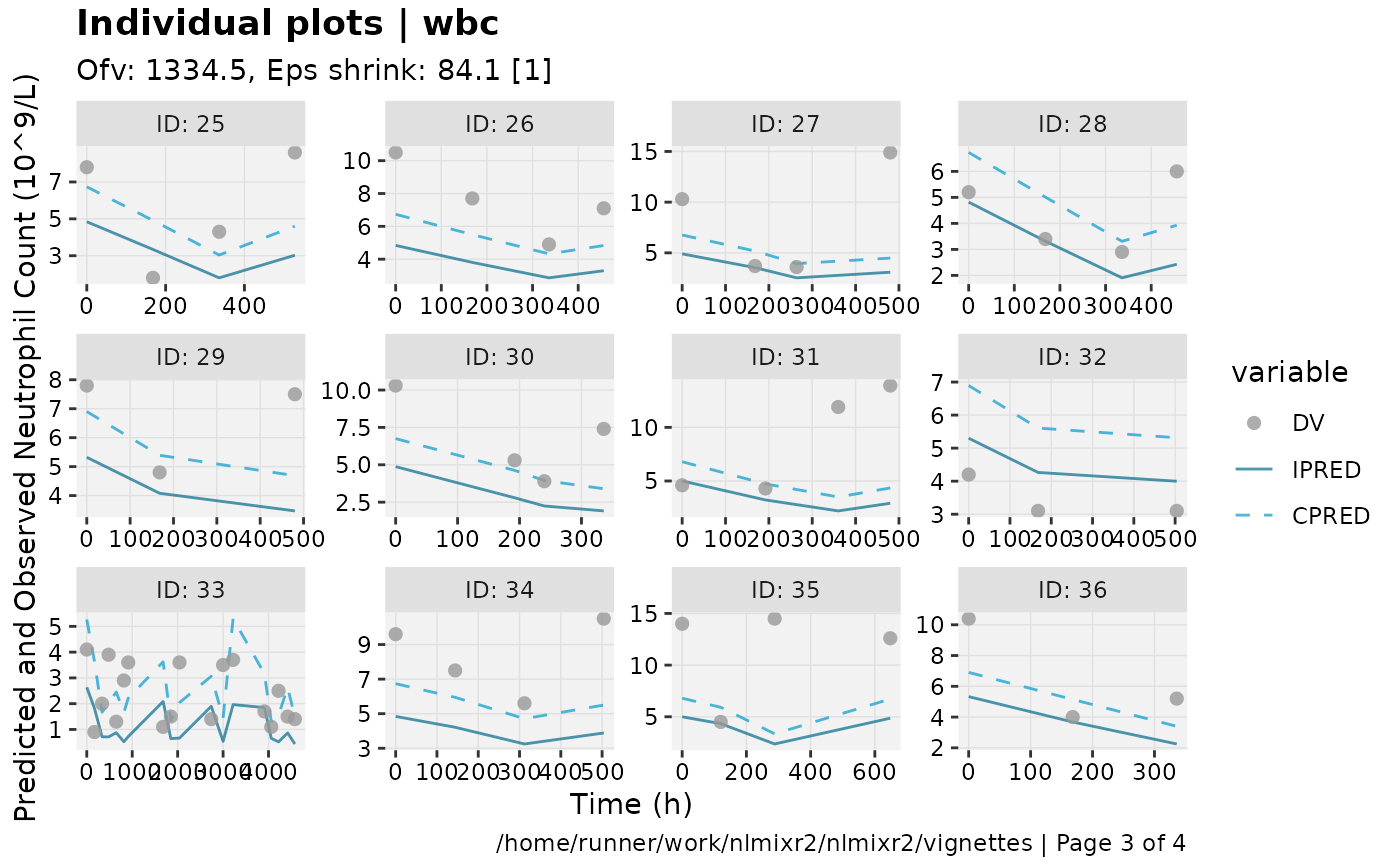
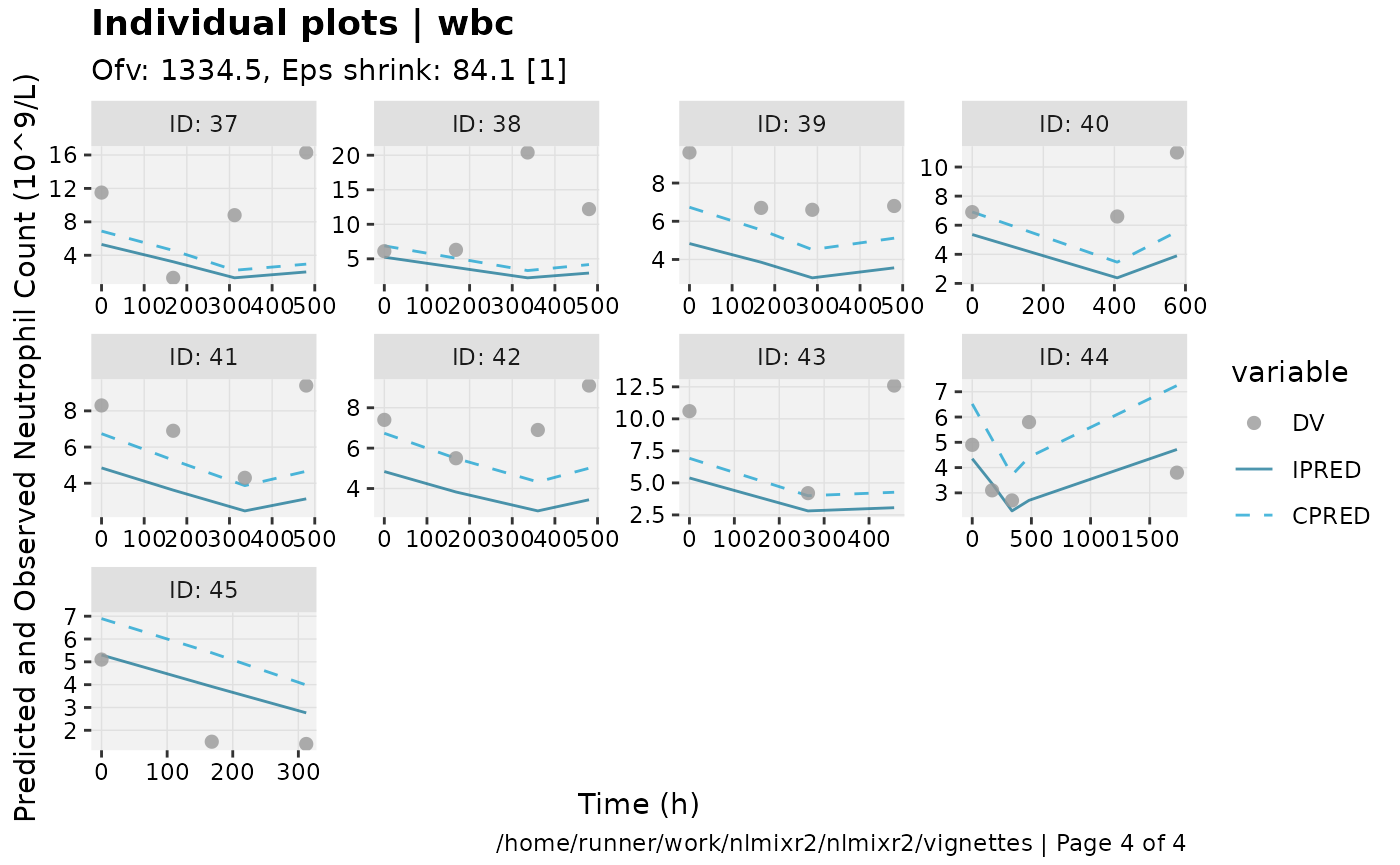
print(ind_plots(xpdb, nrow=3, ncol=4) +
ylab("Predicted and Observed Neutrophil Count (10^9/L)") +
xlab("Time (h)"))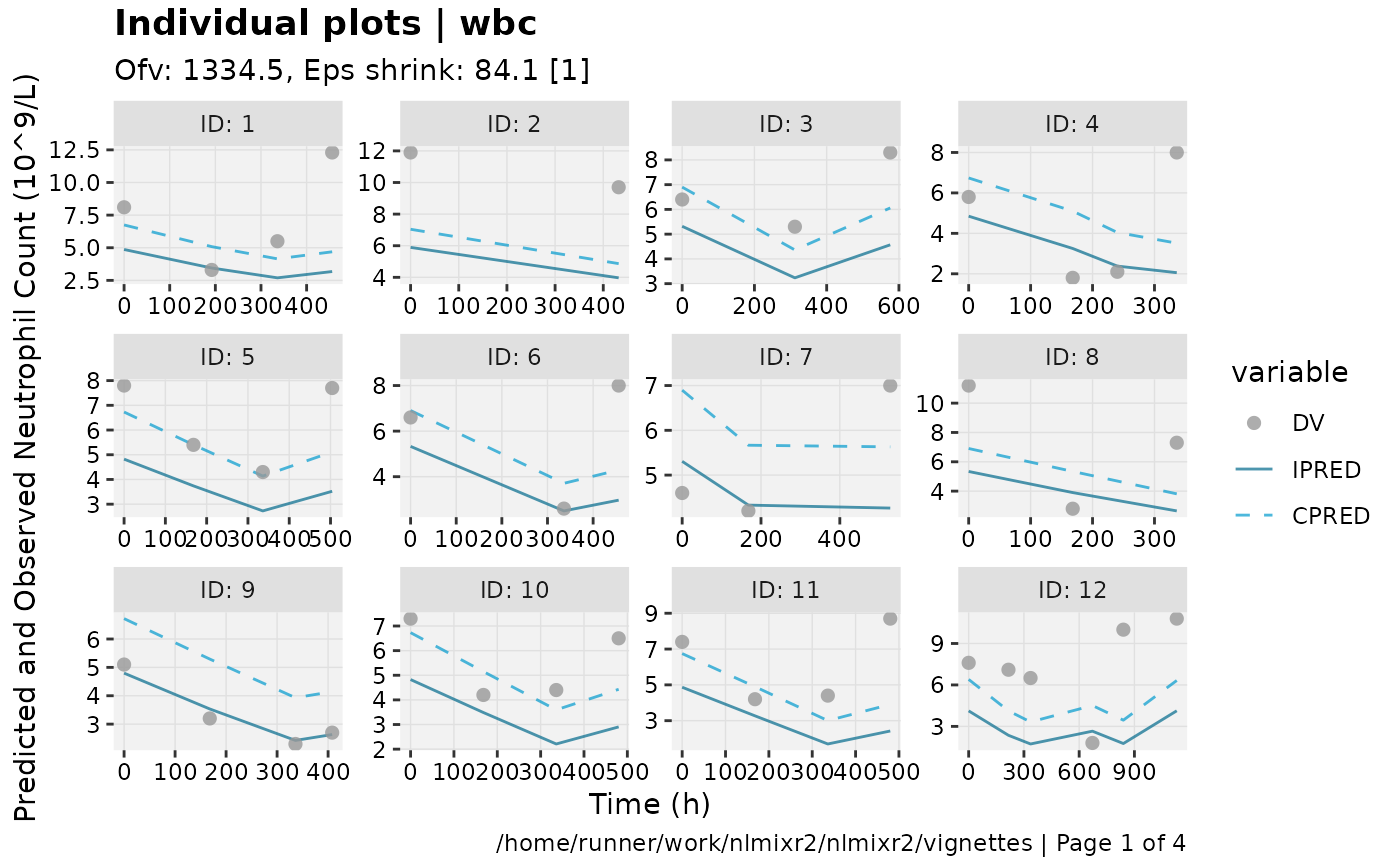
print(res_distrib(xpdb) +
ylab("Density") +
xlab("Conditional Weighted Residuals"))
# 10 bins is slightly better than auto bin
vpcPlot(fit.F, n=500, n_bins = 10, show=list(obs_dv=TRUE),
ylab = "Neutrophil Count (10^9/L)", xlab = "Time (h)")
#> [====|====|====|====|====|====|====|====|====|====] 0:00:03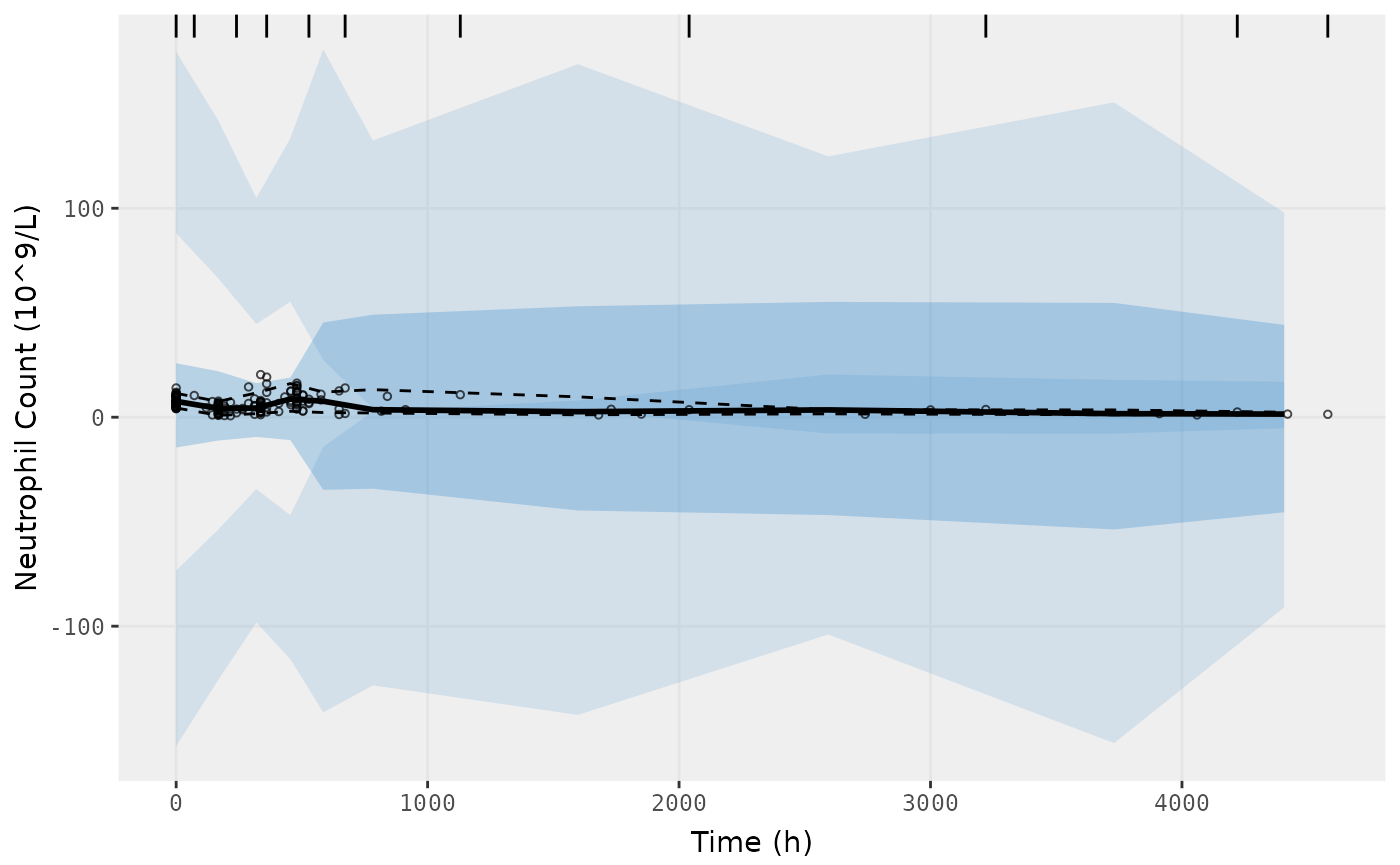
# specify bins
vpcPlot(fit.F, n=500, bins = c(0, 170, 300, 350, 500, 600, 900, 3000, 4580),
show=list(obs_dv=TRUE),
ylab = "Neutrophil Count (10^9/L)", xlab = "Time (h)")
#> [====|====|====|====|====|====|====|====|====|====] 0:00:03